| 登録情報 | データベース: PDB / ID: 2lxb
|
|---|
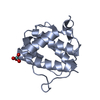
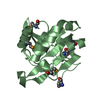
| タイトル | Solution structure of the Sgt2 homodimerization domain |
|---|
 要素 要素 | Small glutamine-rich tetratricopeptide repeat-containing protein 2 |
|---|
 キーワード キーワード | PROTEIN BINDING / four-helix bundle / protein-protein interaction / Get5 binding domain / GET pathway |
|---|
| 機能・相同性 |  機能・相同性情報 機能・相同性情報
TRC complex / Insertion of tail-anchored proteins into the endoplasmic reticulum membrane / post-translational protein targeting to endoplasmic reticulum membrane / heat shock protein binding / Hsp70 protein binding / Hsp90 protein binding / response to heat / molecular adaptor activity / membrane / identical protein binding ...TRC complex / Insertion of tail-anchored proteins into the endoplasmic reticulum membrane / post-translational protein targeting to endoplasmic reticulum membrane / heat shock protein binding / Hsp70 protein binding / Hsp90 protein binding / response to heat / molecular adaptor activity / membrane / identical protein binding / cytoplasm / cytosol類似検索 - 分子機能 SGTA, homodimerisation domain / Homodimerisation domain of SGTA / : / Immunoglobulin FC, subunit C / Tetratricopeptide repeat / TPR repeat region circular profile. / TPR repeat profile. / Tetratricopeptide repeats / Tetratricopeptide repeat / Single alpha-helices involved in coiled-coils or other helix-helix interfaces ...SGTA, homodimerisation domain / Homodimerisation domain of SGTA / : / Immunoglobulin FC, subunit C / Tetratricopeptide repeat / TPR repeat region circular profile. / TPR repeat profile. / Tetratricopeptide repeats / Tetratricopeptide repeat / Single alpha-helices involved in coiled-coils or other helix-helix interfaces / Tetratricopeptide-like helical domain superfamily / Up-down Bundle / Mainly Alpha類似検索 - ドメイン・相同性 Small glutamine-rich tetratricopeptide repeat-containing protein 2類似検索 - 構成要素 |
|---|
| 生物種 |   Saccharomyces cerevisiae (パン酵母) Saccharomyces cerevisiae (パン酵母) |
|---|
| 手法 | 溶液NMR / simulated annealing |
|---|
 データ登録者 データ登録者 | Chartron, J.W. / Vandervelde, D.G. / Clemons Jr., W.M. |
|---|
 引用 引用 |  ジャーナル: Cell Rep / 年: 2012 ジャーナル: Cell Rep / 年: 2012
タイトル: Structures of the Sgt2/SGTA Dimerization Domain with the Get5/UBL4A UBL Domain Reveal an Interaction that Forms a Conserved Dynamic Interface.
著者: Chartron, J.W. / Vandervelde, D.G. / Clemons, W.M. |
|---|
| 履歴 | | 登録 | 2012年8月19日 | 登録サイト: BMRB / 処理サイト: RCSB |
|---|
| 改定 1.0 | 2012年11月21日 | Provider: repository / タイプ: Initial release |
|---|
| 改定 1.1 | 2012年11月28日 | Group: Database references |
|---|
| 改定 1.2 | 2013年1月16日 | Group: Database references |
|---|
| 改定 1.3 | 2023年6月14日 | Group: Data collection / Database references / Other
カテゴリ: database_2 / pdbx_database_status ...database_2 / pdbx_database_status / pdbx_nmr_software / pdbx_nmr_spectrometer / struct_ref_seq_dif
Item: _database_2.pdbx_DOI / _database_2.pdbx_database_accession ..._database_2.pdbx_DOI / _database_2.pdbx_database_accession / _pdbx_database_status.status_code_nmr_data / _pdbx_nmr_software.name / _pdbx_nmr_spectrometer.model / _struct_ref_seq_dif.details |
|---|
| 改定 1.4 | 2024年5月15日 | Group: Data collection / Database references / カテゴリ: chem_comp_atom / chem_comp_bond / database_2 / Item: _database_2.pdbx_DOI |
|---|
|
|---|
 データを開く
データを開く 基本情報
基本情報 要素
要素 キーワード
キーワード 機能・相同性情報
機能・相同性情報
 データ登録者
データ登録者 引用
引用 ジャーナル: Cell Rep / 年: 2012
ジャーナル: Cell Rep / 年: 2012 構造の表示
構造の表示 Molmil
Molmil Jmol/JSmol
Jmol/JSmol ダウンロードとリンク
ダウンロードとリンク ダウンロード
ダウンロード 2lxb.cif.gz
2lxb.cif.gz PDBx/mmCIF形式
PDBx/mmCIF形式 pdb2lxb.ent.gz
pdb2lxb.ent.gz PDB形式
PDB形式 2lxb.json.gz
2lxb.json.gz PDBx/mmJSON形式
PDBx/mmJSON形式 その他のダウンロード
その他のダウンロード https://data.pdbj.org/pub/pdb/validation_reports/lx/2lxb
https://data.pdbj.org/pub/pdb/validation_reports/lx/2lxb ftp://data.pdbj.org/pub/pdb/validation_reports/lx/2lxb
ftp://data.pdbj.org/pub/pdb/validation_reports/lx/2lxb リンク
リンク 集合体
集合体
 要素
要素

 試料調製
試料調製 解析
解析 ムービー
ムービー コントローラー
コントローラー















 PDBj
PDBj


 HSQC
HSQC