| 登録情報 | データベース: PDB / ID: 2kbx
|
|---|
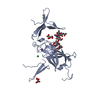
| タイトル | Solution structure of ILK-PINCH complex |
|---|
 要素 要素 | - Integrin-linked protein kinase
- LIM and senescent cell antigen-like-containing domain protein 1
|
|---|
 キーワード キーワード | CELL ADHESION / cytoskeletal regulators / ANK repeat / ATP-binding / Cell junction / Cell membrane / Kinase / Membrane / Nucleotide-binding / Phosphoprotein / Serine/threonine-protein kinase / Transferase / Acetylation / LIM domain / Metal-binding / Zinc |
|---|
| 機能・相同性 |  機能・相同性情報 機能・相同性情報
protein localization to cell cortex / caveola assembly / Regulation of cytoskeletal remodeling and cell spreading by IPP complex components / Localization of the PINCH-ILK-PARVIN complex to focal adhesions / negative regulation of neural precursor cell proliferation / positive regulation of signal transduction / positive regulation of integrin-mediated signaling pathway / nerve development / fibroblast migration / Cell-extracellular matrix interactions ...protein localization to cell cortex / caveola assembly / Regulation of cytoskeletal remodeling and cell spreading by IPP complex components / Localization of the PINCH-ILK-PARVIN complex to focal adhesions / negative regulation of neural precursor cell proliferation / positive regulation of signal transduction / positive regulation of integrin-mediated signaling pathway / nerve development / fibroblast migration / Cell-extracellular matrix interactions / establishment or maintenance of epithelial cell apical/basal polarity / myelination in peripheral nervous system / cell projection organization / positive regulation of BMP signaling pathway / cell-cell junction organization / positive regulation of cell-substrate adhesion / neural precursor cell proliferation / branching involved in ureteric bud morphogenesis / outflow tract morphogenesis / positive regulation of focal adhesion assembly / positive regulation of osteoblast differentiation / cellular response to transforming growth factor beta stimulus / tumor necrosis factor-mediated signaling pathway / positive regulation of GTPase activity / positive regulation of substrate adhesion-dependent cell spreading / substrate adhesion-dependent cell spreading / sarcomere / cell-matrix adhesion / mitotic spindle organization / integrin-mediated signaling pathway / phosphatidylinositol 3-kinase/protein kinase B signal transduction / establishment of protein localization / cell-cell adhesion / cell morphogenesis / platelet aggregation / integrin binding / positive regulation of canonical Wnt signaling pathway / cell-cell junction / actin cytoskeleton / lamellipodium / actin binding / cell cortex / protein-macromolecule adaptor activity / cell differentiation / positive regulation of canonical NF-kappaB signal transduction / protein kinase activity / signaling receptor binding / focal adhesion / negative regulation of DNA-templated transcription / positive regulation of cell population proliferation / centrosome / positive regulation of gene expression / protein kinase binding / chromatin / positive regulation of DNA-templated transcription / perinuclear region of cytoplasm / magnesium ion binding / zinc ion binding / nucleoplasm / ATP binding / nucleus / membrane / plasma membrane / cytosol / cytoplasm類似検索 - 分子機能 Integrin-linked protein kinase, pseudokinase domain / LIM and senescent cell antigen-like-containing domain protein 1-like / : / : / Cysteine Rich Protein / Cysteine Rich Protein / LIM zinc-binding domain signature. / LIM domain / Zinc-binding domain present in Lin-11, Isl-1, Mec-3. / Zinc finger, LIM-type ...Integrin-linked protein kinase, pseudokinase domain / LIM and senescent cell antigen-like-containing domain protein 1-like / : / : / Cysteine Rich Protein / Cysteine Rich Protein / LIM zinc-binding domain signature. / LIM domain / Zinc-binding domain present in Lin-11, Isl-1, Mec-3. / Zinc finger, LIM-type / LIM domain profile. / Ankyrin repeat-containing domain / : / Ankyrin repeats (3 copies) / Ankyrin repeat profile. / Ankyrin repeat region circular profile. / ankyrin repeats / Ankyrin repeat / Ankyrin repeat-containing domain superfamily / Ribbon / Serine Threonine Protein Phosphatase 5, Tetratricopeptide repeat / Alpha Horseshoe / Serine-threonine/tyrosine-protein kinase, catalytic domain / Protein tyrosine and serine/threonine kinase / Protein kinase domain profile. / Protein kinase domain / Protein kinase-like domain superfamily / Mainly Beta / Mainly Alpha類似検索 - ドメイン・相同性 LIM and senescent cell antigen-like-containing domain protein 1 / Scaffold protein ILK類似検索 - 構成要素 |
|---|
| 生物種 |  Homo sapiens (ヒト) Homo sapiens (ヒト) |
|---|
| 手法 | 溶液NMR / simulated annealing |
|---|
| Model details | lowest energy, model 2 |
|---|
 データ登録者 データ登録者 | Qin, J. |
|---|
 引用 引用 |  ジャーナル: To be Published ジャーナル: To be Published
タイトル: Cytosketal proteins
著者: Qin, J. |
|---|
| 履歴 | | 登録 | 2008年12月10日 | 登録サイト: BMRB / 処理サイト: RCSB |
|---|
| 改定 1.0 | 2008年12月30日 | Provider: repository / タイプ: Initial release |
|---|
| 改定 1.1 | 2011年7月13日 | Group: Version format compliance |
|---|
| 改定 1.2 | 2022年3月16日 | Group: Data collection / Database references / Derived calculations
カテゴリ: database_2 / pdbx_nmr_software ...database_2 / pdbx_nmr_software / pdbx_nmr_spectrometer / pdbx_struct_assembly / pdbx_struct_oper_list / struct_site
Item: _database_2.pdbx_DOI / _database_2.pdbx_database_accession ..._database_2.pdbx_DOI / _database_2.pdbx_database_accession / _pdbx_nmr_software.name / _pdbx_nmr_spectrometer.model / _struct_site.pdbx_auth_asym_id / _struct_site.pdbx_auth_comp_id / _struct_site.pdbx_auth_seq_id |
|---|
| 改定 1.3 | 2024年11月27日 | Group: Data collection / Structure summary
カテゴリ: chem_comp_atom / chem_comp_bond ...chem_comp_atom / chem_comp_bond / pdbx_entry_details / pdbx_modification_feature |
|---|
|
|---|
 データを開く
データを開く 基本情報
基本情報 要素
要素 キーワード
キーワード 機能・相同性情報
機能・相同性情報 Homo sapiens (ヒト)
Homo sapiens (ヒト) データ登録者
データ登録者 引用
引用 ジャーナル: To be Published
ジャーナル: To be Published 構造の表示
構造の表示 Molmil
Molmil Jmol/JSmol
Jmol/JSmol ダウンロードとリンク
ダウンロードとリンク ダウンロード
ダウンロード 2kbx.cif.gz
2kbx.cif.gz PDBx/mmCIF形式
PDBx/mmCIF形式 pdb2kbx.ent.gz
pdb2kbx.ent.gz PDB形式
PDB形式 2kbx.json.gz
2kbx.json.gz PDBx/mmJSON形式
PDBx/mmJSON形式 その他のダウンロード
その他のダウンロード 2kbx_validation.pdf.gz
2kbx_validation.pdf.gz wwPDB検証レポート
wwPDB検証レポート 2kbx_full_validation.pdf.gz
2kbx_full_validation.pdf.gz 2kbx_validation.xml.gz
2kbx_validation.xml.gz 2kbx_validation.cif.gz
2kbx_validation.cif.gz https://data.pdbj.org/pub/pdb/validation_reports/kb/2kbx
https://data.pdbj.org/pub/pdb/validation_reports/kb/2kbx ftp://data.pdbj.org/pub/pdb/validation_reports/kb/2kbx
ftp://data.pdbj.org/pub/pdb/validation_reports/kb/2kbx リンク
リンク 集合体
集合体
 要素
要素 Homo sapiens (ヒト) / 遺伝子: ILK, ILK1, ILK2 / 発現宿主:
Homo sapiens (ヒト) / 遺伝子: ILK, ILK1, ILK2 / 発現宿主: 
 Homo sapiens (ヒト) / 遺伝子: LIMS1, PINCH, PINCH1 / 発現宿主:
Homo sapiens (ヒト) / 遺伝子: LIMS1, PINCH, PINCH1 / 発現宿主: 
 HSQC
HSQC 試料調製
試料調製 解析
解析 ムービー
ムービー コントローラー
コントローラー










 PDBj
PDBj

