| 登録情報 | データベース: PDB / ID: 2ge2
|
|---|
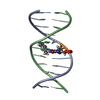
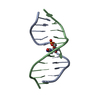
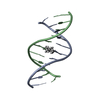
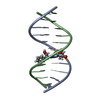
| タイトル | Solution structure of the Duplex DNA Containing the 3-(Deoxyguanosin-N2-yl)-2-Acetoaminofluorene |
|---|
 要素 要素 | - 5'-D(*CP*GP*TP*AP*CP*GP*CP*AP*TP*GP*C)-3'
- 5'-D(*GP*CP*AP*TP*GP*CP*GP*TP*AP*CP*G)-3'
|
|---|
 キーワード キーワード | DNA / acetylaminofluoren (AAF) |
|---|
| 機能・相同性 | 2-ACETYLAMINOFLUORENE-3-YL / DNA / DNA (> 10) 機能・相同性情報 機能・相同性情報 |
|---|
| 手法 | 溶液NMR / restrained molecular dynamics |
|---|
| Model type details | minimized average |
|---|
 データ登録者 データ登録者 | de los Santos, C. / Zaliznyak, T. |
|---|
 引用 引用 |  ジャーナル: Chem.Res.Toxicol. / 年: 2006 ジャーナル: Chem.Res.Toxicol. / 年: 2006
タイトル: Structure and Stability of Duplex DNA Containing the 3-(Deoxyguanosin-N(2)-yl)-2-acetylaminofluorene (dG(N(2))-AAF) Lesion: A Bulky Adduct that Persists in Cellular DNA.
著者: Zaliznyak, T. / Bonala, R. / Johnson, F. / de Los Santos, C. |
|---|
| 履歴 | | 登録 | 2006年3月17日 | 登録サイト: RCSB / 処理サイト: RCSB |
|---|
| 改定 1.0 | 2006年7月4日 | Provider: repository / タイプ: Initial release |
|---|
| 改定 1.1 | 2008年5月1日 | Group: Version format compliance |
|---|
| 改定 1.2 | 2011年7月13日 | Group: Version format compliance |
|---|
| 改定 1.3 | 2022年3月9日 | Group: Data collection / Database references / Derived calculations
カテゴリ: database_2 / pdbx_nmr_software ...database_2 / pdbx_nmr_software / pdbx_struct_assembly / pdbx_struct_oper_list / struct_conn / struct_site
Item: _database_2.pdbx_DOI / _database_2.pdbx_database_accession ..._database_2.pdbx_DOI / _database_2.pdbx_database_accession / _pdbx_nmr_software.name / _struct_conn.pdbx_leaving_atom_flag / _struct_site.pdbx_auth_asym_id / _struct_site.pdbx_auth_comp_id / _struct_site.pdbx_auth_seq_id |
|---|
| 改定 1.4 | 2024年5月29日 | Group: Data collection / カテゴリ: chem_comp_atom / chem_comp_bond |
|---|
|
|---|
 データを開く
データを開く 基本情報
基本情報 要素
要素 キーワード
キーワード 機能・相同性情報
機能・相同性情報 データ登録者
データ登録者 引用
引用 ジャーナル: Chem.Res.Toxicol. / 年: 2006
ジャーナル: Chem.Res.Toxicol. / 年: 2006 構造の表示
構造の表示 Molmil
Molmil Jmol/JSmol
Jmol/JSmol ダウンロードとリンク
ダウンロードとリンク ダウンロード
ダウンロード 2ge2.cif.gz
2ge2.cif.gz PDBx/mmCIF形式
PDBx/mmCIF形式 pdb2ge2.ent.gz
pdb2ge2.ent.gz PDB形式
PDB形式 2ge2.json.gz
2ge2.json.gz PDBx/mmJSON形式
PDBx/mmJSON形式 その他のダウンロード
その他のダウンロード https://data.pdbj.org/pub/pdb/validation_reports/ge/2ge2
https://data.pdbj.org/pub/pdb/validation_reports/ge/2ge2 ftp://data.pdbj.org/pub/pdb/validation_reports/ge/2ge2
ftp://data.pdbj.org/pub/pdb/validation_reports/ge/2ge2 リンク
リンク 集合体
集合体
 要素
要素 試料調製
試料調製 解析
解析 ムービー
ムービー コントローラー
コントローラー








 PDBj
PDBj







































 X-PLOR
X-PLOR