| 登録情報 | データベース: PDB / ID: 2dqy
|
|---|
| タイトル | Crystal structure of human carboxylesterase in complex with cholate and palmitate |
|---|
 要素 要素 | Liver carboxylesterase 1 |
|---|
 キーワード キーワード | HYDROLASE / cholesterol metabolism / foam cells / macrophage / monocyte / atherosclerosis |
|---|
| 機能・相同性 |  機能・相同性情報 機能・相同性情報
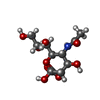
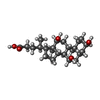
cholesterol ester hydrolysis involved in cholesterol transport / methylumbelliferyl-acetate deacetylase / methylumbelliferyl-acetate deacetylase activity / regulation of bile acid secretion / sterol esterase / sterol ester esterase activity / medium-chain fatty acid metabolic process / carboxylesterase / Physiological factors / carboxylesterase activity ...cholesterol ester hydrolysis involved in cholesterol transport / methylumbelliferyl-acetate deacetylase / methylumbelliferyl-acetate deacetylase activity / regulation of bile acid secretion / sterol esterase / sterol ester esterase activity / medium-chain fatty acid metabolic process / carboxylesterase / Physiological factors / carboxylesterase activity / regulation of bile acid biosynthetic process / cellular response to cholesterol / positive regulation of cholesterol metabolic process / reverse cholesterol transport / Phase I - Functionalization of compounds / carboxylic ester hydrolase activity / cholesterol biosynthetic process / Aspirin ADME / negative regulation of cholesterol storage / cellular response to low-density lipoprotein particle stimulus / positive regulation of cholesterol efflux / Metabolism of Angiotensinogen to Angiotensins / cholesterol metabolic process / lipid catabolic process / lipid droplet / epithelial cell differentiation / cholesterol homeostasis / response to toxic substance / endoplasmic reticulum lumen / endoplasmic reticulum / cytosol / cytoplasm類似検索 - 分子機能 : / Carboxylesterase type B, active site / Carboxylesterases type-B serine active site. / Carboxylesterase type B, conserved site / Carboxylesterases type-B signature 2. / Carboxylesterase, type B / Carboxylesterase family / Alpha/Beta hydrolase fold, catalytic domain / Alpha/Beta hydrolase fold / Rossmann fold ...: / Carboxylesterase type B, active site / Carboxylesterases type-B serine active site. / Carboxylesterase type B, conserved site / Carboxylesterases type-B signature 2. / Carboxylesterase, type B / Carboxylesterase family / Alpha/Beta hydrolase fold, catalytic domain / Alpha/Beta hydrolase fold / Rossmann fold / 3-Layer(aba) Sandwich / Alpha Beta類似検索 - ドメイン・相同性 CHOLIC ACID / PALMITIC ACID / N-acetyl-alpha-neuraminic acid / Liver carboxylesterase 1類似検索 - 構成要素 |
|---|
| 生物種 |  Homo sapiens (ヒト) Homo sapiens (ヒト) |
|---|
| 手法 |  X線回折 / X線回折 /  分子置換 / 解像度: 3 Å 分子置換 / 解像度: 3 Å |
|---|
 データ登録者 データ登録者 | Bencharit, S. / Edwards, C.C. / Morton, C.L. / Howard-Williams, E.L. / Potter, P.M. / Redinbo, M.R. |
|---|
 引用 引用 |  ジャーナル: J.Mol.Biol. / 年: 2006 ジャーナル: J.Mol.Biol. / 年: 2006
タイトル: Multisite promiscuity in the processing of endogenous substrates by human carboxylesterase 1
著者: Bencharit, S. / Edwards, C.C. / Morton, C.L. / Howard-Williams, E.L. / Kuhn, P. / Potter, P.M. / Redinbo, M.R. |
|---|
| 履歴 | | 登録 | 2006年6月2日 | 登録サイト: PDBJ / 処理サイト: PDBJ |
|---|
| 改定 1.0 | 2006年8月29日 | Provider: repository / タイプ: Initial release |
|---|
| 改定 1.1 | 2007年10月22日 | Group: Version format compliance |
|---|
| 改定 1.2 | 2011年7月13日 | Group: Derived calculations / Version format compliance |
|---|
| 改定 1.3 | 2020年7月29日 | Group: Advisory / Data collection ...Advisory / Data collection / Database references / Derived calculations / Structure summary
カテゴリ: chem_comp / database_PDB_caveat ...chem_comp / database_PDB_caveat / entity / pdbx_chem_comp_identifier / pdbx_entity_nonpoly / struct_conn / struct_ref_seq_dif / struct_site / struct_site_gen
Item: _chem_comp.name / _chem_comp.type ..._chem_comp.name / _chem_comp.type / _entity.pdbx_description / _pdbx_entity_nonpoly.name / _struct_conn.pdbx_leaving_atom_flag / _struct_conn.pdbx_role / _struct_conn.ptnr1_auth_comp_id / _struct_conn.ptnr1_auth_seq_id / _struct_conn.ptnr1_label_asym_id / _struct_conn.ptnr1_label_atom_id / _struct_conn.ptnr1_label_comp_id / _struct_conn.ptnr1_label_seq_id / _struct_conn.ptnr2_auth_comp_id / _struct_conn.ptnr2_auth_seq_id / _struct_conn.ptnr2_label_asym_id / _struct_conn.ptnr2_label_atom_id / _struct_conn.ptnr2_label_comp_id / _struct_conn.ptnr2_label_seq_id / _struct_ref_seq_dif.details
解説: Carbohydrate remediation / Provider: repository / タイプ: Remediation |
|---|
| 改定 1.4 | 2023年10月25日 | Group: Data collection / Database references ...Data collection / Database references / Refinement description / Structure summary
カテゴリ: chem_comp / chem_comp_atom ...chem_comp / chem_comp_atom / chem_comp_bond / database_2 / pdbx_initial_refinement_model
Item: _chem_comp.pdbx_synonyms / _database_2.pdbx_DOI / _database_2.pdbx_database_accession |
|---|
| 改定 1.5 | 2024年11月20日 | Group: Structure summary
カテゴリ: pdbx_entry_details / pdbx_modification_feature |
|---|
|
|---|
 データを開く
データを開く 基本情報
基本情報 要素
要素 キーワード
キーワード 機能・相同性情報
機能・相同性情報 Homo sapiens (ヒト)
Homo sapiens (ヒト) X線回折 /
X線回折 /  分子置換 / 解像度: 3 Å
分子置換 / 解像度: 3 Å  データ登録者
データ登録者 引用
引用 ジャーナル: J.Mol.Biol. / 年: 2006
ジャーナル: J.Mol.Biol. / 年: 2006 構造の表示
構造の表示 Molmil
Molmil Jmol/JSmol
Jmol/JSmol ダウンロードとリンク
ダウンロードとリンク ダウンロード
ダウンロード 2dqy.cif.gz
2dqy.cif.gz PDBx/mmCIF形式
PDBx/mmCIF形式 pdb2dqy.ent.gz
pdb2dqy.ent.gz PDB形式
PDB形式 2dqy.json.gz
2dqy.json.gz PDBx/mmJSON形式
PDBx/mmJSON形式 その他のダウンロード
その他のダウンロード 2dqy_validation.pdf.gz
2dqy_validation.pdf.gz wwPDB検証レポート
wwPDB検証レポート 2dqy_full_validation.pdf.gz
2dqy_full_validation.pdf.gz 2dqy_validation.xml.gz
2dqy_validation.xml.gz 2dqy_validation.cif.gz
2dqy_validation.cif.gz https://data.pdbj.org/pub/pdb/validation_reports/dq/2dqy
https://data.pdbj.org/pub/pdb/validation_reports/dq/2dqy ftp://data.pdbj.org/pub/pdb/validation_reports/dq/2dqy
ftp://data.pdbj.org/pub/pdb/validation_reports/dq/2dqy リンク
リンク 集合体
集合体
 要素
要素 Homo sapiens (ヒト) / 細胞株 (発現宿主): sf9
Homo sapiens (ヒト) / 細胞株 (発現宿主): sf9








 X線回折 / 使用した結晶の数: 1
X線回折 / 使用した結晶の数: 1  試料調製
試料調製 解析
解析 分子置換
分子置換 ムービー
ムービー コントローラー
コントローラー

















 PDBj
PDBj














