+ データを開く
データを開く
- 基本情報
基本情報
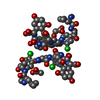
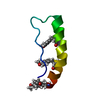
| 登録情報 | データベース: PDB / ID: 1qd8 | |||||||||
|---|---|---|---|---|---|---|---|---|---|---|
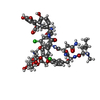
| タイトル | COMPLEX OF VANCOMYCIN WITH N-ACETYL GLYCINE | |||||||||
 要素 要素 | VANCOMYCIN | |||||||||
 キーワード キーワード | ANTIBIOTIC / GLYCOPEPTIDE | |||||||||
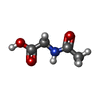
| 機能・相同性 | Vancomycin / ACETYLAMINO-ACETIC ACID / :  機能・相同性情報 機能・相同性情報 | |||||||||
| 生物種 |  AMYCOLATOPSIS ORIENTALIS (バクテリア) AMYCOLATOPSIS ORIENTALIS (バクテリア) | |||||||||
| 手法 |  X線回折 / X線回折 /  シンクロトロン / 解像度: 1 Å シンクロトロン / 解像度: 1 Å | |||||||||
 データ登録者 データ登録者 | Loll, P.J. / Kaplan, J. / Selinsky, B. / Axelsen, P.H. | |||||||||
 引用 引用 |  ジャーナル: J.Med.Chem. / 年: 1999 ジャーナル: J.Med.Chem. / 年: 1999タイトル: Vancomycin Binding to Low-Affinity Ligands: Delineating a Minimum Set of Interactions Necessary for High-Affinity Binding. 著者: Loll, P.J. / Kaplan, J. / Selinsky, B.S. / Axelsen, P.H. | |||||||||
| 履歴 |
|
- 構造の表示
構造の表示
| 構造ビューア | 分子:  Molmil Molmil Jmol/JSmol Jmol/JSmol |
|---|
- ダウンロードとリンク
ダウンロードとリンク
- ダウンロード
ダウンロード
| PDBx/mmCIF形式 |  1qd8.cif.gz 1qd8.cif.gz | 18.2 KB | 表示 |  PDBx/mmCIF形式 PDBx/mmCIF形式 |
|---|---|---|---|---|
| PDB形式 |  pdb1qd8.ent.gz pdb1qd8.ent.gz | 12.4 KB | 表示 |  PDB形式 PDB形式 |
| PDBx/mmJSON形式 |  1qd8.json.gz 1qd8.json.gz | ツリー表示 |  PDBx/mmJSON形式 PDBx/mmJSON形式 | |
| その他 |  その他のダウンロード その他のダウンロード |
-検証レポート
| 文書・要旨 |  1qd8_validation.pdf.gz 1qd8_validation.pdf.gz | 511.9 KB | 表示 |  wwPDB検証レポート wwPDB検証レポート |
|---|---|---|---|---|
| 文書・詳細版 |  1qd8_full_validation.pdf.gz 1qd8_full_validation.pdf.gz | 516.1 KB | 表示 | |
| XML形式データ |  1qd8_validation.xml.gz 1qd8_validation.xml.gz | 3.3 KB | 表示 | |
| CIF形式データ |  1qd8_validation.cif.gz 1qd8_validation.cif.gz | 3.9 KB | 表示 | |
| アーカイブディレクトリ |  https://data.pdbj.org/pub/pdb/validation_reports/qd/1qd8 https://data.pdbj.org/pub/pdb/validation_reports/qd/1qd8 ftp://data.pdbj.org/pub/pdb/validation_reports/qd/1qd8 ftp://data.pdbj.org/pub/pdb/validation_reports/qd/1qd8 | HTTPS FTP |
-関連構造データ
- リンク
リンク
- 集合体
集合体
| 登録構造単位 | 
| ||||||||
|---|---|---|---|---|---|---|---|---|---|
| 1 | 
| ||||||||
| 2 | 
| ||||||||
| 単位格子 |
| ||||||||
| Components on special symmetry positions |
|
- 要素
要素
| #1: タンパク質・ペプチド | | #2: 多糖 | #3: 化合物 | #4: 化合物 | ChemComp-AAC / | #5: 水 | ChemComp-HOH / | 構成要素の詳細 | VANCOMYCIN IS A TRICYCLIC GLYCOPEPTIDE. THE SCAFFOLD IS A HEPTAPEPTIDE WITH THE CONFIGURATION D-D-L- ...VANCOMYCIN | |
|---|
-実験情報
-実験
| 実験 | 手法:  X線回折 / 使用した結晶の数: 1 X線回折 / 使用した結晶の数: 1 |
|---|
- 試料調製
試料調製
| 結晶 | マシュー密度: 2.99 Å3/Da / 溶媒含有率: 58.88 % | ||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 結晶化 | pH: 4.6 詳細: SODIUM CHLORIDE, N-ACETYL GLYCINE, PH 4.6, VAPOR DIFFUSION/HANGING DROP, TEMPERATURE 291K | ||||||||||||||||||||||||
| 結晶化 | *PLUS 手法: 蒸気拡散法, ハンギングドロップ法 | ||||||||||||||||||||||||
| 溶液の組成 | *PLUS
|
-データ収集
| 回折 | 平均測定温度: 100 K |
|---|---|
| 放射光源 | 由来:  シンクロトロン / サイト: シンクロトロン / サイト:  CHESS CHESS  / ビームライン: A1 / 波長: 0.918 / ビームライン: A1 / 波長: 0.918 |
| 検出器 | タイプ: CUSTOM-MADE / 検出器: CCD / 日付: 1996年9月19日 |
| 放射 | プロトコル: SINGLE WAVELENGTH / 単色(M)・ラウエ(L): M / 散乱光タイプ: x-ray |
| 放射波長 | 波長: 0.918 Å / 相対比: 1 |
| 反射 | 解像度: 1→20 Å / Num. obs: 14172 / % possible obs: 93 % / Observed criterion σ(I): 2 / 冗長度: 23.4 % / Rmerge(I) obs: 0.042 / Net I/σ(I): 46.4 |
| 反射 シェル | 解像度: 1→1.04 Å / 冗長度: 2098 % / Rmerge(I) obs: 0.065 / % possible all: 62 |
| 反射 | *PLUS Num. measured all: 34664 |
| 反射 シェル | *PLUS % possible obs: 62 % |
- 解析
解析
| ソフトウェア |
| |||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 精密化 | 解像度: 1→20 Å / 交差検証法: THROUGHOUT / 立体化学のターゲット値: ENGH & HUBER 詳細: REFINEMENT WAS CARRIED OUT AGAINST F -SQUARED USING SHELXL-93. MOLECULAR GEOMETRY AND ATOMIC DISPLACEMENT PARAMETERS WERE RESTRAINED THROUGHOUT. INDEPENDENT VANCOMYCIN MONOMERS WERE ...詳細: REFINEMENT WAS CARRIED OUT AGAINST F -SQUARED USING SHELXL-93. MOLECULAR GEOMETRY AND ATOMIC DISPLACEMENT PARAMETERS WERE RESTRAINED THROUGHOUT. INDEPENDENT VANCOMYCIN MONOMERS WERE RESTRAINED TO HAVE SIMILAR 1-2 AND 1-3 DISTANCES; RESTRAINTS WERE ALSO IMPOSED TO LIMIT DEVIATIONS FROM PLANARITY IN RINGS AND SP2 SYSTEMS. ALONG-BOND COMPONENTS OF ANISOTROPIC DISPLACEMENT PARAMETERS WERE SUBJECTED TO RESTRAINTS. SOLVENT WATER ATOMS WERE RESTRAINED TO BE APPROXIMATELY ISOTROPIC AND WERE MADE SUBJECT TO ANTI-BUMPING RESTRAINTS. CONJUGATE GRADIENT REFINEMENT WAS USED THROUGHOUT, EXCEPT AT THE LAST STAGES, WHEN BLOCKED LEAST SQUARES WAS USED.
| |||||||||||||||||||||||||||||||||
| 精密化ステップ | サイクル: LAST / 解像度: 1→20 Å
| |||||||||||||||||||||||||||||||||
| 拘束条件 |
|
 ムービー
ムービー コントローラー
コントローラー



















 PDBj
PDBj