+ データを開く
データを開く
- 基本情報
基本情報
| 登録情報 | データベース: PDB / ID: 1mzt | ||||||
|---|---|---|---|---|---|---|---|
| タイトル | NMR structure of the fd bacteriophage pVIII coat protein in lipid bilayer membranes | ||||||
 要素 要素 | major coat protein pVIII | ||||||
 キーワード キーワード | VIRAL PROTEIN / fd coat protein / membrane-bound / pVIII | ||||||
| 機能・相同性 | Phage major coat protein, Gp8 / Bacteriophage M13, G8P, capsid domain superfamily / Capsid protein G8P / helical viral capsid / host cell membrane / membrane / Capsid protein G8P 機能・相同性情報 機能・相同性情報 | ||||||
| 生物種 |  Enterobacteria phage fd (ファージ) Enterobacteria phage fd (ファージ) | ||||||
| 手法 | 個体NMR / Calculation of bond orientations, dihedral angles from solid-state NMR restraints, back-calculation of NMR data from oriented structure | ||||||
 データ登録者 データ登録者 | Marassi, F.M. / Opella, S.J. | ||||||
 引用 引用 |  ジャーナル: Protein Sci. / 年: 2003 ジャーナル: Protein Sci. / 年: 2003タイトル: Simultaneous assignment and structure determination of a membrane protein from NMR orientational restraints 著者: Marassi, F.M. / Opella, S.J. #1:  ジャーナル: J.Biomol.NMR / 年: 2002 ジャーナル: J.Biomol.NMR / 年: 2002タイトル: Using Pisa pies to resolve ambiguities in angular constraints from PISEMA spectra of aligned proteins 著者: Marassi, F.M. / Opella, S.J. | ||||||
| 履歴 |
| ||||||
| Remark 999 | SEQUENCE AUTHOR PROVIDED COORDINATES FOR THE PROTEIN BACKBONE ONLY. |
- 構造の表示
構造の表示
| 構造ビューア | 分子:  Molmil Molmil Jmol/JSmol Jmol/JSmol |
|---|
- ダウンロードとリンク
ダウンロードとリンク
- ダウンロード
ダウンロード
| PDBx/mmCIF形式 |  1mzt.cif.gz 1mzt.cif.gz | 14.2 KB | 表示 |  PDBx/mmCIF形式 PDBx/mmCIF形式 |
|---|---|---|---|---|
| PDB形式 |  pdb1mzt.ent.gz pdb1mzt.ent.gz | 6.2 KB | 表示 |  PDB形式 PDB形式 |
| PDBx/mmJSON形式 |  1mzt.json.gz 1mzt.json.gz | ツリー表示 |  PDBx/mmJSON形式 PDBx/mmJSON形式 | |
| その他 |  その他のダウンロード その他のダウンロード |
-検証レポート
| 文書・要旨 |  1mzt_validation.pdf.gz 1mzt_validation.pdf.gz | 244.6 KB | 表示 |  wwPDB検証レポート wwPDB検証レポート |
|---|---|---|---|---|
| 文書・詳細版 |  1mzt_full_validation.pdf.gz 1mzt_full_validation.pdf.gz | 244.4 KB | 表示 | |
| XML形式データ |  1mzt_validation.xml.gz 1mzt_validation.xml.gz | 2.1 KB | 表示 | |
| CIF形式データ |  1mzt_validation.cif.gz 1mzt_validation.cif.gz | 2.2 KB | 表示 | |
| アーカイブディレクトリ |  https://data.pdbj.org/pub/pdb/validation_reports/mz/1mzt https://data.pdbj.org/pub/pdb/validation_reports/mz/1mzt ftp://data.pdbj.org/pub/pdb/validation_reports/mz/1mzt ftp://data.pdbj.org/pub/pdb/validation_reports/mz/1mzt | HTTPS FTP |
-関連構造データ
- リンク
リンク
- 集合体
集合体
| 登録構造単位 | 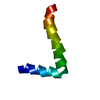
| |||||||||
|---|---|---|---|---|---|---|---|---|---|---|
| 1 |
| |||||||||
| NMR アンサンブル |
|
- 要素
要素
| #1: タンパク質・ペプチド | 分子量: 5244.000 Da / 分子数: 1 / 由来タイプ: 天然 / 由来: (天然)  Enterobacteria phage fd (ファージ) / 属: Inovirus / 生物種: Enterobacteria phage M13 / 参照: UniProt: P69539 Enterobacteria phage fd (ファージ) / 属: Inovirus / 生物種: Enterobacteria phage M13 / 参照: UniProt: P69539 |
|---|
-実験情報
-実験
| 実験 | 手法: 個体NMR |
|---|---|
| NMR実験 | タイプ: 1H/15N PISEMA |
| NMR実験の詳細 | Text: The structure was determined from one uniformly and four selectively 15N-labeled samples. |
- 試料調製
試料調製
| 詳細 | 内容: 8 mg 15N-labeled fd coat protein, 64 mg POPC, 16 mg POPG, lipid bilayers oriented on glass slides 溶媒系: Lipid bilayers hydrated in water |
|---|---|
| 試料状態 | イオン強度: 0 / pH: 7 / 圧: ambient / 温度: 296 K |
| 結晶化 | *PLUS 手法: other / 詳細: NMR |
-NMR測定
| 放射 | プロトコル: SINGLE WAVELENGTH / 単色(M)・ラウエ(L): M |
|---|---|
| 放射波長 | 相対比: 1 |
| NMRスペクトロメーター | タイプ: Chemagnetics CMX / 製造業者: Chemagnetics / モデル: CMX / 磁場強度: 400 MHz |
- 解析
解析
| NMR software |
| ||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 精密化 | 手法: Calculation of bond orientations, dihedral angles from solid-state NMR restraints, back-calculation of NMR data from oriented structure ソフトェア番号: 1 詳細: Structure calculated from 40 chemical shift and 40 dipolar coupling restraints | ||||||||||||||||||||
| 代表構造 | 選択基準: lowest energy | ||||||||||||||||||||
| NMRアンサンブル | コンフォーマー選択の基準: structures with the lowest energy 計算したコンフォーマーの数: 6 / 登録したコンフォーマーの数: 1 |
 ムービー
ムービー コントローラー
コントローラー








 PDBj
PDBj