| 登録情報 | データベース: PDB / ID: 1jrf
|
|---|
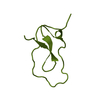
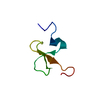
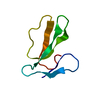
| タイトル | NMR Solution Structure of the Viral Receptor Domain of Tva |
|---|
 要素 要素 | SUBGROUP A ROUS SARCOMA VIRUS RECEPTORS PG800 AND PG950 |
|---|
 キーワード キーワード | SIGNALING PROTEIN / MEMBRANE PROTEIN / DISULFIDE BOND / ALPHA HELIX / CALCIUM CAGE |
|---|
| 機能・相同性 |  機能・相同性情報 機能・相同性情報
Low-density Lipoprotein Receptor / Low-density Lipoprotein Receptor / Low-density lipoprotein receptor domain class A / LDL-receptor class A (LDLRA) domain profile. / Low-density lipoprotein receptor domain class A / Low-density lipoprotein (LDL) receptor class A repeat / LDL receptor-like superfamily / Few Secondary Structures / Irregular類似検索 - ドメイン・相同性 Subgroup A Rous sarcoma virus receptor pg950類似検索 - 構成要素 |
|---|
| 生物種 |  Coturnix japonica (ウズラ) Coturnix japonica (ウズラ) |
|---|
| 手法 | 溶液NMR / simulated annealing |
|---|
 データ登録者 データ登録者 | Wang, Q.-Y. / Huang, W. / Dolmer, K. / Gettins, P.G.W. / Rong, L. |
|---|
 引用 引用 |  ジャーナル: J.Virol. / 年: 2002 ジャーナル: J.Virol. / 年: 2002
タイトル: Solution structure of the viral receptor domain of Tva and its implications in viral entry.
著者: Wang, Q.Y. / Huang, W. / Dolmer, K. / Gettins, P.G. / Rong, L. |
|---|
| 履歴 | | 登録 | 2001年8月13日 | 登録サイト: RCSB / 処理サイト: RCSB |
|---|
| 改定 1.0 | 2002年3月8日 | Provider: repository / タイプ: Initial release |
|---|
| 改定 1.1 | 2008年4月27日 | Group: Version format compliance |
|---|
| 改定 1.2 | 2011年7月13日 | Group: Version format compliance |
|---|
| 改定 1.3 | 2022年2月23日 | Group: Database references / Derived calculations
カテゴリ: database_2 / pdbx_struct_assembly ...database_2 / pdbx_struct_assembly / pdbx_struct_conn_angle / pdbx_struct_oper_list / struct_conn / struct_ref_seq_dif / struct_site
Item: _database_2.pdbx_DOI / _database_2.pdbx_database_accession ..._database_2.pdbx_DOI / _database_2.pdbx_database_accession / _pdbx_struct_conn_angle.ptnr1_auth_comp_id / _pdbx_struct_conn_angle.ptnr1_auth_seq_id / _pdbx_struct_conn_angle.ptnr1_label_atom_id / _pdbx_struct_conn_angle.ptnr1_label_comp_id / _pdbx_struct_conn_angle.ptnr1_label_seq_id / _pdbx_struct_conn_angle.ptnr3_auth_comp_id / _pdbx_struct_conn_angle.ptnr3_auth_seq_id / _pdbx_struct_conn_angle.ptnr3_label_atom_id / _pdbx_struct_conn_angle.ptnr3_label_comp_id / _pdbx_struct_conn_angle.ptnr3_label_seq_id / _pdbx_struct_conn_angle.value / _struct_conn.pdbx_dist_value / _struct_conn.ptnr1_auth_comp_id / _struct_conn.ptnr1_auth_seq_id / _struct_conn.ptnr1_label_asym_id / _struct_conn.ptnr1_label_atom_id / _struct_conn.ptnr1_label_comp_id / _struct_conn.ptnr1_label_seq_id / _struct_conn.ptnr2_auth_comp_id / _struct_conn.ptnr2_auth_seq_id / _struct_conn.ptnr2_label_asym_id / _struct_conn.ptnr2_label_atom_id / _struct_conn.ptnr2_label_comp_id / _struct_conn.ptnr2_label_seq_id / _struct_ref_seq_dif.details / _struct_site.pdbx_auth_asym_id / _struct_site.pdbx_auth_comp_id / _struct_site.pdbx_auth_seq_id |
|---|
| 改定 1.4 | 2024年11月20日 | Group: Data collection / Structure summary
カテゴリ: chem_comp_atom / chem_comp_bond ...chem_comp_atom / chem_comp_bond / pdbx_entry_details / pdbx_modification_feature |
|---|
|
|---|
 データを開く
データを開く 基本情報
基本情報 要素
要素 キーワード
キーワード 機能・相同性情報
機能・相同性情報 Coturnix japonica (ウズラ)
Coturnix japonica (ウズラ) データ登録者
データ登録者 引用
引用 ジャーナル: J.Virol. / 年: 2002
ジャーナル: J.Virol. / 年: 2002 構造の表示
構造の表示 Molmil
Molmil Jmol/JSmol
Jmol/JSmol ダウンロードとリンク
ダウンロードとリンク ダウンロード
ダウンロード 1jrf.cif.gz
1jrf.cif.gz PDBx/mmCIF形式
PDBx/mmCIF形式 pdb1jrf.ent.gz
pdb1jrf.ent.gz PDB形式
PDB形式 1jrf.json.gz
1jrf.json.gz PDBx/mmJSON形式
PDBx/mmJSON形式 その他のダウンロード
その他のダウンロード 1jrf_validation.pdf.gz
1jrf_validation.pdf.gz wwPDB検証レポート
wwPDB検証レポート 1jrf_full_validation.pdf.gz
1jrf_full_validation.pdf.gz 1jrf_validation.xml.gz
1jrf_validation.xml.gz 1jrf_validation.cif.gz
1jrf_validation.cif.gz https://data.pdbj.org/pub/pdb/validation_reports/jr/1jrf
https://data.pdbj.org/pub/pdb/validation_reports/jr/1jrf ftp://data.pdbj.org/pub/pdb/validation_reports/jr/1jrf
ftp://data.pdbj.org/pub/pdb/validation_reports/jr/1jrf リンク
リンク 集合体
集合体
 要素
要素 Coturnix japonica (ウズラ) / プラスミド: pGEX-4T-1 / 生物種 (発現宿主): Escherichia coli / 発現宿主:
Coturnix japonica (ウズラ) / プラスミド: pGEX-4T-1 / 生物種 (発現宿主): Escherichia coli / 発現宿主: 
 試料調製
試料調製 解析
解析 ムービー
ムービー コントローラー
コントローラー








 PDBj
PDBj


 HNCA
HNCA