+ データを開く
データを開く
- 基本情報
基本情報
| 登録情報 | データベース: PDB / ID: 1hu9 | ||||||
|---|---|---|---|---|---|---|---|
| タイトル | LIPOXYGENASE-3 (SOYBEAN) COMPLEX WITH 4-HYDROPEROXY-2-METHOXY-PHENOL | ||||||
 要素 要素 | LIPOXYGENASE-3 | ||||||
 キーワード キーワード | OXIDOREDUCTASE / METALLOPROTEIN / FE(III) COMPLEX / PURPLE LIPOXYGENASE / ENZYME INHIBITOR | ||||||
| 機能・相同性 |  機能・相同性情報 機能・相同性情報linoleate 9S-lipoxygenase / linoleate 9S-lipoxygenase activity / oxylipin biosynthetic process / lipid oxidation / oxidoreductase activity, acting on single donors with incorporation of molecular oxygen, incorporation of two atoms of oxygen / fatty acid biosynthetic process / metal ion binding / cytoplasm 類似検索 - 分子機能 | ||||||
| 生物種 |  | ||||||
| 手法 |  X線回折 / X線回折 /  分子置換 / 解像度: 2.2 Å 分子置換 / 解像度: 2.2 Å | ||||||
 データ登録者 データ登録者 | Zhou, K. / Skrzypczak-Jankun, E. / McCabe, N.P. / Selman, S.H. / Jankun, J. | ||||||
 引用 引用 |  ジャーナル: INT.J.MOL.MED. / 年: 2003 ジャーナル: INT.J.MOL.MED. / 年: 2003タイトル: Structure of curcumin in complex with lipoxygenase and its significance in cancer. 著者: Skrzypczak-Jankun, E. / Zhou, K. / McCabe, N.P. / Selman, S.H. / Jankun, J. #1:  ジャーナル: Int.J.Mol.Med. / 年: 2000 ジャーナル: Int.J.Mol.Med. / 年: 2000タイトル: Curcumin Inhibits Lipooxygenase by Binding to its Center Cavity: Theoretical and X-Ray Evidence 著者: Skrzypczak-Jankun, E. / McCabe, N.P. / Selman, S.H. / Jankun, J. #2:  ジャーナル: Proteins / 年: 1997 ジャーナル: Proteins / 年: 1997タイトル: Structure of Soybean Lipoxygenase L3 and a Comparison with its L1 Isoenzyme 著者: Skrzypczak-Jankun, E. / Amzel, L.M. / Kroa, B.A. / Funk Jr., M.O. #3:  ジャーナル: Biochemistry / 年: 1998 ジャーナル: Biochemistry / 年: 1998タイトル: Structural and Thermochemical Characterization of Lipoxygenase-Catechol Complexes 著者: Pham, C. / Jankun, J. / Skrzypczak-Jankun, E. / Flowers II, R.A. / Funk Jr., M.O. #4:  ジャーナル: Biochemistry / 年: 1994 ジャーナル: Biochemistry / 年: 1994タイトル: Position 713 is Critical for Catalysis But not Iron Binding in Soybean Lipoxygenase 3 著者: Kramer, J.A. / Johnson, K.R. / Dunham, W.R. / Sands, R.H. / Funk Jr., M.O. | ||||||
| 履歴 |
|
- 構造の表示
構造の表示
| 構造ビューア | 分子:  Molmil Molmil Jmol/JSmol Jmol/JSmol |
|---|
- ダウンロードとリンク
ダウンロードとリンク
- ダウンロード
ダウンロード
| PDBx/mmCIF形式 |  1hu9.cif.gz 1hu9.cif.gz | 190.6 KB | 表示 |  PDBx/mmCIF形式 PDBx/mmCIF形式 |
|---|---|---|---|---|
| PDB形式 |  pdb1hu9.ent.gz pdb1hu9.ent.gz | 149.3 KB | 表示 |  PDB形式 PDB形式 |
| PDBx/mmJSON形式 |  1hu9.json.gz 1hu9.json.gz | ツリー表示 |  PDBx/mmJSON形式 PDBx/mmJSON形式 | |
| その他 |  その他のダウンロード その他のダウンロード |
-検証レポート
| 文書・要旨 |  1hu9_validation.pdf.gz 1hu9_validation.pdf.gz | 448.9 KB | 表示 |  wwPDB検証レポート wwPDB検証レポート |
|---|---|---|---|---|
| 文書・詳細版 |  1hu9_full_validation.pdf.gz 1hu9_full_validation.pdf.gz | 482.2 KB | 表示 | |
| XML形式データ |  1hu9_validation.xml.gz 1hu9_validation.xml.gz | 38.9 KB | 表示 | |
| CIF形式データ |  1hu9_validation.cif.gz 1hu9_validation.cif.gz | 56 KB | 表示 | |
| アーカイブディレクトリ |  https://data.pdbj.org/pub/pdb/validation_reports/hu/1hu9 https://data.pdbj.org/pub/pdb/validation_reports/hu/1hu9 ftp://data.pdbj.org/pub/pdb/validation_reports/hu/1hu9 ftp://data.pdbj.org/pub/pdb/validation_reports/hu/1hu9 | HTTPS FTP |
-関連構造データ
| 関連構造データ |  1lnhS S: 精密化の開始モデル |
|---|---|
| 類似構造データ |
- リンク
リンク
- 集合体
集合体
| 登録構造単位 | 
| ||||||||
|---|---|---|---|---|---|---|---|---|---|
| 1 |
| ||||||||
| 単位格子 |
|
- 要素
要素
| #1: タンパク質 | 分子量: 96919.000 Da / 分子数: 1 / 由来タイプ: 天然 詳細: COMPLEX WITH 4-HYDROPEROXY-2-METHOXY-PHENOL A PHOTODEGREDATION PRODUCT OF CURCUMIN 由来: (天然)  |
|---|---|
| #2: 化合物 | ChemComp-FE / |
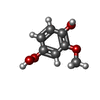
| #3: 化合物 | ChemComp-4HM / |
| #4: 水 | ChemComp-HOH / |
-実験情報
-実験
| 実験 | 手法:  X線回折 / 使用した結晶の数: 2 X線回折 / 使用した結晶の数: 2 |
|---|
- 試料調製
試料調製
| 結晶 | マシュー密度: 2.5 Å3/Da / 溶媒含有率: 50 % |
|---|---|
| 結晶化 | 温度: 296 K / 手法: 蒸気拡散法, シッティングドロップ法 / pH: 5.3 詳細: PEG 8000, phosphate-citrate buffer, sodium azide, pH 5.3, VAPOR DIFFUSION, SITTING DROP, temperature 296K |
-データ収集
| 回折 | 平均測定温度: 295 K |
|---|---|
| 放射光源 | 由来:  回転陽極 / タイプ: RIGAKU RU200 / 波長: 1.5418 回転陽極 / タイプ: RIGAKU RU200 / 波長: 1.5418 |
| 検出器 | タイプ: RIGAKU RAXIS IV / 検出器: IMAGE PLATE / 日付: 1999年8月1日 / 詳細: MIRRORS |
| 放射 | プロトコル: SINGLE WAVELENGTH / 単色(M)・ラウエ(L): M / 散乱光タイプ: x-ray |
| 放射波長 | 波長: 1.5418 Å / 相対比: 1 |
| 反射 | 解像度: 2.2→40 Å / Num. all: 45106 / Num. obs: 45106 / % possible obs: 95.5 % / Observed criterion σ(F): 2 / Observed criterion σ(I): 1 / 冗長度: 3 % / Biso Wilson estimate: 29.5 Å2 / Rmerge(I) obs: 0.07 / Net I/σ(I): 13.1 |
| 反射 シェル | 解像度: 2.2→2.28 Å / 冗長度: 2 % / Rmerge(I) obs: 0.331 / Mean I/σ(I) obs: 1 / Num. unique all: 4304 / % possible all: 90.9 |
- 解析
解析
| ソフトウェア |
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 精密化 | 構造決定の手法:  分子置換 分子置換開始モデル: PDB ENTRY 1LNH 解像度: 2.2→40 Å / Rfactor Rfree error: 0.02 / Data cutoff high absF: 100000 / Data cutoff low absF: 0.01 / Isotropic thermal model: isotropic / 交差検証法: THROUGHOUT / σ(F): 2 / σ(I): 1 / 立体化学のターゲット値: Engh & Huber 詳細: DISORDERED REGIONS 1-8 WERE OMITTED FROM CALCULATIONS. DISORDERED REGIONS 33-45 WERE INCLUDED IN THE REFINEMENT, HOWEVER, THE HIGH B-FACTOR INDICATE DISORDER AND LOW RELIABILITY FOR THIS LOOP. ...詳細: DISORDERED REGIONS 1-8 WERE OMITTED FROM CALCULATIONS. DISORDERED REGIONS 33-45 WERE INCLUDED IN THE REFINEMENT, HOWEVER, THE HIGH B-FACTOR INDICATE DISORDER AND LOW RELIABILITY FOR THIS LOOP. THE IRON BINDING SITE CONSISTS OF HIS 518, HIS 523, HIS 709 ASN 713, ILE 857 (C-TERMINAL) AND 4HM 861.THESE LIGANDS ARE ALL COVALENTLY BOUND TO IRON FE 858 IN AN OCTAHEDRAL COORDINATION.
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 原子変位パラメータ | Biso mean: 35.2 Å2 | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Refine analyze | Luzzati coordinate error obs: 0.24 Å / Luzzati d res low obs: 5 Å | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 精密化ステップ | サイクル: LAST / 解像度: 2.2→40 Å
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 拘束条件 |
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| LS精密化 シェル | Refine-ID: X-RAY DIFFRACTION / Total num. of bins used: 12
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Xplor file |
|
 ムービー
ムービー コントローラー
コントローラー


















 PDBj
PDBj