[English] 日本語
 Yorodumi
Yorodumi- PDB-1g04: SOLUTION STRUCTURE OF SYNTHETIC 26-MER PEPTIDE CONTAINING 145-169... -
+ Open data
Open data
- Basic information
Basic information
| Entry | Database: PDB / ID: 1g04 | ||||||
|---|---|---|---|---|---|---|---|
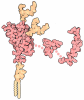
| Title | SOLUTION STRUCTURE OF SYNTHETIC 26-MER PEPTIDE CONTAINING 145-169 SHEEP PRION PROTEIN SEGMENT AND C-TERMINAL CYSTEINE | ||||||
 Components Components | MAJOR PRION PROTEIN | ||||||
 Keywords Keywords | UNKNOWN FUNCTION / prion / beta hairpin | ||||||
| Function / homology |  Function and homology information Function and homology informationside of membrane / tubulin binding / protein homooligomerization / microtubule binding / copper ion binding / Golgi apparatus / identical protein binding / plasma membrane Similarity search - Function | ||||||
| Method | SOLUTION NMR / simulated annealing torsion angle dynamics | ||||||
| Model type details | minimized average | ||||||
 Authors Authors | Kozin, S.A. / Bertho, G. / Mazur, A.K. / Rabesona, H. / Girault, J.-P. / Haertle, T. / Takahashi, M. / Debey, P. / Hui Bon Hoa, G. | ||||||
 Citation Citation |  Journal: J.Biol.Chem. / Year: 2001 Journal: J.Biol.Chem. / Year: 2001Title: Sheep prion protein synthetic peptide spanning helix 1 and beta-strand 2 (residues 142-166) shows beta-hairpin structure in solution. Authors: Kozin, S.A. / Bertho, G. / Mazur, A.K. / Rabesona, H. / Girault, J.P. / Haertle, T. / Takahashi, M. / Debey, P. / Hoa, G.H. | ||||||
| History |
|
- Structure visualization
Structure visualization
| Structure viewer | Molecule:  Molmil Molmil Jmol/JSmol Jmol/JSmol |
|---|
- Downloads & links
Downloads & links
- Download
Download
| PDBx/mmCIF format |  1g04.cif.gz 1g04.cif.gz | 190.3 KB | Display |  PDBx/mmCIF format PDBx/mmCIF format |
|---|---|---|---|---|
| PDB format |  pdb1g04.ent.gz pdb1g04.ent.gz | 157.3 KB | Display |  PDB format PDB format |
| PDBx/mmJSON format |  1g04.json.gz 1g04.json.gz | Tree view |  PDBx/mmJSON format PDBx/mmJSON format | |
| Others |  Other downloads Other downloads |
-Validation report
| Arichive directory |  https://data.pdbj.org/pub/pdb/validation_reports/g0/1g04 https://data.pdbj.org/pub/pdb/validation_reports/g0/1g04 ftp://data.pdbj.org/pub/pdb/validation_reports/g0/1g04 ftp://data.pdbj.org/pub/pdb/validation_reports/g0/1g04 | HTTPS FTP |
|---|
-Related structure data
| Similar structure data |
|---|
- Links
Links
- Assembly
Assembly
| Deposited unit | 
| |||||||||
|---|---|---|---|---|---|---|---|---|---|---|
| 1 |
| |||||||||
| NMR ensembles |
|
- Components
Components
| #1: Protein/peptide | Mass: 3431.729 Da / Num. of mol.: 1 / Source method: obtained synthetically Details: This peptide was chemically synthesized. Except for the C-terminal Cysteine, this sequence occurs naturally in sheep. References: UniProt: P23907 |
|---|
-Experimental details
-Experiment
| Experiment | Method: SOLUTION NMR |
|---|---|
| NMR experiment | Type: 2D NOESY |
- Sample preparation
Sample preparation
| Details | Contents: 4.5mM Solvent system: 10mM sodium phosphate buffer, pH 6.5; 90% H2O, 10% D2O |
|---|---|
| Sample conditions | Ionic strength: 15mM / pH: 6.5 / Pressure: 1 atm / Temperature: 278 K |
| Crystal grow | *PLUS Method: other / Details: NMR |
-NMR measurement
| NMR spectrometer | Type: Bruker AMX / Manufacturer: Bruker / Model: AMX / Field strength: 500 MHz |
|---|
- Processing
Processing
| NMR software | Name: XwinNMR / Version: 2.1 / Developer: bruker sowttfare / Classification: collection |
|---|---|
| Refinement | Method: simulated annealing torsion angle dynamics / Software ordinal: 1 Details: The structures are based on a total of 169 interresidual NOE-derived distance constraints. |
| NMR representative | Selection criteria: minimized average structure |
| NMR ensemble | Conformer selection criteria: structures with favorable non-bond energy Conformers calculated total number: 1000 / Conformers submitted total number: 21 |
 Movie
Movie Controller
Controller









 PDBj
PDBj