+ データを開く
データを開く
- 基本情報
基本情報
| 登録情報 | データベース: PDB / ID: 1fd5 | ||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
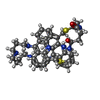
| タイトル | BINDING OF A MACROCYCLIC BISACRIDINE AND AMETANTRONE TO CGTACG INVOLVES SIMILAR UNUSUAL INTERCALATION PLATFORMS (BISACRIDINE COMPLEX) | ||||||||||||||||||
 要素 要素 | DNA (5'-D(* キーワード キーワードDNA / High resolution crystal structure / intercalation platform / MAD / anticancer drug / drug-DNA complex / metal ions / tertiary base pairs | 機能・相同性 | MACROCYCLIC-BIS-9-AMINO-ACRIDINE / : / DNA |  機能・相同性情報 機能・相同性情報手法 |  X線回折 / X線回折 /  シンクロトロン / 解像度: 1.1 Å シンクロトロン / 解像度: 1.1 Å  データ登録者 データ登録者Yang, X.-L. / Robinson, H. / Gao, Y.-G. / Wang, A.H.-J. |  引用 引用 ジャーナル: Biochemistry / 年: 2000 ジャーナル: Biochemistry / 年: 2000タイトル: Binding of a macrocyclic bisacridine and ametantrone to CGTACG involves similar unusual intercalation platforms. 著者: Yang, X.L. / Robinson, H. / Gao, Y.G. / Wang, A.H. 履歴 |
|
- 構造の表示
構造の表示
| 構造ビューア | 分子:  Molmil Molmil Jmol/JSmol Jmol/JSmol |
|---|
- ダウンロードとリンク
ダウンロードとリンク
- ダウンロード
ダウンロード
| PDBx/mmCIF形式 |  1fd5.cif.gz 1fd5.cif.gz | 26.6 KB | 表示 |  PDBx/mmCIF形式 PDBx/mmCIF形式 |
|---|---|---|---|---|
| PDB形式 |  pdb1fd5.ent.gz pdb1fd5.ent.gz | 16.8 KB | 表示 |  PDB形式 PDB形式 |
| PDBx/mmJSON形式 |  1fd5.json.gz 1fd5.json.gz | ツリー表示 |  PDBx/mmJSON形式 PDBx/mmJSON形式 | |
| その他 |  その他のダウンロード その他のダウンロード |
-検証レポート
| アーカイブディレクトリ |  https://data.pdbj.org/pub/pdb/validation_reports/fd/1fd5 https://data.pdbj.org/pub/pdb/validation_reports/fd/1fd5 ftp://data.pdbj.org/pub/pdb/validation_reports/fd/1fd5 ftp://data.pdbj.org/pub/pdb/validation_reports/fd/1fd5 | HTTPS FTP |
|---|
-関連構造データ
- リンク
リンク
- 集合体
集合体
| 登録構造単位 | 
| |||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 1 |
| |||||||||||||||||||||
| 単位格子 |
| |||||||||||||||||||||
| Components on special symmetry positions |
|
- 要素
要素
| #1: DNA鎖 | 分子量: 1809.217 Da / 分子数: 2 / 由来タイプ: 合成 / 詳細: synthetic DNA moleclue #2: 化合物 | #3: 化合物 | ChemComp-B9A / | #4: 化合物 | ChemComp-MG / | #5: 水 | ChemComp-HOH / | |
|---|
-実験情報
-実験
| 実験 | 手法:  X線回折 / 使用した結晶の数: 2 X線回折 / 使用した結晶の数: 2 |
|---|
- 試料調製
試料調製
| 結晶 | マシュー密度: 2.13 Å3/Da / 溶媒含有率: 42.17 % | |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 結晶化 | 温度: 298 K / 手法: 蒸気拡散法, シッティングドロップ法 / pH: 6 詳細: MPD, sodium cacodylate buffer, magnesium chloride, cobalt chloride, spermine, pH 6.0, VAPOR DIFFUSION, SITTING DROP, temperature 298K | |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 結晶化 | *PLUS 手法: 蒸気拡散法 | |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 溶液の組成 | *PLUS
|
-データ収集
| 回折 |
| |||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 放射光源 |
| |||||||||||||||
| 検出器 |
| |||||||||||||||
| 放射 | プロトコル: MAD / 単色(M)・ラウエ(L): M / 散乱光タイプ: x-ray | |||||||||||||||
| 放射波長 |
| |||||||||||||||
| 反射 | 解像度: 1.1→100 Å / Num. all: 196823 / Num. obs: 196823 / % possible obs: 99.9 % / Observed criterion σ(F): 0 / Observed criterion σ(I): 0 / 冗長度: 9.4 % / Biso Wilson estimate: 23 Å2 / Rmerge(I) obs: 0.057 / Net I/σ(I): 40.5 | |||||||||||||||
| 反射 シェル | 解像度: 1.1→1.14 Å / 冗長度: 7.2 % / Rmerge(I) obs: 0.597 / Num. unique all: 1293 / % possible all: 100 | |||||||||||||||
| 反射 | *PLUS Num. obs: 13377 / Num. measured all: 196823 |
- 解析
解析
| ソフトウェア |
| ||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 精密化 | 解像度: 1.1→10 Å / σ(F): 4 / σ(I): 2 立体化学のターゲット値: G.PARKINSON, J.VOJTECHOVSKY, L.CLOWNEY, A.T.BRUNGER, H.M.BERMAN
| ||||||||||||||||||||
| 精密化ステップ | サイクル: LAST / 解像度: 1.1→10 Å
| ||||||||||||||||||||
| 拘束条件 |
| ||||||||||||||||||||
| ソフトウェア | *PLUS 名称: SHELXL-97 / 分類: refinement | ||||||||||||||||||||
| 精密化 | *PLUS 最高解像度: 1.1 Å / 最低解像度: 10 Å / σ(I): 2 / σ(F): 4 / % reflection Rfree: 5 % | ||||||||||||||||||||
| 溶媒の処理 | *PLUS | ||||||||||||||||||||
| 原子変位パラメータ | *PLUS | ||||||||||||||||||||
| 拘束条件 | *PLUS タイプ: s_angle_d / Dev ideal: 2 |
 ムービー
ムービー コントローラー
コントローラー










 PDBj
PDBj