+ データを開く
データを開く
- 基本情報
基本情報
| 登録情報 | データベース: PDB / ID: 1eyo | ||||||
|---|---|---|---|---|---|---|---|
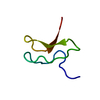
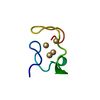
| タイトル | SOLUTION STRUCTURE OF CONOTOXIN TVIIA FROM CONUS TULIPA | ||||||
 要素 要素 | CONOTOXIN TVIIA | ||||||
 キーワード キーワード | TOXIN / cystine knot motif | ||||||
| 機能・相同性 | Conotoxin TVIIAGS / Conotoxin TVIIA/GS family / sodium channel inhibitor activity / toxin activity / extracellular region / Conotoxin TVIIA 機能・相同性情報 機能・相同性情報 | ||||||
| 手法 | 溶液NMR / simulated annealing | ||||||
 データ登録者 データ登録者 | Hill, J.M. / Alewood, P.F. / Craik, D.J. | ||||||
 引用 引用 |  ジャーナル: Eur.J.Biochem. / 年: 2000 ジャーナル: Eur.J.Biochem. / 年: 2000タイトル: Conotoxin TVIIA, a novel peptide from the venom of Conus tulipa 2. Three-dimensional solution structure. 著者: Hill, J.M. / Alewood, P.F. / Craik, D.J. #1:  ジャーナル: Eur.J.Biochem. / 年: 2000 ジャーナル: Eur.J.Biochem. / 年: 2000タイトル: Conotoxin TVIIA, a novel peptide from the venom of Conus tulipa 1. Isolation, characterisation and chemical synthesis 著者: Hill, J.M. / Atkins, A.R. / Loughnan, M.L. / Jones, A. / Adams, D.A. / Martin, R. / Lewis, R.J. / Craik, D.J. / Alewood, P.F. #2:  ジャーナル: Structure / 年: 1997 ジャーナル: Structure / 年: 1997タイトル: Solution structure of the sodium channel antagonist conotoxin GS: a new molecular caliper for probing sodium channel geometry 著者: Hill, J.M. / Alewood, P.F. / Craik, D.J. | ||||||
| 履歴 |
|
- 構造の表示
構造の表示
| 構造ビューア | 分子:  Molmil Molmil Jmol/JSmol Jmol/JSmol |
|---|
- ダウンロードとリンク
ダウンロードとリンク
- ダウンロード
ダウンロード
| PDBx/mmCIF形式 |  1eyo.cif.gz 1eyo.cif.gz | 168.4 KB | 表示 |  PDBx/mmCIF形式 PDBx/mmCIF形式 |
|---|---|---|---|---|
| PDB形式 |  pdb1eyo.ent.gz pdb1eyo.ent.gz | 146.1 KB | 表示 |  PDB形式 PDB形式 |
| PDBx/mmJSON形式 |  1eyo.json.gz 1eyo.json.gz | ツリー表示 |  PDBx/mmJSON形式 PDBx/mmJSON形式 | |
| その他 |  その他のダウンロード その他のダウンロード |
-検証レポート
| アーカイブディレクトリ |  https://data.pdbj.org/pub/pdb/validation_reports/ey/1eyo https://data.pdbj.org/pub/pdb/validation_reports/ey/1eyo ftp://data.pdbj.org/pub/pdb/validation_reports/ey/1eyo ftp://data.pdbj.org/pub/pdb/validation_reports/ey/1eyo | HTTPS FTP |
|---|
-関連構造データ
- リンク
リンク
- 集合体
集合体
| 登録構造単位 | 
| |||||||||
|---|---|---|---|---|---|---|---|---|---|---|
| 1 |
| |||||||||
| NMR アンサンブル |
|
- 要素
要素
| #1: タンパク質・ペプチド | 分子量: 3221.803 Da / 分子数: 1 / 由来タイプ: 合成 詳細: THIS PEPTIDE WAS CHEMICALLY SYNTHESIZED. THIS SEQUENCE OCCURS NATURALLY IN CONUS TULIPA (TULIP CONE) 参照: UniProt: P58923 |
|---|
-実験情報
-実験
| 実験 | 手法: 溶液NMR | ||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| NMR実験 |
| ||||||||||||||||||||
| NMR実験の詳細 | Text: This structure was determined using standard 2D homonuclear techniques. |
- 試料調製
試料調製
| 詳細 | 内容: 2mM conotoxin TVIIA / 溶媒系: 90% H2O/10% D2O or 99.99% D2O |
|---|---|
| 試料状態 | イオン強度: 0 / pH: 3 / 圧: ambient / 温度: 283 K |
| 結晶化 | *PLUS 手法: other / 詳細: NMR |
-NMR測定
| NMRスペクトロメーター |
|
|---|
- 解析
解析
| NMR software | 名称:  X-PLOR / バージョン: 3.1 / 開発者: Brunger / 分類: 精密化 X-PLOR / バージョン: 3.1 / 開発者: Brunger / 分類: 精密化 |
|---|---|
| 精密化 | 手法: simulated annealing / ソフトェア番号: 1 詳細: The structures are based on a total of 562 interproton distance restraints, and 18 backbone and 9 side chain dihedral angle restraints derived from spin-spin coupling constants. |
| 代表構造 | 選択基準: fewest violations,lowest energy |
| NMRアンサンブル | コンフォーマー選択の基準: structures with the least restraint violations,structures with the lowest energy 計算したコンフォーマーの数: 50 / 登録したコンフォーマーの数: 20 |
 ムービー
ムービー コントローラー
コントローラー








 PDBj
PDBj