[English] 日本語
 Yorodumi
Yorodumi- PDB-1abt: NMR SOLUTION STRUCTURE OF AN ALPHA-BUNGAROTOXIN(SLASH)NICOTINIC R... -
+ Open data
Open data
- Basic information
Basic information
| Entry | Database: PDB / ID: 1abt | ||||||
|---|---|---|---|---|---|---|---|
| Title | NMR SOLUTION STRUCTURE OF AN ALPHA-BUNGAROTOXIN(SLASH)NICOTINIC RECEPTOR PEPTIDE COMPLEX | ||||||
 Components Components |
| ||||||
 Keywords Keywords | TOXIN | ||||||
| Function / homology |  Function and homology information Function and homology informationacetylcholine receptor inhibitor activity / acetylcholine-gated monoatomic cation-selective channel activity / ion channel regulator activity / transmembrane signaling receptor activity / toxin activity / postsynaptic membrane / extracellular region Similarity search - Function | ||||||
| Method | SOLUTION NMR | ||||||
 Authors Authors | Basus, V.J. / Song, G. / Hawrot, E. | ||||||
 Citation Citation |  Journal: Biochemistry / Year: 1993 Journal: Biochemistry / Year: 1993Title: NMR solution structure of an alpha-bungarotoxin/nicotinic receptor peptide complex. Authors: Basus, V.J. / Song, G. / Hawrot, E. #1:  Journal: Proc.R.Soc.London,Ser.B / Year: 1990 Journal: Proc.R.Soc.London,Ser.B / Year: 1990Title: The Role of Tyrosine at the Ligand-Binding Site of the Nicotinic Acetylcholine Receptor Authors: Pearce, S.F.A. / Preston-Hurlburt, P. / Hawrot, E. #2:  Journal: Biochemistry / Year: 1988 Journal: Biochemistry / Year: 1988Title: Structural Studies of Alpha-Bungarotoxin. 1. Sequence-Specific 1H NMR Resonance Assignments Authors: Basus, V.J. / Billeter, M. / Love, R.A. / Stroud, R.M. / Kuntz, I.D. | ||||||
| History |
|
- Structure visualization
Structure visualization
| Structure viewer | Molecule:  Molmil Molmil Jmol/JSmol Jmol/JSmol |
|---|
- Downloads & links
Downloads & links
- Download
Download
| PDBx/mmCIF format |  1abt.cif.gz 1abt.cif.gz | 106.5 KB | Display |  PDBx/mmCIF format PDBx/mmCIF format |
|---|---|---|---|---|
| PDB format |  pdb1abt.ent.gz pdb1abt.ent.gz | 83.6 KB | Display |  PDB format PDB format |
| PDBx/mmJSON format |  1abt.json.gz 1abt.json.gz | Tree view |  PDBx/mmJSON format PDBx/mmJSON format | |
| Others |  Other downloads Other downloads |
-Validation report
| Arichive directory |  https://data.pdbj.org/pub/pdb/validation_reports/ab/1abt https://data.pdbj.org/pub/pdb/validation_reports/ab/1abt ftp://data.pdbj.org/pub/pdb/validation_reports/ab/1abt ftp://data.pdbj.org/pub/pdb/validation_reports/ab/1abt | HTTPS FTP |
|---|
-Related structure data
| Similar structure data |
|---|
- Links
Links
- Assembly
Assembly
| Deposited unit | 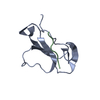
| |||||||||
|---|---|---|---|---|---|---|---|---|---|---|
| 1 |
| |||||||||
| Atom site foot note | 1: TYR A 24 - ARG A 25 MODEL 1 OMEGA =228.97 PEPTIDE BOND DEVIATES SIGNIFICANTLY FROM TRANS CONFORMATION 2: CYS A 29 - ASP A 30 MODEL 1 OMEGA = 17.57 PEPTIDE BOND DEVIATES SIGNIFICANTLY FROM TRANS CONFORMATION 3: GLU A 41 - LEU A 42 MODEL 2 OMEGA =134.97 PEPTIDE BOND DEVIATES SIGNIFICANTLY FROM TRANS CONFORMATION 4: LYS A 38 - VAL A 39 MODEL 3 OMEGA =145.32 PEPTIDE BOND DEVIATES SIGNIFICANTLY FROM TRANS CONFORMATION 5: TYR A 24 - ARG A 25 MODEL 4 OMEGA = 9.57 PEPTIDE BOND DEVIATES SIGNIFICANTLY FROM TRANS CONFORMATION 6: VAL A 39 - VAL A 40 MODEL 4 OMEGA =210.33 PEPTIDE BOND DEVIATES SIGNIFICANTLY FROM TRANS CONFORMATION 7: VAL A 40 - GLU A 41 MODEL 4 OMEGA =128.73 PEPTIDE BOND DEVIATES SIGNIFICANTLY FROM TRANS CONFORMATION | |||||||||
| NMR ensembles |
|
- Components
Components
| #1: Protein | Mass: 8005.281 Da / Num. of mol.: 1 Source method: isolated from a genetically manipulated source References: UniProt: P60615 |
|---|---|
| #2: Protein/peptide | Mass: 1517.726 Da / Num. of mol.: 1 Source method: isolated from a genetically manipulated source References: UniProt: P02710 |
| Has protein modification | Y |
-Experimental details
-Experiment
| Experiment | Method: SOLUTION NMR |
|---|
- Sample preparation
Sample preparation
| Crystal grow | *PLUS Method: other / Details: NMR |
|---|
- Processing
Processing
| NMR software |
| |||||||||
|---|---|---|---|---|---|---|---|---|---|---|
| Refinement | Software ordinal: 1 Details: NOE DATA CAME FROM SPECTRA COLLECTED AT 35 DEGREES AND AT 25 DEGREES CELSIUS, PH 5.8. A LIST OF ALL NMR CONSTRAINTS WAS DEPOSITED IN THE PROTEIN DATA BANK TOGETHER WITH THE STRUCTURE LIST. ...Details: NOE DATA CAME FROM SPECTRA COLLECTED AT 35 DEGREES AND AT 25 DEGREES CELSIUS, PH 5.8. A LIST OF ALL NMR CONSTRAINTS WAS DEPOSITED IN THE PROTEIN DATA BANK TOGETHER WITH THE STRUCTURE LIST. THESE CONSTRAINTS CONSISTED OF 365 INTRAMOLECULAR CONSTRAINTS (146 LONG-RANGE, 155 SEQUENTIAL AND 64 DIHEDRAL ANGLES), AND 24 INTERMOLECULAR CONSTRAINTS BETWEEN THE 74 RESIDUES OF BGTX AND THE FIRST 6 RESIDUES OF THE 12 RESIDUE PEPTIDE FRAGMENT OF NACHR USED IN THIS STUDY (LISTED HERE AS RESIDUES 75 B - 80 B). THE COORDINATES THAT FOLLOW ARE IN FOUR SEPARATE MODELS. THE 12 RESIDUE PEPTIDE FRAGMENT OF NACHR HAS BEEN MODELED FOR ONLY THE FIRST SIX RESIDUES AND HAS BEEN NUMBERED AS A CONTINUATION OF THE NUMBERS FOR THE BGTX PORTION OF THE COMPLEX AND GIVEN THE CHAIN IDENTIFIER 'B', AFTER THE TER ENTRY SEPARATING THE COORDINATES OF THE TWO COMPONENTS OF THE COMPLEX. THE AVERAGE RMS DEVIATION OF THE BACKBONE ATOMS, WHEN MATCHED IN A PAIRWISE MANNER, IS 2.6 ANGSTROMS, WITH THE POORLY DEFINED REGIONS OF RESIDUES 30 A - 38 A, AND 69 A - 74 A OF BGTX EXCLUDED. RESTRAINT VIOLATIONS: VIOLATIONS WERE CATEGORIZED ACCORDING TO SIZE. THE TOTAL NUMBER OF VIOLATIONS IN EACH CATEGORY WAS ADDED, AND THAT NUMBER DIVIDED BY 4 TO DETERMINE THE AVERAGE NUMBER OF VIOLATIONS PER STRUCTURE FOR EACH CATEGORY. VIOLATION RANGE AVERAGE NUMBER OF VIOLATIONS (ANGSTROMS) VIOLATION >0.7 5.0 0.7>=VIOLATION >0.6 6.0 0.6>=VIOLATION >0.5 5.75 0.5>=VIOLATION >0.4 9.5 0.4>=VIOLATION >0.3 17.0 0.3>=VIOLATION >0.2 16.5 0.2>=VIOLATION >0.1 18.0. TO SIMPLIFY THE CALCULATIONS, ONLY THE FIRST SIX AMINO ACIDS (185 - 190) OF THE DODECAPEPTIDE WERE INCORPORATED INTO THE STRUCTURE OF THE COMPLEX. THIS WAS APPROPRIATE AS NO INTERMOLECULAR NOE'S AND NO LONG-RANGE INTRAMOLECULAR NOE'S WERE ASSIGNED INVOLVING PEPTIDE RESIDUES 191 - 196. THE COORDINATES ARE PRESENTED IN FOUR SEPARATE MODELS, WITH TER STATEMENTS TO SEPARATE THE BGTX PART OF THE COMPLEX FROM THE NACHR PORTION OF THE COMPLEX. ALL STRUCTURES WERE MATCHED IN CARTESIAN SPACE SUCH THAT THE RMSD BETWEEN THEM WAS MINIMIZED, WITH THE EXCLUSION OF RESIDUES 30 A - 38 A, AND 69 A - 74 A OF BGTX. | |||||||||
| NMR ensemble | Conformers submitted total number: 4 |
 Movie
Movie Controller
Controller









 PDBj
PDBj


