+ データを開く
データを開く
- 基本情報
基本情報
| 登録情報 | データベース: EMDB / ID: EMD-9015 | |||||||||
|---|---|---|---|---|---|---|---|---|---|---|
| タイトル | Apo-EsCas13d | |||||||||
 マップデータ マップデータ | Apo-EsCas13d | |||||||||
 試料 試料 |
| |||||||||
| 生物種 |  unidentified bacterium (バクテリア) unidentified bacterium (バクテリア) | |||||||||
| 手法 | 単粒子再構成法 / クライオ電子顕微鏡法 / 解像度: 6.5 Å | |||||||||
 データ登録者 データ登録者 | Zhang C / Lyumkis D | |||||||||
| 資金援助 |  米国, 2件 米国, 2件
| |||||||||
 引用 引用 |  ジャーナル: Cell / 年: 2018 ジャーナル: Cell / 年: 2018タイトル: Structural Basis for the RNA-Guided Ribonuclease Activity of CRISPR-Cas13d. 著者: Cheng Zhang / Silvana Konermann / Nicholas J Brideau / Peter Lotfy / Xuebing Wu / Scott J Novick / Timothy Strutzenberg / Patrick R Griffin / Patrick D Hsu / Dmitry Lyumkis /  要旨: CRISPR-Cas endonucleases directed against foreign nucleic acids mediate prokaryotic adaptive immunity and have been tailored for broad genetic engineering applications. Type VI-D CRISPR systems ...CRISPR-Cas endonucleases directed against foreign nucleic acids mediate prokaryotic adaptive immunity and have been tailored for broad genetic engineering applications. Type VI-D CRISPR systems contain the smallest known family of single effector Cas enzymes, and their signature Cas13d ribonuclease employs guide RNAs to cleave matching target RNAs. To understand the molecular basis for Cas13d function and explain its compact molecular architecture, we resolved cryoelectron microscopy structures of Cas13d-guide RNA binary complex and Cas13d-guide-target RNA ternary complex to 3.4 and 3.3 Å resolution, respectively. Furthermore, a 6.5 Å reconstruction of apo Cas13d combined with hydrogen-deuterium exchange revealed conformational dynamics that have implications for RNA scanning. These structures, together with biochemical and cellular characterization, provide insights into its RNA-guided, RNA-targeting mechanism and delineate a blueprint for the rational design of improved transcriptome engineering technologies. | |||||||||
| 履歴 |
|
- 構造の表示
構造の表示
| ムービー |
 ムービービューア ムービービューア |
|---|---|
| 構造ビューア | EMマップ:  SurfView SurfView Molmil Molmil Jmol/JSmol Jmol/JSmol |
| 添付画像 |
- ダウンロードとリンク
ダウンロードとリンク
-EMDBアーカイブ
| マップデータ |  emd_9015.map.gz emd_9015.map.gz | 56.3 MB |  EMDBマップデータ形式 EMDBマップデータ形式 | |
|---|---|---|---|---|
| ヘッダ (付随情報) |  emd-9015-v30.xml emd-9015-v30.xml emd-9015.xml emd-9015.xml | 20.9 KB 20.9 KB | 表示 表示 |  EMDBヘッダ EMDBヘッダ |
| 画像 |  emd_9015.png emd_9015.png | 77.1 KB | ||
| その他 |  emd_9015_additional.map.gz emd_9015_additional.map.gz emd_9015_half_map_1.map.gz emd_9015_half_map_1.map.gz emd_9015_half_map_2.map.gz emd_9015_half_map_2.map.gz | 1 MB 11.1 MB 11.2 MB | ||
| アーカイブディレクトリ |  http://ftp.pdbj.org/pub/emdb/structures/EMD-9015 http://ftp.pdbj.org/pub/emdb/structures/EMD-9015 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-9015 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-9015 | HTTPS FTP |
-関連構造データ
| 関連構造データ |  9013C  9014C  6e9eC  6e9fC C: 同じ文献を引用 ( |
|---|---|
| 類似構造データ | |
| 電子顕微鏡画像生データ |  EMPIAR-10229 (タイトル: Cryo-EM Reconstruction of apo EsCas13d / Data size: 66.9 EMPIAR-10229 (タイトル: Cryo-EM Reconstruction of apo EsCas13d / Data size: 66.9 Data #1: stack of ~150k particles used for ab initio orientation assignment and reconstruction [picked particles - single frame - unprocessed] Data #2: stack of ~16k best particles from above [picked particles - single frame - processed]) |
- リンク
リンク
| EMDBのページ |  EMDB (EBI/PDBe) / EMDB (EBI/PDBe) /  EMDataResource EMDataResource |
|---|
- マップ
マップ
| ファイル |  ダウンロード / ファイル: emd_9015.map.gz / 形式: CCP4 / 大きさ: 64 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) ダウンロード / ファイル: emd_9015.map.gz / 形式: CCP4 / 大きさ: 64 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | Apo-EsCas13d | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 投影像・断面図 | 画像のコントロール
画像は Spider により作成 | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| ボクセルのサイズ | X=Y=Z: 0.79 Å | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
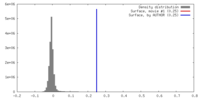
| 密度 |
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 対称性 | 空間群: 1 | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 詳細 | EMDB XML:
CCP4マップ ヘッダ情報:
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
-添付データ
-追加マップ: Apo-EsCas13d, additional map
| ファイル | emd_9015_additional.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | Apo-EsCas13d, additional map | ||||||||||||
| 投影像・断面図 |
| ||||||||||||
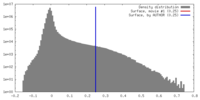
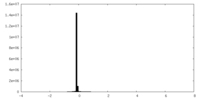
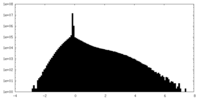
| 密度ヒストグラム |
-ハーフマップ: Apo-EsCas13d, half map #1
| ファイル | emd_9015_half_map_1.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | Apo-EsCas13d, half map #1 | ||||||||||||
| 投影像・断面図 |
| ||||||||||||
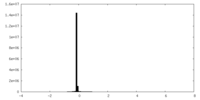
| 密度ヒストグラム |
-ハーフマップ: Apo-EsCas13d, half map #2
| ファイル | emd_9015_half_map_2.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | Apo-EsCas13d, half map #2 | ||||||||||||
| 投影像・断面図 |
| ||||||||||||
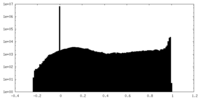
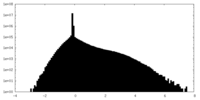
| 密度ヒストグラム |
- 試料の構成要素
試料の構成要素
-全体 : Apo-EsCas13d
| 全体 | 名称: Apo-EsCas13d |
|---|---|
| 要素 |
|
-超分子 #1: Apo-EsCas13d
| 超分子 | 名称: Apo-EsCas13d / タイプ: complex / ID: 1 / 親要素: 0 / 含まれる分子: all |
|---|---|
| 由来(天然) | 生物種:  unidentified bacterium (バクテリア) unidentified bacterium (バクテリア) |
| 組換発現 | 生物種:  |
| 分子量 | 理論値: 110 KDa |
-分子 #1: Apo-esCas13d
| 分子 | 名称: Apo-esCas13d / タイプ: protein_or_peptide / ID: 1 / 光学異性体: LEVO |
|---|---|
| 由来(天然) | 生物種:  unidentified bacterium (バクテリア) unidentified bacterium (バクテリア) |
| 組換発現 | 生物種:  |
| 配列 | 文字列: MGKKIHARDL REQRKTDRTE KFADQNKKRE AERAVPKKDA AVSVKSVSSV SSKKDNVTKS MAKAAGVKSV FAVGNTVYMT SFGRGNDAVL EQKIVDTSHE PLNIDDPAYQ LNVVTMNGYS VTGHRGETVS AVTDNPLRRF NGRKKDEPEQ SVPTDMLCLK PTLEKKFFGK ...文字列: MGKKIHARDL REQRKTDRTE KFADQNKKRE AERAVPKKDA AVSVKSVSSV SSKKDNVTKS MAKAAGVKSV FAVGNTVYMT SFGRGNDAVL EQKIVDTSHE PLNIDDPAYQ LNVVTMNGYS VTGHRGETVS AVTDNPLRRF NGRKKDEPEQ SVPTDMLCLK PTLEKKFFGK EFDDNIHIQL IYNILDIEKI LAVYSTNAIY ALNNMSADEN IENSDFFMKR TTDETFDDFE KKKESTNSRE KADFDAFEKF IGNYRLAYFA DAFYVNKKNP KGKAKNVLRE DKELYSVLTL IGKLRHWCVH SEEGRAEFWL YKLDELKDDF KNVLDVVYNR PVEEINNRFI ENNKVNIQIL GSVYKNTDIA ELVRSYYEFL ITKKYKNMGF SIKKLRESML EGKGYADKEY DSVRNKLYQM TDFILYTGYI NEDSDRADDL VNTLRSSLKE DDKTTVYCKE ADYLWKKYRE SIREVADALD GDNIKKLSKS NIEIQEDKLR KCFISYADSV SEFTKLIYLL TRFLSGKEIN DLVTTLINKF DNIRSFLEIM DELGLDRTFT AEYSFFEGST KYLAELVELN SFVKSCSFDI NAKRTMYRDA LDILGIESDK TEEDIEKMID NILQIDANGD KKLKKNNGLR NFIASNVIDS NRFKYLVRYG NPKKIRETAK CKPAVRFVLN EIPDAQIERY YEACCPKNTA LCSANKRREK LADMIAEIKF ENFSDAGNYQ KANVTSRTSE AEIKRKNQAI IRLYLTVMYI MLKNLVNVNA RYVIAFHCVE RDTKLYAESG LEVGNIEKNK TNLTMAVMGV KLENGIIKTE FDKSFAENAA NRYLRNARWY KLILDNLKKS ERAVVNEFRN TVCHLNAIRN ININIKEIKE VENYFALYHY LIQKHLENRF ADKKVERDTG DFISKLEEHK TYCKDFVKAY CTPFGYNLVR YKNLTIDGLF DKNYPGKDDS DEQK |
-実験情報
-構造解析
| 手法 | クライオ電子顕微鏡法 |
|---|---|
 解析 解析 | 単粒子再構成法 |
| 試料の集合状態 | particle |
- 試料調製
試料調製
| 濃度 | 1 mg/mL | |||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 緩衝液 | pH: 7.5 構成要素:
| |||||||||||||||||||||
| グリッド | 前処理 - タイプ: PLASMA CLEANING / 前処理 - 雰囲気: OTHER / 詳細: unspecified | |||||||||||||||||||||
| 凍結 | 凍結剤: ETHANE / チャンバー内湿度: 80 % / 装置: HOMEMADE PLUNGER |
- 電子顕微鏡法
電子顕微鏡法
| 顕微鏡 | FEI TALOS ARCTICA |
|---|---|
| 撮影 | フィルム・検出器のモデル: GATAN K2 SUMMIT (4k x 4k) 検出モード: COUNTING / デジタル化 - サイズ - 横: 3838 pixel / デジタル化 - サイズ - 縦: 3710 pixel / デジタル化 - 画像ごとのフレーム数: 1-120 / 実像数: 1158 / 平均電子線量: 56.8 e/Å2 |
| 電子線 | 加速電圧: 200 kV / 電子線源:  FIELD EMISSION GUN FIELD EMISSION GUN |
| 電子光学系 | C2レンズ絞り径: 70.0 µm / 照射モード: FLOOD BEAM / 撮影モード: BRIGHT FIELD / Cs: 2.7 mm / 最大 デフォーカス(公称値): 2.0 µm / 最小 デフォーカス(公称値): 1.0 µm / 倍率(公称値): 57000 |
| 試料ステージ | 試料ホルダーモデル: FEI TITAN KRIOS AUTOGRID HOLDER ホルダー冷却材: NITROGEN |
| 実験機器 |  モデル: Talos Arctica / 画像提供: FEI Company |
+ 画像解析
画像解析
-原子モデル構築 1
| 精密化 | 空間: REAL / プロトコル: AB INITIO MODEL / 当てはまり具合の基準: Correlation coefficient |
|---|
 ムービー
ムービー コントローラー
コントローラー














 Z (Sec.)
Z (Sec.) Y (Row.)
Y (Row.) X (Col.)
X (Col.)