+ データを開く
データを開く
- 基本情報
基本情報
| 登録情報 | データベース: EMDB / ID: EMD-7788 | |||||||||
|---|---|---|---|---|---|---|---|---|---|---|
| タイトル | Insulin Receptor ectodomain in complex with two insulin molecules plunged with a spot-to-plunge time of 200 ms | |||||||||
 マップデータ マップデータ | CryoSPARC auto-generated sharpened full map from the last iteration of independent refinement. | |||||||||
 試料 試料 |
| |||||||||
| 生物種 |  Homo sapiens (ヒト) Homo sapiens (ヒト) | |||||||||
| 手法 | 単粒子再構成法 / クライオ電子顕微鏡法 / 解像度: 4.93 Å | |||||||||
 データ登録者 データ登録者 | Noble AJ / Wei H / Dandey VP / Zhang Z / Potter CS / Carragher B | |||||||||
 引用 引用 |  ジャーナル: Nat Methods / 年: 2018 ジャーナル: Nat Methods / 年: 2018タイトル: Reducing effects of particle adsorption to the air-water interface in cryo-EM. 著者: Alex J Noble / Hui Wei / Venkata P Dandey / Zhening Zhang / Yong Zi Tan / Clinton S Potter / Bridget Carragher /  要旨: Most protein particles prepared in vitreous ice for single-particle cryo-electron microscopy (cryo-EM) are adsorbed to air-water or substrate-water interfaces, which can cause the particles to adopt ...Most protein particles prepared in vitreous ice for single-particle cryo-electron microscopy (cryo-EM) are adsorbed to air-water or substrate-water interfaces, which can cause the particles to adopt preferred orientations. By using a rapid plunge-freezing robot and nanowire grids, we were able to reduce some of the deleterious effects of the air-water interface by decreasing the dwell time of particles in thin liquid films. We demonstrated this by using single-particle cryo-EM and cryo-electron tomography (cryo-ET) to examine hemagglutinin, insulin receptor complex, and apoferritin. | |||||||||
| 履歴 |
|
- 構造の表示
構造の表示
| ムービー |
 ムービービューア ムービービューア |
|---|---|
| 構造ビューア | EMマップ:  SurfView SurfView Molmil Molmil Jmol/JSmol Jmol/JSmol |
| 添付画像 |
- ダウンロードとリンク
ダウンロードとリンク
-EMDBアーカイブ
| マップデータ |  emd_7788.map.gz emd_7788.map.gz | 86 MB |  EMDBマップデータ形式 EMDBマップデータ形式 | |
|---|---|---|---|---|
| ヘッダ (付随情報) |  emd-7788-v30.xml emd-7788-v30.xml emd-7788.xml emd-7788.xml | 15.8 KB 15.8 KB | 表示 表示 |  EMDBヘッダ EMDBヘッダ |
| 画像 |  emd_7788.png emd_7788.png | 62.4 KB | ||
| マスクデータ |  emd_7788_msk_1.map emd_7788_msk_1.map | 91.1 MB |  マスクマップ マスクマップ | |
| その他 |  emd_7788_half_map_1.map.gz emd_7788_half_map_1.map.gz emd_7788_half_map_2.map.gz emd_7788_half_map_2.map.gz | 84.5 MB 84.5 MB | ||
| アーカイブディレクトリ |  http://ftp.pdbj.org/pub/emdb/structures/EMD-7788 http://ftp.pdbj.org/pub/emdb/structures/EMD-7788 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-7788 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-7788 | HTTPS FTP |
-検証レポート
| 文書・要旨 |  emd_7788_validation.pdf.gz emd_7788_validation.pdf.gz | 79 KB | 表示 |  EMDB検証レポート EMDB検証レポート |
|---|---|---|---|---|
| 文書・詳細版 |  emd_7788_full_validation.pdf.gz emd_7788_full_validation.pdf.gz | 78.1 KB | 表示 | |
| XML形式データ |  emd_7788_validation.xml.gz emd_7788_validation.xml.gz | 495 B | 表示 | |
| アーカイブディレクトリ |  https://ftp.pdbj.org/pub/emdb/validation_reports/EMD-7788 https://ftp.pdbj.org/pub/emdb/validation_reports/EMD-7788 ftp://ftp.pdbj.org/pub/emdb/validation_reports/EMD-7788 ftp://ftp.pdbj.org/pub/emdb/validation_reports/EMD-7788 | HTTPS FTP |
-関連構造データ
- リンク
リンク
| EMDBのページ |  EMDB (EBI/PDBe) / EMDB (EBI/PDBe) /  EMDataResource EMDataResource |
|---|
- マップ
マップ
| ファイル |  ダウンロード / ファイル: emd_7788.map.gz / 形式: CCP4 / 大きさ: 91.1 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) ダウンロード / ファイル: emd_7788.map.gz / 形式: CCP4 / 大きさ: 91.1 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | CryoSPARC auto-generated sharpened full map from the last iteration of independent refinement. | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 投影像・断面図 | 画像のコントロール
画像は Spider により作成 | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| ボクセルのサイズ | X=Y=Z: 1.1 Å | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
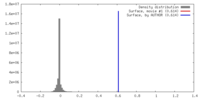
| 密度 |
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 対称性 | 空間群: 1 | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 詳細 | EMDB XML:
CCP4マップ ヘッダ情報:
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
-添付データ
-マスク #1
| ファイル |  emd_7788_msk_1.map emd_7788_msk_1.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
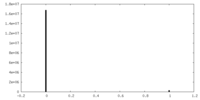
| 投影像・断面図 |
| ||||||||||||
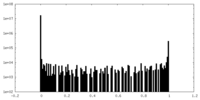
| 密度ヒストグラム |
-ハーフマップ: CryoSPARC auto-generated half-map from the last iteration of...
| ファイル | emd_7788_half_map_1.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | CryoSPARC auto-generated half-map from the last iteration of independent refinement. | ||||||||||||
| 投影像・断面図 |
| ||||||||||||
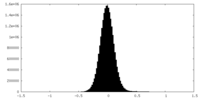
| 密度ヒストグラム |
-ハーフマップ: CryoSPARC auto-generated half-map from the last iteration of...
| ファイル | emd_7788_half_map_2.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | CryoSPARC auto-generated half-map from the last iteration of independent refinement. | ||||||||||||
| 投影像・断面図 |
| ||||||||||||
| 密度ヒストグラム |
- 試料の構成要素
試料の構成要素
-全体 : Insulin Receptor Ectodomain in complex with two insulin molecules
| 全体 | 名称: Insulin Receptor Ectodomain in complex with two insulin molecules |
|---|---|
| 要素 |
|
-超分子 #1: Insulin Receptor Ectodomain in complex with two insulin molecules
| 超分子 | 名称: Insulin Receptor Ectodomain in complex with two insulin molecules タイプ: complex / ID: 1 / 親要素: 0 |
|---|---|
| 由来(天然) | 生物種:  Homo sapiens (ヒト) Homo sapiens (ヒト) |
| 組換発現 | 生物種:  |
| 分子量 | 実験値: 215 KDa |
-実験情報
-構造解析
| 手法 | クライオ電子顕微鏡法 |
|---|---|
 解析 解析 | 単粒子再構成法 |
| 試料の集合状態 | particle |
- 試料調製
試料調製
| 緩衝液 | pH: 7.5 |
|---|---|
| グリッド | モデル: Homemade |
| 凍結 | 凍結剤: ETHANE / 装置: OTHER 詳細: 200 ms spot-to-plunge time. The value given for _emd_vitrification.instrument is SPOTITON. This is not in a list of allowed values set(['LEICA EM CPC', 'GATAN CRYOPLUNGE 3', 'LEICA PLUNGER', ...詳細: 200 ms spot-to-plunge time. The value given for _emd_vitrification.instrument is SPOTITON. This is not in a list of allowed values set(['LEICA EM CPC', 'GATAN CRYOPLUNGE 3', 'LEICA PLUNGER', 'FEI VITROBOT MARK II', 'HOMEMADE PLUNGER', 'REICHERT-JUNG PLUNGER', 'FEI VITROBOT MARK I', 'LEICA KF80', 'FEI VITROBOT MARK III', 'LEICA EM GP', 'OTHER', 'FEI VITROBOT MARK IV']) so OTHER is written into the XML file. |
- 電子顕微鏡法
電子顕微鏡法
| 顕微鏡 | FEI TITAN KRIOS |
|---|---|
| 特殊光学系 | 球面収差補正装置: Corrected so that Cs is as close to 0 as possible. エネルギーフィルター - 名称: GIF Bioquantum |
| 撮影 | フィルム・検出器のモデル: GATAN K2 QUANTUM (4k x 4k) 検出モード: COUNTING / 平均露光時間: 10.0 sec. / 平均電子線量: 66.0 e/Å2 |
| 電子線 | 加速電圧: 300 kV / 電子線源:  FIELD EMISSION GUN FIELD EMISSION GUN |
| 電子光学系 | 照射モード: FLOOD BEAM / 撮影モード: BRIGHT FIELD / Cs: 0.01 mm / 倍率(公称値): 105000 |
| 試料ステージ | 試料ホルダーモデル: FEI TITAN KRIOS AUTOGRID HOLDER ホルダー冷却材: NITROGEN |
| 実験機器 |  モデル: Titan Krios / 画像提供: FEI Company |
 ムービー
ムービー コントローラー
コントローラー





















 Z (Sec.)
Z (Sec.) Y (Row.)
Y (Row.) X (Col.)
X (Col.)