+ データを開く
データを開く
- 基本情報
基本情報
| 登録情報 |  | |||||||||
|---|---|---|---|---|---|---|---|---|---|---|
| タイトル | CNGA1 channel closed state in nanodisc with diC8-PIP2 cGMP-free | |||||||||
 マップデータ マップデータ | ||||||||||
 試料 試料 |
| |||||||||
 キーワード キーワード | Cyclic nucleotide-gated channel / Rod photoreceptor / CNGA1 / Ion channel / TRANSPORT PROTEIN | |||||||||
| 機能・相同性 |  機能・相同性情報 機能・相同性情報intracellular cyclic nucleotide activated cation channel complex / intracellularly cGMP-activated cation channel activity / intracellularly cAMP-activated cation channel activity / rod photoreceptor outer segment / sensory perception of chemical stimulus / photoreceptor outer segment membrane / sodium channel activity / sodium ion transport / cGMP binding / monoatomic cation transmembrane transport ...intracellular cyclic nucleotide activated cation channel complex / intracellularly cGMP-activated cation channel activity / intracellularly cAMP-activated cation channel activity / rod photoreceptor outer segment / sensory perception of chemical stimulus / photoreceptor outer segment membrane / sodium channel activity / sodium ion transport / cGMP binding / monoatomic cation transmembrane transport / cAMP binding / visual perception / calcium channel activity / Activation of the phototransduction cascade / calcium ion transport / Inactivation, recovery and regulation of the phototransduction cascade / plasma membrane 類似検索 - 分子機能 | |||||||||
| 生物種 |  Homo sapiens (ヒト) Homo sapiens (ヒト) | |||||||||
| 手法 | 単粒子再構成法 / クライオ電子顕微鏡法 / 解像度: 2.11 Å | |||||||||
 データ登録者 データ登録者 | Park T / Nimigean CM | |||||||||
| 資金援助 |  米国, 1件 米国, 1件
| |||||||||
 引用 引用 |  ジャーナル: bioRxiv / 年: 2025 ジャーナル: bioRxiv / 年: 2025タイトル: PIP2 Binding at Allosteric Site Blocks Activation in Human Rod CNG Channels. 著者: Taehyun Park / Crina M Nimigean /  要旨: Phosphatidylinositol-4,5-bisphosphate (PIP2) is a ubiquitous signaling lipid that regulates multiple ion channels. In human cyclic nucleotide-gated (CNG) channels, including the rod photoreceptor ...Phosphatidylinositol-4,5-bisphosphate (PIP2) is a ubiquitous signaling lipid that regulates multiple ion channels. In human cyclic nucleotide-gated (CNG) channels, including the rod photoreceptor channel, PIP2 has been reported to exert inhibitory effects, but the underlying mechanism has remained unclear. Because this inhibition lowers the apparent cGMP sensitivity of rod CNG channels, it can play a key role in controlling the light sensitivity and dynamic range of rod photoreceptors. Here we report how PIP2 modulates the function of human CNGA1 channels, the major subunit of human rod photoreceptor CNG channels. Ensemble ion flux assays with liposome-reconstituted purified CNGA1 channels demonstrated robust inhibition by PIP2 via a reduction in apparent cGMP sensitivity, and single-channel recordings revealed PIP2 reduces the channel's open probability without altering unitary conductance. To uncover the structural basis, we determined cryo-EM structures of CNGA1 in lipid nanodiscs under multiple ligand conditions. In PIP2-free conditions, closed, intermediate, and open conformations were observed, whereas in the presence of PIP2, the open state was absent. Density consistent with bound PIP2 was detected at inter-protomer grooves between the voltage-sensing and pore domains indicating that PIP2 binding stabilizes non-conductive conformations by sterically preventing C-linker elevation and outward movement of helix S6, conformational changes needed for pore dilation. Collectively, our results establish a structural mechanism for PIP2-mediated inhibition of rod CNG channels, define a mechanistic framework for phosphoinositide control of ligand-gated channels across the CNG superfamily, and provide an inhibitory allosteric binding site for future drug targeting in this channel family. | |||||||||
| 履歴 |
|
- 構造の表示
構造の表示
| 添付画像 |
|---|
- ダウンロードとリンク
ダウンロードとリンク
-EMDBアーカイブ
| マップデータ |  emd_74539.map.gz emd_74539.map.gz | 125.7 MB |  EMDBマップデータ形式 EMDBマップデータ形式 | |
|---|---|---|---|---|
| ヘッダ (付随情報) |  emd-74539-v30.xml emd-74539-v30.xml emd-74539.xml emd-74539.xml | 18 KB 18 KB | 表示 表示 |  EMDBヘッダ EMDBヘッダ |
| 画像 |  emd_74539.png emd_74539.png | 51.6 KB | ||
| マスクデータ |  emd_74539_msk_1.map emd_74539_msk_1.map | 166.4 MB |  マスクマップ マスクマップ | |
| Filedesc metadata |  emd-74539.cif.gz emd-74539.cif.gz | 6.4 KB | ||
| その他 |  emd_74539_half_map_1.map.gz emd_74539_half_map_1.map.gz emd_74539_half_map_2.map.gz emd_74539_half_map_2.map.gz | 126.3 MB 126.5 MB | ||
| アーカイブディレクトリ |  http://ftp.pdbj.org/pub/emdb/structures/EMD-74539 http://ftp.pdbj.org/pub/emdb/structures/EMD-74539 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-74539 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-74539 | HTTPS FTP |
-関連構造データ
| 関連構造データ |  9zq0MC  9zpvC  9zpwC  9zpxC  9zpyC  9zpzC  9zq1C M: このマップから作成された原子モデル C: 同じ文献を引用 ( |
|---|---|
| 類似構造データ | 類似検索 - 機能・相同性  F&H 検索 F&H 検索 |
- リンク
リンク
| EMDBのページ |  EMDB (EBI/PDBe) / EMDB (EBI/PDBe) /  EMDataResource EMDataResource |
|---|---|
| 「今月の分子」の関連する項目 |
- マップ
マップ
| ファイル |  ダウンロード / ファイル: emd_74539.map.gz / 形式: CCP4 / 大きさ: 166.4 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) ダウンロード / ファイル: emd_74539.map.gz / 形式: CCP4 / 大きさ: 166.4 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) | ||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| ボクセルのサイズ | X=Y=Z: 0.9 Å | ||||||||||||||||||||
| 密度 |
| ||||||||||||||||||||
| 対称性 | 空間群: 1 | ||||||||||||||||||||
| 詳細 | EMDB XML:
|
-添付データ
-マスク #1
| ファイル |  emd_74539_msk_1.map emd_74539_msk_1.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 投影像・断面図 |
| ||||||||||||
| 密度ヒストグラム |
-ハーフマップ: #2
| ファイル | emd_74539_half_map_1.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 投影像・断面図 |
| ||||||||||||
| 密度ヒストグラム |
-ハーフマップ: #1
| ファイル | emd_74539_half_map_2.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 投影像・断面図 |
| ||||||||||||
| 密度ヒストグラム |
- 試料の構成要素
試料の構成要素
-全体 : Homotetramer complex of Cyclic nucleotide-gated channel alpha-1
| 全体 | 名称: Homotetramer complex of Cyclic nucleotide-gated channel alpha-1 |
|---|---|
| 要素 |
|
-超分子 #1: Homotetramer complex of Cyclic nucleotide-gated channel alpha-1
| 超分子 | 名称: Homotetramer complex of Cyclic nucleotide-gated channel alpha-1 タイプ: complex / ID: 1 / 親要素: 0 / 含まれる分子: #1 |
|---|---|
| 由来(天然) | 生物種:  Homo sapiens (ヒト) Homo sapiens (ヒト) |
| 分子量 | 理論値: 316.5 KDa |
-分子 #1: Cyclic nucleotide-gated channel alpha-1
| 分子 | 名称: Cyclic nucleotide-gated channel alpha-1 / タイプ: protein_or_peptide / ID: 1 / コピー数: 4 / 光学異性体: LEVO |
|---|---|
| 由来(天然) | 生物種:  Homo sapiens (ヒト) Homo sapiens (ヒト) |
| 分子量 | 理論値: 64.519238 KDa |
| 組換発現 | 生物種:  Homo sapiens (ヒト) Homo sapiens (ヒト) |
| 配列 | 文字列: DYKDDDDKGG SASKDKKEEE KKEVVVIDPS GNTYYNWLFC ITLPVMYNWT MVIARACFDE LQSDYLEYWL ILDYVSDIVY LIDMFVRTR TGYLEQGLLV KEELKLINKY KSNLQFKLDV LSLIPTDLLY FKLGWNYPEI RLNRLLRFSR MFEFFQRTET R TNYPNIFR ...文字列: DYKDDDDKGG SASKDKKEEE KKEVVVIDPS GNTYYNWLFC ITLPVMYNWT MVIARACFDE LQSDYLEYWL ILDYVSDIVY LIDMFVRTR TGYLEQGLLV KEELKLINKY KSNLQFKLDV LSLIPTDLLY FKLGWNYPEI RLNRLLRFSR MFEFFQRTET R TNYPNIFR ISNLVMYIVI IIHWNACVFY SISKAIGFGN DTWVYPDIND PEFGRLARKY VYSLYWSTLT LTTIGETPPP VR DSEYVFV VVDFLIGVLI FATIVGNIGS MISNMNAARA EFQARIDAIK QYMHFRNVSK DMEKRVIKWF DYLWTNKKTV DEK EVLKYL PDKLRAEIAI NVHLDTLKKV RIFADCEAGL LVELVLKLQP QVYSPGDYIC KKGDIGREMY IIKEGKLAVV ADDG VTQFV VLSDGSYFGE ISILNIKGSK AGNRRTANIK SIGYSDLFCL SKDDLMEALT EYPDAKTMLE EKGKQILMKD GLLDL NIAN AGSDPKDLEE KVTRMEGSVD LLQTRFARIL AEYESMQQKL KQRLTKVEKF LKPLIDTEFS SIEGPGAESG PIDST UniProtKB: Cyclic nucleotide-gated channel alpha-1 |
-分子 #2: CHOLESTEROL
| 分子 | 名称: CHOLESTEROL / タイプ: ligand / ID: 2 / コピー数: 4 / 式: CLR |
|---|---|
| 分子量 | 理論値: 386.654 Da |
| Chemical component information |  ChemComp-CLR: |
-分子 #3: 1,2-DIOLEOYL-SN-GLYCERO-3-PHOSPHOCHOLINE
| 分子 | 名称: 1,2-DIOLEOYL-SN-GLYCERO-3-PHOSPHOCHOLINE / タイプ: ligand / ID: 3 / コピー数: 28 / 式: PCW |
|---|---|
| 分子量 | 理論値: 787.121 Da |
| Chemical component information |  ChemComp-PCW: |
-分子 #4: [(2R)-2-octanoyloxy-3-[oxidanyl-[(1R,2R,3S,4R,5R,6S)-2,3,6-tris(o...
| 分子 | 名称: [(2R)-2-octanoyloxy-3-[oxidanyl-[(1R,2R,3S,4R,5R,6S)-2,3,6-tris(oxidanyl)-4,5-diphosphonooxy-cyclohexyl]oxy-phosphoryl]oxy-propyl] octanoate タイプ: ligand / ID: 4 / コピー数: 4 / 式: PIO |
|---|---|
| 分子量 | 理論値: 746.566 Da |
| Chemical component information | 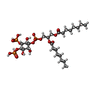 ChemComp-PIO: |
-分子 #5: POTASSIUM ION
| 分子 | 名称: POTASSIUM ION / タイプ: ligand / ID: 5 / コピー数: 5 / 式: K |
|---|---|
| 分子量 | 理論値: 39.098 Da |
-実験情報
-構造解析
| 手法 | クライオ電子顕微鏡法 |
|---|---|
 解析 解析 | 単粒子再構成法 |
| 試料の集合状態 | particle |
- 試料調製
試料調製
| 緩衝液 | pH: 7.4 構成要素:
詳細: 25 mM HEPES, 150 mM KCl, pH7.4 | |||||||||
|---|---|---|---|---|---|---|---|---|---|---|
| グリッド | モデル: Quantifoil R1.2/1.3 / 材質: GOLD | |||||||||
| 凍結 | 凍結剤: ETHANE / チャンバー内湿度: 100 % / チャンバー内温度: 295 K / 装置: FEI VITROBOT MARK IV |
- 電子顕微鏡法
電子顕微鏡法
| 顕微鏡 | TFS KRIOS |
|---|---|
| 撮影 | フィルム・検出器のモデル: GATAN K3 (6k x 4k) / 平均電子線量: 48.48 e/Å2 |
| 電子線 | 加速電圧: 300 kV / 電子線源:  FIELD EMISSION GUN FIELD EMISSION GUN |
| 電子光学系 | 照射モード: FLOOD BEAM / 撮影モード: BRIGHT FIELD / 最大 デフォーカス(公称値): 2.4 µm / 最小 デフォーカス(公称値): 0.6 µm |
| 実験機器 |  モデル: Titan Krios / 画像提供: FEI Company |
 ムービー
ムービー コントローラー
コントローラー
















 Z
Z Y
Y X
X

























