+ データを開く
データを開く
- 基本情報
基本情報
| 登録情報 |  | |||||||||
|---|---|---|---|---|---|---|---|---|---|---|
| タイトル | Poliovirus type 2 (strain MEF-1) stabilised virus-like particle (PV2 SC5a) from a yeast expression system. | |||||||||
 マップデータ マップデータ | ||||||||||
 試料 試料 |
| |||||||||
 キーワード キーワード | Capsid protein / virus-like particle / vaccine / VIRUS LIKE PARTICLE | |||||||||
| 機能・相同性 |  機能・相同性情報 機能・相同性情報symbiont-mediated suppression of host cytoplasmic pattern recognition receptor signaling pathway via inhibition of RIG-I activity / receptor-mediated endocytosis of virus by host cell / symbiont-mediated suppression of host cytoplasmic pattern recognition receptor signaling pathway via inhibition of MDA-5 activity / symbiont-mediated suppression of host cytoplasmic pattern recognition receptor signaling pathway via inhibition of MAVS activity / ribonucleoside triphosphate phosphatase activity / picornain 2A / symbiont-mediated suppression of host mRNA export from nucleus / symbiont genome entry into host cell via pore formation in plasma membrane / picornain 3C / T=pseudo3 icosahedral viral capsid ...symbiont-mediated suppression of host cytoplasmic pattern recognition receptor signaling pathway via inhibition of RIG-I activity / receptor-mediated endocytosis of virus by host cell / symbiont-mediated suppression of host cytoplasmic pattern recognition receptor signaling pathway via inhibition of MDA-5 activity / symbiont-mediated suppression of host cytoplasmic pattern recognition receptor signaling pathway via inhibition of MAVS activity / ribonucleoside triphosphate phosphatase activity / picornain 2A / symbiont-mediated suppression of host mRNA export from nucleus / symbiont genome entry into host cell via pore formation in plasma membrane / picornain 3C / T=pseudo3 icosahedral viral capsid / host cell cytoplasmic vesicle membrane / viral capsid / host cell / nucleoside-triphosphate phosphatase / channel activity / monoatomic ion transmembrane transport / host cell cytoplasm / DNA replication / RNA helicase activity / symbiont-mediated suppression of host gene expression / symbiont entry into host cell / symbiont-mediated activation of host autophagy / RNA-directed RNA polymerase / cysteine-type endopeptidase activity / viral RNA genome replication / RNA-directed RNA polymerase activity / DNA-templated transcription / virion attachment to host cell / host cell nucleus / structural molecule activity / proteolysis / RNA binding / zinc ion binding / ATP binding / membrane 類似検索 - 分子機能 | |||||||||
| 生物種 |  Poliovirus 2 (ポリオウイルス) Poliovirus 2 (ポリオウイルス) | |||||||||
| 手法 | 単粒子再構成法 / クライオ電子顕微鏡法 / 解像度: 2.1 Å | |||||||||
 データ登録者 データ登録者 | Bahar MW / Sherry L / Stonehouse NJ / Rowlands DJ / Fry EE / Stuart DI | |||||||||
| 資金援助 |  米国, 1件 米国, 1件
| |||||||||
 引用 引用 |  ジャーナル: NPJ Vaccines / 年: 2025 ジャーナル: NPJ Vaccines / 年: 2025タイトル: Production of an immunogenic trivalent poliovirus virus-like particle vaccine candidate in yeast using controlled fermentation. 著者: Lee Sherry / Keith Grehan / Mohammad W Bahar / Jessica J Swanson / Helen Fox / Sue Matthews / Sarah Carlyle / Ling Qin / Claudine Porta / Steven Wilkinson / Suzanne Robb / Naomi Clark / John ...著者: Lee Sherry / Keith Grehan / Mohammad W Bahar / Jessica J Swanson / Helen Fox / Sue Matthews / Sarah Carlyle / Ling Qin / Claudine Porta / Steven Wilkinson / Suzanne Robb / Naomi Clark / John Liddell / Elizabeth E Fry / David I Stuart / Andrew J Macadam / David J Rowlands / Nicola J Stonehouse /  要旨: The success of the poliovirus (PV) vaccines has enabled the near-eradication of wild PV, however, their continued use post-eradication poses concerns, due to the potential for virus escape during ...The success of the poliovirus (PV) vaccines has enabled the near-eradication of wild PV, however, their continued use post-eradication poses concerns, due to the potential for virus escape during vaccine manufacture. Recombinant virus-like particles (VLPs) that lack the viral genome remove this risk. Here, we demonstrate the production of PV VLPs for all three serotypes by controlled fermentation using Pichia pastoris. We determined the cryo-EM structure of a new PV2 mutant, termed SC5a, in comparison to PV2-SC6b VLPs described previously and investigated the immunogenicity of PV2-SC5a VLPs. Finally, a trivalent immunogenicity trial using bioreactor-derived VLPs of all three serotypes in the presence of Alhydrogel adjuvant, showed that these VLPs outperform the current IPV vaccine in the standard vaccine potency assay, offering the potential for dose-sparing. Overall, these results provide further evidence that yeast-produced VLPs have the potential to be a next-generation polio vaccine in a post-eradication world. | |||||||||
| 履歴 |
|
- 構造の表示
構造の表示
| 添付画像 |
|---|
- ダウンロードとリンク
ダウンロードとリンク
-EMDBアーカイブ
| マップデータ |  emd_51952.map.gz emd_51952.map.gz | 685 MB |  EMDBマップデータ形式 EMDBマップデータ形式 | |
|---|---|---|---|---|
| ヘッダ (付随情報) |  emd-51952-v30.xml emd-51952-v30.xml emd-51952.xml emd-51952.xml | 27.4 KB 27.4 KB | 表示 表示 |  EMDBヘッダ EMDBヘッダ |
| FSC (解像度算出) |  emd_51952_fsc.xml emd_51952_fsc.xml | 18.9 KB | 表示 |  FSCデータファイル FSCデータファイル |
| 画像 |  emd_51952.png emd_51952.png | 280.2 KB | ||
| Filedesc metadata |  emd-51952.cif.gz emd-51952.cif.gz | 8.3 KB | ||
| その他 |  emd_51952_half_map_1.map.gz emd_51952_half_map_1.map.gz emd_51952_half_map_2.map.gz emd_51952_half_map_2.map.gz | 673.5 MB 673.5 MB | ||
| アーカイブディレクトリ |  http://ftp.pdbj.org/pub/emdb/structures/EMD-51952 http://ftp.pdbj.org/pub/emdb/structures/EMD-51952 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-51952 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-51952 | HTTPS FTP |
-検証レポート
| 文書・要旨 |  emd_51952_validation.pdf.gz emd_51952_validation.pdf.gz | 1.1 MB | 表示 |  EMDB検証レポート EMDB検証レポート |
|---|---|---|---|---|
| 文書・詳細版 |  emd_51952_full_validation.pdf.gz emd_51952_full_validation.pdf.gz | 1.1 MB | 表示 | |
| XML形式データ |  emd_51952_validation.xml.gz emd_51952_validation.xml.gz | 28.8 KB | 表示 | |
| CIF形式データ |  emd_51952_validation.cif.gz emd_51952_validation.cif.gz | 38.1 KB | 表示 | |
| アーカイブディレクトリ |  https://ftp.pdbj.org/pub/emdb/validation_reports/EMD-51952 https://ftp.pdbj.org/pub/emdb/validation_reports/EMD-51952 ftp://ftp.pdbj.org/pub/emdb/validation_reports/EMD-51952 ftp://ftp.pdbj.org/pub/emdb/validation_reports/EMD-51952 | HTTPS FTP |
-関連構造データ
| 関連構造データ |  9h94MC  9h93C M: このマップから作成された原子モデル C: 同じ文献を引用 ( |
|---|---|
| 類似構造データ | 類似検索 - 機能・相同性  F&H 検索 F&H 検索 |
- リンク
リンク
| EMDBのページ |  EMDB (EBI/PDBe) / EMDB (EBI/PDBe) /  EMDataResource EMDataResource |
|---|---|
| 「今月の分子」の関連する項目 |
- マップ
マップ
| ファイル |  ダウンロード / ファイル: emd_51952.map.gz / 形式: CCP4 / 大きさ: 729 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) ダウンロード / ファイル: emd_51952.map.gz / 形式: CCP4 / 大きさ: 729 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) | ||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 投影像・断面図 | 画像のコントロール
画像は Spider により作成 | ||||||||||||||||||||||||||||||||||||
| ボクセルのサイズ | X=Y=Z: 0.83 Å | ||||||||||||||||||||||||||||||||||||
| 密度 |
| ||||||||||||||||||||||||||||||||||||
| 対称性 | 空間群: 1 | ||||||||||||||||||||||||||||||||||||
| 詳細 | EMDB XML:
|
-添付データ
-ハーフマップ: #2
| ファイル | emd_51952_half_map_1.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 投影像・断面図 |
| ||||||||||||
| 密度ヒストグラム |
-ハーフマップ: #1
| ファイル | emd_51952_half_map_2.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 投影像・断面図 |
| ||||||||||||
| 密度ヒストグラム |
- 試料の構成要素
試料の構成要素
-全体 : Poliovirus 2
| 全体 | 名称:  Poliovirus 2 (ポリオウイルス) Poliovirus 2 (ポリオウイルス) |
|---|---|
| 要素 |
|
-超分子 #1: Poliovirus 2
| 超分子 | 名称: Poliovirus 2 / タイプ: virus / ID: 1 / 親要素: 0 / 含まれる分子: #1-#3 詳細: Recombinantly expressed virus-like particle of poliovirus type 2 (MEF-1 strain). NCBI-ID: 12083 / 生物種: Poliovirus 2 / Sci species strain: MEF-1 / ウイルスタイプ: VIRUS-LIKE PARTICLE / ウイルス・単離状態: SEROTYPE / ウイルス・エンベロープ: No / ウイルス・中空状態: Yes |
|---|---|
| 宿主 | 生物種:  Homo sapiens (ヒト) Homo sapiens (ヒト) |
| 分子量 | 理論値: 5.81 MDa |
| ウイルス殻 | Shell ID: 1 / 名称: Virus shell 1 / 直径: 310.0 Å / T番号(三角分割数): 1 |
-分子 #1: Capsid protein VP1
| 分子 | 名称: Capsid protein VP1 / タイプ: protein_or_peptide / ID: 1 / コピー数: 1 / 光学異性体: LEVO |
|---|---|
| 由来(天然) | 生物種:  Poliovirus 2 (ポリオウイルス) / 株: MEF-1 Poliovirus 2 (ポリオウイルス) / 株: MEF-1 |
| 分子量 | 理論値: 33.073246 KDa |
| 組換発現 | 生物種:  Komagataella pastoris (菌類) Komagataella pastoris (菌類) |
| 配列 | 文字列: GLGDLIEGVV EGVTRNALTP LTPANNLPDT QSSGPAHSKE IPALTAVETG ATNPLVPSDT VQTRHVIQKR TRSESTVESF FARGACVAI IEVDNDAPTK RASKLFSVWK ITYKDTVQLR RKLEFFTYSR FDMELTFVVT SNYTDANNGH ALNQVYQIMF I PPGAPIPG ...文字列: GLGDLIEGVV EGVTRNALTP LTPANNLPDT QSSGPAHSKE IPALTAVETG ATNPLVPSDT VQTRHVIQKR TRSESTVESF FARGACVAI IEVDNDAPTK RASKLFSVWK ITYKDTVQLR RKLEFFTYSR FDMELTFVVT SNYTDANNGH ALNQVYQIMF I PPGAPIPG KWNDYTWQTS SNPSVFYTYG APPARISVPY VGIANAYSHF YDGFAKVPLA GQASTEGDSL YGAASLNDFG SL AVRVVND HNPTKLTSKI RVYMKPKHVR VWCPRPPRAV PYYGPGVDYK DGLAPLPEKG LTTY UniProtKB: Genome polyprotein |
-分子 #2: Capsid protein VP0
| 分子 | 名称: Capsid protein VP0 / タイプ: protein_or_peptide / ID: 2 / コピー数: 1 / 光学異性体: LEVO |
|---|---|
| 由来(天然) | 生物種:  Poliovirus 2 (ポリオウイルス) / 株: MEF-1 Poliovirus 2 (ポリオウイルス) / 株: MEF-1 |
| 分子量 | 理論値: 37.456855 KDa |
| 組換発現 | 生物種:  Komagataella pastoris (菌類) Komagataella pastoris (菌類) |
| 配列 | 文字列: MGAQVSSQKV GAHENSNRAY GGSTINYTTI NYYRDSASNA ASKQDFAQDP SKFTEPIKDV LIKTAPTLNS PNIEACGYSD RVMQLTLGN STITTQEAAN SVVAYGRWPE YIKDSEANPV DQPTEPDVAA CRFYTLDTVT WRKESRGWWW KLPDALKDMG L FGQNMFYH ...文字列: MGAQVSSQKV GAHENSNRAY GGSTINYTTI NYYRDSASNA ASKQDFAQDP SKFTEPIKDV LIKTAPTLNS PNIEACGYSD RVMQLTLGN STITTQEAAN SVVAYGRWPE YIKDSEANPV DQPTEPDVAA CRFYTLDTVT WRKESRGWWW KLPDALKDMG L FGQNMFYH YLGRAGYTVH VQCNASKFHQ GALGVFAVPE MCLAGDSTTH MFTKYENANP GEKGGEFKGS FTLDTNATNP AR NFCPVDY LFGSGVLAGN AFVYPHQIIN LRTNNCATLV LPYVNSLSID SMTKHNNWGI AILPLAPLDF ATESSTEIPI TLT IAPMCC EFNGLRNITV PRTQ UniProtKB: Genome polyprotein |
-分子 #3: Capsid protein VP3
| 分子 | 名称: Capsid protein VP3 / タイプ: protein_or_peptide / ID: 3 / コピー数: 1 / 光学異性体: LEVO |
|---|---|
| 由来(天然) | 生物種:  Poliovirus 2 (ポリオウイルス) / 株: MEF-1 Poliovirus 2 (ポリオウイルス) / 株: MEF-1 |
| 分子量 | 理論値: 26.49134 KDa |
| 組換発現 | 生物種:  Komagataella pastoris (菌類) Komagataella pastoris (菌類) |
| 配列 | 文字列: GLPVLNTPGS NQYLTADNYQ SPCAIPEFDV TPPIDIPGEV RNMMELAEID TMIPLNLTNQ RKNTMDMYRV ELNDAAHSDT PILCFSLSP ASDPRLAHTM LGEILNYYTH WAGSLKFTFL FCGSMMATGK LLVSYAPPGA EAPKSRKEAM LGTHVIWDIG L QSSCTMVV ...文字列: GLPVLNTPGS NQYLTADNYQ SPCAIPEFDV TPPIDIPGEV RNMMELAEID TMIPLNLTNQ RKNTMDMYRV ELNDAAHSDT PILCFSLSP ASDPRLAHTM LGEILNYYTH WAGSLKFTFL FCGSMMATGK LLVSYAPPGA EAPKSRKEAM LGTHVIWDIG L QSSCTMVV PWISNTTYRL TINDSFTEGG YISMFYQTRV VVPLSTPRKM DILGFVSACN DFSVRLLRDT THISQEAMPQ UniProtKB: Genome polyprotein |
-分子 #4: SPHINGOSINE
| 分子 | 名称: SPHINGOSINE / タイプ: ligand / ID: 4 / コピー数: 1 / 式: SPH |
|---|---|
| 分子量 | 理論値: 299.492 Da |
| Chemical component information | 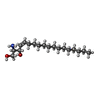 ChemComp-SPH: |
-分子 #5: water
| 分子 | 名称: water / タイプ: ligand / ID: 5 / コピー数: 194 / 式: HOH |
|---|---|
| 分子量 | 理論値: 18.015 Da |
| Chemical component information |  ChemComp-HOH: |
-実験情報
-構造解析
| 手法 | クライオ電子顕微鏡法 |
|---|---|
 解析 解析 | 単粒子再構成法 |
| 試料の集合状態 | particle |
- 試料調製
試料調製
| 濃度 | 0.6 mg/mL | ||||||
|---|---|---|---|---|---|---|---|
| 緩衝液 | pH: 7 / 構成要素:
| ||||||
| グリッド | モデル: Quantifoil R2/1 / 材質: COPPER / メッシュ: 200 / 支持フィルム - 材質: CARBON / 支持フィルム - トポロジー: CONTINUOUS / 支持フィルム - Film thickness: 2 / 前処理 - タイプ: GLOW DISCHARGE / 前処理 - 時間: 30 sec. / 前処理 - 雰囲気: AIR | ||||||
| 凍結 | 凍結剤: ETHANE-PROPANE / チャンバー内湿度: 100 % / チャンバー内温度: 277.15 K / 装置: FEI VITROBOT MARK IV 詳細: 3ul of sample double blotted for 3.5 seconds with -15 blot force on FEI Vitrobot mark IV.. | ||||||
| 詳細 | Sample purified by sucrose density gradient ultracentrifugation. |
- 電子顕微鏡法
電子顕微鏡法
| 顕微鏡 | TFS KRIOS |
|---|---|
| 特殊光学系 | エネルギーフィルター - 名称: GIF Bioquantum / エネルギーフィルター - スリット幅: 20 eV |
| 撮影 | フィルム・検出器のモデル: GATAN K3 BIOQUANTUM (6k x 4k) 撮影したグリッド数: 1 / 実像数: 1862 / 平均露光時間: 3.0 sec. / 平均電子線量: 47.5 e/Å2 詳細: Pixel sampling was 0.831 A/pixel. Super-resolution collection mode was used 0.415 A/pixel. Energy filter was Gatan GIF Quantum. |
| 電子線 | 加速電圧: 300 kV / 電子線源:  FIELD EMISSION GUN FIELD EMISSION GUN |
| 電子光学系 | C2レンズ絞り径: 100.0 µm / 照射モード: FLOOD BEAM / 撮影モード: DARK FIELD / Cs: 2.7 mm 最大 デフォーカス(公称値): 2.3000000000000003 µm 最小 デフォーカス(公称値): 0.5 µm / 倍率(公称値): 150000 |
| 試料ステージ | 試料ホルダーモデル: FEI TITAN KRIOS AUTOGRID HOLDER ホルダー冷却材: NITROGEN |
| 実験機器 |  モデル: Titan Krios / 画像提供: FEI Company |
+ 画像解析
画像解析
-原子モデル構築 1
| 初期モデル | PDB ID: Chain - Source name: PDB / Chain - Initial model type: experimental model |
|---|---|
| 詳細 | Initial model was rigid body fitted using UCSF chimera and Coot. Global minimization and B-factor refinement was performed in real space using phenix_real.space.refine. |
| 精密化 | 空間: REAL / プロトコル: RIGID BODY FIT 当てはまり具合の基準: Cross-correlation coefficient |
| 得られたモデル |  PDB-9h94: |
 ムービー
ムービー コントローラー
コントローラー







 Z (Sec.)
Z (Sec.) Y (Row.)
Y (Row.) X (Col.)
X (Col.)






































