+ データを開く
データを開く
- 基本情報
基本情報
| 登録情報 | データベース: EMDB / ID: EMD-4439 | |||||||||
|---|---|---|---|---|---|---|---|---|---|---|
| タイトル | Full MloK1 consensus map from single particle analysis of 2D crystals | |||||||||
 マップデータ マップデータ | Full MloK1 consensus map from single particle analysis of 2D crystals comprising 2x2 unit cells, sharpened. | |||||||||
 試料 試料 |
| |||||||||
| 生物種 |  Mesorhizobium loti MAFF303099 (根粒菌) Mesorhizobium loti MAFF303099 (根粒菌) | |||||||||
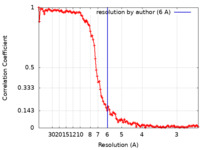
| 手法 | 単粒子再構成法 / クライオ電子顕微鏡法 / 解像度: 6.0 Å | |||||||||
 データ登録者 データ登録者 | Righetto R / Biyani N / Kowal J / Chami M / Stahlberg H | |||||||||
| 資金援助 |  スイス, 1件 スイス, 1件
| |||||||||
 引用 引用 |  ジャーナル: Nat Commun / 年: 2019 ジャーナル: Nat Commun / 年: 2019タイトル: Retrieving high-resolution information from disordered 2D crystals by single-particle cryo-EM. 著者: Ricardo D Righetto / Nikhil Biyani / Julia Kowal / Mohamed Chami / Henning Stahlberg /  要旨: Electron crystallography can reveal the structure of membrane proteins within 2D crystals under close-to-native conditions. High-resolution structural information can only be reached if crystals are ...Electron crystallography can reveal the structure of membrane proteins within 2D crystals under close-to-native conditions. High-resolution structural information can only be reached if crystals are perfectly flat and highly ordered. In practice, such crystals are difficult to obtain. Available image unbending algorithms correct for disorder, but only perform well on images of non-tilted, flat crystals, while out-of-plane distortions are not addressed. Here, we present an approach that employs single-particle refinement procedures to locally unbend crystals in 3D. With this method, density maps of the MloK1 potassium channel with a resolution of 4 Å were obtained from images of 2D crystals that do not diffract beyond 10 Å. Furthermore, 3D classification allowed multiple structures to be resolved, revealing a series of MloK1 conformations within a single 2D crystal. This conformational heterogeneity explains the poor diffraction observed and is related to channel function. The approach is implemented in the FOCUS package. | |||||||||
| 履歴 |
|
- 構造の表示
構造の表示
| ムービー |
 ムービービューア ムービービューア |
|---|---|
| 構造ビューア | EMマップ:  SurfView SurfView Molmil Molmil Jmol/JSmol Jmol/JSmol |
| 添付画像 |
- ダウンロードとリンク
ダウンロードとリンク
-EMDBアーカイブ
| マップデータ |  emd_4439.map.gz emd_4439.map.gz | 116.4 MB |  EMDBマップデータ形式 EMDBマップデータ形式 | |
|---|---|---|---|---|
| ヘッダ (付随情報) |  emd-4439-v30.xml emd-4439-v30.xml emd-4439.xml emd-4439.xml | 15.5 KB 15.5 KB | 表示 表示 |  EMDBヘッダ EMDBヘッダ |
| FSC (解像度算出) |  emd_4439_fsc.xml emd_4439_fsc.xml | 11.3 KB | 表示 |  FSCデータファイル FSCデータファイル |
| 画像 |  emd_4439.png emd_4439.png | 68.7 KB | ||
| その他 |  emd_4439_half_map_1.map.gz emd_4439_half_map_1.map.gz emd_4439_half_map_2.map.gz emd_4439_half_map_2.map.gz | 47.5 MB 47.5 MB | ||
| アーカイブディレクトリ |  http://ftp.pdbj.org/pub/emdb/structures/EMD-4439 http://ftp.pdbj.org/pub/emdb/structures/EMD-4439 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-4439 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-4439 | HTTPS FTP |
-検証レポート
| 文書・要旨 |  emd_4439_validation.pdf.gz emd_4439_validation.pdf.gz | 471.3 KB | 表示 |  EMDB検証レポート EMDB検証レポート |
|---|---|---|---|---|
| 文書・詳細版 |  emd_4439_full_validation.pdf.gz emd_4439_full_validation.pdf.gz | 470.4 KB | 表示 | |
| XML形式データ |  emd_4439_validation.xml.gz emd_4439_validation.xml.gz | 17 KB | 表示 | |
| アーカイブディレクトリ |  https://ftp.pdbj.org/pub/emdb/validation_reports/EMD-4439 https://ftp.pdbj.org/pub/emdb/validation_reports/EMD-4439 ftp://ftp.pdbj.org/pub/emdb/validation_reports/EMD-4439 ftp://ftp.pdbj.org/pub/emdb/validation_reports/EMD-4439 | HTTPS FTP |
-関連構造データ
| 関連構造データ |  4432C  4441C  4513C  4514C  4515C  4516C  4517C  4518C  4519C  6i9dC  6iaxC  6qcyC  6qczC  6qd0C  6qd1C  6qd2C  6qd3C  6qd4C C: 同じ文献を引用 ( |
|---|---|
| 類似構造データ |
- リンク
リンク
| EMDBのページ |  EMDB (EBI/PDBe) / EMDB (EBI/PDBe) /  EMDataResource EMDataResource |
|---|
- マップ
マップ
| ファイル |  ダウンロード / ファイル: emd_4439.map.gz / 形式: CCP4 / 大きさ: 125 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) ダウンロード / ファイル: emd_4439.map.gz / 形式: CCP4 / 大きさ: 125 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | Full MloK1 consensus map from single particle analysis of 2D crystals comprising 2x2 unit cells, sharpened. | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 投影像・断面図 | 画像のコントロール
画像は Spider により作成 | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| ボクセルのサイズ | X=Y=Z: 1.3 Å | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 密度 |
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 対称性 | 空間群: 1 | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 詳細 | EMDB XML:
CCP4マップ ヘッダ情報:
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
-添付データ
-ハーフマップ: #1
| ファイル | emd_4439_half_map_1.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 投影像・断面図 |
| ||||||||||||
| 密度ヒストグラム |
-ハーフマップ: #2
| ファイル | emd_4439_half_map_2.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 投影像・断面図 |
| ||||||||||||
| 密度ヒストグラム |
- 試料の構成要素
試料の構成要素
-全体 : MloK1 potassium channel in lipidic bilayer of 2D crystals
| 全体 | 名称: MloK1 potassium channel in lipidic bilayer of 2D crystals |
|---|---|
| 要素 |
|
-超分子 #1: MloK1 potassium channel in lipidic bilayer of 2D crystals
| 超分子 | 名称: MloK1 potassium channel in lipidic bilayer of 2D crystals タイプ: complex / ID: 1 / 親要素: 0 / 含まれる分子: #1 |
|---|---|
| 由来(天然) | 生物種:  Mesorhizobium loti MAFF303099 (根粒菌) Mesorhizobium loti MAFF303099 (根粒菌) |
| 組換発現 | 生物種:  |
| 分子量 | 実験値: 160 KDa |
-実験情報
-構造解析
| 手法 | クライオ電子顕微鏡法 |
|---|---|
 解析 解析 | 単粒子再構成法 |
| 試料の集合状態 | 2D array |
- 試料調製
試料調製
| 緩衝液 | pH: 7.6 詳細: 20 mM KCl, 20 mM Tris-HCl pH 7.6, 1 mM BaCl2, 1 mM EDTA, 0.2 mM cAMP |
|---|---|
| 凍結 | 凍結剤: ETHANE |
- 電子顕微鏡法
電子顕微鏡法
| 顕微鏡 | FEI TITAN KRIOS |
|---|---|
| 撮影 | フィルム・検出器のモデル: GATAN K2 SUMMIT (4k x 4k) 検出モード: COUNTING / 実像数: 270 / 平均露光時間: 16.0 sec. / 平均電子線量: 45.0 e/Å2 詳細: The dataset of 346 movies recorded and processed for Kowal et al. (2018) 2 was employed. As reported, the data were collected on an FEI Titan Krios TEM equipped with a Gatan K2 DED. Total ...詳細: The dataset of 346 movies recorded and processed for Kowal et al. (2018) 2 was employed. As reported, the data were collected on an FEI Titan Krios TEM equipped with a Gatan K2 DED. Total dose: 40 e-/A^2 distributed over 40 movie frames. Pixel size: 1.3 A on the sample level (counting mode). Nominal tilt range: -55 to +55 degrees. |
| 電子線 | 加速電圧: 300 kV / 電子線源:  FIELD EMISSION GUN FIELD EMISSION GUN |
| 電子光学系 | 照射モード: OTHER / 撮影モード: BRIGHT FIELD / Cs: 2.7 mm / 最大 デフォーカス(公称値): 4.3 µm / 最小 デフォーカス(公称値): 0.75 µm / 倍率(公称値): 50000 |
| 試料ステージ | 試料ホルダーモデル: FEI TITAN KRIOS AUTOGRID HOLDER ホルダー冷却材: NITROGEN |
| 実験機器 |  モデル: Titan Krios / 画像提供: FEI Company |
 ムービー
ムービー コントローラー
コントローラー








 Z (Sec.)
Z (Sec.) Y (Row.)
Y (Row.) X (Col.)
X (Col.)