+ データを開く
データを開く
- 基本情報
基本情報
| 登録情報 |  | |||||||||
|---|---|---|---|---|---|---|---|---|---|---|
| タイトル | Eastern equine encephalitis virus (PE-6) VLP in complex with VLDLR LA(1-3) (icosahedral) | |||||||||
 マップデータ マップデータ | EEEV PE-6 VLP in complex with VLDLR LA(1-3) icosahedral reconstruction | |||||||||
 試料 試料 |
| |||||||||
 キーワード キーワード | virus / receptor / VIRUS LIKE PARTICLE | |||||||||
| 生物種 |   Eastern equine encephalitis virus (東部ウマ脳炎ウイルス) Eastern equine encephalitis virus (東部ウマ脳炎ウイルス) | |||||||||
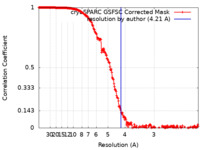
| 手法 | 単粒子再構成法 / クライオ電子顕微鏡法 / 解像度: 4.21 Å | |||||||||
 データ登録者 データ登録者 | Adams LJ / Fremont DH | |||||||||
| 資金援助 |  米国, 1件 米国, 1件
| |||||||||
 引用 引用 |  ジャーナル: Cell / 年: 2024 ジャーナル: Cell / 年: 2024タイトル: Structural and functional basis of VLDLR usage by Eastern equine encephalitis virus. 著者: Lucas J Adams / Saravanan Raju / Hongming Ma / Theron Gilliland / Douglas S Reed / William B Klimstra / Daved H Fremont / Michael S Diamond /  要旨: The very-low-density lipoprotein receptor (VLDLR) comprises eight LDLR type A (LA) domains and supports entry of distantly related alphaviruses, including Eastern equine encephalitis virus (EEEV) and ...The very-low-density lipoprotein receptor (VLDLR) comprises eight LDLR type A (LA) domains and supports entry of distantly related alphaviruses, including Eastern equine encephalitis virus (EEEV) and Semliki Forest virus (SFV). Here, by resolving multiple cryo-electron microscopy structures of EEEV-VLDLR complexes and performing mutagenesis and functional studies, we show that EEEV uses multiple sites (E1/E2 cleft and E2 A domain) to engage more than one LA domain simultaneously. However, no single LA domain is necessary or sufficient to support efficient EEEV infection. Whereas all EEEV strains show conservation of two VLDLR-binding sites, the EEEV PE-6 strain and a few other EEE complex members feature a single amino acid substitution that enables binding of LA domains to an additional site on the E2 B domain. These structural and functional analyses informed the design of a minimal VLDLR decoy receptor that neutralizes EEEV infection and protects mice from lethal challenge. | |||||||||
| 履歴 |
|
- 構造の表示
構造の表示
| 添付画像 |
|---|
- ダウンロードとリンク
ダウンロードとリンク
-EMDBアーカイブ
| マップデータ |  emd_42193.map.gz emd_42193.map.gz | 1.3 GB |  EMDBマップデータ形式 EMDBマップデータ形式 | |
|---|---|---|---|---|
| ヘッダ (付随情報) |  emd-42193-v30.xml emd-42193-v30.xml emd-42193.xml emd-42193.xml | 14.1 KB 14.1 KB | 表示 表示 |  EMDBヘッダ EMDBヘッダ |
| FSC (解像度算出) |  emd_42193_fsc.xml emd_42193_fsc.xml | 25.4 KB | 表示 |  FSCデータファイル FSCデータファイル |
| 画像 |  emd_42193.png emd_42193.png | 51.3 KB | ||
| Filedesc metadata |  emd-42193.cif.gz emd-42193.cif.gz | 3.9 KB | ||
| その他 |  emd_42193_additional_1.map.gz emd_42193_additional_1.map.gz emd_42193_half_map_1.map.gz emd_42193_half_map_1.map.gz emd_42193_half_map_2.map.gz emd_42193_half_map_2.map.gz | 702.1 MB 1.3 GB 1.3 GB | ||
| アーカイブディレクトリ |  http://ftp.pdbj.org/pub/emdb/structures/EMD-42193 http://ftp.pdbj.org/pub/emdb/structures/EMD-42193 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-42193 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-42193 | HTTPS FTP |
-検証レポート
| 文書・要旨 |  emd_42193_validation.pdf.gz emd_42193_validation.pdf.gz | 1.4 MB | 表示 |  EMDB検証レポート EMDB検証レポート |
|---|---|---|---|---|
| 文書・詳細版 |  emd_42193_full_validation.pdf.gz emd_42193_full_validation.pdf.gz | 1.4 MB | 表示 | |
| XML形式データ |  emd_42193_validation.xml.gz emd_42193_validation.xml.gz | 34.2 KB | 表示 | |
| CIF形式データ |  emd_42193_validation.cif.gz emd_42193_validation.cif.gz | 45.8 KB | 表示 | |
| アーカイブディレクトリ |  https://ftp.pdbj.org/pub/emdb/validation_reports/EMD-42193 https://ftp.pdbj.org/pub/emdb/validation_reports/EMD-42193 ftp://ftp.pdbj.org/pub/emdb/validation_reports/EMD-42193 ftp://ftp.pdbj.org/pub/emdb/validation_reports/EMD-42193 | HTTPS FTP |
-関連構造データ
- リンク
リンク
| EMDBのページ |  EMDB (EBI/PDBe) / EMDB (EBI/PDBe) /  EMDataResource EMDataResource |
|---|
- マップ
マップ
| ファイル |  ダウンロード / ファイル: emd_42193.map.gz / 形式: CCP4 / 大きさ: 1.4 GB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) ダウンロード / ファイル: emd_42193.map.gz / 形式: CCP4 / 大きさ: 1.4 GB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) | ||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | EEEV PE-6 VLP in complex with VLDLR LA(1-3) icosahedral reconstruction | ||||||||||||||||||||||||||||||||||||
| 投影像・断面図 | 画像のコントロール
画像は Spider により作成 | ||||||||||||||||||||||||||||||||||||
| ボクセルのサイズ | X=Y=Z: 1.081 Å | ||||||||||||||||||||||||||||||||||||
| 密度 |
| ||||||||||||||||||||||||||||||||||||
| 対称性 | 空間群: 1 | ||||||||||||||||||||||||||||||||||||
| 詳細 | EMDB XML:
|
-添付データ
-追加マップ: EEEV PE-6 VLP in complex with VLDLR LA(1-3)...
| ファイル | emd_42193_additional_1.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | EEEV PE-6 VLP in complex with VLDLR LA(1-3) icosahedral reconstruction (unsharpened map) | ||||||||||||
| 投影像・断面図 |
| ||||||||||||
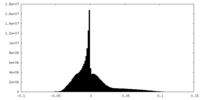
| 密度ヒストグラム |
-ハーフマップ: EEEV PE-6 VLP in complex with VLDLR LA(1-3)...
| ファイル | emd_42193_half_map_1.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | EEEV PE-6 VLP in complex with VLDLR LA(1-3) icosahedral reconstruction (half map A) | ||||||||||||
| 投影像・断面図 |
| ||||||||||||
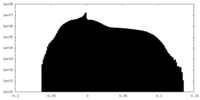
| 密度ヒストグラム |
-ハーフマップ: EEEV PE-6 VLP in complex with VLDLR LA(1-3)...
| ファイル | emd_42193_half_map_2.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | EEEV PE-6 VLP in complex with VLDLR LA(1-3) icosahedral reconstruction (half map B) | ||||||||||||
| 投影像・断面図 |
| ||||||||||||
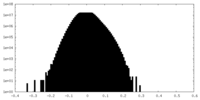
| 密度ヒストグラム |
- 試料の構成要素
試料の構成要素
-全体 : Eastern equine encephalitis virus
| 全体 | 名称:   Eastern equine encephalitis virus (東部ウマ脳炎ウイルス) Eastern equine encephalitis virus (東部ウマ脳炎ウイルス) |
|---|---|
| 要素 |
|
-超分子 #1: Eastern equine encephalitis virus
| 超分子 | 名称: Eastern equine encephalitis virus / タイプ: virus / ID: 1 / 親要素: 0 / NCBI-ID: 11021 / 生物種: Eastern equine encephalitis virus / Sci species strain: PE-6 / ウイルスタイプ: VIRUS-LIKE PARTICLE / ウイルス・単離状態: STRAIN / ウイルス・エンベロープ: Yes / ウイルス・中空状態: Yes |
|---|
-実験情報
-構造解析
| 手法 | クライオ電子顕微鏡法 |
|---|---|
 解析 解析 | 単粒子再構成法 |
| 試料の集合状態 | particle |
- 試料調製
試料調製
| 緩衝液 | pH: 7.4 |
|---|---|
| 凍結 | 凍結剤: ETHANE |
- 電子顕微鏡法
電子顕微鏡法
| 顕微鏡 | FEI TITAN KRIOS |
|---|---|
| 撮影 | フィルム・検出器のモデル: FEI FALCON IV (4k x 4k) 平均電子線量: 37.9 e/Å2 |
| 電子線 | 加速電圧: 300 kV / 電子線源:  FIELD EMISSION GUN FIELD EMISSION GUN |
| 電子光学系 | 照射モード: FLOOD BEAM / 撮影モード: BRIGHT FIELD / 最大 デフォーカス(公称値): 2.2 µm 最小 デフォーカス(公称値): 0.7000000000000001 µm |
| 実験機器 |  モデル: Titan Krios / 画像提供: FEI Company |
 ムービー
ムービー コントローラー
コントローラー























 Z (Sec.)
Z (Sec.) Y (Row.)
Y (Row.) X (Col.)
X (Col.)