[English] 日本語
 Yorodumi
Yorodumi- EMDB-40722: Cryo-EM structure of TRPM2 chanzyme in the presence of EDTA (apo ... -
+ Open data
Open data
- Basic information
Basic information
| Entry |  | |||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| Title | Cryo-EM structure of TRPM2 chanzyme in the presence of EDTA (apo state) | |||||||||||||||
 Map data Map data | Sharpened composite map. | |||||||||||||||
 Sample Sample |
| |||||||||||||||
 Keywords Keywords | TRPM2 Chanzyme / Channel-enzyme / TRANSPORT PROTEIN | |||||||||||||||
| Function / homology |  Function and homology information Function and homology information | |||||||||||||||
| Biological species |  Salpingoeca rosetta (eukaryote) Salpingoeca rosetta (eukaryote) | |||||||||||||||
| Method | single particle reconstruction / cryo EM / Resolution: 2.77 Å | |||||||||||||||
 Authors Authors | Huang Y / Kumar S / Lu W / Du J | |||||||||||||||
| Funding support |  United States, 4 items United States, 4 items
| |||||||||||||||
 Citation Citation |  Journal: Nat Struct Mol Biol / Year: 2024 Journal: Nat Struct Mol Biol / Year: 2024Title: Coupling enzymatic activity and gating in an ancient TRPM chanzyme and its molecular evolution. Authors: Yihe Huang / Sushant Kumar / Junuk Lee / Wei Lü / Juan Du /  Abstract: Channel enzymes represent a class of ion channels with enzymatic activity directly or indirectly linked to their channel function. We investigated a TRPM2 chanzyme from choanoflagellates that ...Channel enzymes represent a class of ion channels with enzymatic activity directly or indirectly linked to their channel function. We investigated a TRPM2 chanzyme from choanoflagellates that integrates two seemingly incompatible functions into a single peptide: a channel module activated by ADP-ribose with high open probability and an enzyme module (NUDT9-H domain) consuming ADP-ribose at a remarkably slow rate. Using time-resolved cryogenic-electron microscopy, we captured a complete series of structural snapshots of gating and catalytic cycles, revealing the coupling mechanism between channel gating and enzymatic activity. The slow kinetics of the NUDT9-H enzyme module confers a self-regulatory mechanism: ADPR binding triggers NUDT9-H tetramerization, promoting channel opening, while subsequent hydrolysis reduces local ADPR, inducing channel closure. We further demonstrated how the NUDT9-H domain has evolved from a structurally semi-independent ADP-ribose hydrolase module in early species to a fully integrated component of a gating ring essential for channel activation in advanced species. | |||||||||||||||
| History |
|
- Structure visualization
Structure visualization
| Supplemental images |
|---|
- Downloads & links
Downloads & links
-EMDB archive
| Map data |  emd_40722.map.gz emd_40722.map.gz | 16.6 MB |  EMDB map data format EMDB map data format | |
|---|---|---|---|---|
| Header (meta data) |  emd-40722-v30.xml emd-40722-v30.xml emd-40722.xml emd-40722.xml | 22.7 KB 22.7 KB | Display Display |  EMDB header EMDB header |
| Images |  emd_40722.png emd_40722.png | 142.5 KB | ||
| Filedesc metadata |  emd-40722.cif.gz emd-40722.cif.gz | 7.2 KB | ||
| Others |  emd_40722_additional_1.map.gz emd_40722_additional_1.map.gz emd_40722_additional_2.map.gz emd_40722_additional_2.map.gz emd_40722_additional_3.map.gz emd_40722_additional_3.map.gz | 114.8 MB 17 MB 112.6 MB | ||
| Archive directory |  http://ftp.pdbj.org/pub/emdb/structures/EMD-40722 http://ftp.pdbj.org/pub/emdb/structures/EMD-40722 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-40722 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-40722 | HTTPS FTP |
-Related structure data
| Related structure data |  8sr8MC  8sr7C  8sr9C  8sraC  8srbC  8srcC  8srdC  8sreC  8srfC  8srgC  8srhC  8sriC  8srjC  8srkC C: citing same article ( M: atomic model generated by this map |
|---|---|
| Similar structure data | Similarity search - Function & homology  F&H Search F&H Search |
- Links
Links
| EMDB pages |  EMDB (EBI/PDBe) / EMDB (EBI/PDBe) /  EMDataResource EMDataResource |
|---|---|
| Related items in Molecule of the Month |
- Map
Map
| File |  Download / File: emd_40722.map.gz / Format: CCP4 / Size: 149.9 MB / Type: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) Download / File: emd_40722.map.gz / Format: CCP4 / Size: 149.9 MB / Type: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) | ||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| Annotation | Sharpened composite map. | ||||||||||||||||||||||||||||||||||||
| Projections & slices | Image control
Images are generated by Spider. | ||||||||||||||||||||||||||||||||||||
| Voxel size | X=Y=Z: 1.048 Å | ||||||||||||||||||||||||||||||||||||
| Density |
| ||||||||||||||||||||||||||||||||||||
| Symmetry | Space group: 1 | ||||||||||||||||||||||||||||||||||||
| Details | EMDB XML:
|
-Supplemental data
-Additional map: Unsharpened composite map.
| File | emd_40722_additional_1.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| Annotation | Unsharpened composite map. | ||||||||||||
| Projections & Slices |
| ||||||||||||
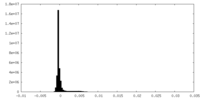
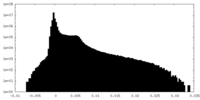
| Density Histograms |
-Additional map: Sharpened consensus map.
| File | emd_40722_additional_2.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| Annotation | Sharpened consensus map. | ||||||||||||
| Projections & Slices |
| ||||||||||||
| Density Histograms |
-Additional map: Unsharpened consensus map.
| File | emd_40722_additional_3.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| Annotation | Unsharpened consensus map. | ||||||||||||
| Projections & Slices |
| ||||||||||||
| Density Histograms |
- Sample components
Sample components
-Entire : TRPM2 chanzyme in the presence of EDTA (apo state)
| Entire | Name: TRPM2 chanzyme in the presence of EDTA (apo state) |
|---|---|
| Components |
|
-Supramolecule #1: TRPM2 chanzyme in the presence of EDTA (apo state)
| Supramolecule | Name: TRPM2 chanzyme in the presence of EDTA (apo state) / type: complex / ID: 1 / Parent: 0 / Macromolecule list: #1 |
|---|---|
| Source (natural) | Organism:  Salpingoeca rosetta (eukaryote) Salpingoeca rosetta (eukaryote) |
-Macromolecule #1: TRPM2 chanzyme
| Macromolecule | Name: TRPM2 chanzyme / type: protein_or_peptide / ID: 1 / Number of copies: 4 / Enantiomer: LEVO |
|---|---|
| Source (natural) | Organism:  Salpingoeca rosetta (eukaryote) Salpingoeca rosetta (eukaryote) |
| Molecular weight | Theoretical: 168.252484 KDa |
| Recombinant expression | Organism:  Homo sapiens (human) Homo sapiens (human) |
| Sequence | String: MQRARPGELV EVIMFRPTGK ARVSNLDESM AMEFTDLRTR AMSSAAMIRQ SVAAKTLLIE NEDGKGSTRM EVQDFMKRFH MHASEDDKT GSPSTAWGTL RFPTKEATAP YLRLSVNDDP EDALLFVKAM LAQKYGETYD RPSLILSVTG GARNFTLPPR L ETAIAKGL ...String: MQRARPGELV EVIMFRPTGK ARVSNLDESM AMEFTDLRTR AMSSAAMIRQ SVAAKTLLIE NEDGKGSTRM EVQDFMKRFH MHASEDDKT GSPSTAWGTL RFPTKEATAP YLRLSVNDDP EDALLFVKAM LAQKYGETYD RPSLILSVTG GARNFTLPPR L ETAIAKGL RLAAQRTNAW VVTGGTNTGV MKLTGQIMEA LSKTQSHFIP PTIGIATYGV IIGGDDMTRG EPPKIGLEYE MH KKDPPKT TPLDDNHNLF LLVDDGSTNK FGKEIKFRAA FENAAGQAFA APVVTIVVQG GPGTLGTALQ AVRQGTPIVV VDG SGLAAD VLAYAYNFMH NPLTRFKSYT IDDLRQKVAQ TFNPKSSQQL TNLLDSALEC VQDPNLVVVY SLQESGIDEF DDCI LKAIF SSQGKLGNKL KQAMYFDQLD VAKRALSEAS KNGQHNEIAA CINDNLMAAM MHNKPHFVEL YLGFDAKIYE LKPSE EVAK TNITALDELP SFALAIEELY KREAKKPHSH VQRLVSLSNT DVLGRHYRVS TQRGDGTTRR IGRDLANTRA YNVLRM DQI FARLVSKDFS VNRDFTIYDS KYDKVPGIQF RRTAQASHML FLWAICLDRF RMARHFWLIG DQSIINALVA SRILERL ST HRALQGPHLA EERAKMQHNA KKFEELAVGV LGECHGSDSH MASEMLHSKN DMFNKKNAIN IAYDAKSLAF LSHPATQS V INADWYGHLK SVTSFWAVLF AFFFPFFVLP FINFSEDHAE QQVEAPRDFF TDAPRSSHSA NSTTSGAHRL RRKFAKFYS APYTRFISDL LSHFVLCVVT SYFVLDKLED TISAIEWILL VWFVALLLEE LRQMIFCDGI AEYISDTWNR LDLIMITLFF VGFFTHASD PSNQDSKVVS KGIHAFLVVV LWLRFMRYYA LSKNLGPKLI MMMEMMKDVS TFVFLLLIFL IGYGVAAQSL L SPDEDFSS RTFIGVLFRP YFQIYGELFL DDLNSEANCL GDTPFTECSR ETVRMVPFFL AVYILGSNVL LVNLLIAMFN DT YMKVQEA AEDLWRKQNY ELCAEYKDRP FLPAPFILLA HVHMLFMRLL RLCGVHTQEH EKIQDDETKR KITTFEELNT DKF LRRWER ERQEMLEARV KMTNDNVVQA MGMMDQLLEH MISFRFSLDQ QATKIKQEIR DDGLPSTEPT GLVSRTPSQP INRL NSAVA VHGHTAEAAE WYVPPEEYPK SGGVKRYLID ASMVPLSIMC PSYDPVEYTH PSVAAQPVWA DPADPRKIKF NVKDE VNGK VVDRTSCHPS GISIDSNTGR PINPWGRTGM TGRGLLGKWG VNQAADTVVT RWKRSPDGSI LERDGKKVLE FVAIQR QDN KMWAIPGGFV DNGEDVALTS GREFMEEALG MGTSADLMSA ESKDSLAALF SSGTIVARIY CEDPRNTDNA WVETTCV NF HDESGRHAAR LKLQGGDDAE HARWMMVHGG LNLFASHRTL LQHVTSALNA YF UniProtKB: Nudt9 protein |
-Macromolecule #2: CHOLESTEROL
| Macromolecule | Name: CHOLESTEROL / type: ligand / ID: 2 / Number of copies: 12 / Formula: CLR |
|---|---|
| Molecular weight | Theoretical: 386.654 Da |
| Chemical component information |  ChemComp-CLR: |
-Experimental details
-Structure determination
| Method | cryo EM |
|---|---|
 Processing Processing | single particle reconstruction |
| Aggregation state | particle |
- Sample preparation
Sample preparation
| Concentration | 8.5 mg/mL |
|---|---|
| Buffer | pH: 8 |
| Vitrification | Cryogen name: ETHANE |
- Electron microscopy
Electron microscopy
| Microscope | FEI TITAN KRIOS |
|---|---|
| Image recording | Film or detector model: GATAN K2 SUMMIT (4k x 4k) / Average exposure time: 0.2 sec. / Average electron dose: 54.0 e/Å2 |
| Electron beam | Acceleration voltage: 300 kV / Electron source:  FIELD EMISSION GUN FIELD EMISSION GUN |
| Electron optics | Illumination mode: FLOOD BEAM / Imaging mode: BRIGHT FIELD / Nominal defocus max: 2.5 µm / Nominal defocus min: 1.0 µm |
| Experimental equipment |  Model: Titan Krios / Image courtesy: FEI Company |
+ Image processing
Image processing
-Atomic model buiding 1
| Refinement | Space: REAL / Protocol: AB INITIO MODEL |
|---|---|
| Output model |  PDB-8sr8: |
 Movie
Movie Controller
Controller







































 Z (Sec.)
Z (Sec.) Y (Row.)
Y (Row.) X (Col.)
X (Col.)