+ データを開く
データを開く
- 基本情報
基本情報
| 登録情報 |  | |||||||||
|---|---|---|---|---|---|---|---|---|---|---|
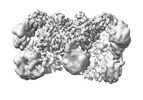
| タイトル | Composite map of the Hir complex with Asf1/H3/H4 | |||||||||
 マップデータ マップデータ | a composite map of the Hir with Asf1/H3/H4 | |||||||||
 試料 試料 |
| |||||||||
 キーワード キーワード | Histone / Complex / Replication-Independent / CHAPERONE | |||||||||
| 機能・相同性 |  機能・相同性情報 機能・相同性情報negative regulation of chromatin organization / HIR complex / negative regulation of transcription by RNA polymerase III / Formation of Senescence-Associated Heterochromatin Foci (SAHF) / sexual sporulation resulting in formation of a cellular spore / cupric reductase (NADH) activity / HATs acetylate histones / global genome nucleotide-excision repair / RNA polymerase I upstream activating factor complex / Condensation of Prophase Chromosomes ...negative regulation of chromatin organization / HIR complex / negative regulation of transcription by RNA polymerase III / Formation of Senescence-Associated Heterochromatin Foci (SAHF) / sexual sporulation resulting in formation of a cellular spore / cupric reductase (NADH) activity / HATs acetylate histones / global genome nucleotide-excision repair / RNA polymerase I upstream activating factor complex / Condensation of Prophase Chromosomes / SIRT1 negatively regulates rRNA expression / Activated PKN1 stimulates transcription of AR (androgen receptor) regulated genes KLK2 and KLK3 / Assembly of the ORC complex at the origin of replication / HDACs deacetylate histones / DNA replication-dependent chromatin assembly / Recruitment and ATM-mediated phosphorylation of repair and signaling proteins at DNA double strand breaks / Oxidative Stress Induced Senescence / RMTs methylate histone arginines / nucleosome disassembly / SUMOylation of chromatin organization proteins / transcription elongation-coupled chromatin remodeling / RNA Polymerase I Promoter Escape / positive regulation of transcription by RNA polymerase I / nucleolar large rRNA transcription by RNA polymerase I / Estrogen-dependent gene expression / rRNA transcription / chromosome, centromeric region / intracellular copper ion homeostasis / CENP-A containing nucleosome / aerobic respiration / transcription elongation by RNA polymerase II / G1/S transition of mitotic cell cycle / structural constituent of chromatin / transcription corepressor activity / nucleosome / nucleosome assembly / chromosome / chromatin organization / histone binding / chromatin remodeling / protein heterodimerization activity / regulation of transcription by RNA polymerase II / regulation of DNA-templated transcription / chromatin / negative regulation of transcription by RNA polymerase II / DNA binding / identical protein binding / nucleus / cytosol 類似検索 - 分子機能 | |||||||||
| 生物種 |  | |||||||||
| 手法 | 単粒子再構成法 / クライオ電子顕微鏡法 / 解像度: 2.96 Å | |||||||||
 データ登録者 データ登録者 | Kim HJ / Murakami K | |||||||||
| 資金援助 |  米国, 1件 米国, 1件
| |||||||||
 引用 引用 |  ジャーナル: Mol Cell / 年: 2024 ジャーナル: Mol Cell / 年: 2024タイトル: Structure of the Hir histone chaperone complex. 著者: Hee Jong Kim / Mary R Szurgot / Trevor van Eeuwen / M Daniel Ricketts / Pratik Basnet / Athena L Zhang / Austin Vogt / Samah Sharmin / Craig D Kaplan / Benjamin A Garcia / Ronen Marmorstein / Kenji Murakami /  要旨: The evolutionarily conserved HIRA/Hir histone chaperone complex and ASF1a/Asf1 co-chaperone cooperate to deposit histone (H3/H4) tetramers on DNA for replication-independent chromatin assembly. The ...The evolutionarily conserved HIRA/Hir histone chaperone complex and ASF1a/Asf1 co-chaperone cooperate to deposit histone (H3/H4) tetramers on DNA for replication-independent chromatin assembly. The molecular architecture of the HIRA/Hir complex and its mode of histone deposition have remained unknown. Here, we report the cryo-EM structure of the S. cerevisiae Hir complex with Asf1/H3/H4 at 2.9-6.8 Å resolution. We find that the Hir complex forms an arc-shaped dimer with a Hir1/Hir2/Hir3/Hpc2 stoichiometry of 2/4/2/4. The core of the complex containing two Hir1/Hir2/Hir2 trimers and N-terminal segments of Hir3 forms a central cavity containing two copies of Hpc2, with one engaged by Asf1/H3/H4, in a suitable position to accommodate a histone (H3/H4) tetramer, while the C-terminal segments of Hir3 harbor nucleic acid binding activity to wrap DNA around the Hpc2-assisted histone tetramer. The structure suggests a model for how the Hir/Asf1 complex promotes the formation of histone tetramers for their subsequent deposition onto DNA. | |||||||||
| 履歴 |
|
- 構造の表示
構造の表示
| 添付画像 |
|---|
- ダウンロードとリンク
ダウンロードとリンク
-EMDBアーカイブ
| マップデータ |  emd_40037.map.gz emd_40037.map.gz | 21.8 MB |  EMDBマップデータ形式 EMDBマップデータ形式 | |
|---|---|---|---|---|
| ヘッダ (付随情報) |  emd-40037-v30.xml emd-40037-v30.xml emd-40037.xml emd-40037.xml | 9.5 KB 9.5 KB | 表示 表示 |  EMDBヘッダ EMDBヘッダ |
| 画像 |  emd_40037.png emd_40037.png | 74.9 KB | ||
| Filedesc metadata |  emd-40037.cif.gz emd-40037.cif.gz | 3.9 KB | ||
| アーカイブディレクトリ |  http://ftp.pdbj.org/pub/emdb/structures/EMD-40037 http://ftp.pdbj.org/pub/emdb/structures/EMD-40037 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-40037 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-40037 | HTTPS FTP |
-検証レポート
| 文書・要旨 |  emd_40037_validation.pdf.gz emd_40037_validation.pdf.gz | 351.8 KB | 表示 |  EMDB検証レポート EMDB検証レポート |
|---|---|---|---|---|
| 文書・詳細版 |  emd_40037_full_validation.pdf.gz emd_40037_full_validation.pdf.gz | 351.4 KB | 表示 | |
| XML形式データ |  emd_40037_validation.xml.gz emd_40037_validation.xml.gz | 4.2 KB | 表示 | |
| CIF形式データ |  emd_40037_validation.cif.gz emd_40037_validation.cif.gz | 4.7 KB | 表示 | |
| アーカイブディレクトリ |  https://ftp.pdbj.org/pub/emdb/validation_reports/EMD-40037 https://ftp.pdbj.org/pub/emdb/validation_reports/EMD-40037 ftp://ftp.pdbj.org/pub/emdb/validation_reports/EMD-40037 ftp://ftp.pdbj.org/pub/emdb/validation_reports/EMD-40037 | HTTPS FTP |
-関連構造データ
- リンク
リンク
| EMDBのページ |  EMDB (EBI/PDBe) / EMDB (EBI/PDBe) /  EMDataResource EMDataResource |
|---|---|
| 「今月の分子」の関連する項目 |
- マップ
マップ
| ファイル |  ダウンロード / ファイル: emd_40037.map.gz / 形式: CCP4 / 大きさ: 512.5 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) ダウンロード / ファイル: emd_40037.map.gz / 形式: CCP4 / 大きさ: 512.5 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) | ||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | a composite map of the Hir with Asf1/H3/H4 | ||||||||||||||||||||||||||||||||||||
| 投影像・断面図 | 画像のコントロール
画像は Spider により作成 これらの図は立方格子座標系で作成されたものです | ||||||||||||||||||||||||||||||||||||
| ボクセルのサイズ | X=Y=Z: 1.36 Å | ||||||||||||||||||||||||||||||||||||
| 密度 |
| ||||||||||||||||||||||||||||||||||||
| 対称性 | 空間群: 1 | ||||||||||||||||||||||||||||||||||||
| 詳細 | EMDB XML:
|
-添付データ
- 試料の構成要素
試料の構成要素
-全体 : the yeast Hir complex with Asf1/H3/H4
| 全体 | 名称: the yeast Hir complex with Asf1/H3/H4 |
|---|---|
| 要素 |
|
-超分子 #1: the yeast Hir complex with Asf1/H3/H4
| 超分子 | 名称: the yeast Hir complex with Asf1/H3/H4 / タイプ: complex / ID: 1 / 親要素: 0 |
|---|---|
| 由来(天然) | 生物種:  |
| 分子量 | 理論値: 1.24 MDa |
-超分子 #2: the yeast Hir complex
| 超分子 | 名称: the yeast Hir complex / タイプ: complex / ID: 2 / 親要素: 1 |
|---|---|
| 由来(天然) | 生物種:  |
-超分子 #3: Asf1/H3/H4
| 超分子 | 名称: Asf1/H3/H4 / タイプ: complex / ID: 3 / 親要素: 1 |
|---|---|
| 由来(天然) | 生物種:  |
-実験情報
-構造解析
| 手法 | クライオ電子顕微鏡法 |
|---|---|
 解析 解析 | 単粒子再構成法 |
| 試料の集合状態 | particle |
- 試料調製
試料調製
| 緩衝液 | pH: 7.6 |
|---|---|
| 凍結 | 凍結剤: ETHANE |
- 電子顕微鏡法
電子顕微鏡法
| 顕微鏡 | FEI TITAN KRIOS |
|---|---|
| 撮影 | フィルム・検出器のモデル: GATAN K3 BIOQUANTUM (6k x 4k) 平均電子線量: 42.0 e/Å2 |
| 電子線 | 加速電圧: 300 kV / 電子線源:  FIELD EMISSION GUN FIELD EMISSION GUN |
| 電子光学系 | C2レンズ絞り径: 100.0 µm / 照射モード: FLOOD BEAM / 撮影モード: BRIGHT FIELD / Cs: 2.7 mm / 最大 デフォーカス(公称値): 3.0 µm / 最小 デフォーカス(公称値): 1.0 µm |
| 実験機器 |  モデル: Titan Krios / 画像提供: FEI Company |
- 画像解析
画像解析
| 初期モデル | モデルのタイプ: INSILICO MODEL |
|---|---|
| 最終 再構成 | 解像度のタイプ: BY AUTHOR / 解像度: 2.96 Å / 解像度の算出法: FSC 0.143 CUT-OFF / 使用した粒子像数: 639000 |
| 初期 角度割当 | タイプ: MAXIMUM LIKELIHOOD |
| 最終 角度割当 | タイプ: MAXIMUM LIKELIHOOD |
 ムービー
ムービー コントローラー
コントローラー



















 Z (Sec.)
Z (Sec.) Y (Row.)
Y (Row.) X (Col.)
X (Col.)




















