+ データを開く
データを開く
- 基本情報
基本情報
| 登録情報 |  | |||||||||
|---|---|---|---|---|---|---|---|---|---|---|
| タイトル | CryoEM structure of ADP-DNA-MuB conformation4 | |||||||||
 マップデータ マップデータ | CryoEM structure of ADP-DNA-MuB conformation4 | |||||||||
 試料 試料 |
| |||||||||
 キーワード キーワード | Cryo-EM / ADP-DNA-MuB conformation4 / Ring / VIRAL PROTEIN | |||||||||
| 生物種 |  Escherichia phage Mu (ファージ) Escherichia phage Mu (ファージ) | |||||||||
| 手法 | 単粒子再構成法 / クライオ電子顕微鏡法 / 解像度: 7.72 Å | |||||||||
 データ登録者 データ登録者 | Zhang X / Zhang K / Li S | |||||||||
| 資金援助 | 1件
| |||||||||
 引用 引用 |  ジャーナル: Nat Commun / 年: 2024 ジャーナル: Nat Commun / 年: 2024タイトル: Elucidating the Architectural dynamics of MuB filaments in bacteriophage Mu DNA transposition. 著者: Xiaolong Zhao / Yongxiang Gao / Qingguo Gong / Kaiming Zhang / Shanshan Li /  要旨: MuB is a non-specific DNA-binding protein and AAA+ ATPase that significantly influences the DNA transposition process of bacteriophage Mu, especially in target DNA selection for transposition. While ...MuB is a non-specific DNA-binding protein and AAA+ ATPase that significantly influences the DNA transposition process of bacteriophage Mu, especially in target DNA selection for transposition. While studies have established the ATP-dependent formation of MuB filament as pivotal to this process, the high-resolution structure of a full-length MuB protomer and the underlying molecular mechanisms governing its oligomerization remain elusive. Here, we use cryo-EM to obtain a 3.4-Å resolution structure of the ATP(+)-DNA(+)-MuB helical filament, which encapsulates the DNA substrate within its axial channel. The structure categorizes MuB within the initiator clade of the AAA+ protein family and precisely locates the ATP and DNA binding sites. Further investigation into the oligomeric states of MuB show the existence of various forms of the filament. These findings lead to a mechanistic model where MuB forms opposite helical filaments along the DNA, exposing potential target sites on the bare DNA and then recruiting MuA, which stimulates MuB's ATPase activity and disrupts the previously formed helical structure. When this happens, MuB generates larger ring structures and dissociates from the DNA. | |||||||||
| 履歴 |
|
- 構造の表示
構造の表示
| 添付画像 |
|---|
- ダウンロードとリンク
ダウンロードとリンク
-EMDBアーカイブ
| マップデータ |  emd_38699.map.gz emd_38699.map.gz | 103.2 MB |  EMDBマップデータ形式 EMDBマップデータ形式 | |
|---|---|---|---|---|
| ヘッダ (付随情報) |  emd-38699-v30.xml emd-38699-v30.xml emd-38699.xml emd-38699.xml | 14.1 KB 14.1 KB | 表示 表示 |  EMDBヘッダ EMDBヘッダ |
| 画像 |  emd_38699.png emd_38699.png | 39.7 KB | ||
| Filedesc metadata |  emd-38699.cif.gz emd-38699.cif.gz | 3.8 KB | ||
| その他 |  emd_38699_additional_1.map.gz emd_38699_additional_1.map.gz emd_38699_half_map_1.map.gz emd_38699_half_map_1.map.gz emd_38699_half_map_2.map.gz emd_38699_half_map_2.map.gz | 203 MB 200.5 MB 200.5 MB | ||
| アーカイブディレクトリ |  http://ftp.pdbj.org/pub/emdb/structures/EMD-38699 http://ftp.pdbj.org/pub/emdb/structures/EMD-38699 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-38699 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-38699 | HTTPS FTP |
-検証レポート
| 文書・要旨 |  emd_38699_validation.pdf.gz emd_38699_validation.pdf.gz | 775.2 KB | 表示 |  EMDB検証レポート EMDB検証レポート |
|---|---|---|---|---|
| 文書・詳細版 |  emd_38699_full_validation.pdf.gz emd_38699_full_validation.pdf.gz | 774.8 KB | 表示 | |
| XML形式データ |  emd_38699_validation.xml.gz emd_38699_validation.xml.gz | 15.7 KB | 表示 | |
| CIF形式データ |  emd_38699_validation.cif.gz emd_38699_validation.cif.gz | 18.6 KB | 表示 | |
| アーカイブディレクトリ |  https://ftp.pdbj.org/pub/emdb/validation_reports/EMD-38699 https://ftp.pdbj.org/pub/emdb/validation_reports/EMD-38699 ftp://ftp.pdbj.org/pub/emdb/validation_reports/EMD-38699 ftp://ftp.pdbj.org/pub/emdb/validation_reports/EMD-38699 | HTTPS FTP |
-関連構造データ
- リンク
リンク
| EMDBのページ |  EMDB (EBI/PDBe) / EMDB (EBI/PDBe) /  EMDataResource EMDataResource |
|---|
- マップ
マップ
| ファイル |  ダウンロード / ファイル: emd_38699.map.gz / 形式: CCP4 / 大きさ: 216 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) ダウンロード / ファイル: emd_38699.map.gz / 形式: CCP4 / 大きさ: 216 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) | ||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | CryoEM structure of ADP-DNA-MuB conformation4 | ||||||||||||||||||||||||||||||||||||
| 投影像・断面図 | 画像のコントロール
画像は Spider により作成 | ||||||||||||||||||||||||||||||||||||
| ボクセルのサイズ | X=Y=Z: 0.82 Å | ||||||||||||||||||||||||||||||||||||
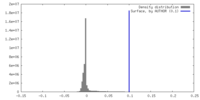
| 密度 |
| ||||||||||||||||||||||||||||||||||||
| 対称性 | 空間群: 1 | ||||||||||||||||||||||||||||||||||||
| 詳細 | EMDB XML:
|
-添付データ
-追加マップ: CryoEM structure of ADP-DNA-MuB conformation4
| ファイル | emd_38699_additional_1.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | CryoEM structure of ADP-DNA-MuB conformation4 | ||||||||||||
| 投影像・断面図 |
| ||||||||||||
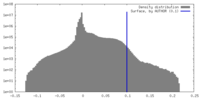
| 密度ヒストグラム |
-ハーフマップ: CryoEM structure of ADP-DNA-MuB conformation4
| ファイル | emd_38699_half_map_1.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | CryoEM structure of ADP-DNA-MuB conformation4 | ||||||||||||
| 投影像・断面図 |
| ||||||||||||
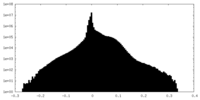
| 密度ヒストグラム |
-ハーフマップ: CryoEM structure of ADP-DNA-MuB conformation4
| ファイル | emd_38699_half_map_2.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | CryoEM structure of ADP-DNA-MuB conformation4 | ||||||||||||
| 投影像・断面図 |
| ||||||||||||
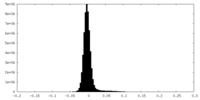
| 密度ヒストグラム |
- 試料の構成要素
試料の構成要素
-全体 : ADP-DNA-MuB conformation4 in Bacteriophage Mu DNA Transposition
| 全体 | 名称: ADP-DNA-MuB conformation4 in Bacteriophage Mu DNA Transposition |
|---|---|
| 要素 |
|
-超分子 #1: ADP-DNA-MuB conformation4 in Bacteriophage Mu DNA Transposition
| 超分子 | 名称: ADP-DNA-MuB conformation4 in Bacteriophage Mu DNA Transposition タイプ: complex / ID: 1 / 親要素: 0 / 含まれる分子: #1 |
|---|---|
| 由来(天然) | 生物種:  Escherichia phage Mu (ファージ) Escherichia phage Mu (ファージ) |
-実験情報
-構造解析
| 手法 | クライオ電子顕微鏡法 |
|---|---|
 解析 解析 | 単粒子再構成法 |
| 試料の集合状態 | particle |
- 試料調製
試料調製
| 緩衝液 | pH: 7.8 |
|---|---|
| 凍結 | 凍結剤: ETHANE |
- 電子顕微鏡法
電子顕微鏡法
| 顕微鏡 | FEI TITAN KRIOS |
|---|---|
| 撮影 | フィルム・検出器のモデル: GATAN K3 (6k x 4k) / 実像数: 9510 / 平均電子線量: 60.9 e/Å2 |
| 電子線 | 加速電圧: 300 kV / 電子線源:  FIELD EMISSION GUN FIELD EMISSION GUN |
| 電子光学系 | 照射モード: FLOOD BEAM / 撮影モード: BRIGHT FIELD / 最大 デフォーカス(公称値): 3.0 µm / 最小 デフォーカス(公称値): 2.0 µm |
| 実験機器 |  モデル: Titan Krios / 画像提供: FEI Company |
- 画像解析
画像解析
| 初期モデル | モデルのタイプ: NONE |
|---|---|
| 最終 再構成 | 想定した対称性 - 点群: C1 (非対称) / 解像度のタイプ: BY AUTHOR / 解像度: 7.72 Å / 解像度の算出法: FSC 0.143 CUT-OFF / 使用した粒子像数: 75913 |
| 初期 角度割当 | タイプ: MAXIMUM LIKELIHOOD |
| 最終 角度割当 | タイプ: MAXIMUM LIKELIHOOD |
 ムービー
ムービー コントローラー
コントローラー











 Z (Sec.)
Z (Sec.) Y (Row.)
Y (Row.) X (Col.)
X (Col.)