+ データを開く
データを開く
- 基本情報
基本情報
| 登録情報 |  | |||||||||
|---|---|---|---|---|---|---|---|---|---|---|
| タイトル | Conventional Reconstruction of the MC-45 de novo processed ribosome 50S | |||||||||
 マップデータ マップデータ | ||||||||||
 試料 試料 |
| |||||||||
 キーワード キーワード | ribosome 50S / RIBOSOME | |||||||||
| 生物種 |  | |||||||||
| 手法 | 単粒子再構成法 / 解像度: 3.16 Å | |||||||||
 データ登録者 データ登録者 | Zhang XZ / Zhu DJ / Cao WL | |||||||||
| 資金援助 |  中国, 1件 中国, 1件
| |||||||||
 引用 引用 |  ジャーナル: Sci Adv / 年: 2024 ジャーナル: Sci Adv / 年: 2024タイトル: Correction of preferred orientation-induced distortion in cryo-electron microscopy maps. 著者: Dongjie Zhu / Weili Cao / Junxi Li / Chunling Wu / Duanfang Cao / Xinzheng Zhang /  要旨: Reconstruction maps of cryo-electron microscopy (cryo-EM) exhibit distortion when the cryo-EM dataset is incomplete, usually caused by unevenly distributed orientations. Prior efforts had been ...Reconstruction maps of cryo-electron microscopy (cryo-EM) exhibit distortion when the cryo-EM dataset is incomplete, usually caused by unevenly distributed orientations. Prior efforts had been attempted to address this preferred orientation problem using tilt-collection strategy and modifications to grids or to air-water interfaces. However, these approaches often require time-consuming experiments, and the effect was always protein dependent. Here, we developed a procedure containing removing misaligned particles and an iterative reconstruction method based on signal-to-noise ratio of Fourier component to correct this distortion by recovering missing data using a purely computational algorithm. This procedure called signal-to-noise ratio iterative reconstruction method (SIRM) was applied on incomplete datasets of various proteins to fix distortion in cryo-EM maps and to a more isotropic resolution. In addition, SIRM provides a better reference map for further reconstruction refinements, resulting in an improved alignment, which ultimately improves map quality and benefits model building. | |||||||||
| 履歴 |
|
- 構造の表示
構造の表示
| 添付画像 |
|---|
- ダウンロードとリンク
ダウンロードとリンク
-EMDBアーカイブ
| マップデータ |  emd_38081.map.gz emd_38081.map.gz | 204.3 MB |  EMDBマップデータ形式 EMDBマップデータ形式 | |
|---|---|---|---|---|
| ヘッダ (付随情報) |  emd-38081-v30.xml emd-38081-v30.xml emd-38081.xml emd-38081.xml | 12.3 KB 12.3 KB | 表示 表示 |  EMDBヘッダ EMDBヘッダ |
| 画像 |  emd_38081.png emd_38081.png | 75.7 KB | ||
| マスクデータ |  emd_38081_msk_1.map emd_38081_msk_1.map | 216 MB |  マスクマップ マスクマップ | |
| Filedesc metadata |  emd-38081.cif.gz emd-38081.cif.gz | 3.8 KB | ||
| その他 |  emd_38081_half_map_1.map.gz emd_38081_half_map_1.map.gz emd_38081_half_map_2.map.gz emd_38081_half_map_2.map.gz | 200.7 MB 200.7 MB | ||
| アーカイブディレクトリ |  http://ftp.pdbj.org/pub/emdb/structures/EMD-38081 http://ftp.pdbj.org/pub/emdb/structures/EMD-38081 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-38081 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-38081 | HTTPS FTP |
-検証レポート
| 文書・要旨 |  emd_38081_validation.pdf.gz emd_38081_validation.pdf.gz | 1.3 MB | 表示 |  EMDB検証レポート EMDB検証レポート |
|---|---|---|---|---|
| 文書・詳細版 |  emd_38081_full_validation.pdf.gz emd_38081_full_validation.pdf.gz | 1.3 MB | 表示 | |
| XML形式データ |  emd_38081_validation.xml.gz emd_38081_validation.xml.gz | 15.8 KB | 表示 | |
| CIF形式データ |  emd_38081_validation.cif.gz emd_38081_validation.cif.gz | 18.6 KB | 表示 | |
| アーカイブディレクトリ |  https://ftp.pdbj.org/pub/emdb/validation_reports/EMD-38081 https://ftp.pdbj.org/pub/emdb/validation_reports/EMD-38081 ftp://ftp.pdbj.org/pub/emdb/validation_reports/EMD-38081 ftp://ftp.pdbj.org/pub/emdb/validation_reports/EMD-38081 | HTTPS FTP |
-関連構造データ
- リンク
リンク
| EMDBのページ |  EMDB (EBI/PDBe) / EMDB (EBI/PDBe) /  EMDataResource EMDataResource |
|---|
- マップ
マップ
| ファイル |  ダウンロード / ファイル: emd_38081.map.gz / 形式: CCP4 / 大きさ: 216 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) ダウンロード / ファイル: emd_38081.map.gz / 形式: CCP4 / 大きさ: 216 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) | ||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 投影像・断面図 | 画像のコントロール
画像は Spider により作成 | ||||||||||||||||||||||||||||||||||||
| ボクセルのサイズ | X=Y=Z: 0.94666 Å | ||||||||||||||||||||||||||||||||||||
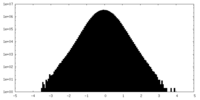
| 密度 |
| ||||||||||||||||||||||||||||||||||||
| 対称性 | 空間群: 1 | ||||||||||||||||||||||||||||||||||||
| 詳細 | EMDB XML:
|
-添付データ
-マスク #1
| ファイル |  emd_38081_msk_1.map emd_38081_msk_1.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 投影像・断面図 |
| ||||||||||||
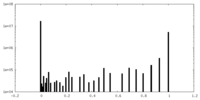
| 密度ヒストグラム |
-ハーフマップ: #2
| ファイル | emd_38081_half_map_1.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 投影像・断面図 |
| ||||||||||||
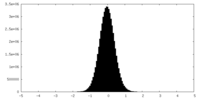
| 密度ヒストグラム |
-ハーフマップ: #1
| ファイル | emd_38081_half_map_2.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 投影像・断面図 |
| ||||||||||||
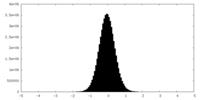
| 密度ヒストグラム |
- 試料の構成要素
試料の構成要素
-全体 : E. coli 70S ribosome, from EMPIAR-10509
| 全体 | 名称: E. coli 70S ribosome, from EMPIAR-10509 |
|---|---|
| 要素 |
|
-超分子 #1: E. coli 70S ribosome, from EMPIAR-10509
| 超分子 | 名称: E. coli 70S ribosome, from EMPIAR-10509 / タイプ: complex / ID: 1 / 親要素: 0 |
|---|---|
| 由来(天然) | 生物種:  |
-実験情報
-構造解析
 解析 解析 | 単粒子再構成法 |
|---|---|
| 試料の集合状態 | particle |
- 試料調製
試料調製
| 緩衝液 | pH: 7.5 |
|---|
- 電子顕微鏡法
電子顕微鏡法
| 顕微鏡 | FEI TITAN KRIOS |
|---|---|
| 撮影 | フィルム・検出器のモデル: GATAN K3 (6k x 4k) / 平均電子線量: 40.0 e/Å2 詳細: We used EMPIAR-10509. This repository was not recorded by us. |
| 電子線 | 加速電圧: 300 kV / 電子線源:  FIELD EMISSION GUN FIELD EMISSION GUN |
| 電子光学系 | 照射モード: FLOOD BEAM / 撮影モード: BRIGHT FIELD / 最大 デフォーカス(公称値): 1.5 µm / 最小 デフォーカス(公称値): 0.8 µm |
| 実験機器 |  モデル: Titan Krios / 画像提供: FEI Company |
- 画像解析
画像解析
| 初期モデル | モデルのタイプ: EMDB MAP EMDB ID: |
|---|---|
| 最終 再構成 | 想定した対称性 - 点群: C1 (非対称) / 解像度のタイプ: BY AUTHOR / 解像度: 3.16 Å / 解像度の算出法: FSC 0.143 CUT-OFF / ソフトウェア - 名称: cryoSPARC (ver. 3.3) / 使用した粒子像数: 38800 |
| 初期 角度割当 | タイプ: MAXIMUM LIKELIHOOD |
| 最終 角度割当 | タイプ: MAXIMUM LIKELIHOOD / ソフトウェア - 名称: cryoSPARC (ver. 3.3) |
 ムービー
ムービー コントローラー
コントローラー










 Z (Sec.)
Z (Sec.) Y (Row.)
Y (Row.) X (Col.)
X (Col.)