+ Open data
Open data
- Basic information
Basic information
| Entry |  | |||||||||
|---|---|---|---|---|---|---|---|---|---|---|
| Title | Cryo-EM structure of DSR2-DSAD1 | |||||||||
 Map data Map data | ||||||||||
 Sample Sample |
| |||||||||
 Keywords Keywords | cryo-EM structure of a protein / ANTIVIRAL PROTEIN | |||||||||
| Function / homology | symbiont-mediated suppression of host innate immune response / : / SPbeta prophage-derived DSR anti-defense 1 Function and homology information Function and homology information | |||||||||
| Biological species |  | |||||||||
| Method | single particle reconstruction / cryo EM / Resolution: 3.4 Å | |||||||||
 Authors Authors | Zhang H / Li Z / Li XZ | |||||||||
| Funding support | 1 items
| |||||||||
 Citation Citation |  Journal: Nat Commun / Year: 2024 Journal: Nat Commun / Year: 2024Title: Insights into the modulation of bacterial NADase activity by phage proteins. Authors: Hang Yin / Xuzichao Li / Xiaoshen Wang / Chendi Zhang / Jiaqi Gao / Guimei Yu / Qiuqiu He / Jie Yang / Xiang Liu / Yong Wei / Zhuang Li / Heng Zhang /  Abstract: The Silent Information Regulator 2 (SIR2) protein is widely implicated in antiviral response by depleting the cellular metabolite NAD. The defense-associated sirtuin 2 (DSR2) effector, a SIR2 domain- ...The Silent Information Regulator 2 (SIR2) protein is widely implicated in antiviral response by depleting the cellular metabolite NAD. The defense-associated sirtuin 2 (DSR2) effector, a SIR2 domain-containing protein, protects bacteria from phage infection by depleting NAD, while an anti-DSR2 protein (DSR anti-defense 1, DSAD1) is employed by some phages to evade this host defense. The NADase activity of DSR2 is unleashed by recognizing the phage tail tube protein (TTP). However, the activation and inhibition mechanisms of DSR2 are unclear. Here, we determine the cryo-EM structures of DSR2 in multiple states. DSR2 is arranged as a dimer of dimers, which is facilitated by the tetramerization of SIR2 domains. Moreover, the DSR2 assembly is essential for activating the NADase function. The activator TTP binding would trigger the opening of the catalytic pocket and the decoupling of the N-terminal SIR2 domain from the C-terminal domain (CTD) of DSR2. Importantly, we further show that the activation mechanism is conserved among other SIR2-dependent anti-phage systems. Interestingly, the inhibitor DSAD1 mimics TTP to trap DSR2, thus occupying the TTP-binding pocket and inhibiting the NADase function. Together, our results provide molecular insights into the regulatory mechanism of SIR2-dependent NAD depletion in antiviral immunity. | |||||||||
| History |
|
- Structure visualization
Structure visualization
| Supplemental images |
|---|
- Downloads & links
Downloads & links
-EMDB archive
| Map data |  emd_37603.map.gz emd_37603.map.gz | 72.2 MB |  EMDB map data format EMDB map data format | |
|---|---|---|---|---|
| Header (meta data) |  emd-37603-v30.xml emd-37603-v30.xml emd-37603.xml emd-37603.xml | 17.5 KB 17.5 KB | Display Display |  EMDB header EMDB header |
| FSC (resolution estimation) |  emd_37603_fsc.xml emd_37603_fsc.xml | 10.7 KB | Display |  FSC data file FSC data file |
| Images |  emd_37603.png emd_37603.png | 100 KB | ||
| Filedesc metadata |  emd-37603.cif.gz emd-37603.cif.gz | 6.5 KB | ||
| Others |  emd_37603_half_map_1.map.gz emd_37603_half_map_1.map.gz emd_37603_half_map_2.map.gz emd_37603_half_map_2.map.gz | 80.8 MB 80.8 MB | ||
| Archive directory |  http://ftp.pdbj.org/pub/emdb/structures/EMD-37603 http://ftp.pdbj.org/pub/emdb/structures/EMD-37603 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-37603 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-37603 | HTTPS FTP |
-Related structure data
| Related structure data |  8wknMC  8k98C  8k9aC  8w56C  8xknC M: atomic model generated by this map C: citing same article ( |
|---|---|
| Similar structure data | Similarity search - Function & homology  F&H Search F&H Search |
- Links
Links
| EMDB pages |  EMDB (EBI/PDBe) / EMDB (EBI/PDBe) /  EMDataResource EMDataResource |
|---|
- Map
Map
| File |  Download / File: emd_37603.map.gz / Format: CCP4 / Size: 103 MB / Type: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) Download / File: emd_37603.map.gz / Format: CCP4 / Size: 103 MB / Type: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) | ||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| Projections & slices | Image control
Images are generated by Spider. | ||||||||||||||||||||||||||||||||||||
| Voxel size | X=Y=Z: 0.85 Å | ||||||||||||||||||||||||||||||||||||
| Density |
| ||||||||||||||||||||||||||||||||||||
| Symmetry | Space group: 1 | ||||||||||||||||||||||||||||||||||||
| Details | EMDB XML:
|
-Supplemental data
-Half map: #2
| File | emd_37603_half_map_1.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| Projections & Slices |
| ||||||||||||
| Density Histograms |
-Half map: #1
| File | emd_37603_half_map_2.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| Projections & Slices |
| ||||||||||||
| Density Histograms |
- Sample components
Sample components
-Entire : cryo-EM structure of a protein
| Entire | Name: cryo-EM structure of a protein |
|---|---|
| Components |
|
-Supramolecule #1: cryo-EM structure of a protein
| Supramolecule | Name: cryo-EM structure of a protein / type: complex / ID: 1 / Parent: 0 / Macromolecule list: #1 |
|---|---|
| Source (natural) | Organism:  |
-Macromolecule #1: SIR2-like domain-containing protein
| Macromolecule | Name: SIR2-like domain-containing protein / type: protein_or_peptide / ID: 1 / Number of copies: 4 / Enantiomer: LEVO |
|---|---|
| Source (natural) | Organism:  |
| Molecular weight | Theoretical: 118.635789 KDa |
| Recombinant expression | Organism:  |
| Sequence | String: MVKVDLESKR YGEKLKEVFL MLDNNVVECI KEITESSRNG KLVFFVGAGV STLSDYPQWW RLVDKYHEEL YGSPKKGNYS SDEYLRIPQ IFYNVKGEMA FDGILKDFFQ VDKPTNPIHD KILAMNPAHV ITTNYDNLID TACWKRGKYF SVISAEEDVA N ATSSRYLL ...String: MVKVDLESKR YGEKLKEVFL MLDNNVVECI KEITESSRNG KLVFFVGAGV STLSDYPQWW RLVDKYHEEL YGSPKKGNYS SDEYLRIPQ IFYNVKGEMA FDGILKDFFQ VDKPTNPIHD KILAMNPAHV ITTNYDNLID TACWKRGKYF SVISAEEDVA N ATSSRYLL KVHGDFRKGF KGENVVLKED DYLNYDQNYP LISNLMKTII ATHTIVFIGY GLGDYNINML LNWVRKLQKD SF HKPFFIR TDPSPIENET LIYYENKGLR IIDAASLIDS NEYDYLERYS AVMDLLIESQ ENKFITKDDE VIDYIYGKIS PLF ALQYIR KIDLKHVFEY DYHFEVNGTV VRHKNKGFGY MERFFELKES CDERSKLSKK QYERFNALFN FFEKNGVICM AKDA GTLNT SIEINSLAYH GKYDVMKKFI EEQSVSIEDD YKKAFFLACL GRWEESYDLY SNIILNSIDE SNGCVYYLSQ INRYR IYQS ITQAVTQFNG LGLLTFGRHY KPFTDEFLAR IEREMTNFNI DDLFNGMPFE FQKKYKILEF LSDNQFLYDD TVKLFE LTN KVRSEMSEGS YSFGMSSDIV VLLRLYDNLR FLYENCLWSV SFHEFHQYIR NSMSLLIEKA EYERTRDIDE LGFSFFG KK SGFFMEYYDF VNISRHFKID DIKNLERSCS IDKIRFGEQE KIEEYLVGIA EEITKQFSAN GMNVVFYTQF ISEAKAAL Y FAKYVKLSEE GLGKIVKALL FYFPERDLDI GKRYVWLERL TKCNELPKSI ISIIDDFLVL QAEKHIDQNY SEVSSNGLY SRDYGALIKH FEKNFISKRL SEITLCLTQD KQKQIDFLFK LLPLLSTNAK SHLLSFKSVE NINDLMNGIR IGLIDEFTPE HEELIIEYL ETRKVNYIVE KEKGIQTFSS NDYMSTFGIW YFLEEINNSK MEEFIGMDDQ YDFFVDPENF DYKKFIPSWL K NYNDKLLG KIAGNKHMKH HVIEVLKERV KNSNDKRYLE ILMNYFI UniProtKB: UNIPROTKB: A0A162TTM4 |
-Macromolecule #2: SPbeta prophage-derived uncharacterized protein YotI
| Macromolecule | Name: SPbeta prophage-derived uncharacterized protein YotI / type: protein_or_peptide / ID: 2 / Number of copies: 1 / Enantiomer: LEVO |
|---|---|
| Source (natural) | Organism:  |
| Molecular weight | Theoretical: 13.87293 KDa |
| Recombinant expression | Organism:  |
| Sequence | String: MIEIFKDTGA THDLVYHSKI NTFVWDVEFD IVLSDSKELN KCYFVKCFNP YRINGKCDFA VSSIDIFSEG KRLLIENEFN FKITKAVHV ATSKDVTEIV LHLSERISSP FPIVKEVVYL D UniProtKB: SPbeta prophage-derived DSR anti-defense 1 |
-Experimental details
-Structure determination
| Method | cryo EM |
|---|---|
 Processing Processing | single particle reconstruction |
| Aggregation state | particle |
- Sample preparation
Sample preparation
| Buffer | pH: 7.5 |
|---|---|
| Vitrification | Cryogen name: ETHANE |
- Electron microscopy
Electron microscopy
| Microscope | FEI TITAN KRIOS |
|---|---|
| Image recording | Film or detector model: GATAN K3 (6k x 4k) / Average electron dose: 40.0 e/Å2 |
| Electron beam | Acceleration voltage: 300 kV / Electron source:  FIELD EMISSION GUN FIELD EMISSION GUN |
| Electron optics | Illumination mode: FLOOD BEAM / Imaging mode: BRIGHT FIELD / Nominal defocus max: 2.5 µm / Nominal defocus min: 0.5 µm |
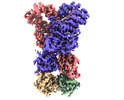
| Experimental equipment |  Model: Titan Krios / Image courtesy: FEI Company |
 Movie
Movie Controller
Controller







 X (Sec.)
X (Sec.) Y (Row.)
Y (Row.) Z (Col.)
Z (Col.)