+ データを開く
データを開く
- 基本情報
基本情報
| 登録情報 |  | |||||||||
|---|---|---|---|---|---|---|---|---|---|---|
| タイトル | Cryo-EM structure of mGlu2-mGlu3 heterodimer in presence of LY341495 (dimerization mode II) | |||||||||
 マップデータ マップデータ | ||||||||||
 試料 試料 |
| |||||||||
 キーワード キーワード | Complex structure / mGlu2-3 heterodimer / MEMBRANE PROTEIN | |||||||||
| 機能・相同性 |  機能・相同性情報 機能・相同性情報regulation of cellular component organization / regulation of response to drug / group II metabotropic glutamate receptor activity / regulation of cellular response to stress / macrolide binding / activin receptor binding / TORC1 complex / regulation of skeletal muscle contraction by regulation of release of sequestered calcium ion / cytoplasmic side of membrane / transforming growth factor beta receptor binding ...regulation of cellular component organization / regulation of response to drug / group II metabotropic glutamate receptor activity / regulation of cellular response to stress / macrolide binding / activin receptor binding / TORC1 complex / regulation of skeletal muscle contraction by regulation of release of sequestered calcium ion / cytoplasmic side of membrane / transforming growth factor beta receptor binding / intracellular glutamate homeostasis / TGFBR1 LBD Mutants in Cancer / behavioral response to nicotine / regulation of protein metabolic process / type I transforming growth factor beta receptor binding / negative regulation of adenylate cyclase activity / negative regulation of activin receptor signaling pathway / G protein-coupled glutamate receptor signaling pathway / astrocyte projection / heart trabecula formation / I-SMAD binding / Class C/3 (Metabotropic glutamate/pheromone receptors) / glutamate receptor activity / regulation of amyloid precursor protein catabolic process / terminal cisterna / ryanodine receptor complex / glutamate secretion / long-term synaptic depression / signaling receptor inhibitor activity / regulation of glutamate secretion / 'de novo' protein folding / ventricular cardiac muscle tissue morphogenesis / FK506 binding / cellular response to stress / regulation of dopamine secretion / TGF-beta receptor signaling activates SMADs / mTORC1-mediated signalling / regulation of ryanodine-sensitive calcium-release channel activity / Calcineurin activates NFAT / regulation of immune response / postsynaptic modulation of chemical synaptic transmission / heart morphogenesis / regulation of synaptic transmission, glutamatergic / supramolecular fiber organization / presynaptic modulation of chemical synaptic transmission / sarcoplasmic reticulum membrane / calcium channel regulator activity / negative regulation of autophagy / T cell activation / protein maturation / sarcoplasmic reticulum / TGF-beta receptor signaling in EMT (epithelial to mesenchymal transition) / peptidyl-prolyl cis-trans isomerase activity / peptidylprolyl isomerase / response to cocaine / negative regulation of transforming growth factor beta receptor signaling pathway / G protein-coupled receptor activity / Z disc / SARS-CoV-1 activates/modulates innate immune responses / protein folding / regulation of protein localization / presynaptic membrane / protein refolding / scaffold protein binding / G alpha (i) signalling events / chemical synaptic transmission / dendritic spine / amyloid fibril formation / Potential therapeutics for SARS / gene expression / transmembrane transporter binding / postsynaptic membrane / positive regulation of canonical NF-kappaB signal transduction / non-specific serine/threonine protein kinase / positive regulation of phosphatidylinositol 3-kinase/protein kinase B signal transduction / postsynaptic density / axon / protein serine/threonine kinase activity / dendrite / protein-containing complex binding / glutamatergic synapse / ATP binding / membrane / plasma membrane / cytosol / cytoplasm 類似検索 - 分子機能 | |||||||||
| 生物種 |  Homo sapiens (ヒト) Homo sapiens (ヒト) | |||||||||
| 手法 | 単粒子再構成法 / クライオ電子顕微鏡法 / 解像度: 3.4 Å | |||||||||
 データ登録者 データ登録者 | Wang X / Wang M / Xu T / Feng Y / Han S / Zhao Q / Wu B | |||||||||
| 資金援助 |  中国, 2件 中国, 2件
| |||||||||
 引用 引用 |  ジャーナル: Cell Res / 年: 2023 ジャーナル: Cell Res / 年: 2023タイトル: Structural insights into dimerization and activation of the mGlu2-mGlu3 and mGlu2-mGlu4 heterodimers. 著者: Xinwei Wang / Mu Wang / Tuo Xu / Ye Feng / Qiang Shao / Shuo Han / Xiaojing Chu / Yechun Xu / Shuling Lin / Qiang Zhao / Beili Wu /  要旨: Heterodimerization of the metabotropic glutamate receptors (mGlus) has shown importance in the functional modulation of the receptors and offers potential drug targets for treating central nervous ...Heterodimerization of the metabotropic glutamate receptors (mGlus) has shown importance in the functional modulation of the receptors and offers potential drug targets for treating central nervous system diseases. However, due to a lack of molecular details of the mGlu heterodimers, understanding of the mechanisms underlying mGlu heterodimerization and activation is limited. Here we report twelve cryo-electron microscopy (cryo-EM) structures of the mGlu2-mGlu3 and mGlu2-mGlu4 heterodimers in different conformational states, including inactive, intermediate inactive, intermediate active and fully active conformations. These structures provide a full picture of conformational rearrangement of mGlu2-mGlu3 upon activation. The Venus flytrap domains undergo a sequential conformational change, while the transmembrane domains exhibit a substantial rearrangement from an inactive, symmetric dimer with diverse dimerization patterns to an active, asymmetric dimer in a conserved dimerization mode. Combined with functional data, these structures reveal that stability of the inactive conformations of the subunits and the subunit-G protein interaction pattern are determinants of asymmetric signal transduction of the heterodimers. Furthermore, a novel binding site for two mGlu4 positive allosteric modulators was observed in the asymmetric dimer interfaces of the mGlu2-mGlu4 heterodimer and mGlu4 homodimer, and may serve as a drug recognition site. These findings greatly extend our knowledge about signal transduction of the mGlus. | |||||||||
| 履歴 |
|
- 構造の表示
構造の表示
| 添付画像 |
|---|
- ダウンロードとリンク
ダウンロードとリンク
-EMDBアーカイブ
| マップデータ |  emd_36166.map.gz emd_36166.map.gz | 168.3 MB |  EMDBマップデータ形式 EMDBマップデータ形式 | |
|---|---|---|---|---|
| ヘッダ (付随情報) |  emd-36166-v30.xml emd-36166-v30.xml emd-36166.xml emd-36166.xml | 17.6 KB 17.6 KB | 表示 表示 |  EMDBヘッダ EMDBヘッダ |
| FSC (解像度算出) |  emd_36166_fsc.xml emd_36166_fsc.xml | 2.3 MB | 表示 |  FSCデータファイル FSCデータファイル |
| 画像 |  emd_36166.png emd_36166.png | 61.4 KB | ||
| Filedesc metadata |  emd-36166.cif.gz emd-36166.cif.gz | 6.9 KB | ||
| その他 |  emd_36166_half_map_1.map.gz emd_36166_half_map_1.map.gz emd_36166_half_map_2.map.gz emd_36166_half_map_2.map.gz | 165.3 MB 165.3 MB | ||
| アーカイブディレクトリ |  http://ftp.pdbj.org/pub/emdb/structures/EMD-36166 http://ftp.pdbj.org/pub/emdb/structures/EMD-36166 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-36166 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-36166 | HTTPS FTP |
-検証レポート
| 文書・要旨 |  emd_36166_validation.pdf.gz emd_36166_validation.pdf.gz | 849.5 KB | 表示 |  EMDB検証レポート EMDB検証レポート |
|---|---|---|---|---|
| 文書・詳細版 |  emd_36166_full_validation.pdf.gz emd_36166_full_validation.pdf.gz | 849.1 KB | 表示 | |
| XML形式データ |  emd_36166_validation.xml.gz emd_36166_validation.xml.gz | 182.5 KB | 表示 | |
| CIF形式データ |  emd_36166_validation.cif.gz emd_36166_validation.cif.gz | 629.3 KB | 表示 | |
| アーカイブディレクトリ |  https://ftp.pdbj.org/pub/emdb/validation_reports/EMD-36166 https://ftp.pdbj.org/pub/emdb/validation_reports/EMD-36166 ftp://ftp.pdbj.org/pub/emdb/validation_reports/EMD-36166 ftp://ftp.pdbj.org/pub/emdb/validation_reports/EMD-36166 | HTTPS FTP |
-関連構造データ
| 関連構造データ |  8jcvMC  8jcuC  8jcwC  8jcxC  8jcyC  8jczC  8jd0C  8jd1C  8jd2C  8jd3C  8jd4C  8jd5C  8jd6C M: このマップから作成された原子モデル C: 同じ文献を引用 ( |
|---|---|
| 類似構造データ | 類似検索 - 機能・相同性  F&H 検索 F&H 検索 |
- リンク
リンク
| EMDBのページ |  EMDB (EBI/PDBe) / EMDB (EBI/PDBe) /  EMDataResource EMDataResource |
|---|---|
| 「今月の分子」の関連する項目 |
- マップ
マップ
| ファイル |  ダウンロード / ファイル: emd_36166.map.gz / 形式: CCP4 / 大きさ: 178 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) ダウンロード / ファイル: emd_36166.map.gz / 形式: CCP4 / 大きさ: 178 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) | ||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 投影像・断面図 | 画像のコントロール
画像は Spider により作成 | ||||||||||||||||||||||||||||||||||||
| ボクセルのサイズ | X=Y=Z: 1.071 Å | ||||||||||||||||||||||||||||||||||||
| 密度 |
| ||||||||||||||||||||||||||||||||||||
| 対称性 | 空間群: 1 | ||||||||||||||||||||||||||||||||||||
| 詳細 | EMDB XML:
|
-添付データ
-ハーフマップ: #2
| ファイル | emd_36166_half_map_1.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 投影像・断面図 |
| ||||||||||||
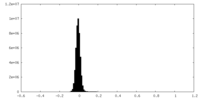
| 密度ヒストグラム |
-ハーフマップ: #1
| ファイル | emd_36166_half_map_2.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 投影像・断面図 |
| ||||||||||||
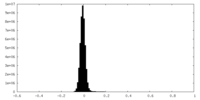
| 密度ヒストグラム |
- 試料の構成要素
試料の構成要素
-全体 : mGlu2-3 heterodimer in presence of LY341495
| 全体 | 名称: mGlu2-3 heterodimer in presence of LY341495 |
|---|---|
| 要素 |
|
-超分子 #1: mGlu2-3 heterodimer in presence of LY341495
| 超分子 | 名称: mGlu2-3 heterodimer in presence of LY341495 / タイプ: complex / ID: 1 / 親要素: 0 / 含まれる分子: #1-#2 |
|---|---|
| 由来(天然) | 生物種:  Homo sapiens (ヒト) Homo sapiens (ヒト) |
-分子 #1: Metabotropic glutamate receptor 2,Peptidyl-prolyl cis-trans isome...
| 分子 | 名称: Metabotropic glutamate receptor 2,Peptidyl-prolyl cis-trans isomerase FKBP1A タイプ: protein_or_peptide / ID: 1 詳細: Author stated 'all the data are processed in Cryosparc with default prameters, as all the other deposition. There should be no contamination.' コピー数: 1 / 光学異性体: LEVO / EC番号: peptidylprolyl isomerase |
|---|---|
| 由来(天然) | 生物種:  Homo sapiens (ヒト) Homo sapiens (ヒト) |
| 分子量 | 理論値: 109.340875 KDa |
| 組換発現 | 生物種:  |
| 配列 | 文字列: DYKDDDDGAP EGPAKKVLTL EGDLVLGGLF PVHQKGGPAE DCGPVNEHRG IQRLEAMLFA LDRINRDPHL LPGVRLGAHI LDSCSKDTH ALEQALDFVR ASLSRGADGS RHICPDGSYA THGDAPTAIT GVIGGSYSDV SIQVANLLRL FQIPQISYAS T SAKLSDKS ...文字列: DYKDDDDGAP EGPAKKVLTL EGDLVLGGLF PVHQKGGPAE DCGPVNEHRG IQRLEAMLFA LDRINRDPHL LPGVRLGAHI LDSCSKDTH ALEQALDFVR ASLSRGADGS RHICPDGSYA THGDAPTAIT GVIGGSYSDV SIQVANLLRL FQIPQISYAS T SAKLSDKS RYDYFARTVP PDFFQAKAMA EILRFFNWTY VSTVASEGDY GETGIEAFEL EARARNICVA TSEKVGRAMS RA AFEGVVR ALLQKPSARV AVLFTRSEDA RELLAASQRL NASFTWVASD GWGALESVVA GSEGAAEGAI TIELASYPIS DFA SYFQSL DPWNNSRNPW FREFWEQRFR CSFRQRDCAA HSLRAVPFEQ ESKIMFVVNA VYAMAHALHN MHRALCPNTT RLCD AMRPV NGRRLYKDFV LNVKFDAPFR PADTHNEVRF DRFGDGIGRY NIFTYLRAGS GRYRYQKVGY WAEGLTLDTS LIPWA SPSA GPLPASRCSE PCLQNEVKSV QPGEVCCWLC IPCQPYEYRL DEFTCADCGL GYWPNASLTG CFALPQEYIR WGDAWA VGP VTIACLGALA TLFVLGVFVR HNATPVVKAS GRELCYILLG GVFLCYCMTF IFIAKPSTAV CTLRRLGLGT AFSVCYS AL LTKTNRIARI FGGAREGAQR PRFISPASQV AICLALISGQ LLIVVAWLVV EAPGTGKETA PERREVVTLR CNHRDASM L GSLAYNVLLI ALCTLYAFKT RKCPENFNEA KFIGFTMYTT CIIWLAFLPI FYVTSSDYRV QTTTMCVSVS LSGSVVLGC LFAPKLHIIL FQPQKNVVSH RAPTSRFGSA AARASSSLGQ GSGSQFVPTV CNGREVVDST TSSLLEVLFQ GPGVQVETIS PGDGRTFPK RGQTCVVHYT GMLEDGKKFD SSRDRNKPFK FMLGKQEVIR GWEEGVAQMS VGQRAKLTIS PDYAYGATGH P GIIPPHAT LVFDVELLKL EFAAAHHHHH HHHHH UniProtKB: Metabotropic glutamate receptor 2, Peptidyl-prolyl cis-trans isomerase FKBP1A |
-分子 #2: Metabotropic glutamate receptor 3,Serine/threonine-protein kinase mTOR
| 分子 | 名称: Metabotropic glutamate receptor 3,Serine/threonine-protein kinase mTOR タイプ: protein_or_peptide / ID: 2 / コピー数: 1 / 光学異性体: LEVO / EC番号: non-specific serine/threonine protein kinase |
|---|---|
| 由来(天然) | 生物種:  Homo sapiens (ヒト) Homo sapiens (ヒト) |
| 分子量 | 理論値: 112.712961 KDa |
| 組換発現 | 生物種:  |
| 配列 | 文字列: DYKDDDDKGA PWSHPQFEKG SGSWSHPQFE KLGDHNFLRR EIKIEGDLVL GGLFPINEKG TGTEECGRIN EDRGIQRLEA MLFAIDEIN KDDYLLPGVK LGVHILDTCS RDTYALEQSL EFVRASLTKV DEAEYMCPDG SYAIQENIPL LIAGVIGGSY S SVSIQVAN ...文字列: DYKDDDDKGA PWSHPQFEKG SGSWSHPQFE KLGDHNFLRR EIKIEGDLVL GGLFPINEKG TGTEECGRIN EDRGIQRLEA MLFAIDEIN KDDYLLPGVK LGVHILDTCS RDTYALEQSL EFVRASLTKV DEAEYMCPDG SYAIQENIPL LIAGVIGGSY S SVSIQVAN LLRLFQIPQI SYASTSAKLS DKSRYDYFAR TVPPDFYQAK AMAEILRFFN WTYVSTVASE GDYGETGIEA FE QEARLRN ICIATAEKVG RSNIRKSYDS VIRELLQKPN ARVVVLFMRS DDSRELIAAA SRANASFTWV ASDGWGAQES IIK GSEHVA YGAITLELAS QPVRQFDRYF QSLNPYNNHR NPWFRDFWEQ KFQCSLQNKR NHRRVCDKHL AIDSSNYEQE SKIM FVVNA VYAMAHALHK MQRTLCPNTT KLCDAMKILD GKKLYKDYLL KINFTAPFNP NKDADSIVKF DTFGDGMGRY NVFNF QNVG GKYSYLKVGH WAETLSLDVN SIHWSRNSVP TSQCSDPCAP NEMKNMQPGD VCCWICIPCE PYEYLADEFT CMDCGS GQW PTADLTGCYD LPEDYIRWED AWAIGPVTIA CLGFMCTCMV VTVFIKHNNT PLVKASGREL CYILLFGVGL SYCMTFF FI AKPSPVICAL RRLGLGSSFA ICYSALLTKT NCIARIFDGV KNGAQRPKFI SPSSQVFICL GLILVQIVMV SVWLILEA P GTRRYTLAEK RETVILKCNV KDSSMLISLT YDVILVILCT VYAFKTRKCP ENFNEAKFIG FTMYTTCIIW LAFLPIFYV TSSDYRVQTT TMCISVSLSG FVVLGCLFAP KVHIILFQPQ KNVVTHRLHL NRFSVSGTGT TYSQSSASTY VPTVCNGREV LDSTTSSLL EVLFQGPAIL WHEMWHEGLE EASRLYFGER NVKGMFEVLE PLHAMMERGP QTLKETSFNQ AYGRDLMEAQ E WCRKYMKS GNVKDLTQAW DLYYHVFRRI SKQEF UniProtKB: Metabotropic glutamate receptor 3, Serine/threonine-protein kinase mTOR |
-分子 #3: 2-acetamido-2-deoxy-beta-D-glucopyranose
| 分子 | 名称: 2-acetamido-2-deoxy-beta-D-glucopyranose / タイプ: ligand / ID: 3 / コピー数: 2 / 式: NAG |
|---|---|
| 分子量 | 理論値: 221.208 Da |
| Chemical component information |  ChemComp-NAG: |
-分子 #4: 2-[(1S,2S)-2-carboxycyclopropyl]-3-(9H-xanthen-9-yl)-D-alanine
| 分子 | 名称: 2-[(1S,2S)-2-carboxycyclopropyl]-3-(9H-xanthen-9-yl)-D-alanine タイプ: ligand / ID: 4 / コピー数: 2 / 式: Z99 |
|---|---|
| 分子量 | 理論値: 353.369 Da |
| Chemical component information |  ChemComp-Z99: |
-実験情報
-構造解析
| 手法 | クライオ電子顕微鏡法 |
|---|---|
 解析 解析 | 単粒子再構成法 |
| 試料の集合状態 | particle |
- 試料調製
試料調製
| 緩衝液 | pH: 7.5 |
|---|---|
| 凍結 | 凍結剤: ETHANE |
- 電子顕微鏡法
電子顕微鏡法
| 顕微鏡 | FEI TITAN KRIOS |
|---|---|
| 撮影 | フィルム・検出器のモデル: GATAN K3 BIOQUANTUM (6k x 4k) 平均電子線量: 70.0 e/Å2 |
| 電子線 | 加速電圧: 300 kV / 電子線源:  FIELD EMISSION GUN FIELD EMISSION GUN |
| 電子光学系 | 照射モード: SPOT SCAN / 撮影モード: BRIGHT FIELD / 最大 デフォーカス(公称値): 1.5 µm / 最小 デフォーカス(公称値): 0.8 µm |
| 実験機器 |  モデル: Titan Krios / 画像提供: FEI Company |
 ムービー
ムービー コントローラー
コントローラー

































 Z (Sec.)
Z (Sec.) Y (Row.)
Y (Row.) X (Col.)
X (Col.)