+ データを開く
データを開く
- 基本情報
基本情報
| 登録情報 | データベース: EMDB / ID: EMD-30572 | |||||||||
|---|---|---|---|---|---|---|---|---|---|---|
| タイトル | Structure of COVID-19 RNA-dependent RNA polymerase bound to suramin | |||||||||
 マップデータ マップデータ | ||||||||||
 試料 試料 |
| |||||||||
 キーワード キーワード | COVID-19 / RNA polymerase / suramin binding / VIRAL PROTEIN | |||||||||
| 機能・相同性 |  機能・相同性情報 機能・相同性情報protein guanylyltransferase activity / RNA endonuclease activity producing 3'-phosphomonoesters, hydrolytic mechanism / mRNA guanylyltransferase activity / 5'-3' RNA helicase activity / 付加脱離酵素(リアーゼ); P-Oリアーゼ類; - / Assembly of the SARS-CoV-2 Replication-Transcription Complex (RTC) / symbiont-mediated suppression of host cytoplasmic pattern recognition receptor signaling pathway via inhibition of TBK1 activity / Maturation of replicase proteins / TRAF3-dependent IRF activation pathway / ISG15-specific peptidase activity ...protein guanylyltransferase activity / RNA endonuclease activity producing 3'-phosphomonoesters, hydrolytic mechanism / mRNA guanylyltransferase activity / 5'-3' RNA helicase activity / 付加脱離酵素(リアーゼ); P-Oリアーゼ類; - / Assembly of the SARS-CoV-2 Replication-Transcription Complex (RTC) / symbiont-mediated suppression of host cytoplasmic pattern recognition receptor signaling pathway via inhibition of TBK1 activity / Maturation of replicase proteins / TRAF3-dependent IRF activation pathway / ISG15-specific peptidase activity / Transcription of SARS-CoV-2 sgRNAs / Translation of Replicase and Assembly of the Replication Transcription Complex / snRNP Assembly / Replication of the SARS-CoV-2 genome / 加水分解酵素; エステル加水分解酵素; 5'-リン酸モノエステル産生エキソリボヌクレアーゼ / host cell endoplasmic reticulum-Golgi intermediate compartment / double membrane vesicle viral factory outer membrane / SARS coronavirus main proteinase / 5'-3' DNA helicase activity / 3'-5'-RNA exonuclease activity / host cell endosome / symbiont-mediated degradation of host mRNA / mRNA guanylyltransferase / symbiont-mediated suppression of host ISG15-protein conjugation / G-quadruplex RNA binding / symbiont-mediated suppression of host toll-like receptor signaling pathway / symbiont-mediated suppression of host cytoplasmic pattern recognition receptor signaling pathway via inhibition of IRF3 activity / omega peptidase activity / mRNA (guanine-N7)-methyltransferase / SARS-CoV-2 modulates host translation machinery / methyltransferase cap1 / host cell Golgi apparatus / symbiont-mediated suppression of host NF-kappaB cascade / symbiont-mediated perturbation of host ubiquitin-like protein modification / DNA helicase / methyltransferase cap1 activity / ubiquitinyl hydrolase 1 / cysteine-type deubiquitinase activity / mRNA 5'-cap (guanine-N7-)-methyltransferase activity / 加水分解酵素; プロテアーゼ; ペプチド結合加水分解酵素; システインプロテアーゼ / single-stranded RNA binding / regulation of autophagy / host cell perinuclear region of cytoplasm / viral protein processing / lyase activity / host cell endoplasmic reticulum membrane / RNA helicase / symbiont-mediated suppression of host type I interferon-mediated signaling pathway / symbiont-mediated suppression of host gene expression / copper ion binding / viral translational frameshifting / symbiont-mediated activation of host autophagy / RNA-directed RNA polymerase / cysteine-type endopeptidase activity / viral RNA genome replication / RNA-directed RNA polymerase activity / DNA-templated transcription / lipid binding / host cell nucleus / SARS-CoV-2 activates/modulates innate and adaptive immune responses / ATP hydrolysis activity / proteolysis / RNA binding / zinc ion binding / ATP binding / membrane 類似検索 - 分子機能 | |||||||||
| 生物種 |  | |||||||||
| 手法 | 単粒子再構成法 / クライオ電子顕微鏡法 / 解像度: 2.57 Å | |||||||||
 データ登録者 データ登録者 | Li Z / Yin W | |||||||||
 引用 引用 |  ジャーナル: Nat Struct Mol Biol / 年: 2021 ジャーナル: Nat Struct Mol Biol / 年: 2021タイトル: Structural basis for inhibition of the SARS-CoV-2 RNA polymerase by suramin. 著者: Wanchao Yin / Xiaodong Luan / Zhihai Li / Ziwei Zhou / Qingxing Wang / Minqi Gao / Xiaoxi Wang / Fulai Zhou / Jingjing Shi / Erli You / Mingliang Liu / Qingxia Wang / Yi Jiang / Hualiang ...著者: Wanchao Yin / Xiaodong Luan / Zhihai Li / Ziwei Zhou / Qingxing Wang / Minqi Gao / Xiaoxi Wang / Fulai Zhou / Jingjing Shi / Erli You / Mingliang Liu / Qingxia Wang / Yi Jiang / Hualiang Jiang / Gengfu Xiao / Leike Zhang / Xuekui Yu / Shuyang Zhang / H Eric Xu /  要旨: The COVID-19 pandemic caused by nonstop infections of SARS-CoV-2 has continued to ravage many countries worldwide. Here we report that suramin, a 100-year-old drug, is a potent inhibitor of the SARS- ...The COVID-19 pandemic caused by nonstop infections of SARS-CoV-2 has continued to ravage many countries worldwide. Here we report that suramin, a 100-year-old drug, is a potent inhibitor of the SARS-CoV-2 RNA-dependent RNA polymerase (RdRp) and acts by blocking the binding of RNA to the enzyme. In biochemical assays, suramin and its derivatives are at least 20-fold more potent than remdesivir, the currently approved nucleotide drug for treatment of COVID-19. The 2.6 Å cryo-electron microscopy structure of the viral RdRp bound to suramin reveals two binding sites. One site directly blocks the binding of the RNA template strand and the other site clashes with the RNA primer strand near the RdRp catalytic site, thus inhibiting RdRp activity. Suramin blocks viral replication in Vero E6 cells, although the reasons underlying this effect are likely various. Our results provide a structural mechanism for a nonnucleotide inhibitor of the SARS-CoV-2 RdRp. | |||||||||
| 履歴 |
|
- 構造の表示
構造の表示
| ムービー |
 ムービービューア ムービービューア |
|---|---|
| 構造ビューア | EMマップ:  SurfView SurfView Molmil Molmil Jmol/JSmol Jmol/JSmol |
| 添付画像 |
- ダウンロードとリンク
ダウンロードとリンク
-EMDBアーカイブ
| マップデータ |  emd_30572.map.gz emd_30572.map.gz | 60.1 MB |  EMDBマップデータ形式 EMDBマップデータ形式 | |
|---|---|---|---|---|
| ヘッダ (付随情報) |  emd-30572-v30.xml emd-30572-v30.xml emd-30572.xml emd-30572.xml | 17.8 KB 17.8 KB | 表示 表示 |  EMDBヘッダ EMDBヘッダ |
| 画像 |  emd_30572.png emd_30572.png | 29 KB | ||
| Filedesc metadata |  emd-30572.cif.gz emd-30572.cif.gz | 6.8 KB | ||
| アーカイブディレクトリ |  http://ftp.pdbj.org/pub/emdb/structures/EMD-30572 http://ftp.pdbj.org/pub/emdb/structures/EMD-30572 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-30572 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-30572 | HTTPS FTP |
-検証レポート
| 文書・要旨 |  emd_30572_validation.pdf.gz emd_30572_validation.pdf.gz | 594.3 KB | 表示 |  EMDB検証レポート EMDB検証レポート |
|---|---|---|---|---|
| 文書・詳細版 |  emd_30572_full_validation.pdf.gz emd_30572_full_validation.pdf.gz | 593.9 KB | 表示 | |
| XML形式データ |  emd_30572_validation.xml.gz emd_30572_validation.xml.gz | 6.1 KB | 表示 | |
| CIF形式データ |  emd_30572_validation.cif.gz emd_30572_validation.cif.gz | 7 KB | 表示 | |
| アーカイブディレクトリ |  https://ftp.pdbj.org/pub/emdb/validation_reports/EMD-30572 https://ftp.pdbj.org/pub/emdb/validation_reports/EMD-30572 ftp://ftp.pdbj.org/pub/emdb/validation_reports/EMD-30572 ftp://ftp.pdbj.org/pub/emdb/validation_reports/EMD-30572 | HTTPS FTP |
-関連構造データ
- リンク
リンク
| EMDBのページ |  EMDB (EBI/PDBe) / EMDB (EBI/PDBe) /  EMDataResource EMDataResource |
|---|---|
| 「今月の分子」の関連する項目 |
- マップ
マップ
| ファイル |  ダウンロード / ファイル: emd_30572.map.gz / 形式: CCP4 / 大きさ: 64 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) ダウンロード / ファイル: emd_30572.map.gz / 形式: CCP4 / 大きさ: 64 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 投影像・断面図 | 画像のコントロール
画像は Spider により作成 | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| ボクセルのサイズ | X=Y=Z: 1.069 Å | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 密度 |
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 対称性 | 空間群: 1 | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 詳細 | EMDB XML:
CCP4マップ ヘッダ情報:
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
-添付データ
- 試料の構成要素
試料の構成要素
-全体 : COVID-19 RdRp complex bound to suramin
| 全体 | 名称: COVID-19 RdRp complex bound to suramin |
|---|---|
| 要素 |
|
-超分子 #1: COVID-19 RdRp complex bound to suramin
| 超分子 | 名称: COVID-19 RdRp complex bound to suramin / タイプ: complex / ID: 1 / 親要素: 0 / 含まれる分子: #1-#3 |
|---|---|
| 由来(天然) | 生物種:  |
-分子 #1: Non-structural protein 8
| 分子 | 名称: Non-structural protein 8 / タイプ: protein_or_peptide / ID: 1 / コピー数: 2 / 光学異性体: LEVO |
|---|---|
| 由来(天然) | 生物種:  |
| 分子量 | 理論値: 22.034242 KDa |
| 組換発現 | 生物種:  |
| 配列 | 文字列: MAIASEFSSL PSYAAFATAQ EAYEQAVANG DSEVVLKKLK KSLNVAKSEF DRDAAMQRKL EKMADQAMTQ MYKQARSEDK RAKVTSAMQ TMLFTMLRKL DNDALNNIIN NARDGCVPLN IIPLTTAAKL MVVIPDYNTY KNTCDGTTFT YASALWEIQQ V VDADSKIV ...文字列: MAIASEFSSL PSYAAFATAQ EAYEQAVANG DSEVVLKKLK KSLNVAKSEF DRDAAMQRKL EKMADQAMTQ MYKQARSEDK RAKVTSAMQ TMLFTMLRKL DNDALNNIIN NARDGCVPLN IIPLTTAAKL MVVIPDYNTY KNTCDGTTFT YASALWEIQQ V VDADSKIV QLSEISMDNS PNLAWPLIVT ALRANSAVKL Q UniProtKB: Replicase polyprotein 1ab |
-分子 #2: Non-structural protein 7
| 分子 | 名称: Non-structural protein 7 / タイプ: protein_or_peptide / ID: 2 / コピー数: 1 / 光学異性体: LEVO |
|---|---|
| 由来(天然) | 生物種:  |
| 分子量 | 理論値: 9.38 KDa |
| 組換発現 | 生物種:  |
| 配列 | 文字列: MSKMSDVKCT SVVLLSVLQQ LRVESSSKLW AQCVQLHNDI LLAKDTTEAF EKMVSLLSVL LSMQGAVDIN KLCEEMLDNR ATLQ UniProtKB: Replicase polyprotein 1ab |
-分子 #3: RNA-directed RNA polymerase
| 分子 | 名称: RNA-directed RNA polymerase / タイプ: protein_or_peptide / ID: 3 / コピー数: 1 / 光学異性体: LEVO / EC番号: RNA-directed RNA polymerase |
|---|---|
| 由来(天然) | 生物種:  |
| 分子量 | 理論値: 107.96525 KDa |
| 組換発現 | 生物種:  |
| 配列 | 文字列: MSADAQSFLN RVCGVSAARL TPCGTGTSTD VVYRAFDIYN DKVAGFAKFL KTNCCRFQEK DEDDNLIDSY FVVKRHTFSN YQHEETIYN LLKDCPAVAK HDFFKFRIDG DMVPHISRQR LTKYTMADLV YALRHFDEGN CDTLKEILVT YNCCDDDYFN K KDWYDFVE ...文字列: MSADAQSFLN RVCGVSAARL TPCGTGTSTD VVYRAFDIYN DKVAGFAKFL KTNCCRFQEK DEDDNLIDSY FVVKRHTFSN YQHEETIYN LLKDCPAVAK HDFFKFRIDG DMVPHISRQR LTKYTMADLV YALRHFDEGN CDTLKEILVT YNCCDDDYFN K KDWYDFVE NPDILRVYAN LGERVRQALL KTVQFCDAMR NAGIVGVLTL DNQDLNGNWY DFGDFIQTTP GSGVPVVDSY YS LLMPILT LTRALTAESH VDTDLTKPYI KWDLLKYDFT EERLKLFDRY FKYWDQTYHP NCVNCLDDRC ILHCANFNVL FST VFPPTS FGPLVRKIFV DGVPFVVSTG YHFRELGVVH NQDVNLHSSR LSFKELLVYA ADPAMHAASG NLLLDKRTTC FSVA ALTNN VAFQTVKPGN FNKDFYDFAV SKGFFKEGSS VELKHFFFAQ DGNAAISDYD YYRYNLPTMC DIRQLLFVVE VVDKY FDCY DGGCINANQV IVNNLDKSAG FPFNKWGKAR LYYDSMSYED QDALFAYTKR NVIPTITQMN LKYAISAKNR ARTVAG VSI CSTMTNRQFH QKLLKSIAAT RGATVVIGTS KFYGGWHNML KTVYSDVENP HLMGWDYPKC DRAMPNMLRI MASLVLA RK HTTCCSLSHR FYRLANECAQ VLSEMVMCGG SLYVKPGGTS SGDATTAYAN SVFNICQAVT ANVNALLSTD GNKIADKY V RNLQHRLYEC LYRNRDVDTD FVNEFYAYLR KHFSMMILSD DAVVCFNSTY ASQGLVASIK NFKSVLYYQN NVFMSEAKC WTETDLTKGP HEFCSQHTML VKQGDDYVYL PYPDPSRILG AGCFVDDIVK TDGTLMIERF VSLAIDAYPL TKHPNQEYAD VFHLYLQYI RKLHDELTGH MLDMYSVMLT NDNTSRYWEP EFYEAMYTPH TVLQGGSENL YFQG UniProtKB: Replicase polyprotein 1ab |
-分子 #4: ZINC ION
| 分子 | 名称: ZINC ION / タイプ: ligand / ID: 4 / コピー数: 2 / 式: ZN |
|---|---|
| 分子量 | 理論値: 65.409 Da |
-分子 #5: 8-(3-(3-aminobenzamido)-4-methylbenzamido)naphthalene-1,3,5-trisu...
| 分子 | 名称: 8-(3-(3-aminobenzamido)-4-methylbenzamido)naphthalene-1,3,5-trisulfonic acid タイプ: ligand / ID: 5 / コピー数: 2 / 式: H3U |
|---|---|
| 分子量 | 理論値: 635.643 Da |
| Chemical component information | 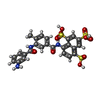 ChemComp-H3U: |
-実験情報
-構造解析
| 手法 | クライオ電子顕微鏡法 |
|---|---|
 解析 解析 | 単粒子再構成法 |
| 試料の集合状態 | particle |
- 試料調製
試料調製
| 緩衝液 | pH: 7.4 |
|---|---|
| 凍結 | 凍結剤: ETHANE |
- 電子顕微鏡法
電子顕微鏡法
| 顕微鏡 | FEI TITAN KRIOS |
|---|---|
| 撮影 | フィルム・検出器のモデル: GATAN K3 BIOQUANTUM (6k x 4k) 平均電子線量: 68.0 e/Å2 |
| 電子線 | 加速電圧: 300 kV / 電子線源:  FIELD EMISSION GUN FIELD EMISSION GUN |
| 電子光学系 | 照射モード: FLOOD BEAM / 撮影モード: BRIGHT FIELD |
| 実験機器 |  モデル: Titan Krios / 画像提供: FEI Company |
 ムービー
ムービー コントローラー
コントローラー






















 Z (Sec.)
Z (Sec.) Y (Row.)
Y (Row.) X (Col.)
X (Col.)





















