+ データを開く
データを開く
- 基本情報
基本情報
| 登録情報 |  | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| タイトル | Structure of the L. blandensis dGTPase in the apo form | ||||||||||||
 マップデータ マップデータ | DeepEMhancer post-processed map | ||||||||||||
 試料 試料 |
| ||||||||||||
 キーワード キーワード | dGTPase / nucleotide binding / HYDROLASE | ||||||||||||
| 機能・相同性 |  機能・相同性情報 機能・相同性情報 | ||||||||||||
| 生物種 |  Leeuwenhoekiella blandensis MED217 (バクテリア) Leeuwenhoekiella blandensis MED217 (バクテリア) | ||||||||||||
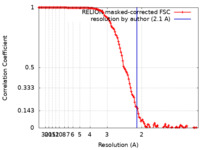
| 手法 | 単粒子再構成法 / クライオ電子顕微鏡法 / 解像度: 2.1 Å | ||||||||||||
 データ登録者 データ登録者 | Klemm BP / Sikkema AP | ||||||||||||
| 資金援助 |  米国, 3件 米国, 3件
| ||||||||||||
 引用 引用 |  ジャーナル: J Biol Chem / 年: 2022 ジャーナル: J Biol Chem / 年: 2022タイトル: High-resolution structures of the SAMHD1 dGTPase homolog from Leeuwenhoekiella blandensis reveal a novel mechanism of allosteric activation by dATP. 著者: Bradley P Klemm / Andrew P Sikkema / Allen L Hsu / James C Horng / Traci M Tanaka Hall / Mario J Borgnia / Roel M Schaaper /  要旨: Deoxynucleoside triphosphate (dNTP) triphosphohydrolases (dNTPases) are important enzymes that may perform multiple functions in the cell, including regulating the dNTP pools and contributing to ...Deoxynucleoside triphosphate (dNTP) triphosphohydrolases (dNTPases) are important enzymes that may perform multiple functions in the cell, including regulating the dNTP pools and contributing to innate immunity against viruses. Among the homologs that are best studied are human sterile alpha motif and HD domain-containing protein 1 (SAMHD1), a tetrameric dNTPase, and the hexameric Escherichia coli dGTPase; however, it is unclear whether these are representative of all dNTPases given their wide distribution throughout life. Here, we investigated a hexameric homolog from the marine bacterium Leeuwenhoekiella blandensis, revealing that it is a dGTPase that is subject to allosteric activation by dATP, specifically. Allosteric regulation mediated solely by dATP represents a novel regulatory feature among dNTPases that may facilitate maintenance of cellular dNTP pools in L. blandensis. We present high-resolution X-ray crystallographic structures (1.80-2.26 Å) in catalytically important conformations as well as cryo-EM structures (2.1-2.7 Å) of the enzyme bound to dGTP and dATP ligands. The structures, the highest resolution cryo-EM structures of any SAMHD1-like dNTPase to date, reveal an intact metal-binding site with the dGTP substrate coordinated to three metal ions. These structural and biochemical data yield insights into the catalytic mechanism and support a conserved catalytic mechanism for the tetrameric and hexameric dNTPase homologs. We conclude that the allosteric activation by dATP appears to rely on structural connectivity between the allosteric and active sites, as opposed to the changes in oligomeric state upon ligand binding used by SAMHD1. | ||||||||||||
| 履歴 |
|
- 構造の表示
構造の表示
| 添付画像 |
|---|
- ダウンロードとリンク
ダウンロードとリンク
-EMDBアーカイブ
| マップデータ |  emd_26126.map.gz emd_26126.map.gz | 159.1 MB |  EMDBマップデータ形式 EMDBマップデータ形式 | |
|---|---|---|---|---|
| ヘッダ (付随情報) |  emd-26126-v30.xml emd-26126-v30.xml emd-26126.xml emd-26126.xml | 27.3 KB 27.3 KB | 表示 表示 |  EMDBヘッダ EMDBヘッダ |
| FSC (解像度算出) |  emd_26126_fsc.xml emd_26126_fsc.xml | 13 KB | 表示 |  FSCデータファイル FSCデータファイル |
| 画像 |  emd_26126.png emd_26126.png | 135.4 KB | ||
| マスクデータ |  emd_26126_msk_1.map emd_26126_msk_1.map | 190.1 MB |  マスクマップ マスクマップ | |
| Filedesc metadata |  emd-26126.cif.gz emd-26126.cif.gz | 6.9 KB | ||
| その他 |  emd_26126_additional_1.map.gz emd_26126_additional_1.map.gz emd_26126_additional_2.map.gz emd_26126_additional_2.map.gz emd_26126_additional_3.map.gz emd_26126_additional_3.map.gz emd_26126_half_map_1.map.gz emd_26126_half_map_1.map.gz emd_26126_half_map_2.map.gz emd_26126_half_map_2.map.gz | 149.4 MB 19.6 MB 176.2 MB 150.8 MB 150.8 MB | ||
| アーカイブディレクトリ |  http://ftp.pdbj.org/pub/emdb/structures/EMD-26126 http://ftp.pdbj.org/pub/emdb/structures/EMD-26126 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-26126 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-26126 | HTTPS FTP |
-関連構造データ
| 関連構造データ |  7tu5MC  7tu0C  7tu1C  7tu2C  7tu3C  7tu4C  7tu6C  7tu7C  7tu8C C: 同じ文献を引用 ( M: このマップから作成された原子モデル |
|---|---|
| 類似構造データ | 類似検索 - 機能・相同性  F&H 検索 F&H 検索 |
- リンク
リンク
| EMDBのページ |  EMDB (EBI/PDBe) / EMDB (EBI/PDBe) /  EMDataResource EMDataResource |
|---|---|
| 「今月の分子」の関連する項目 |
- マップ
マップ
| ファイル |  ダウンロード / ファイル: emd_26126.map.gz / 形式: CCP4 / 大きさ: 190.1 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) ダウンロード / ファイル: emd_26126.map.gz / 形式: CCP4 / 大きさ: 190.1 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) | ||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | DeepEMhancer post-processed map | ||||||||||||||||||||||||||||||||||||
| 投影像・断面図 | 画像のコントロール
画像は Spider により作成 | ||||||||||||||||||||||||||||||||||||
| ボクセルのサイズ | X=Y=Z: 0.646 Å | ||||||||||||||||||||||||||||||||||||
| 密度 |
| ||||||||||||||||||||||||||||||||||||
| 対称性 | 空間群: 1 | ||||||||||||||||||||||||||||||||||||
| 詳細 | EMDB XML:
|
-添付データ
-マスク #1
| ファイル |  emd_26126_msk_1.map emd_26126_msk_1.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 投影像・断面図 |
| ||||||||||||
| 密度ヒストグラム |
-追加マップ: Full-map from RELION refinement
| ファイル | emd_26126_additional_1.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | Full-map from RELION refinement | ||||||||||||
| 投影像・断面図 |
| ||||||||||||
| 密度ヒストグラム |
-追加マップ: RELION post-processed map
| ファイル | emd_26126_additional_2.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | RELION post-processed map | ||||||||||||
| 投影像・断面図 |
| ||||||||||||
| 密度ヒストグラム |
-追加マップ: PHENIX auto-sharpened map
| ファイル | emd_26126_additional_3.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | PHENIX auto-sharpened map | ||||||||||||
| 投影像・断面図 |
| ||||||||||||
| 密度ヒストグラム |
-ハーフマップ: Half-map 1
| ファイル | emd_26126_half_map_1.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | Half-map 1 | ||||||||||||
| 投影像・断面図 |
| ||||||||||||
| 密度ヒストグラム |
-ハーフマップ: Half-map 2
| ファイル | emd_26126_half_map_2.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | Half-map 2 | ||||||||||||
| 投影像・断面図 |
| ||||||||||||
| 密度ヒストグラム |
- 試料の構成要素
試料の構成要素
-全体 : dGTP triphosphohydrolase
| 全体 | 名称: dGTP triphosphohydrolase |
|---|---|
| 要素 |
|
-超分子 #1: dGTP triphosphohydrolase
| 超分子 | 名称: dGTP triphosphohydrolase / タイプ: complex / ID: 1 / 親要素: 0 / 含まれる分子: #1 |
|---|---|
| 由来(天然) | 生物種:  Leeuwenhoekiella blandensis MED217 (バクテリア) Leeuwenhoekiella blandensis MED217 (バクテリア) |
-分子 #1: dGTP triphosphohydrolase
| 分子 | 名称: dGTP triphosphohydrolase / タイプ: protein_or_peptide / ID: 1 / コピー数: 6 / 光学異性体: LEVO / EC番号: dGTPase |
|---|---|
| 由来(天然) | 生物種:  Leeuwenhoekiella blandensis MED217 (バクテリア) Leeuwenhoekiella blandensis MED217 (バクテリア)株: CECT 7118 / CCUG 51940 / MED217 |
| 分子量 | 理論値: 52.723242 KDa |
| 組換発現 | 生物種:  |
| 配列 | 文字列: MHHHHHHSSG VDLGTENLYF QSNANWEHLL SLKRQGDTAK RLRIEQDDTR LGFEVDYDRI IFSAPFRSLQ DKTQVIPLSK TDFVHTRLT HSLEVSVVGR SLGRMVGKKL LEKYPHLEQV YGYKFNDFGA IVAAAALAHD IGNPPFGHSG EKAIGEFFKN G YGKRYKDS ...文字列: MHHHHHHSSG VDLGTENLYF QSNANWEHLL SLKRQGDTAK RLRIEQDDTR LGFEVDYDRI IFSAPFRSLQ DKTQVIPLSK TDFVHTRLT HSLEVSVVGR SLGRMVGKKL LEKYPHLEQV YGYKFNDFGA IVAAAALAHD IGNPPFGHSG EKAIGEFFKN G YGKRYKDS LTAKEYQDLI KFEGNANGFK VLSQSKPGAQ GGLRLSYATL GAFMKYPKES LPHKPSDHIA DKKYGFFQSE RA LFEDVAQ ELGLLKRSTT DDVSWSRHPL AYLVEAADDI CYTIIDFEDG INLGLIPEEY ALEYMVKLVG QTIDRNKYNA LQE TSDRVS YLRALAIGTL INESVDTFMK YEEEILAGTF DQSLIDKSNY QAQITDIINL SIERIYNSRE VIEKEIAGYE ILST LLEAR CRALDNNDTH YNQLIQQLLA PNDHSEKSLY ENLIQICAEV STMTDGKALR NYKKIKGLD UniProtKB: dGTP triphosphohydrolase |
-分子 #2: MAGNESIUM ION
| 分子 | 名称: MAGNESIUM ION / タイプ: ligand / ID: 2 / コピー数: 6 / 式: MG |
|---|---|
| 分子量 | 理論値: 24.305 Da |
-分子 #3: water
| 分子 | 名称: water / タイプ: ligand / ID: 3 / コピー数: 6 / 式: HOH |
|---|---|
| 分子量 | 理論値: 18.015 Da |
| Chemical component information |  ChemComp-HOH: |
-実験情報
-構造解析
| 手法 | クライオ電子顕微鏡法 |
|---|---|
 解析 解析 | 単粒子再構成法 |
| 試料の集合状態 | particle |
- 試料調製
試料調製
| 濃度 | 0.2 mg/mL | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 緩衝液 | pH: 7.5 構成要素:
| ||||||||||||
| グリッド | モデル: UltrAuFoil R1.2/1.3 / 材質: GOLD / メッシュ: 300 / 前処理 - タイプ: GLOW DISCHARGE | ||||||||||||
| 凍結 | 凍結剤: ETHANE / チャンバー内湿度: 95 % / チャンバー内温度: 290 K / 装置: LEICA EM GP / 詳細: 3.5 second blot time (front). | ||||||||||||
| 詳細 | Hexamer concentration is listed. |
- 電子顕微鏡法
電子顕微鏡法
| 顕微鏡 | FEI TITAN KRIOS |
|---|---|
| 特殊光学系 | エネルギーフィルター - 名称: GIF Bioquantum / エネルギーフィルター - スリット幅: 20 eV |
| 詳細 | Defocus values as determined by CTFFIND-4.1 |
| 撮影 | フィルム・検出器のモデル: GATAN K2 SUMMIT (4k x 4k) 検出モード: COUNTING / デジタル化 - サイズ - 横: 3838 pixel / デジタル化 - サイズ - 縦: 3710 pixel / 撮影したグリッド数: 1 / 実像数: 3780 / 平均露光時間: 4.0 sec. / 平均電子線量: 58.6 e/Å2 |
| 電子線 | 加速電圧: 300 kV / 電子線源:  FIELD EMISSION GUN FIELD EMISSION GUN |
| 電子光学系 | 照射モード: FLOOD BEAM / 撮影モード: BRIGHT FIELD / Cs: 2.7 mm / 最大 デフォーカス(公称値): 2.5 µm / 最小 デフォーカス(公称値): 0.5 µm / 倍率(公称値): 215000 |
| 試料ステージ | 試料ホルダーモデル: FEI TITAN KRIOS AUTOGRID HOLDER ホルダー冷却材: NITROGEN |
| 実験機器 |  モデル: Titan Krios / 画像提供: FEI Company |
+ 画像解析
画像解析
-原子モデル構築 1
| 初期モデル | PDB ID: Chain - Source name: PDB / Chain - Initial model type: experimental model |
|---|---|
| 詳細 | The hexameric biological assembly of PDB ID: 3BG2 was used as the initial input model to fit into the EM map. |
| 精密化 | 空間: REAL / プロトコル: RIGID BODY FIT |
| 得られたモデル |  PDB-7tu5: |
 ムービー
ムービー コントローラー
コントローラー








 Z (Sec.)
Z (Sec.) Y (Row.)
Y (Row.) X (Col.)
X (Col.)