+ データを開く
データを開く
- 基本情報
基本情報
| 登録情報 | データベース: EMDB / ID: EMD-25178 | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| タイトル | Sub-tomogram averaged structure of HIV-1 Envelope protein in native membrane | ||||||||||||
 マップデータ マップデータ | |||||||||||||
 試料 試料 |
| ||||||||||||
 キーワード キーワード | HIV-1 / envelope protein / glycoprotein / Env / membrane bound / VIRAL PROTEIN | ||||||||||||
| 機能・相同性 |  機能・相同性情報 機能・相同性情報symbiont-mediated perturbation of host defense response / positive regulation of plasma membrane raft polarization / positive regulation of receptor clustering / host cell endosome membrane / clathrin-dependent endocytosis of virus by host cell / viral protein processing / fusion of virus membrane with host plasma membrane / fusion of virus membrane with host endosome membrane / viral envelope / virion attachment to host cell ...symbiont-mediated perturbation of host defense response / positive regulation of plasma membrane raft polarization / positive regulation of receptor clustering / host cell endosome membrane / clathrin-dependent endocytosis of virus by host cell / viral protein processing / fusion of virus membrane with host plasma membrane / fusion of virus membrane with host endosome membrane / viral envelope / virion attachment to host cell / host cell plasma membrane / virion membrane / structural molecule activity / membrane 類似検索 - 分子機能 | ||||||||||||
| 生物種 |   Human immunodeficiency virus 1 (ヒト免疫不全ウイルス) Human immunodeficiency virus 1 (ヒト免疫不全ウイルス) | ||||||||||||
| 手法 | サブトモグラム平均法 / クライオ電子顕微鏡法 / 解像度: 9.1 Å | ||||||||||||
 データ登録者 データ登録者 | Mangala Prasad V / Lee KK | ||||||||||||
| 資金援助 |  米国, 3件 米国, 3件
| ||||||||||||
 引用 引用 |  ジャーナル: Cell / 年: 2022 ジャーナル: Cell / 年: 2022タイトル: Cryo-ET of Env on intact HIV virions reveals structural variation and positioning on the Gag lattice. 著者: Vidya Mangala Prasad / Daniel P Leaman / Klaus N Lovendahl / Jacob T Croft / Mark A Benhaim / Edgar A Hodge / Michael B Zwick / Kelly K Lee /  要旨: HIV-1 Env mediates viral entry into host cells and is the sole target for neutralizing antibodies. However, Env structure and organization in its native virion context has eluded detailed ...HIV-1 Env mediates viral entry into host cells and is the sole target for neutralizing antibodies. However, Env structure and organization in its native virion context has eluded detailed characterization. Here, we used cryo-electron tomography to analyze Env in mature and immature HIV-1 particles. Immature particles showed distinct Env positioning relative to the underlying Gag lattice, providing insights into long-standing questions about Env incorporation. A 9.1-Å sub-tomogram-averaged reconstruction of virion-bound Env in conjunction with structural mass spectrometry revealed unexpected features, including a variable central core of the gp41 subunit, heterogeneous glycosylation between protomers, and a flexible stalk that allows Env tilting and variable exposure of neutralizing epitopes. Together, our results provide an integrative understanding of HIV assembly and structural variation in Env antigen presentation. | ||||||||||||
| 履歴 |
|
- 構造の表示
構造の表示
| ムービー |
 ムービービューア ムービービューア |
|---|---|
| 構造ビューア | EMマップ:  SurfView SurfView Molmil Molmil Jmol/JSmol Jmol/JSmol |
| 添付画像 |
- ダウンロードとリンク
ダウンロードとリンク
-EMDBアーカイブ
| マップデータ |  emd_25178.map.gz emd_25178.map.gz | 855.6 KB |  EMDBマップデータ形式 EMDBマップデータ形式 | |
|---|---|---|---|---|
| ヘッダ (付随情報) |  emd-25178-v30.xml emd-25178-v30.xml emd-25178.xml emd-25178.xml | 17.8 KB 17.8 KB | 表示 表示 |  EMDBヘッダ EMDBヘッダ |
| FSC (解像度算出) |  emd_25178_fsc.xml emd_25178_fsc.xml | 4.3 KB | 表示 |  FSCデータファイル FSCデータファイル |
| 画像 |  emd_25178.png emd_25178.png | 57.5 KB | ||
| Filedesc metadata |  emd-25178.cif.gz emd-25178.cif.gz | 7.4 KB | ||
| アーカイブディレクトリ |  http://ftp.pdbj.org/pub/emdb/structures/EMD-25178 http://ftp.pdbj.org/pub/emdb/structures/EMD-25178 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-25178 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-25178 | HTTPS FTP |
-関連構造データ
- リンク
リンク
| EMDBのページ |  EMDB (EBI/PDBe) / EMDB (EBI/PDBe) /  EMDataResource EMDataResource |
|---|---|
| 「今月の分子」の関連する項目 |
- マップ
マップ
| ファイル |  ダウンロード / ファイル: emd_25178.map.gz / 形式: CCP4 / 大きさ: 6.6 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) ダウンロード / ファイル: emd_25178.map.gz / 形式: CCP4 / 大きさ: 6.6 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 投影像・断面図 | 画像のコントロール
画像は Spider により作成 | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| ボクセルのサイズ | X=Y=Z: 2.58 Å | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 密度 |
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 対称性 | 空間群: 1 | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 詳細 | EMDB XML:
CCP4マップ ヘッダ情報:
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
-添付データ
- 試料の構成要素
試料の構成要素
-全体 : Human immunodeficiency virus 1
| 全体 | 名称:   Human immunodeficiency virus 1 (ヒト免疫不全ウイルス) Human immunodeficiency virus 1 (ヒト免疫不全ウイルス) |
|---|---|
| 要素 |
|
-超分子 #1: Human immunodeficiency virus 1
| 超分子 | 名称: Human immunodeficiency virus 1 / タイプ: virus / ID: 1 / 親要素: 0 / 含まれる分子: #1-#2 / 詳細: Env glycoprotein displayed on surface of HIV-1 / NCBI-ID: 11676 / 生物種: Human immunodeficiency virus 1 / ウイルスタイプ: VIRUS-LIKE PARTICLE / ウイルス・単離状態: STRAIN / ウイルス・エンベロープ: Yes / ウイルス・中空状態: No |
|---|---|
| 分子量 | 理論値: 430 KDa |
-分子 #1: Envelope glycoprotein gp120
| 分子 | 名称: Envelope glycoprotein gp120 / タイプ: protein_or_peptide / ID: 1 / コピー数: 3 / 光学異性体: LEVO |
|---|---|
| 由来(天然) | 生物種:   Human immunodeficiency virus 1 (ヒト免疫不全ウイルス) Human immunodeficiency virus 1 (ヒト免疫不全ウイルス) |
| 分子量 | 理論値: 52.170992 KDa |
| 組換発現 | 生物種:  Homo sapiens (ヒト) Homo sapiens (ヒト) |
| 配列 | 文字列: KLWVTVYYGV PVWKEATTTL FCASDAKAYD TEVHNVWATH ACVPTDPNPQ EVVLENVTEN FNMWKNNMVE QMHEDIISLW DQSLKPCVK LTPLCVTLNC TDLRNVTNIN NSSEGMRGEI KNCSFNITTS IRDKVKKDYA LFYRLDVVPI DNDNTSYRLI N CNTSTITQ ...文字列: KLWVTVYYGV PVWKEATTTL FCASDAKAYD TEVHNVWATH ACVPTDPNPQ EVVLENVTEN FNMWKNNMVE QMHEDIISLW DQSLKPCVK LTPLCVTLNC TDLRNVTNIN NSSEGMRGEI KNCSFNITTS IRDKVKKDYA LFYRLDVVPI DNDNTSYRLI N CNTSTITQ ACPKVSFEPI PIHYCTPAGF AILKCKDKKF NGTGPCKNVS TVQCTHGIRP VVSTQLLLNG SLAEEEVVIR SS NFTDNAK NIIVQLKESV EINCTRPNNN TRKSIHIGPG RAFYTTGEII GDIRQAHCNI SRTKWNNTLN QIATKLKEQF GNN KTIVFN QSSGGDPEIV MHSFNCGGEF FYCNSTQLFN STWNFNGTWN LTQSNGTEGN DTITLPCRIK QIINMWQEVG KAMY APPIR GQIRCSSNIT GLILTRDGGT NSSGSEIFRP GGGDMRDNWR SELYKYKVVK IEPLGVAPTK UniProtKB: Envelope glycoprotein gp160 |
-分子 #2: Envelope glycoprotein gp41
| 分子 | 名称: Envelope glycoprotein gp41 / タイプ: protein_or_peptide / ID: 2 / コピー数: 3 / 光学異性体: LEVO |
|---|---|
| 由来(天然) | 生物種:   Human immunodeficiency virus 1 (ヒト免疫不全ウイルス) Human immunodeficiency virus 1 (ヒト免疫不全ウイルス) |
| 分子量 | 理論値: 16.420559 KDa |
| 組換発現 | 生物種:  Homo sapiens (ヒト) Homo sapiens (ヒト) |
| 配列 | 文字列: GFLGAAGSTM GAASMTLTVQ ARQLLSGIVQ QQNNLLRAIE AQQHLLQLTV WGIRQLQARV LAVERYLRDQ QLLGIWGCSG KLICTTAVP WNASWSNKSL EQIWNNMTWM EWDREINNYT SLIHSLIEEA QNQQEKNEQE LLELD UniProtKB: Envelope glycoprotein gp160 |
-分子 #12: 2-acetamido-2-deoxy-beta-D-glucopyranose
| 分子 | 名称: 2-acetamido-2-deoxy-beta-D-glucopyranose / タイプ: ligand / ID: 12 / コピー数: 21 / 式: NAG |
|---|---|
| 分子量 | 理論値: 221.208 Da |
| Chemical component information |  ChemComp-NAG: |
-分子 #13: alpha-L-fucopyranose
| 分子 | 名称: alpha-L-fucopyranose / タイプ: ligand / ID: 13 / コピー数: 3 / 式: FUC |
|---|---|
| 分子量 | 理論値: 164.156 Da |
| Chemical component information | 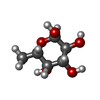 ChemComp-FUC: |
-実験情報
-構造解析
| 手法 | クライオ電子顕微鏡法 |
|---|---|
 解析 解析 | サブトモグラム平均法 |
| 試料の集合状態 | particle |
- 試料調製
試料調製
| 緩衝液 | pH: 7.4 / 構成要素 - 濃度: 1.0 X / 構成要素 - 名称: Phosphate buffer saline |
|---|---|
| グリッド | モデル: C-flat-1.2/1.3 / 材質: COPPER / メッシュ: 400 / 支持フィルム - 材質: CARBON / 前処理 - タイプ: GLOW DISCHARGE / 前処理 - 時間: 30 sec. |
| 凍結 | 凍結剤: ETHANE / チャンバー内湿度: 100 % / チャンバー内温度: 277 K / 装置: FEI VITROBOT MARK IV |
- 電子顕微鏡法
電子顕微鏡法
| 顕微鏡 | FEI TITAN KRIOS |
|---|---|
| 撮影 | フィルム・検出器のモデル: GATAN K2 SUMMIT (4k x 4k) 検出モード: COUNTING / 平均電子線量: 2.0 e/Å2 |
| 電子線 | 加速電圧: 300 kV / 電子線源:  FIELD EMISSION GUN FIELD EMISSION GUN |
| 電子光学系 | C2レンズ絞り径: 50.0 µm / 照射モード: FLOOD BEAM / 撮影モード: BRIGHT FIELD / Cs: 2.7 mm / 最大 デフォーカス(公称値): 5.0 µm / 最小 デフォーカス(公称値): 2.5 µm / 倍率(公称値): 58000 |
| 試料ステージ | 試料ホルダーモデル: FEI TITAN KRIOS AUTOGRID HOLDER ホルダー冷却材: NITROGEN |
| 実験機器 |  モデル: Titan Krios / 画像提供: FEI Company |
+ 画像解析
画像解析
-原子モデル構築 1
| 初期モデル | PDB ID: Chain - Source name: PDB / Chain - Initial model type: experimental model |
|---|---|
| 詳細 | 6ulc model was rigid body fitted into EM map. The flexible terminal Gp41 stalk region alone was fitted into density using COOT |
| 精密化 | プロトコル: RIGID BODY FIT |
| 得られたモデル |  PDB-7ska: |
 ムービー
ムービー コントローラー
コントローラー

















 Z (Sec.)
Z (Sec.) Y (Row.)
Y (Row.) X (Col.)
X (Col.)























