+ データを開く
データを開く
- 基本情報
基本情報
| 登録情報 | データベース: EMDB / ID: EMD-1528 | |||||||||
|---|---|---|---|---|---|---|---|---|---|---|
| タイトル | Single copies of Sec61 and TRAP associate with a nontranslating mammalian ribosome | |||||||||
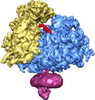
 マップデータ マップデータ | This is an average volume from 101000 aligned mammalian ribosome-channel complexes. | |||||||||
 試料 試料 |
| |||||||||
 キーワード キーワード | cryo electron microscopy / single particle analysis / ribosome / Sec61 channel / TRAP / ER membrane. co-translational protein translocation | |||||||||
| 機能・相同性 |  機能・相同性情報 機能・相同性情報intracellular protein transmembrane transport / SRP-dependent cotranslational protein targeting to membrane, translocation / signal sequence binding / protein secretion / protein transmembrane transporter activity / protein targeting / protein transport / plasma membrane 類似検索 - 分子機能 | |||||||||
| 生物種 |  | |||||||||
| 手法 | 単粒子再構成法 / クライオ電子顕微鏡法 / 解像度: 8.7 Å | |||||||||
 データ登録者 データ登録者 | Menetret JF / Hegde RS / Aguiar M / Gygi SP / Park E / Rapoport TA / Akey CW | |||||||||
 引用 引用 |  ジャーナル: Structure / 年: 2008 ジャーナル: Structure / 年: 2008タイトル: Single copies of Sec61 and TRAP associate with a nontranslating mammalian ribosome. 著者: Jean-François Ménétret / Ramanujan S Hegde / Mike Aguiar / Steven P Gygi / Eunyong Park / Tom A Rapoport / Christopher W Akey /  要旨: During cotranslational protein translocation, the ribosome associates with a membrane channel, formed by the Sec61 complex, and recruits the translocon-associated protein complex (TRAP). Here we ...During cotranslational protein translocation, the ribosome associates with a membrane channel, formed by the Sec61 complex, and recruits the translocon-associated protein complex (TRAP). Here we report the structure of a ribosome-channel complex from mammalian endoplasmic reticulum in which the channel has been visualized at 11 A resolution. In this complex, single copies of Sec61 and TRAP associate with a nontranslating ribosome and this stoichiometry was verified by quantitative mass spectrometry. A bilayer-like density surrounds the channel and can be attributed to lipid and detergent. The crystal structure of an archaeal homolog of the Sec61 complex was then docked into the map. In this model, two cytoplasmic loops of Sec61 may interact with RNA helices H6, H7, and H50, while the central pore is located below the ribosome tunnel exit. Hence, this copy of Sec61 is positioned to capture and translocate the nascent chain. Finally, we show that mammalian and bacterial ribosome-channel complexes have similar architectures. | |||||||||
| 履歴 |
|
- 構造の表示
構造の表示
| ムービー |
 ムービービューア ムービービューア |
|---|---|
| 構造ビューア | EMマップ:  SurfView SurfView Molmil Molmil Jmol/JSmol Jmol/JSmol |
| 添付画像 |
- ダウンロードとリンク
ダウンロードとリンク
-EMDBアーカイブ
| マップデータ |  emd_1528.map.gz emd_1528.map.gz | 4.3 MB |  EMDBマップデータ形式 EMDBマップデータ形式 | |
|---|---|---|---|---|
| ヘッダ (付随情報) |  emd-1528-v30.xml emd-1528-v30.xml emd-1528.xml emd-1528.xml | 10.6 KB 10.6 KB | 表示 表示 |  EMDBヘッダ EMDBヘッダ |
| 画像 |  EMD1528_Ribi_channel_complex.jpg EMD1528_Ribi_channel_complex.jpg | 177.5 KB | ||
| アーカイブディレクトリ |  http://ftp.pdbj.org/pub/emdb/structures/EMD-1528 http://ftp.pdbj.org/pub/emdb/structures/EMD-1528 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-1528 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-1528 | HTTPS FTP |
-検証レポート
| 文書・要旨 |  emd_1528_validation.pdf.gz emd_1528_validation.pdf.gz | 331.8 KB | 表示 |  EMDB検証レポート EMDB検証レポート |
|---|---|---|---|---|
| 文書・詳細版 |  emd_1528_full_validation.pdf.gz emd_1528_full_validation.pdf.gz | 331.4 KB | 表示 | |
| XML形式データ |  emd_1528_validation.xml.gz emd_1528_validation.xml.gz | 5.8 KB | 表示 | |
| アーカイブディレクトリ |  https://ftp.pdbj.org/pub/emdb/validation_reports/EMD-1528 https://ftp.pdbj.org/pub/emdb/validation_reports/EMD-1528 ftp://ftp.pdbj.org/pub/emdb/validation_reports/EMD-1528 ftp://ftp.pdbj.org/pub/emdb/validation_reports/EMD-1528 | HTTPS FTP |
-関連構造データ
- リンク
リンク
| EMDBのページ |  EMDB (EBI/PDBe) / EMDB (EBI/PDBe) /  EMDataResource EMDataResource |
|---|---|
| 「今月の分子」の関連する項目 |
- マップ
マップ
| ファイル |  ダウンロード / ファイル: emd_1528.map.gz / 形式: CCP4 / 大きさ: 17.7 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) ダウンロード / ファイル: emd_1528.map.gz / 形式: CCP4 / 大きさ: 17.7 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | This is an average volume from 101000 aligned mammalian ribosome-channel complexes. | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 投影像・断面図 | 画像のコントロール
画像は Spider により作成 | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| ボクセルのサイズ | X=Y=Z: 2.73 Å | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 密度 |
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 対称性 | 空間群: 1 | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 詳細 | EMDB XML:
CCP4マップ ヘッダ情報:
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
-添付データ
- 試料の構成要素
試料の構成要素
-全体 : Mammalian native ribosome-channel complex
| 全体 | 名称: Mammalian native ribosome-channel complex |
|---|---|
| 要素 |
|
-超分子 #1000: Mammalian native ribosome-channel complex
| 超分子 | 名称: Mammalian native ribosome-channel complex / タイプ: sample / ID: 1000 / Number unique components: 3 |
|---|---|
| 分子量 | 理論値: 3.77 MDa / 手法: from primary sequence |
-超分子 #1: ribosome channel complex
| 超分子 | 名称: ribosome channel complex / タイプ: complex / ID: 1 / Name.synonym: ribosome-channel complex 詳細: Sample solubilized from ER membranes with digitonin. 組換発現: No / Ribosome-details: ribosome-eukaryote: ALL |
|---|---|
| 由来(天然) | 生物種:  |
| 分子量 | 理論値: 3.77 MDa |
-実験情報
-構造解析
| 手法 | クライオ電子顕微鏡法 |
|---|---|
 解析 解析 | 単粒子再構成法 |
| 試料の集合状態 | particle |
- 試料調製
試料調製
| 緩衝液 | pH: 7.5 詳細: 30mM Hepes 50mM KAc, 10mM Mg acetate and 1.5% digitonin. |
|---|---|
| グリッド | 詳細: 400 mesh Cu grids with thin continuous carbon film |
| 凍結 | 凍結剤: ETHANE / チャンバー内湿度: 90 % / チャンバー内温度: 111 K / 装置: HOMEMADE PLUNGER 詳細: Vitrification instrument: home-made plunger. in cold room 手法: 1 second blot |
- 電子顕微鏡法
電子顕微鏡法
| 顕微鏡 | FEI TECNAI F20 |
|---|---|
| 温度 | 平均: 93 K |
| アライメント法 | Legacy - 非点収差: corrected on-axis at 150K mag |
| 詳細 | data were collected on Oxford and Gatan cryo-holders |
| 日付 | 2001年7月27日 |
| 撮影 | カテゴリ: FILM / フィルム・検出器のモデル: KODAK SO-163 FILM / デジタル化 - スキャナー: OTHER / デジタル化 - サンプリング間隔: 4.54 µm / 実像数: 500 / 平均電子線量: 15 e/Å2 / 詳細: Creoscitex Eversmart was used to scan negatives. / Od range: 1 / ビット/ピクセル: 8 |
| 電子線 | 加速電圧: 200 kV / 電子線源:  FIELD EMISSION GUN FIELD EMISSION GUN |
| 電子光学系 | 倍率(補正後): 51000 / 照射モード: FLOOD BEAM / 撮影モード: BRIGHT FIELD / Cs: 2.0 mm / 最大 デフォーカス(公称値): 3.0 µm / 最小 デフォーカス(公称値): 0.5 µm / 倍率(公称値): 50000 |
| 試料ステージ | 試料ホルダー: single tilt / 試料ホルダーモデル: GATAN LIQUID NITROGEN |
| 実験機器 |  モデル: Tecnai F20 / 画像提供: FEI Company |
- 画像解析
画像解析
| 詳細 | 101000 particles were selected using boxer (of EMAN) used as semi-automatic selection program |
|---|---|
| CTF補正 | 詳細: per micrograph |
| 最終 再構成 | 想定した対称性 - 点群: C1 (非対称) / アルゴリズム: OTHER / 解像度のタイプ: BY AUTHOR / 解像度: 8.7 Å / 解像度の算出法: FSC 0.5 CUT-OFF / ソフトウェア - 名称: EMAN / 使用した粒子像数: 79000 |
-原子モデル構築 1
| 初期モデル | (PDB ID:  2zkr , ) |
|---|---|
| ソフトウェア | 名称: Chimera (UCSF) |
| 詳細 | Protocol: rigid body and manual fitting. The PDBs were fitted using Chimera. The ribosome binding loops of 1RHZ were then flexibly fitted into the riboeome and the stereochemistry was regularized with Coot. |
| 精密化 | 空間: REAL / プロトコル: RIGID BODY FIT |
| 得られたモデル |  PDB-3dkn: |
 ムービー
ムービー コントローラー
コントローラー













 Z (Sec.)
Z (Sec.) Y (Row.)
Y (Row.) X (Col.)
X (Col.)