+ データを開く
データを開く
- 基本情報
基本情報
| 登録情報 |  | ||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| タイトル | Cryo-EM reconstruction of DNA bound Arp4-Ies4-N-actin-Arp8-Ino80HSA subcomplex (A-module) of S. cerevisiae INO80 | ||||||||||||||||||
 マップデータ マップデータ | map | ||||||||||||||||||
 試料 試料 |
| ||||||||||||||||||
| 生物種 |  | ||||||||||||||||||
| 手法 | 単粒子再構成法 / クライオ電子顕微鏡法 / 解像度: 7.5 Å | ||||||||||||||||||
 データ登録者 データ登録者 | Kunert F / Metzner FJ / Eustermann S / Jung J / Woike S / Schall K / Kostrewa D / Hopfner KP | ||||||||||||||||||
| 資金援助 | European Union,  ドイツ, 5件 ドイツ, 5件
| ||||||||||||||||||
 引用 引用 |  ジャーナル: Sci Adv / 年: 2022 ジャーナル: Sci Adv / 年: 2022タイトル: Structural mechanism of extranucleosomal DNA readout by the INO80 complex. 著者: Franziska Kunert / Felix J Metzner / James Jung / Markus Höpfler / Stephan Woike / Kevin Schall / Dirk Kostrewa / Manuela Moldt / Jia-Xuan Chen / Susanne Bantele / Boris Pfander / Sebastian ...著者: Franziska Kunert / Felix J Metzner / James Jung / Markus Höpfler / Stephan Woike / Kevin Schall / Dirk Kostrewa / Manuela Moldt / Jia-Xuan Chen / Susanne Bantele / Boris Pfander / Sebastian Eustermann / Karl-Peter Hopfner /  要旨: The nucleosomal landscape of chromatin depends on the concerted action of chromatin remodelers. The INO80 remodeler specifically places nucleosomes at the boundary of gene regulatory elements, which ...The nucleosomal landscape of chromatin depends on the concerted action of chromatin remodelers. The INO80 remodeler specifically places nucleosomes at the boundary of gene regulatory elements, which is proposed to be the result of an ATP-dependent nucleosome sliding activity that is regulated by extranucleosomal DNA features. Here, we use cryo-electron microscopy and functional assays to reveal how INO80 binds and is regulated by extranucleosomal DNA. Structures of the regulatory A-module bound to DNA clarify the mechanism of linker DNA binding. The A-module is connected to the motor unit via an HSA/post-HSA lever element to chemomechanically couple the motor and linker DNA sensing. Two notable sites of curved DNA recognition by coordinated action of the four actin/actin-related proteins and the motor suggest how sliding by INO80 can be regulated by extranucleosomal DNA features. Last, the structures clarify the recruitment of YY1/Ies4 subunits and reveal deep architectural similarities between the regulatory modules of INO80 and SWI/SNF complexes. | ||||||||||||||||||
| 履歴 |
|
- 構造の表示
構造の表示
| 添付画像 |
|---|
- ダウンロードとリンク
ダウンロードとリンク
-EMDBアーカイブ
| マップデータ |  emd_15186.map.gz emd_15186.map.gz | 49.5 MB |  EMDBマップデータ形式 EMDBマップデータ形式 | |
|---|---|---|---|---|
| ヘッダ (付随情報) |  emd-15186-v30.xml emd-15186-v30.xml emd-15186.xml emd-15186.xml | 19.8 KB 19.8 KB | 表示 表示 |  EMDBヘッダ EMDBヘッダ |
| 画像 |  emd_15186.png emd_15186.png | 59.8 KB | ||
| その他 |  emd_15186_half_map_1.map.gz emd_15186_half_map_1.map.gz emd_15186_half_map_2.map.gz emd_15186_half_map_2.map.gz | 49.7 MB 49.7 MB | ||
| アーカイブディレクトリ |  http://ftp.pdbj.org/pub/emdb/structures/EMD-15186 http://ftp.pdbj.org/pub/emdb/structures/EMD-15186 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-15186 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-15186 | HTTPS FTP |
-検証レポート
| 文書・要旨 |  emd_15186_validation.pdf.gz emd_15186_validation.pdf.gz | 668.4 KB | 表示 |  EMDB検証レポート EMDB検証レポート |
|---|---|---|---|---|
| 文書・詳細版 |  emd_15186_full_validation.pdf.gz emd_15186_full_validation.pdf.gz | 668 KB | 表示 | |
| XML形式データ |  emd_15186_validation.xml.gz emd_15186_validation.xml.gz | 12.2 KB | 表示 | |
| CIF形式データ |  emd_15186_validation.cif.gz emd_15186_validation.cif.gz | 14.3 KB | 表示 | |
| アーカイブディレクトリ |  https://ftp.pdbj.org/pub/emdb/validation_reports/EMD-15186 https://ftp.pdbj.org/pub/emdb/validation_reports/EMD-15186 ftp://ftp.pdbj.org/pub/emdb/validation_reports/EMD-15186 ftp://ftp.pdbj.org/pub/emdb/validation_reports/EMD-15186 | HTTPS FTP |
-関連構造データ
- リンク
リンク
| EMDBのページ |  EMDB (EBI/PDBe) / EMDB (EBI/PDBe) /  EMDataResource EMDataResource |
|---|
- マップ
マップ
| ファイル |  ダウンロード / ファイル: emd_15186.map.gz / 形式: CCP4 / 大きさ: 64 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) ダウンロード / ファイル: emd_15186.map.gz / 形式: CCP4 / 大きさ: 64 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) | ||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | map | ||||||||||||||||||||||||||||||||||||
| 投影像・断面図 | 画像のコントロール
画像は Spider により作成 | ||||||||||||||||||||||||||||||||||||
| ボクセルのサイズ | X=Y=Z: 1.059 Å | ||||||||||||||||||||||||||||||||||||
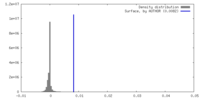
| 密度 |
| ||||||||||||||||||||||||||||||||||||
| 対称性 | 空間群: 1 | ||||||||||||||||||||||||||||||||||||
| 詳細 | EMDB XML:
|
-添付データ
-ハーフマップ: half map A
| ファイル | emd_15186_half_map_1.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | half map A | ||||||||||||
| 投影像・断面図 |
| ||||||||||||
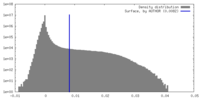
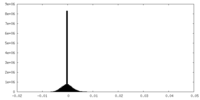
| 密度ヒストグラム |
-ハーフマップ: half map B
| ファイル | emd_15186_half_map_2.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | half map B | ||||||||||||
| 投影像・断面図 |
| ||||||||||||
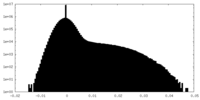
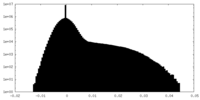
| 密度ヒストグラム |
- 試料の構成要素
試料の構成要素
-全体 : INO80 A-Module (Arp4-Ies4-N-actin-Arp8-Ino80HSA) bound to DNA
| 全体 | 名称: INO80 A-Module (Arp4-Ies4-N-actin-Arp8-Ino80HSA) bound to DNA |
|---|---|
| 要素 |
|
-超分子 #1: INO80 A-Module (Arp4-Ies4-N-actin-Arp8-Ino80HSA) bound to DNA
| 超分子 | 名称: INO80 A-Module (Arp4-Ies4-N-actin-Arp8-Ino80HSA) bound to DNA タイプ: complex / ID: 1 / キメラ: Yes / 親要素: 0 / 含まれる分子: all |
|---|---|
| 由来(天然) | 生物種:  |
-分子 #1: Ino80
| 分子 | 名称: Ino80 / タイプ: protein_or_peptide / ID: 1 / 光学異性体: LEVO |
|---|---|
| 由来(天然) | 生物種:  |
| 配列 | 文字列: MSLAVLLNKE DKDISDFSKT TAGKSAKKNS RERVADVAPT RVLDKKQAYL SQLNSEFNRI KRRDSIEQLY QDWKFINLQE FELISEWNQQ SKDWQFDNTN DSQDLHFKKL YRDMSMINKE WAEYQSFKNA NLSDIINEKD ADEDEEDDED ELEDGEEDME EDEASTGRHT ...文字列: MSLAVLLNKE DKDISDFSKT TAGKSAKKNS RERVADVAPT RVLDKKQAYL SQLNSEFNRI KRRDSIEQLY QDWKFINLQE FELISEWNQQ SKDWQFDNTN DSQDLHFKKL YRDMSMINKE WAEYQSFKNA NLSDIINEKD ADEDEEDDED ELEDGEEDME EDEASTGRHT NGKSMRGNGI QKSRKKDAAA AAAIGKAIKD DQTHADTVVT VNGDENEDGN NGEDEDNDND NENNNDNDND NENENDNDSD NDDEEENGEE DEEEEEIEDL DEEDFAAFEE QDDNDDEDFN PDVEKRRKRS SSSSSSTKLS MNSLSLITSK KINKNITINS DRPKIVRELI KMCNKNKHQK IKKRRFTNCI VTDYNPIDSK LNIKITLKQY HVKRLKKLIN DAKREREREE ALKNNVGLDG NDLDNDEDGS ESHKRRKLNN NTANGADDAN KRKFNTRHGL PTYGMKMNAK EARAIQRHYD NTYTTIWKDM ARKDSTKMSR LVQQIQSIRS TNFRKTSSLC AREAKKWQSK NFKQIKDFQT RARRGIREMS NFWKKNEREE RDLKKKIEKE AMEQAKKEEE EKESKRQAKK LNFLLTQTEL YSHFIGRKDY KDDDDKGTDY KDDDDK |
-分子 #2: Arp8
| 分子 | 名称: Arp8 / タイプ: protein_or_peptide / ID: 2 / 光学異性体: LEVO |
|---|---|
| 由来(天然) | 生物種:  |
| 配列 | 文字列: MSQEEAESSI IYEEPIDIPL EDDDDEDELE EENSVPLSSQ ADQENAENES DDSVDNVVGS ETPRSVTGLS VDPRDVADEE DEDEEGEDED EDEDDNDVDN EDENDNDNAN ENENELGSSR DKRAPPAVQT SKRYKKYPKL DPAKAPPGKK VPLHLLEKRR LGRIKAAEEF ...文字列: MSQEEAESSI IYEEPIDIPL EDDDDEDELE EENSVPLSSQ ADQENAENES DDSVDNVVGS ETPRSVTGLS VDPRDVADEE DEDEEGEDED EDEDDNDVDN EDENDNDNAN ENENELGSSR DKRAPPAVQT SKRYKKYPKL DPAKAPPGKK VPLHLLEKRR LGRIKAAEEF AKTLKKIGIE KVETTTLPAT GLFQPLMLIN QKNYSSDYLK KDDQIFALRD RKFLRNNNTS QISSTNTPDV IDLKSLPHSE ASAAPLNDEI DLNDPTATIV IHPGSNSIKI GFPKDDHPVV VPNCVAVPKK WLDLENSEHV ENVCLQREQS EEFNNIKSEM EKNFRERMRY YKRKVPGNAH EQVVSFNENS KPEIISEKND PSPIEWIFDD SKLYYGSDAL RCVDEKFVIR KPFRGGSFNV KSPYYKSLAE LISDVTKLLE HALNSETLNV KPTKFNQYKV VLVIPDIFKK SHVETFIRVL LTELQFQAVA IIQESLATCY GAGISTSTCV VNIGAAETRI ACVDEGTVLE HSAITLDYGG DDITRLFALF LLQSDFPLQD WKIDSKHGWL LAERLKKNFT TFQDADVAVQ LYNFMNRSPN QPTEKYEFKL FDEVMLAPLA LFFPQIFKLI RTSSHKNSSL EFQLPESRDL FTNELNDWNS LSQFESKEGN LYCDLNDDLK ILNRILDAHN IIDQLQDKPE NYGNTLKENF APLEKAIVQS IANASITADV TRMNSFYSNI LIVGGSSKIP ALDFILTDRI NIWRPSLLSS ASFPQFYKKL TKEIKDLEGH YVNAPDKTED ENKQILQAQI KEKIVEELEE QHQNIEHQNG NEHIFPVSII PPPRDMNPAL IIWKGASVLA QIKLVEELFI TNSDWDVHGS RILQYKCIFT Y |
-分子 #3: Actin
| 分子 | 名称: Actin / タイプ: protein_or_peptide / ID: 3 / 光学異性体: LEVO |
|---|---|
| 由来(天然) | 生物種:  |
| 配列 | 文字列: MDSEVAALVI DNGSGMCKAG FAGDDAPRAV FPSIVGRPRH QGIMVGMGQK DSYVGDEAQS KRGILTLRYP IEHGIVTNWD DMEKIWHHTF YNELRVAPEE HPVLLTEAPM NPKSNREKMT QIMFETFNVP AFYVSIQAVL SLYSSGRTTG IVLDSGDGVT HVVPIYAGFS ...文字列: MDSEVAALVI DNGSGMCKAG FAGDDAPRAV FPSIVGRPRH QGIMVGMGQK DSYVGDEAQS KRGILTLRYP IEHGIVTNWD DMEKIWHHTF YNELRVAPEE HPVLLTEAPM NPKSNREKMT QIMFETFNVP AFYVSIQAVL SLYSSGRTTG IVLDSGDGVT HVVPIYAGFS LPHAILRIDL AGRDLTDYLM KILSERGYSF STTAEREIVR DIKEKLCYVA LDFEQEMQTA AQSSSIEKSY ELPDGQVITI GNERFRAPEA LFHPSVLGLE SAGIDQTTYN SIMKCDVDVR KELYGNIVMS GGTTMFPGIA ERMQKEITAL APSSMKVKII APPERKYSVW IGGSILASLT TFQQMWISKQ EYDESGPSIV HHKCF |
-分子 #4: Arp4
| 分子 | 名称: Arp4 / タイプ: protein_or_peptide / ID: 4 / 光学異性体: LEVO |
|---|---|
| 由来(天然) | 生物種:  |
| 配列 | 文字列: MSNAALQVYG GDEVSAVVID PGSYTTNIGY SGSDFPQSIL PSVYGKYTAD EGNKKIFSEQ SIGIPRKDYE LKPIIENGLV IDWDTAQEQW QWALQNELYL NSNSGIPALL TEPVWNSTEN RKKSLEVLLE GMQFEACYLA PTSTCVSFAA GRPNCLVVDI GHDTCSVSPI ...文字列: MSNAALQVYG GDEVSAVVID PGSYTTNIGY SGSDFPQSIL PSVYGKYTAD EGNKKIFSEQ SIGIPRKDYE LKPIIENGLV IDWDTAQEQW QWALQNELYL NSNSGIPALL TEPVWNSTEN RKKSLEVLLE GMQFEACYLA PTSTCVSFAA GRPNCLVVDI GHDTCSVSPI VDGMTLSKST RRNFIAGKFI NHLIKKALEP KEIIPLFAIK QRKPEFIKKT FDYEVDKSLY DYANNRGFFQ ECKETLCHIC PTKTLEETKT ELSSTAKRSI ESPWNEEIVF DNETRYGFAE ELFLPKEDDI PANWPRSNSG VVKTWRNDYV PLKRTKPSGV NKSDKKVTPT EEKEQEAVSK STSPAANSAD TPNETGKRPL EEEKPPKENN ELIGLADLVY SSIMSSDVDL RATLAHNVVL TGGTSSIPGL SDRLMTELNK ILPSLKFRIL TTGHTIERQY QSWLGGSILT SLGTFHQLWV GKKEYEEVGV ERLLNDRFR |
-分子 #5: Ies4
| 分子 | 名称: Ies4 / タイプ: protein_or_peptide / ID: 5 / 光学異性体: LEVO |
|---|---|
| 由来(天然) | 生物種:  |
| 配列 | 文字列: MSQESSVLSE SQEQLANNPK IEDTSPPSAN SRDNSKPVLP WDYKNKAIEI KSFSGYKVNF TGWIRRDVRE ERQRGSEFTA SDVKGSDDKA TRKKEPADED PEVKQLEKEG EDGLDS |
-分子 #6: DNA
| 分子 | 名称: DNA / タイプ: dna / ID: 6 / 分類: DNA |
|---|---|
| 由来(天然) | 生物種:  |
| 配列 | 文字列: CTTACCCTGC GTGCCCGCGC ACCCTGGCGA CTTCGCCTCG TTTTGGCGAT TTTCTTAG |
-実験情報
-構造解析
| 手法 | クライオ電子顕微鏡法 |
|---|---|
 解析 解析 | 単粒子再構成法 |
| 試料の集合状態 | particle |
- 試料調製
試料調製
| 緩衝液 | pH: 8 |
|---|---|
| 凍結 | 凍結剤: ETHANE |
- 電子顕微鏡法
電子顕微鏡法
| 顕微鏡 | FEI TITAN KRIOS |
|---|---|
| 撮影 | フィルム・検出器のモデル: GATAN K2 SUMMIT (4k x 4k) 平均電子線量: 44.68 e/Å2 |
| 電子線 | 加速電圧: 300 kV / 電子線源:  FIELD EMISSION GUN FIELD EMISSION GUN |
| 電子光学系 | 照射モード: FLOOD BEAM / 撮影モード: BRIGHT FIELD / 最大 デフォーカス(公称値): 2.9 µm / 最小 デフォーカス(公称値): 1.1 µm |
| 実験機器 |  モデル: Titan Krios / 画像提供: FEI Company |
- 画像解析
画像解析
| 最終 再構成 | 解像度のタイプ: BY AUTHOR / 解像度: 7.5 Å / 解像度の算出法: FSC 0.143 CUT-OFF / 使用した粒子像数: 69226 |
|---|---|
| 初期 角度割当 | タイプ: MAXIMUM LIKELIHOOD |
| 最終 角度割当 | タイプ: MAXIMUM LIKELIHOOD |
 ムービー
ムービー コントローラー
コントローラー























 Z (Sec.)
Z (Sec.) Y (Row.)
Y (Row.) X (Col.)
X (Col.)