+ データを開く
データを開く
- 基本情報
基本情報
| 登録情報 |  | |||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| タイトル | OMCC C1 at 3.28A - Refinement without symmetry of the outer membrane core complex (O- and I-layer) from the fully-assembled R388 type IV secretion system. | |||||||||||||||
 マップデータ マップデータ | OMCC C1 at 3.28 - 3D refinement of the Core Complex (OMCC) without symmetry using all particles - Unsharpened | |||||||||||||||
 試料 試料 |
| |||||||||||||||
 キーワード キーワード | type IV secretion system / type 4 secretion system / T4SS / OMCC / core complex / O-layer / I-layer / R388 plasmid / conjugation / bacterial secretion / secretion / secretion system / protein complex / VirB7 / VirB9 / VirB10 / TrwN / TrwF / TrwE / MEMBRANE PROTEIN | |||||||||||||||
| 生物種 |  | |||||||||||||||
| 手法 | 単粒子再構成法 / クライオ電子顕微鏡法 / 解像度: 3.61 Å | |||||||||||||||
 データ登録者 データ登録者 | Mace K / Vadakkepat AK / Waksman G / Lukoyanova N | |||||||||||||||
| 資金援助 |  英国, 4件 英国, 4件
| |||||||||||||||
 引用 引用 |  ジャーナル: Nature / 年: 2022 ジャーナル: Nature / 年: 2022タイトル: Cryo-EM structure of a type IV secretion system. 著者: Kévin Macé / Abhinav K Vadakkepat / Adam Redzej / Natalya Lukoyanova / Clasien Oomen / Nathalie Braun / Marta Ukleja / Fang Lu / Tiago R D Costa / Elena V Orlova / David Baker / Qian Cong / ...著者: Kévin Macé / Abhinav K Vadakkepat / Adam Redzej / Natalya Lukoyanova / Clasien Oomen / Nathalie Braun / Marta Ukleja / Fang Lu / Tiago R D Costa / Elena V Orlova / David Baker / Qian Cong / Gabriel Waksman /     要旨: Bacterial conjugation is the fundamental process of unidirectional transfer of DNAs, often plasmid DNAs, from a donor cell to a recipient cell. It is the primary means by which antibiotic resistance ...Bacterial conjugation is the fundamental process of unidirectional transfer of DNAs, often plasmid DNAs, from a donor cell to a recipient cell. It is the primary means by which antibiotic resistance genes spread among bacterial populations. In Gram-negative bacteria, conjugation is mediated by a large transport apparatus-the conjugative type IV secretion system (T4SS)-produced by the donor cell and embedded in both its outer and inner membranes. The T4SS also elaborates a long extracellular filament-the conjugative pilus-that is essential for DNA transfer. Here we present a high-resolution cryo-electron microscopy (cryo-EM) structure of a 2.8 megadalton T4SS complex composed of 92 polypeptides representing 8 of the 10 essential T4SS components involved in pilus biogenesis. We added the two remaining components to the structural model using co-evolution analysis of protein interfaces, to enable the reconstitution of the entire system including the pilus. This structure describes the exceptionally large protein-protein interaction network required to assemble the many components that constitute a T4SS and provides insights on the unique mechanism by which they elaborate pili. | |||||||||||||||
| 履歴 |
|
- 構造の表示
構造の表示
| 添付画像 |
|---|
- ダウンロードとリンク
ダウンロードとリンク
-EMDBアーカイブ
| マップデータ |  emd_13765.map.gz emd_13765.map.gz | 50.6 MB |  EMDBマップデータ形式 EMDBマップデータ形式 | |
|---|---|---|---|---|
| ヘッダ (付随情報) |  emd-13765-v30.xml emd-13765-v30.xml emd-13765.xml emd-13765.xml | 23.3 KB 23.3 KB | 表示 表示 |  EMDBヘッダ EMDBヘッダ |
| 画像 |  emd_13765.png emd_13765.png | 105 KB | ||
| マスクデータ |  emd_13765_msk_1.map emd_13765_msk_1.map | 103 MB |  マスクマップ マスクマップ | |
| Filedesc metadata |  emd-13765.cif.gz emd-13765.cif.gz | 4.5 KB | ||
| その他 |  emd_13765_additional_1.map.gz emd_13765_additional_1.map.gz emd_13765_additional_2.map.gz emd_13765_additional_2.map.gz emd_13765_additional_3.map.gz emd_13765_additional_3.map.gz emd_13765_additional_4.map.gz emd_13765_additional_4.map.gz emd_13765_half_map_1.map.gz emd_13765_half_map_1.map.gz emd_13765_half_map_2.map.gz emd_13765_half_map_2.map.gz | 58.9 MB 97.2 MB 51.5 MB 97 MB 95.5 MB 95.5 MB | ||
| アーカイブディレクトリ |  http://ftp.pdbj.org/pub/emdb/structures/EMD-13765 http://ftp.pdbj.org/pub/emdb/structures/EMD-13765 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-13765 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-13765 | HTTPS FTP |
-検証レポート
| 文書・要旨 |  emd_13765_validation.pdf.gz emd_13765_validation.pdf.gz | 788 KB | 表示 |  EMDB検証レポート EMDB検証レポート |
|---|---|---|---|---|
| 文書・詳細版 |  emd_13765_full_validation.pdf.gz emd_13765_full_validation.pdf.gz | 787.5 KB | 表示 | |
| XML形式データ |  emd_13765_validation.xml.gz emd_13765_validation.xml.gz | 13.5 KB | 表示 | |
| CIF形式データ |  emd_13765_validation.cif.gz emd_13765_validation.cif.gz | 15.8 KB | 表示 | |
| アーカイブディレクトリ |  https://ftp.pdbj.org/pub/emdb/validation_reports/EMD-13765 https://ftp.pdbj.org/pub/emdb/validation_reports/EMD-13765 ftp://ftp.pdbj.org/pub/emdb/validation_reports/EMD-13765 ftp://ftp.pdbj.org/pub/emdb/validation_reports/EMD-13765 | HTTPS FTP |
-関連構造データ
- リンク
リンク
| EMDBのページ |  EMDB (EBI/PDBe) / EMDB (EBI/PDBe) /  EMDataResource EMDataResource |
|---|
- マップ
マップ
| ファイル |  ダウンロード / ファイル: emd_13765.map.gz / 形式: CCP4 / 大きさ: 103 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) ダウンロード / ファイル: emd_13765.map.gz / 形式: CCP4 / 大きさ: 103 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) | ||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | OMCC C1 at 3.28 - 3D refinement of the Core Complex (OMCC) without symmetry using all particles - Unsharpened | ||||||||||||||||||||||||||||||||||||
| 投影像・断面図 | 画像のコントロール
画像は Spider により作成 | ||||||||||||||||||||||||||||||||||||
| ボクセルのサイズ | X=Y=Z: 1.067 Å | ||||||||||||||||||||||||||||||||||||
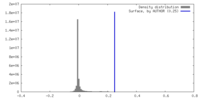
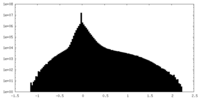
| 密度 |
| ||||||||||||||||||||||||||||||||||||
| 対称性 | 空間群: 1 | ||||||||||||||||||||||||||||||||||||
| 詳細 | EMDB XML:
|
-添付データ
-マスク #1
| ファイル |  emd_13765_msk_1.map emd_13765_msk_1.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 投影像・断面図 |
| ||||||||||||
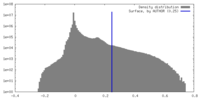
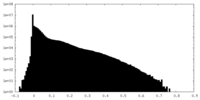
| 密度ヒストグラム |
-追加マップ: Original Ab initio OMCC - Ab initio reconstruction...
| ファイル | emd_13765_additional_1.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | Original Ab initio OMCC - Ab initio reconstruction without symmetry from 100,000 particles | ||||||||||||
| 投影像・断面図 |
| ||||||||||||
| 密度ヒストグラム |
-追加マップ: Ab initio model for OMCC C1 - 3D...
| ファイル | emd_13765_additional_2.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | Ab initio model for OMCC C1 - 3D refinement using original ab initio as initial model, without symmetry from 100,000 particles - Sharpened | ||||||||||||
| 投影像・断面図 |
| ||||||||||||
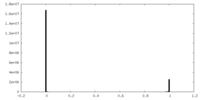
| 密度ヒストグラム |
-追加マップ: Ab initio model for OMCC C1 - 3D...
| ファイル | emd_13765_additional_3.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | Ab initio model for OMCC C1 - 3D refinement using original ab initio as initial model, without symmetry from 100,000 particles - Unsharpened | ||||||||||||
| 投影像・断面図 |
| ||||||||||||
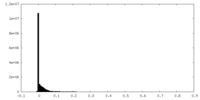
| 密度ヒストグラム |
-追加マップ: OMCC C1 at 3.28 - 3D refinement of...
| ファイル | emd_13765_additional_4.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | OMCC C1 at 3.28 - 3D refinement of the Core Complex (OMCC) without symmetry using all particles - Sharpened | ||||||||||||
| 投影像・断面図 |
| ||||||||||||
| 密度ヒストグラム |
-ハーフマップ: OMCC C1 at 3.28 - Half-A
| ファイル | emd_13765_half_map_1.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | OMCC C1 at 3.28 - Half-A | ||||||||||||
| 投影像・断面図 |
| ||||||||||||
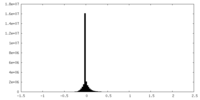
| 密度ヒストグラム |
-ハーフマップ: OMCC C1 at 3.28 - Half-B
| ファイル | emd_13765_half_map_2.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | OMCC C1 at 3.28 - Half-B | ||||||||||||
| 投影像・断面図 |
| ||||||||||||
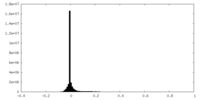
| 密度ヒストグラム |
- 試料の構成要素
試料の構成要素
-全体 : Type IV secretion system complex
| 全体 | 名称: Type IV secretion system complex |
|---|---|
| 要素 |
|
-超分子 #1: Type IV secretion system complex
| 超分子 | 名称: Type IV secretion system complex / タイプ: complex / ID: 1 / 親要素: 0 / 含まれる分子: #1-#3 |
|---|---|
| 由来(天然) | 生物種:  |
| 分子量 | 理論値: 2.808 MDa |
-実験情報
-構造解析
| 手法 | クライオ電子顕微鏡法 |
|---|---|
 解析 解析 | 単粒子再構成法 |
| 試料の集合状態 | particle |
- 試料調製
試料調製
| 緩衝液 | pH: 7.6 |
|---|---|
| 凍結 | 凍結剤: ETHANE |
- 電子顕微鏡法
電子顕微鏡法
| 顕微鏡 | FEI TITAN KRIOS |
|---|---|
| 撮影 | フィルム・検出器のモデル: GATAN K3 (6k x 4k) / 平均電子線量: 57.5 e/Å2 |
| 電子線 | 加速電圧: 300 kV / 電子線源:  FIELD EMISSION GUN FIELD EMISSION GUN |
| 電子光学系 | 照射モード: OTHER / 撮影モード: OTHER / 最大 デフォーカス(公称値): 3.0 µm / 最小 デフォーカス(公称値): 1.5 µm |
| 実験機器 |  モデル: Titan Krios / 画像提供: FEI Company |
- 画像解析
画像解析
| 初期モデル | モデルのタイプ: OTHER / 詳細: CryoSPARC ab-initio |
|---|---|
| 最終 再構成 | 解像度のタイプ: BY AUTHOR / 解像度: 3.61 Å / 解像度の算出法: FSC 0.143 CUT-OFF / 使用した粒子像数: 349413 |
| 初期 角度割当 | タイプ: MAXIMUM LIKELIHOOD |
| 最終 角度割当 | タイプ: OTHER / 詳細: Stochastic gradient descent (SGD) |
 ムービー
ムービー コントローラー
コントローラー






















 Z (Sec.)
Z (Sec.) Y (Row.)
Y (Row.) X (Col.)
X (Col.)