+ データを開く
データを開く
- 基本情報
基本情報
| 登録情報 |  | |||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| タイトル | Structure of MCM2-7 DH complexed with Cdc7-Dbf4 in the presence of ADP:BeF3, state I (composite map) | |||||||||||||||
 マップデータ マップデータ | Composite map of MD-(ADP:BeF3) state I | |||||||||||||||
 試料 試料 |
| |||||||||||||||
 キーワード キーワード | Helicase / Activation / Kinase / Phosphorylation / REPLICATION | |||||||||||||||
| 機能・相同性 |  機能・相同性情報 機能・相同性情報positive regulation of spindle attachment to meiosis I kinetochore / positive regulation of meiotic DNA double-strand break formation involved in reciprocal meiotic recombination / positive regulation of DNA replication initiation / positive regulation of kinetochore assembly / positive regulation of meiotic DNA double-strand break formation / negative regulation of exit from mitosis / Dbf4-dependent protein kinase complex / positive regulation of protein localization to kinetochore / positive regulation of meiosis I / positive regulation of nuclear cell cycle DNA replication ...positive regulation of spindle attachment to meiosis I kinetochore / positive regulation of meiotic DNA double-strand break formation involved in reciprocal meiotic recombination / positive regulation of DNA replication initiation / positive regulation of kinetochore assembly / positive regulation of meiotic DNA double-strand break formation / negative regulation of exit from mitosis / Dbf4-dependent protein kinase complex / positive regulation of protein localization to kinetochore / positive regulation of meiosis I / positive regulation of nuclear cell cycle DNA replication / regulation of cell cycle phase transition / MCM core complex / Assembly of the pre-replicative complex / Switching of origins to a post-replicative state / MCM complex binding / mitotic DNA replication preinitiation complex assembly / nuclear DNA replication / premeiotic DNA replication / replication fork protection complex / pre-replicative complex assembly involved in nuclear cell cycle DNA replication / mitotic DNA replication / Activation of the pre-replicative complex / CMG complex / nuclear pre-replicative complex / Activation of ATR in response to replication stress / DNA replication preinitiation complex / protein-containing complex localization / MCM complex / mitotic DNA replication checkpoint signaling / double-strand break repair via break-induced replication / mitotic DNA replication initiation / single-stranded DNA helicase activity / regulation of DNA-templated DNA replication initiation / silent mating-type cassette heterochromatin formation / DNA strand elongation involved in DNA replication / nuclear replication fork / DNA replication origin binding / chromosome, centromeric region / DNA replication initiation / subtelomeric heterochromatin formation / DNA helicase activity / protein serine/threonine kinase activator activity / chromosome segregation / transcription elongation by RNA polymerase II / helicase activity / heterochromatin formation / single-stranded DNA binding / DNA helicase / chromosome, telomeric region / DNA replication / non-specific serine/threonine protein kinase / cell division / protein serine kinase activity / protein serine/threonine kinase activity / centrosome / DNA damage response / chromatin binding / chromatin / signal transduction / ATP hydrolysis activity / zinc ion binding / nucleoplasm / ATP binding / metal ion binding / identical protein binding / nucleus / cytoplasm 類似検索 - 分子機能 | |||||||||||||||
| 生物種 |  | |||||||||||||||
| 手法 | 単粒子再構成法 / クライオ電子顕微鏡法 / 解像度: 3.8 Å | |||||||||||||||
 データ登録者 データ登録者 | Saleh A / Noguchi Y | |||||||||||||||
| 資金援助 |  英国, 4件 英国, 4件
| |||||||||||||||
 引用 引用 |  ジャーナル: Nat Commun / 年: 2022 ジャーナル: Nat Commun / 年: 2022タイトル: The structural basis of Cdc7-Dbf4 kinase dependent targeting and phosphorylation of the MCM2-7 double hexamer. 著者: Almutasem Saleh / Yasunori Noguchi / Ricardo Aramayo / Marina E Ivanova / Kathryn M Stevens / Alex Montoya / S Sunidhi / Nicolas Lopez Carranza / Marcin J Skwark / Christian Speck /  要旨: The controlled assembly of replication forks is critical for genome stability. The Dbf4-dependent Cdc7 kinase (DDK) initiates replisome assembly by phosphorylating the MCM2-7 replicative helicase at ...The controlled assembly of replication forks is critical for genome stability. The Dbf4-dependent Cdc7 kinase (DDK) initiates replisome assembly by phosphorylating the MCM2-7 replicative helicase at the N-terminal tails of Mcm2, Mcm4 and Mcm6. At present, it remains poorly understood how DDK docks onto the helicase and how the kinase targets distal Mcm subunits for phosphorylation. Using cryo-electron microscopy and biochemical analysis we discovered that an interaction between the HBRCT domain of Dbf4 with Mcm2 serves as an anchoring point, which supports binding of DDK across the MCM2-7 double-hexamer interface and phosphorylation of Mcm4 on the opposite hexamer. Moreover, a rotation of DDK along its anchoring point allows phosphorylation of Mcm2 and Mcm6. In summary, our work provides fundamental insights into DDK structure, control and selective activation of the MCM2-7 helicase during DNA replication. Importantly, these insights can be exploited for development of novel DDK inhibitors. | |||||||||||||||
| 履歴 |
|
- 構造の表示
構造の表示
| 添付画像 |
|---|
- ダウンロードとリンク
ダウンロードとリンク
-EMDBアーカイブ
| マップデータ |  emd_13620.map.gz emd_13620.map.gz | 162.5 MB |  EMDBマップデータ形式 EMDBマップデータ形式 | |
|---|---|---|---|---|
| ヘッダ (付随情報) |  emd-13620-v30.xml emd-13620-v30.xml emd-13620.xml emd-13620.xml | 30.2 KB 30.2 KB | 表示 表示 |  EMDBヘッダ EMDBヘッダ |
| 画像 |  emd_13620.png emd_13620.png | 72.3 KB | ||
| マスクデータ |  emd_13620_msk_1.map emd_13620_msk_1.map | 178 MB |  マスクマップ マスクマップ | |
| Filedesc metadata |  emd-13620.cif.gz emd-13620.cif.gz | 10.8 KB | ||
| アーカイブディレクトリ |  http://ftp.pdbj.org/pub/emdb/structures/EMD-13620 http://ftp.pdbj.org/pub/emdb/structures/EMD-13620 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-13620 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-13620 | HTTPS FTP |
-検証レポート
| 文書・要旨 |  emd_13620_validation.pdf.gz emd_13620_validation.pdf.gz | 653.5 KB | 表示 |  EMDB検証レポート EMDB検証レポート |
|---|---|---|---|---|
| 文書・詳細版 |  emd_13620_full_validation.pdf.gz emd_13620_full_validation.pdf.gz | 653.1 KB | 表示 | |
| XML形式データ |  emd_13620_validation.xml.gz emd_13620_validation.xml.gz | 6.9 KB | 表示 | |
| CIF形式データ |  emd_13620_validation.cif.gz emd_13620_validation.cif.gz | 7.8 KB | 表示 | |
| アーカイブディレクトリ |  https://ftp.pdbj.org/pub/emdb/validation_reports/EMD-13620 https://ftp.pdbj.org/pub/emdb/validation_reports/EMD-13620 ftp://ftp.pdbj.org/pub/emdb/validation_reports/EMD-13620 ftp://ftp.pdbj.org/pub/emdb/validation_reports/EMD-13620 | HTTPS FTP |
-関連構造データ
| 関連構造データ |  7pt7MC  7pt6C M: このマップから作成された原子モデル C: 同じ文献を引用 ( |
|---|---|
| 類似構造データ | 類似検索 - 機能・相同性  F&H 検索 F&H 検索 |
- リンク
リンク
| EMDBのページ |  EMDB (EBI/PDBe) / EMDB (EBI/PDBe) /  EMDataResource EMDataResource |
|---|---|
| 「今月の分子」の関連する項目 |
- マップ
マップ
| ファイル |  ダウンロード / ファイル: emd_13620.map.gz / 形式: CCP4 / 大きさ: 178 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) ダウンロード / ファイル: emd_13620.map.gz / 形式: CCP4 / 大きさ: 178 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) | ||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | Composite map of MD-(ADP:BeF3) state I | ||||||||||||||||||||||||||||||||||||
| 投影像・断面図 | 画像のコントロール
画像は Spider により作成 | ||||||||||||||||||||||||||||||||||||
| ボクセルのサイズ | X=Y=Z: 1.072 Å | ||||||||||||||||||||||||||||||||||||
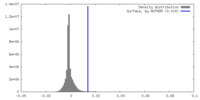
| 密度 |
| ||||||||||||||||||||||||||||||||||||
| 対称性 | 空間群: 1 | ||||||||||||||||||||||||||||||||||||
| 詳細 | EMDB XML:
|
-添付データ
-マスク #1
| ファイル |  emd_13620_msk_1.map emd_13620_msk_1.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 投影像・断面図 |
| ||||||||||||
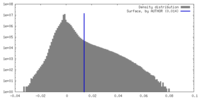
| 密度ヒストグラム |
- 試料の構成要素
試料の構成要素
+全体 : MCM2-7 double hexamer bound to one copy of Cdc7-Dbf4
+超分子 #1: MCM2-7 double hexamer bound to one copy of Cdc7-Dbf4
+分子 #1: Undefined Mcm4 flexible N-terminal tail
+分子 #2: DNA replication licensing factor MCM2
+分子 #3: DNA replication licensing factor MCM3
+分子 #4: DNA replication licensing factor MCM4
+分子 #5: Minichromosome maintenance protein 5
+分子 #6: DNA replication licensing factor MCM6
+分子 #7: DNA replication licensing factor MCM7
+分子 #8: Cell division control protein 7
+分子 #9: DDK kinase regulatory subunit DBF4
+分子 #10: ADENOSINE-5'-DIPHOSPHATE
+分子 #11: MAGNESIUM ION
+分子 #12: ZINC ION
+分子 #13: BERYLLIUM TRIFLUORIDE ION
-実験情報
-構造解析
| 手法 | クライオ電子顕微鏡法 |
|---|---|
 解析 解析 | 単粒子再構成法 |
| 試料の集合状態 | particle |
- 試料調製
試料調製
| 緩衝液 | pH: 7.5 |
|---|---|
| グリッド | モデル: Quantifoil R2/2 / 材質: COPPER / メッシュ: 300 / 支持フィルム - 材質: CARBON / 支持フィルム - トポロジー: CONTINUOUS / 支持フィルム - Film thickness: 2 / 前処理 - タイプ: GLOW DISCHARGE / 前処理 - 時間: 25 sec. / 前処理 - 雰囲気: AIR / 詳細: 15 mA |
| 凍結 | 凍結剤: ETHANE / チャンバー内湿度: 100 % / チャンバー内温度: 277 K / 装置: FEI VITROBOT MARK IV / 詳細: blot for 1.5 seconds and blot force +2. |
- 電子顕微鏡法
電子顕微鏡法
| 顕微鏡 | FEI TITAN KRIOS |
|---|---|
| 撮影 | フィルム・検出器のモデル: GATAN K3 (6k x 4k) / 実像数: 13470 / 平均電子線量: 48.4 e/Å2 |
| 電子線 | 加速電圧: 300 kV / 電子線源:  FIELD EMISSION GUN FIELD EMISSION GUN |
| 電子光学系 | 照射モード: FLOOD BEAM / 撮影モード: BRIGHT FIELD / Cs: 2.7 mm / 倍率(公称値): 81000 |
| 試料ステージ | 試料ホルダーモデル: FEI TITAN KRIOS AUTOGRID HOLDER ホルダー冷却材: NITROGEN |
| 実験機器 |  モデル: Titan Krios / 画像提供: FEI Company |
- 画像解析
画像解析
| 初期モデル | モデルのタイプ: INSILICO MODEL In silico モデル: An ab initio initial model was generated using RELION |
|---|---|
| 最終 再構成 | 想定した対称性 - 点群: C1 (非対称) / 解像度のタイプ: BY AUTHOR / 解像度: 3.8 Å / 解像度の算出法: FSC 0.143 CUT-OFF / ソフトウェア: (名称: RELION, PHENIX) 詳細: Multi-body auto-refined maps were combined to generate a composite map using an atomic model (derived from MD-(ADP:BeF3) state I), with the program combine_focused_maps in Phenix 使用した粒子像数: 30807 |
| 初期 角度割当 | タイプ: MAXIMUM LIKELIHOOD / ソフトウェア - 名称: RELION |
| 最終 角度割当 | タイプ: MAXIMUM LIKELIHOOD / ソフトウェア - 名称: RELION |
 ムービー
ムービー コントローラー
コントローラー































 X (Sec.)
X (Sec.) Y (Row.)
Y (Row.) Z (Col.)
Z (Col.)