+ データを開く
データを開く
- 基本情報
基本情報
| 登録情報 | データベース: EMDB / ID: EMD-10539 | |||||||||
|---|---|---|---|---|---|---|---|---|---|---|
| タイトル | Processive human polymerase delta holoenzyme | |||||||||
 マップデータ マップデータ | ||||||||||
 試料 試料 |
| |||||||||
 キーワード キーワード | Protein / REPLICATION | |||||||||
| 機能・相同性 |  機能・相同性情報 機能・相同性情報delta DNA polymerase complex / DNA synthesis involved in UV-damage excision repair / zeta DNA polymerase complex / nucleotide-excision repair complex / Cytosolic iron-sulfur cluster assembly / dinucleotide insertion or deletion binding / PCNA-p21 complex / mitotic telomere maintenance via semi-conservative replication / purine-specific mismatch base pair DNA N-glycosylase activity / nucleotide-excision repair, DNA gap filling ...delta DNA polymerase complex / DNA synthesis involved in UV-damage excision repair / zeta DNA polymerase complex / nucleotide-excision repair complex / Cytosolic iron-sulfur cluster assembly / dinucleotide insertion or deletion binding / PCNA-p21 complex / mitotic telomere maintenance via semi-conservative replication / purine-specific mismatch base pair DNA N-glycosylase activity / nucleotide-excision repair, DNA gap filling / nuclear lamina / Polymerase switching / Processive synthesis on the lagging strand / DNA replication proofreading / MutLalpha complex binding / PCNA complex / 3'-5'-DNA exonuclease activity / Telomere C-strand (Lagging Strand) Synthesis / Removal of the Flap Intermediate / Mismatch repair (MMR) directed by MSH2:MSH3 (MutSbeta) / Mismatch repair (MMR) directed by MSH2:MSH6 (MutSalpha) / Transcription of E2F targets under negative control by DREAM complex / Polymerase switching on the C-strand of the telomere / Processive synthesis on the C-strand of the telomere / replisome / Removal of the Flap Intermediate from the C-strand / response to L-glutamate / aggresome / 加水分解酵素; エステル加水分解酵素; 5'-リン酸モノエステル産生エンドデオキシリボヌクレアーゼ / error-free translesion synthesis / response to dexamethasone / DNA biosynthetic process / DNA strand elongation involved in DNA replication / histone acetyltransferase binding / leading strand elongation / G1/S-Specific Transcription / DNA polymerase processivity factor activity / DNA synthesis involved in DNA repair / nuclear replication fork / replication fork processing / SUMOylation of DNA replication proteins / PCNA-Dependent Long Patch Base Excision Repair / error-prone translesion synthesis / fatty acid homeostasis / response to cadmium ion / estrous cycle / mismatch repair / response to UV / cyclin-dependent protein kinase holoenzyme complex / translesion synthesis / base-excision repair, gap-filling / DNA polymerase binding / epithelial cell differentiation / positive regulation of endothelial cell proliferation / liver regeneration / TP53 Regulates Transcription of Genes Involved in G2 Cell Cycle Arrest / positive regulation of DNA replication / nuclear estrogen receptor binding / positive regulation of DNA repair / replication fork / Translesion synthesis by REV1 / Translesion synthesis by POLK / Translesion synthesis by POLI / male germ cell nucleus / Gap-filling DNA repair synthesis and ligation in GG-NER / Termination of translesion DNA synthesis / Translesion Synthesis by POLH / Recognition of DNA damage by PCNA-containing replication complex / receptor tyrosine kinase binding / DNA-templated DNA replication / HDR through Homologous Recombination (HRR) / cellular response to xenobiotic stimulus / Dual Incision in GG-NER / cellular response to hydrogen peroxide / Dual incision in TC-NER / Gap-filling DNA repair synthesis and ligation in TC-NER / cellular response to UV / response to estradiol / E3 ubiquitin ligases ubiquitinate target proteins / heart development / chromatin organization / 4 iron, 4 sulfur cluster binding / DNA-directed DNA polymerase / damaged DNA binding / DNA-directed DNA polymerase activity / protein-macromolecule adaptor activity / chromosome, telomeric region / DNA replication / nuclear body / nucleotide binding / DNA repair / chromatin binding / centrosome / chromatin / protein-containing complex binding / enzyme binding / negative regulation of transcription by RNA polymerase II / DNA binding / extracellular exosome / zinc ion binding 類似検索 - 分子機能 | |||||||||
| 生物種 |  Homo sapiens (ヒト) / synthetic construct (人工物) Homo sapiens (ヒト) / synthetic construct (人工物) | |||||||||
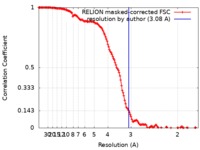
| 手法 | 単粒子再構成法 / クライオ電子顕微鏡法 / 解像度: 3.08 Å | |||||||||
 データ登録者 データ登録者 | Lancey C / Hamdan SM | |||||||||
| 資金援助 |  英国, 1件 英国, 1件
| |||||||||
 引用 引用 |  ジャーナル: Nat Commun / 年: 2020 ジャーナル: Nat Commun / 年: 2020タイトル: Structure of the processive human Pol δ holoenzyme. 著者: Claudia Lancey / Muhammad Tehseen / Vlad-Stefan Raducanu / Fahad Rashid / Nekane Merino / Timothy J Ragan / Christos G Savva / Manal S Zaher / Afnan Shirbini / Francisco J Blanco / Samir M ...著者: Claudia Lancey / Muhammad Tehseen / Vlad-Stefan Raducanu / Fahad Rashid / Nekane Merino / Timothy J Ragan / Christos G Savva / Manal S Zaher / Afnan Shirbini / Francisco J Blanco / Samir M Hamdan / Alfredo De Biasio /    要旨: In eukaryotes, DNA polymerase δ (Pol δ) bound to the proliferating cell nuclear antigen (PCNA) replicates the lagging strand and cooperates with flap endonuclease 1 (FEN1) to process the Okazaki ...In eukaryotes, DNA polymerase δ (Pol δ) bound to the proliferating cell nuclear antigen (PCNA) replicates the lagging strand and cooperates with flap endonuclease 1 (FEN1) to process the Okazaki fragments for their ligation. We present the high-resolution cryo-EM structure of the human processive Pol δ-DNA-PCNA complex in the absence and presence of FEN1. Pol δ is anchored to one of the three PCNA monomers through the C-terminal domain of the catalytic subunit. The catalytic core sits on top of PCNA in an open configuration while the regulatory subunits project laterally. This arrangement allows PCNA to thread and stabilize the DNA exiting the catalytic cleft and recruit FEN1 to one unoccupied monomer in a toolbelt fashion. Alternative holoenzyme conformations reveal important functional interactions that maintain PCNA orientation during synthesis. This work sheds light on the structural basis of Pol δ's activity in replicating the human genome. | |||||||||
| 履歴 |
|
- 構造の表示
構造の表示
| ムービー |
 ムービービューア ムービービューア |
|---|---|
| 構造ビューア | EMマップ:  SurfView SurfView Molmil Molmil Jmol/JSmol Jmol/JSmol |
| 添付画像 |
- ダウンロードとリンク
ダウンロードとリンク
-EMDBアーカイブ
| マップデータ |  emd_10539.map.gz emd_10539.map.gz | 15.3 MB |  EMDBマップデータ形式 EMDBマップデータ形式 | |
|---|---|---|---|---|
| ヘッダ (付随情報) |  emd-10539-v30.xml emd-10539-v30.xml emd-10539.xml emd-10539.xml | 30 KB 30 KB | 表示 表示 |  EMDBヘッダ EMDBヘッダ |
| FSC (解像度算出) |  emd_10539_fsc.xml emd_10539_fsc.xml | 14.2 KB | 表示 |  FSCデータファイル FSCデータファイル |
| 画像 |  emd_10539.png emd_10539.png | 58.4 KB | ||
| Filedesc metadata |  emd-10539.cif.gz emd-10539.cif.gz | 9.3 KB | ||
| アーカイブディレクトリ |  http://ftp.pdbj.org/pub/emdb/structures/EMD-10539 http://ftp.pdbj.org/pub/emdb/structures/EMD-10539 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-10539 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-10539 | HTTPS FTP |
-関連構造データ
| 関連構造データ |  6tnyMC  6s1mC  6s1nC  6s1oC  6tnzC C: 同じ文献を引用 ( M: このマップから作成された原子モデル |
|---|---|
| 類似構造データ | |
| 電子顕微鏡画像生データ |  EMPIAR-10823 (タイトル: Cryo electron micrographs of Pol delta-PCNA-DNA-FEN1 sample EMPIAR-10823 (タイトル: Cryo electron micrographs of Pol delta-PCNA-DNA-FEN1 sampleData size: 1.6 TB Data #1: Cryo-electron micrographs of Pol delta-FEN1 toolbelt [micrographs - multiframe]) |
- リンク
リンク
| EMDBのページ |  EMDB (EBI/PDBe) / EMDB (EBI/PDBe) /  EMDataResource EMDataResource |
|---|---|
| 「今月の分子」の関連する項目 |
- マップ
マップ
| ファイル |  ダウンロード / ファイル: emd_10539.map.gz / 形式: CCP4 / 大きさ: 244.1 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) ダウンロード / ファイル: emd_10539.map.gz / 形式: CCP4 / 大きさ: 244.1 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 投影像・断面図 | 画像のコントロール
画像は Spider により作成 | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| ボクセルのサイズ | X=Y=Z: 0.87 Å | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 密度 |
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 対称性 | 空間群: 1 | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 詳細 | EMDB XML:
CCP4マップ ヘッダ情報:
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
-添付データ
- 試料の構成要素
試料の構成要素
+全体 : Toolbelt
+超分子 #1: Toolbelt
+超分子 #2: DNA polymerase
+超分子 #3: Proliferating cell nuclear antigen
+超分子 #4: DNA primer, template
+分子 #1: DNA polymerase delta catalytic subunit
+分子 #2: DNA polymerase delta subunit 2
+分子 #3: DNA polymerase delta subunit 3
+分子 #4: DNA polymerase delta subunit 4
+分子 #5: Proliferating cell nuclear antigen
+分子 #6: DNA primer
+分子 #7: DNA template
+分子 #8: ZINC ION
+分子 #9: IRON/SULFUR CLUSTER
+分子 #10: THYMIDINE-5'-TRIPHOSPHATE
-実験情報
-構造解析
| 手法 | クライオ電子顕微鏡法 |
|---|---|
 解析 解析 | 単粒子再構成法 |
| 試料の集合状態 | particle |
- 試料調製
試料調製
| 緩衝液 | pH: 7.5 構成要素:
| |||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| グリッド | モデル: Quantifoil, UltrAuFoil, R1.2/1.3 / 材質: GOLD / メッシュ: 300 / 支持フィルム - 材質: GRAPHENE OXIDE / 支持フィルム - トポロジー: CONTINUOUS / 前処理 - タイプ: GLOW DISCHARGE / 前処理 - 時間: 300 sec. | |||||||||||||||||||||
| 凍結 | 凍結剤: ETHANE / チャンバー内湿度: 100 % / チャンバー内温度: 277 K / 装置: FEI VITROBOT MARK IV | |||||||||||||||||||||
| 詳細 | Complex separated by gel filtration |
- 電子顕微鏡法
電子顕微鏡法
| 顕微鏡 | FEI TITAN KRIOS |
|---|---|
| 温度 | 最低: 77.0 K / 最高: 77.0 K |
| 撮影 | フィルム・検出器のモデル: GATAN K3 BIOQUANTUM (6k x 4k) デジタル化 - サイズ - 横: 11520 pixel / デジタル化 - サイズ - 縦: 8184 pixel / 撮影したグリッド数: 1 / 実像数: 5071 / 平均露光時間: 3.0 sec. / 平均電子線量: 44.0 e/Å2 / 詳細: Data were collected in super resolution mode |
| 電子線 | 加速電圧: 300 kV / 電子線源:  FIELD EMISSION GUN FIELD EMISSION GUN |
| 電子光学系 | C2レンズ絞り径: 50.0 µm / 倍率(補正後): 57471 / 照射モード: FLOOD BEAM / 撮影モード: BRIGHT FIELD / Cs: 2.7 mm 最大 デフォーカス(公称値): 2.3000000000000003 µm 最小 デフォーカス(公称値): 1.1 µm / 倍率(公称値): 105000 |
| 試料ステージ | 試料ホルダーモデル: FEI TITAN KRIOS AUTOGRID HOLDER ホルダー冷却材: NITROGEN |
| 実験機器 |  モデル: Titan Krios / 画像提供: FEI Company |
 ムービー
ムービー コントローラー
コントローラー

































 Z (Sec.)
Z (Sec.) Y (Row.)
Y (Row.) X (Col.)
X (Col.)