+ データを開く
データを開く
- 基本情報
基本情報
| 登録情報 | データベース: PDB / ID: 9oa8 | ||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
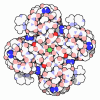
| タイトル | Cryo-EM structure of KCa3.1/calmodulin channel in complex with NS309 | ||||||||||||||||||||||||||||||||||||
 要素 要素 |
| ||||||||||||||||||||||||||||||||||||
 キーワード キーワード | TRANSPORT PROTEIN / Ion channel / Intermediate conductance calcium-activated potassium channel / Calmodulin binding protein | ||||||||||||||||||||||||||||||||||||
| 機能・相同性 |  機能・相同性情報 機能・相同性情報intermediate conductance calcium-activated potassium channel activity / saliva secretion / small conductance calcium-activated potassium channel activity / stabilization of membrane potential / Ca2+ activated K+ channels / macropinocytosis / calcium-activated potassium channel activity / transporter inhibitor activity / regulation of calcium ion import across plasma membrane / : ...intermediate conductance calcium-activated potassium channel activity / saliva secretion / small conductance calcium-activated potassium channel activity / stabilization of membrane potential / Ca2+ activated K+ channels / macropinocytosis / calcium-activated potassium channel activity / transporter inhibitor activity / regulation of calcium ion import across plasma membrane / : / positive regulation of potassium ion transmembrane transport / positive regulation of T cell receptor signaling pathway / type 3 metabotropic glutamate receptor binding / establishment of protein localization to membrane / cell volume homeostasis / phospholipid translocation / negative regulation of ryanodine-sensitive calcium-release channel activity / organelle localization by membrane tethering / response to corticosterone / mitochondrion-endoplasmic reticulum membrane tethering / autophagosome membrane docking / regulation of synaptic vesicle exocytosis / negative regulation of calcium ion export across plasma membrane / regulation of ryanodine-sensitive calcium-release channel activity / regulation of cardiac muscle cell action potential / presynaptic endocytosis / calcineurin-mediated signaling / nitric-oxide synthase binding / regulation of cell communication by electrical coupling involved in cardiac conduction / adenylate cyclase binding / protein phosphatase activator activity / regulation of synaptic vesicle endocytosis / immune system process / potassium channel activity / detection of calcium ion / regulation of cardiac muscle contraction / postsynaptic cytosol / cell surface receptor signaling pathway via JAK-STAT / catalytic complex / phosphatidylinositol 3-kinase binding / calcium channel inhibitor activity / presynaptic cytosol / cellular response to interferon-beta / regulation of release of sequestered calcium ion into cytosol by sarcoplasmic reticulum / titin binding / regulation of calcium-mediated signaling / regulation of cardiac muscle contraction by regulation of the release of sequestered calcium ion / voltage-gated potassium channel complex / potassium ion transmembrane transport / calcium channel complex / regulation of heart rate / establishment of localization in cell / calyx of Held / nitric-oxide synthase regulator activity / adenylate cyclase activator activity / positive regulation of protein secretion / response to amphetamine / regulation of cytokinesis / sarcomere / protein serine/threonine kinase activator activity / spindle microtubule / positive regulation of receptor signaling pathway via JAK-STAT / calcium channel regulator activity / potassium ion transport / defense response / response to calcium ion / cellular response to type II interferon / G2/M transition of mitotic cell cycle / Schaffer collateral - CA1 synapse / ruffle membrane / spindle pole / calcium-dependent protein binding / calcium ion transport / myelin sheath / synaptic vesicle membrane / growth cone / sperm midpiece / protein phosphatase binding / vesicle / protein homotetramerization / transmembrane transporter binding / calmodulin binding / neuron projection / protein domain specific binding / neuronal cell body / calcium ion binding / centrosome / protein kinase binding / chromatin / protein homodimerization activity / protein-containing complex / mitochondrion / nucleoplasm / membrane / nucleus / plasma membrane / cytoplasm / cytosol 類似検索 - 分子機能 | ||||||||||||||||||||||||||||||||||||
| 生物種 |  Homo sapiens (ヒト) Homo sapiens (ヒト) | ||||||||||||||||||||||||||||||||||||
| 手法 | 電子顕微鏡法 / 単粒子再構成法 / クライオ電子顕微鏡法 / 解像度: 3.59 Å | ||||||||||||||||||||||||||||||||||||
 データ登録者 データ登録者 | Nam, Y.W. / Zhang, M. | ||||||||||||||||||||||||||||||||||||
| 資金援助 |  米国, 4件 米国, 4件
| ||||||||||||||||||||||||||||||||||||
 引用 引用 |  ジャーナル: Nat Commun / 年: 2026 ジャーナル: Nat Commun / 年: 2026タイトル: Structural basis for the subtype-selectivity of K2.2 channel activators. 著者: Young-Woo Nam / Alena Ramanishka / Yang Xu / Rose Marie Haynes Yasuda / Joshua A Nasburg / Dohyun Im / Meng Cui / K George Chandy / Heike Wulff / Miao Zhang /    要旨: Small-conductance (K2.2) and intermediate-conductance (K3.1) Ca-activated K channels are gated by a Ca-calmodulin dependent mechanism. NS309 potentiates the activity of both K2.2 and K3.1, while ...Small-conductance (K2.2) and intermediate-conductance (K3.1) Ca-activated K channels are gated by a Ca-calmodulin dependent mechanism. NS309 potentiates the activity of both K2.2 and K3.1, while rimtuzalcap selectively activates K2.2. Rimtuzalcap has been used in clinical trials for the treatment of spinocerebellar ataxia and essential tremor. We report cryo-electron microscopy structures of NS309-bound K2.2 and K3.1, in addition to structures of rimtuzalcap-bound K2.2 and mutant K3.1_R355K. The different conformations of calmodulin and the cytoplasmic HC helices in the two channels underlie the subtype-selectivity of rimtuzalcap for K2.2. NS309 binds to pre-existing pockets in both channels, while the bulkier rimtuzalcap binds in an induced-fit pocket in K2.2 requiring conformational changes. In K2.2, calmodulin's N-lobes are sufficiently far apart to enable conformational changes to accommodate either NS309 or rimtuzalcap. In K3.1, calmodulin's N-lobes are closer to each other and constrained by K3.1's HC helices, which allows binding of NS309 but not rimtuzalcap. Replacement of arginine-355 in K3.1's HB helix with lysine (K3.1_R355K) allows the binding of rimtuzalcap and renders the mutant channel sensitive to rimtuzalcap. These structures provide a framework for structure-based drug design targeting K2.2 channels. #1: ジャーナル: Res Sq / 年: 2025 タイトル: Structural basis for the subtype-selectivity of K2.2 channel activators. 著者: Miao Zhang / Young-Woo Nam / Alena Ramanishka / Yang Xu / Rose Marie Yasuda / Dohyun Im / Meng Cui / George Chandy / Heike Wulff /  要旨: Small-conductance (K2.2) and intermediate-conductance (K3.1) Ca-activated K channels are gated by a Ca-calmodulin dependent mechanism. NS309 potentiates the activity of both K2.2 and K3.1, while ...Small-conductance (K2.2) and intermediate-conductance (K3.1) Ca-activated K channels are gated by a Ca-calmodulin dependent mechanism. NS309 potentiates the activity of both K2.2 and K3.1, while rimtuzalcap selectively activates K2.2. Rimtuzalcap has been used in clinical trials for the treatment of spinocerebellar ataxia and essential tremor. We report cryo-electron microscopy structures of K2.2 channels bound with NS309 and rimtuzalcap, in addition to K3.1 channels with NS309. The different conformations of calmodulin and the cytoplasmic HC helices in the two channels underlie the subtype-selectivity of rimtuzalcap for K2.2. Calmodulin's N-lobes in the K2.2 structure are far apart and undergo conformational changes to accommodate either NS309 or rimtuzalcap. Calmodulin's Nlobes in the K3.1 structure are closer to each other and are constrained by the HC helices of K3.1, which allows binding of NS309 but not of the bulkier rimtuzalcap. These structures provide a framework for structure-based drug design targeting K2.2 channels. | ||||||||||||||||||||||||||||||||||||
| 履歴 |
|
- 構造の表示
構造の表示
| 構造ビューア | 分子:  Molmil Molmil Jmol/JSmol Jmol/JSmol |
|---|
- ダウンロードとリンク
ダウンロードとリンク
- ダウンロード
ダウンロード
| PDBx/mmCIF形式 |  9oa8.cif.gz 9oa8.cif.gz | 343.4 KB | 表示 |  PDBx/mmCIF形式 PDBx/mmCIF形式 |
|---|---|---|---|---|
| PDB形式 |  pdb9oa8.ent.gz pdb9oa8.ent.gz | 276 KB | 表示 |  PDB形式 PDB形式 |
| PDBx/mmJSON形式 |  9oa8.json.gz 9oa8.json.gz | ツリー表示 |  PDBx/mmJSON形式 PDBx/mmJSON形式 | |
| その他 |  その他のダウンロード その他のダウンロード |
-検証レポート
| アーカイブディレクトリ |  https://data.pdbj.org/pub/pdb/validation_reports/oa/9oa8 https://data.pdbj.org/pub/pdb/validation_reports/oa/9oa8 ftp://data.pdbj.org/pub/pdb/validation_reports/oa/9oa8 ftp://data.pdbj.org/pub/pdb/validation_reports/oa/9oa8 | HTTPS FTP |
|---|
-関連構造データ
| 関連構造データ |  70275MC  9o7sC  9o85C  9o93C  9y5qC  9ydzC M: このデータのモデリングに利用したマップデータ C: 同じ文献を引用 ( |
|---|---|
| 類似構造データ | 類似検索 - 機能・相同性  F&H 検索 F&H 検索 |
- リンク
リンク
- 集合体
集合体
| 登録構造単位 | 
|
|---|---|
| 1 |
|
- 要素
要素
| #1: タンパク質 | 分子量: 42598.633 Da / 分子数: 4 / 由来タイプ: 組換発現 / 由来: (組換発現)  Homo sapiens (ヒト) / 遺伝子: KCNN4, IK1, IKCA1, KCA4, SK4 / 発現宿主: Homo sapiens (ヒト) / 遺伝子: KCNN4, IK1, IKCA1, KCA4, SK4 / 発現宿主:  Homo sapiens (ヒト) / 参照: UniProt: O15554 Homo sapiens (ヒト) / 参照: UniProt: O15554#2: タンパク質 | 分子量: 16521.094 Da / 分子数: 4 / 由来タイプ: 組換発現 / 由来: (組換発現)   Homo sapiens (ヒト) / 参照: UniProt: P0DP29 Homo sapiens (ヒト) / 参照: UniProt: P0DP29#3: 化合物 | #4: 化合物 | ChemComp-1KP / ( #5: 化合物 | ChemComp-CA / 研究の焦点であるリガンドがあるか | Y | Has protein modification | N | |
|---|
-実験情報
-実験
| 実験 | 手法: 電子顕微鏡法 |
|---|---|
| EM実験 | 試料の集合状態: PARTICLE / 3次元再構成法: 単粒子再構成法 |
- 試料調製
試料調製
| 構成要素 | 名称: Human KCa3.1/calmodulin channel in complex with NS309 タイプ: COMPLEX / Entity ID: #1-#2 / 由来: MULTIPLE SOURCES |
|---|---|
| 分子量 | 値: 0.23166 MDa / 実験値: NO |
| 由来(天然) | 生物種:  Homo sapiens (ヒト) Homo sapiens (ヒト) |
| 由来(組換発現) | 生物種:  Homo sapiens (ヒト) / 株: HEK293s / 細胞: HEK293 / プラスミド: pGEBacMam Homo sapiens (ヒト) / 株: HEK293s / 細胞: HEK293 / プラスミド: pGEBacMam |
| 緩衝液 | pH: 8 |
| 試料 | 濃度: 2 mg/ml / 包埋: NO / シャドウイング: NO / 染色: NO / 凍結: YES |
| 急速凍結 | 凍結剤: ETHANE |
- 電子顕微鏡撮影
電子顕微鏡撮影
| 実験機器 |  モデル: Titan Krios / 画像提供: FEI Company |
|---|---|
| 顕微鏡 | モデル: TFS KRIOS |
| 電子銃 | 電子線源:  FIELD EMISSION GUN / 加速電圧: 300 kV / 照射モード: FLOOD BEAM FIELD EMISSION GUN / 加速電圧: 300 kV / 照射モード: FLOOD BEAM |
| 電子レンズ | モード: BRIGHT FIELD / 最大 デフォーカス(公称値): 2200 nm / 最小 デフォーカス(公称値): 1300 nm |
| 試料ホルダ | 試料ホルダーモデル: FEI TITAN KRIOS AUTOGRID HOLDER |
| 撮影 | 電子線照射量: 50 e/Å2 フィルム・検出器のモデル: FEI FALCON IV (4k x 4k) |
- 解析
解析
| EMソフトウェア |
| ||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| CTF補正 | タイプ: PHASE FLIPPING AND AMPLITUDE CORRECTION | ||||||||||||||||||||||||
| 3次元再構成 | 解像度: 3.59 Å / 解像度の算出法: FSC 0.143 CUT-OFF / 粒子像の数: 119846 / 対称性のタイプ: POINT | ||||||||||||||||||||||||
| 精密化 | 最高解像度: 3.59 Å 立体化学のターゲット値: REAL-SPACE (WEIGHTED MAP SUM AT ATOM CENTERS) | ||||||||||||||||||||||||
| 拘束条件 |
|
 ムービー
ムービー コントローラー
コントローラー








 PDBj
PDBj