+ データを開く
データを開く
- 基本情報
基本情報
| 登録情報 | データベース: PDB / ID: 9i6f | |||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
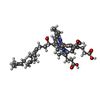
| タイトル | Cryo-EM structure of HIGD2A bound complex IV | |||||||||||||||||||||
 要素 要素 |
| |||||||||||||||||||||
 キーワード キーワード | MEMBRANE PROTEIN / Human mitochondria / respirasome complex / assembly / cytochrome c oxidase / complex IV / HIGD2A | |||||||||||||||||||||
| 機能・相同性 |  機能・相同性情報 機能・相同性情報Complex IV assembly / respiratory chain complex IV assembly / Respiratory electron transport / mitochondrial respirasome assembly / respiratory gaseous exchange by respiratory system / respiratory chain complex IV / Mitochondrial translation termination / respiratory chain complex / cytochrome-c oxidase / cellular respiration ...Complex IV assembly / respiratory chain complex IV assembly / Respiratory electron transport / mitochondrial respirasome assembly / respiratory gaseous exchange by respiratory system / respiratory chain complex IV / Mitochondrial translation termination / respiratory chain complex / cytochrome-c oxidase / cellular respiration / oxidative phosphorylation / mitochondrial electron transport, cytochrome c to oxygen / cytochrome-c oxidase activity / response to copper ion / response to electrical stimulus / ATP synthesis coupled electron transport / enzyme regulator activity / lactation / response to nutrient / Mitochondrial protein degradation / substantia nigra development / proton transmembrane transport / cerebellum development / acrosomal vesicle / aerobic respiration / central nervous system development / respiratory electron transport chain / TP53 Regulates Metabolic Genes / generation of precursor metabolites and energy / Cytoprotection by HMOX1 / mitochondrial intermembrane space / mitochondrial membrane / sperm principal piece / response to oxidative stress / response to ethanol / response to hypoxia / electron transfer activity / oxidoreductase activity / mitochondrial inner membrane / mitochondrial matrix / copper ion binding / heme binding / negative regulation of apoptotic process / mitochondrion / nucleoplasm / membrane / metal ion binding / cytosol 類似検索 - 分子機能 | |||||||||||||||||||||
| 生物種 |  Homo sapiens (ヒト) Homo sapiens (ヒト) | |||||||||||||||||||||
| 手法 | 電子顕微鏡法 / 単粒子再構成法 / クライオ電子顕微鏡法 / 解像度: 2.95 Å | |||||||||||||||||||||
 データ登録者 データ登録者 | Nguyen, M.D. / Rorbach, J. / Singh, V. | |||||||||||||||||||||
| 資金援助 |  スウェーデン, 1件 スウェーデン, 1件
| |||||||||||||||||||||
 引用 引用 |  ジャーナル: Nat Commun / 年: 2026 ジャーナル: Nat Commun / 年: 2026タイトル: Structural basis for late maturation steps of mitochondrial respiratory chain complex IV within the human respirasome. 著者: Minh Duc Nguyen / Ana Sierra-Magro / Vivek Singh / Anas Khawaja / Alba Timón-Gómez / Antoni Barrientos / Joanna Rorbach /    要旨: The mitochondrial respiratory chain comprises four multimeric complexes (CI-CIV) that drive oxidative phosphorylation by transferring electrons to oxygen and generating the proton gradient required ...The mitochondrial respiratory chain comprises four multimeric complexes (CI-CIV) that drive oxidative phosphorylation by transferring electrons to oxygen and generating the proton gradient required for ATP synthesis. These complexes can associate into supercomplexes (SCs), such as the CI + CIII₂ + CIV respirasome, but how SCs form, by joining preassembled complexes or by engaging partially assembled intermediates, remains unresolved. Here, we use cryo-electron microscopy to determine high-resolution structures of native human CI + CIII₂ + CIV late-assembly intermediates. Together with biochemical analyses, these structures show that respirasome biogenesis concludes with the final maturation of CIV while it is associated with fully assembled CI and CIII₂. We identify HIGD2A as a placeholder factor within isolated and supercomplexed CIV that is replaced by subunit NDUFA4 during the last step of CIV and respirasome assembly. This mechanism suggests that placeholders such as HIGD2A act as molecular timers, preventing premature incorporation of NDUFA4 or its isoforms and ensuring the orderly progression of pre-SC particles into functional respirasomes. Since defects in CIV assembly, including NDUFA4 deficiencies, cause severe encephalomyopathies and neurodegenerative disorders, understanding the molecular architecture and assembly pathways of isolated and supercomplexed CIV offers insight into the pathogenic mechanisms underlying these conditions. | |||||||||||||||||||||
| 履歴 |
|
- 構造の表示
構造の表示
| 構造ビューア | 分子:  Molmil Molmil Jmol/JSmol Jmol/JSmol |
|---|
- ダウンロードとリンク
ダウンロードとリンク
- ダウンロード
ダウンロード
| PDBx/mmCIF形式 |  9i6f.cif.gz 9i6f.cif.gz | 737.8 KB | 表示 |  PDBx/mmCIF形式 PDBx/mmCIF形式 |
|---|---|---|---|---|
| PDB形式 |  pdb9i6f.ent.gz pdb9i6f.ent.gz | 613.2 KB | 表示 |  PDB形式 PDB形式 |
| PDBx/mmJSON形式 |  9i6f.json.gz 9i6f.json.gz | ツリー表示 |  PDBx/mmJSON形式 PDBx/mmJSON形式 | |
| その他 |  その他のダウンロード その他のダウンロード |
-検証レポート
| アーカイブディレクトリ |  https://data.pdbj.org/pub/pdb/validation_reports/i6/9i6f https://data.pdbj.org/pub/pdb/validation_reports/i6/9i6f ftp://data.pdbj.org/pub/pdb/validation_reports/i6/9i6f ftp://data.pdbj.org/pub/pdb/validation_reports/i6/9i6f | HTTPS FTP |
|---|
-関連構造データ
- リンク
リンク
- 集合体
集合体
| 登録構造単位 | 
|
|---|---|
| 1 |
|
- 要素
要素
-タンパク質 , 1種, 1分子 N
| #1: タンパク質 | 分子量: 11542.502 Da / 分子数: 1 / 由来タイプ: 天然 / 由来: (天然)  Homo sapiens (ヒト) / 参照: UniProt: Q9BW72 Homo sapiens (ヒト) / 参照: UniProt: Q9BW72 |
|---|
-Cytochrome c oxidase subunit ... , 13種, 13分子 ABCDEFGHIJKLM
| #2: タンパク質 | 分子量: 57104.930 Da / 分子数: 1 / 由来タイプ: 天然 / 由来: (天然)  Homo sapiens (ヒト) / 参照: UniProt: P00395, cytochrome-c oxidase Homo sapiens (ヒト) / 参照: UniProt: P00395, cytochrome-c oxidase |
|---|---|
| #3: タンパク質 | 分子量: 25580.900 Da / 分子数: 1 / 由来タイプ: 天然 / 由来: (天然)  Homo sapiens (ヒト) / 参照: UniProt: P00403, cytochrome-c oxidase Homo sapiens (ヒト) / 参照: UniProt: P00403, cytochrome-c oxidase |
| #4: タンパク質 | 分子量: 30003.678 Da / 分子数: 1 / 由来タイプ: 天然 / 由来: (天然)  Homo sapiens (ヒト) / 参照: UniProt: P00414, cytochrome-c oxidase Homo sapiens (ヒト) / 参照: UniProt: P00414, cytochrome-c oxidase |
| #5: タンパク質 | 分子量: 19609.758 Da / 分子数: 1 / 由来タイプ: 天然 / 由来: (天然)  Homo sapiens (ヒト) / 参照: UniProt: P13073 Homo sapiens (ヒト) / 参照: UniProt: P13073 |
| #6: タンパク質 | 分子量: 16785.178 Da / 分子数: 1 / 由来タイプ: 天然 / 由来: (天然)  Homo sapiens (ヒト) / 参照: UniProt: P20674 Homo sapiens (ヒト) / 参照: UniProt: P20674 |
| #7: タンパク質 | 分子量: 13714.709 Da / 分子数: 1 / 由来タイプ: 天然 / 由来: (天然)  Homo sapiens (ヒト) / 参照: UniProt: P10606 Homo sapiens (ヒト) / 参照: UniProt: P10606 |
| #8: タンパク質 | 分子量: 12173.858 Da / 分子数: 1 / 由来タイプ: 天然 / 由来: (天然)  Homo sapiens (ヒト) / 参照: UniProt: P12074 Homo sapiens (ヒト) / 参照: UniProt: P12074 |
| #9: タンパク質 | 分子量: 10204.382 Da / 分子数: 1 / 由来タイプ: 天然 / 由来: (天然)  Homo sapiens (ヒト) / 参照: UniProt: P14854 Homo sapiens (ヒト) / 参照: UniProt: P14854 |
| #10: タンパク質 | 分子量: 8798.474 Da / 分子数: 1 / 由来タイプ: 天然 / 由来: (天然)  Homo sapiens (ヒト) / 参照: UniProt: P09669 Homo sapiens (ヒト) / 参照: UniProt: P09669 |
| #11: タンパク質 | 分子量: 9409.977 Da / 分子数: 1 / 由来タイプ: 天然 / 由来: (天然)  Homo sapiens (ヒト) / 参照: UniProt: P14406 Homo sapiens (ヒト) / 参照: UniProt: P14406 |
| #12: タンパク質 | 分子量: 9172.496 Da / 分子数: 1 / 由来タイプ: 天然 / 由来: (天然)  Homo sapiens (ヒト) / 参照: UniProt: P24311 Homo sapiens (ヒト) / 参照: UniProt: P24311 |
| #13: タンパク質 | 分子量: 7256.501 Da / 分子数: 1 / 由来タイプ: 天然 / 由来: (天然)  Homo sapiens (ヒト) / 参照: UniProt: P15954 Homo sapiens (ヒト) / 参照: UniProt: P15954 |
| #14: タンパク質 | 分子量: 7589.089 Da / 分子数: 1 / 由来タイプ: 天然 / 由来: (天然)  Homo sapiens (ヒト) / 参照: UniProt: P10176 Homo sapiens (ヒト) / 参照: UniProt: P10176 |
-非ポリマー , 7種, 13分子 











| #15: 化合物 | | #16: 化合物 | ChemComp-MG / | #17: 化合物 | ChemComp-PEE / #18: 化合物 | #19: 化合物 | ChemComp-PGV / ( | #20: 化合物 | ChemComp-CDL / | #21: 化合物 | ChemComp-ZN / | |
|---|
-詳細
| 研究の焦点であるリガンドがあるか | Y |
|---|---|
| Has protein modification | Y |
-実験情報
-実験
| 実験 | 手法: 電子顕微鏡法 |
|---|---|
| EM実験 | 試料の集合状態: PARTICLE / 3次元再構成法: 単粒子再構成法 |
- 試料調製
試料調製
| 構成要素 | 名称: Complex IV / タイプ: CELL / Entity ID: #1-#14 / 由来: NATURAL | |||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 由来(天然) | 生物種:  Homo sapiens (ヒト) Homo sapiens (ヒト) | |||||||||||||||||||||||||
| 緩衝液 | pH: 7.4 詳細: 25 mM HEPES-KOH pH=7.5, 50 mM KCl, 20 mM Mg(OAc)2, 0.01% (v/v) LMNG, 0.001 % cardiolipin, 0.001 % GD, 0.1mM DTT | |||||||||||||||||||||||||
| 緩衝液成分 |
| |||||||||||||||||||||||||
| 試料 | 包埋: NO / シャドウイング: NO / 染色: NO / 凍結: YES | |||||||||||||||||||||||||
| 試料支持 | グリッドの材料: COPPER / グリッドのサイズ: 300 divisions/in. / グリッドのタイプ: Quantifoil R2/2 | |||||||||||||||||||||||||
| 急速凍結 | 装置: FEI VITROBOT MARK IV / 凍結剤: ETHANE / 湿度: 100 % / 凍結前の試料温度: 277 K |
- 電子顕微鏡撮影
電子顕微鏡撮影
| 実験機器 |  モデル: Titan Krios / 画像提供: FEI Company |
|---|---|
| 顕微鏡 | モデル: TFS KRIOS |
| 電子銃 | 電子線源: OTHER / 加速電圧: 300 kV / 照射モード: OTHER |
| 電子レンズ | モード: OTHER / 最大 デフォーカス(公称値): 2000 nm / 最小 デフォーカス(公称値): 600 nm |
| 試料ホルダ | 凍結剤: NITROGEN |
| 撮影 | 電子線照射量: 35 e/Å2 / フィルム・検出器のモデル: GATAN K3 (6k x 4k) / 実像数: 17476 |
- 解析
解析
| EMソフトウェア | 名称: PHENIX / バージョン: 1.21rc1_5156 / カテゴリ: モデル精密化 | ||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| CTF補正 | タイプ: PHASE FLIPPING AND AMPLITUDE CORRECTION | ||||||||||||||||||||||||
| 3次元再構成 | 解像度: 2.95 Å / 解像度の算出法: FSC 0.143 CUT-OFF / 粒子像の数: 129242 / 対称性のタイプ: POINT | ||||||||||||||||||||||||
| 原子モデル構築 | PDB-ID: 5Z62 Accession code: 5Z62 / Source name: PDB / タイプ: experimental model | ||||||||||||||||||||||||
| 精密化 | 最高解像度: 2.95 Å 立体化学のターゲット値: REAL-SPACE (WEIGHTED MAP SUM AT ATOM CENTERS) | ||||||||||||||||||||||||
| 拘束条件 |
|
 ムービー
ムービー コントローラー
コントローラー














 PDBj
PDBj











