+ データを開く
データを開く
- 基本情報
基本情報
| 登録情報 | データベース: PDB / ID: 9buo | ||||||
|---|---|---|---|---|---|---|---|
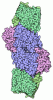
| タイトル | CryoEM structure of DPOR in the presence of ADP-AlF3 | ||||||
 要素 要素 |
| ||||||
 キーワード キーワード | OXIDOREDUCTASE / Plant Protein / Electron Transfer Enzymes / Photosynthesis | ||||||
| 機能・相同性 |  機能・相同性情報 機能・相同性情報ferredoxin:protochlorophyllide reductase (ATP-dependent) / photosynthesis, dark reaction / light-independent bacteriochlorophyll biosynthetic process / oxidoreductase activity, acting on iron-sulfur proteins as donors / oxidoreductase activity, acting on the CH-CH group of donors, iron-sulfur protein as acceptor / 4 iron, 4 sulfur cluster binding / ATP binding / metal ion binding 類似検索 - 分子機能 | ||||||
| 生物種 |  Cereibacter sphaeroides (バクテリア) Cereibacter sphaeroides (バクテリア) | ||||||
| 手法 | 電子顕微鏡法 / 単粒子再構成法 / クライオ電子顕微鏡法 / 解像度: 3.68 Å | ||||||
 データ登録者 データ登録者 | Kashyap, R. / Antony, E. | ||||||
| 資金援助 |  米国, 1件 米国, 1件
| ||||||
 引用 引用 |  ジャーナル: Nat Commun / 年: 2025 ジャーナル: Nat Commun / 年: 2025タイトル: Cryo-EM captures the coordination of asymmetric electron transfer through a di-copper site in DPOR. 著者: Rajnandani Kashyap / Natalie Walsh / Jaigeeth Deveryshetty / Monika Tokmina-Lukaszewska / Kewei Zhao / Yunqiao J Gan / Brian M Hoffman / Ritimukta Sarangi / Brian Bothner / Brian Bennett / Edwin Antony /  要旨: Enzymes that catalyze long-range electron transfer (ET) reactions often function as higher order complexes that possess two structurally symmetrical halves. The functional advantages for such an ...Enzymes that catalyze long-range electron transfer (ET) reactions often function as higher order complexes that possess two structurally symmetrical halves. The functional advantages for such an architecture remain a mystery. Using cryoelectron microscopy we capture snapshots of the nitrogenase-like dark-operative protochlorophyllide oxidoreductase (DPOR) during substrate binding and turnover. DPOR catalyzes reduction of the C17 = C18 double bond in protochlorophyllide during the dark chlorophyll biosynthetic pathway. DPOR is composed of electron donor (L-protein) and acceptor (NB-protein) component proteins that transiently form a complex in the presence of ATP to facilitate ET. NB-protein is an αβ heterotetramer with two structurally identical halves. However, our structures reveal that NB-protein becomes functionally asymmetric upon substrate binding. Asymmetry results in allosteric inhibition of L-protein engagement and ET in one half. Residues that form a conduit for ET are aligned in one half while misaligned in the other. An ATP hydrolysis-coupled conformational switch is triggered once ET is accomplished in one half. These structural changes are then relayed to the other half through a di-nuclear copper center at the tetrameric interface of the NB-protein and leads to activation of ET and substrate reduction. These findings provide a mechanistic blueprint for regulation of long-range electron transfer reactions. | ||||||
| 履歴 |
|
- 構造の表示
構造の表示
| 構造ビューア | 分子:  Molmil Molmil Jmol/JSmol Jmol/JSmol |
|---|
- ダウンロードとリンク
ダウンロードとリンク
- ダウンロード
ダウンロード
| PDBx/mmCIF形式 |  9buo.cif.gz 9buo.cif.gz | 469.2 KB | 表示 |  PDBx/mmCIF形式 PDBx/mmCIF形式 |
|---|---|---|---|---|
| PDB形式 |  pdb9buo.ent.gz pdb9buo.ent.gz | 376.1 KB | 表示 |  PDB形式 PDB形式 |
| PDBx/mmJSON形式 |  9buo.json.gz 9buo.json.gz | ツリー表示 |  PDBx/mmJSON形式 PDBx/mmJSON形式 | |
| その他 |  その他のダウンロード その他のダウンロード |
-検証レポート
| アーカイブディレクトリ |  https://data.pdbj.org/pub/pdb/validation_reports/bu/9buo https://data.pdbj.org/pub/pdb/validation_reports/bu/9buo ftp://data.pdbj.org/pub/pdb/validation_reports/bu/9buo ftp://data.pdbj.org/pub/pdb/validation_reports/bu/9buo | HTTPS FTP |
|---|
-関連構造データ
| 関連構造データ |  44913MC  8vqhC  8vqiC  8vqjC  9e7hC  9efuC M: このデータのモデリングに利用したマップデータ C: 同じ文献を引用 ( |
|---|---|
| 類似構造データ | 類似検索 - 機能・相同性  F&H 検索 F&H 検索 |
- リンク
リンク
- 集合体
集合体
| 登録構造単位 | 
|
|---|---|
| 1 |
|
- 要素
要素
-タンパク質 , 1種, 4分子 GHEF
| #1: タンパク質 | 分子量: 34850.340 Da / 分子数: 4 / 由来タイプ: 組換発現 由来: (組換発現)  Cereibacter sphaeroides (バクテリア) Cereibacter sphaeroides (バクテリア)遺伝子: bchL, RHOS4_18930, RSP_0288 / 発現宿主:  参照: UniProt: Q9RFD6, ferredoxin:protochlorophyllide reductase (ATP-dependent) |
|---|
-Light-independent protochlorophyllide reductase subunit ... , 2種, 4分子 ACBD
| #2: タンパク質 | 分子量: 46188.773 Da / 分子数: 2 / 由来タイプ: 組換発現 由来: (組換発現)  Cereibacter sphaeroides (バクテリア) Cereibacter sphaeroides (バクテリア)遺伝子: bchN, RSKD131_1611 / 発現宿主:  参照: UniProt: B9KK24, ferredoxin:protochlorophyllide reductase (ATP-dependent) #3: タンパク質 | 分子量: 58302.234 Da / 分子数: 2 / 由来タイプ: 組換発現 由来: (組換発現)  Cereibacter sphaeroides (バクテリア) Cereibacter sphaeroides (バクテリア)遺伝子: bchB, RHOS4_18910, RSP_0286 / 発現宿主:  参照: UniProt: Q9Z5D9, ferredoxin:protochlorophyllide reductase (ATP-dependent) |
|---|
-非ポリマー , 3種, 8分子 




| #4: 化合物 | ChemComp-SF4 / #5: 化合物 | #6: 化合物 | |
|---|
-詳細
| 研究の焦点であるリガンドがあるか | Y |
|---|---|
| Has protein modification | N |
-実験情報
-実験
| 実験 | 手法: 電子顕微鏡法 |
|---|---|
| EM実験 | 試料の集合状態: PARTICLE / 3次元再構成法: 単粒子再構成法 |
- 試料調製
試料調製
| 構成要素 | 名称: CryoEM structure of DPOR in the presence of ADP-AlF3 タイプ: COMPLEX / Entity ID: #1-#3 / 由来: RECOMBINANT |
|---|---|
| 分子量 | 値: 0.3478 MDa / 実験値: YES |
| 由来(天然) | 生物種:  Cereibacter sphaeroides (バクテリア) Cereibacter sphaeroides (バクテリア) |
| 由来(組換発現) | 生物種:  |
| 緩衝液 | pH: 7.5 |
| 試料 | 包埋: NO / シャドウイング: NO / 染色: NO / 凍結: YES |
| 急速凍結 | 装置: FEI VITROBOT MARK IV / 凍結剤: ETHANE / 湿度: 100 % / 凍結前の試料温度: 277.15 K |
- 電子顕微鏡撮影
電子顕微鏡撮影
| 実験機器 |  モデル: Titan Krios / 画像提供: FEI Company |
|---|---|
| 顕微鏡 | モデル: TFS KRIOS |
| 電子銃 | 電子線源:  FIELD EMISSION GUN / 加速電圧: 300 kV / 照射モード: OTHER FIELD EMISSION GUN / 加速電圧: 300 kV / 照射モード: OTHER |
| 電子レンズ | モード: BRIGHT FIELD / 倍率(公称値): 105000 X / 最大 デフォーカス(公称値): 2200 nm / 最小 デフォーカス(公称値): 1000 nm / Cs: 2.7 mm / C2レンズ絞り径: 70 µm |
| 撮影 | 電子線照射量: 50 e/Å2 フィルム・検出器のモデル: GATAN K3 BIOQUANTUM (6k x 4k) |
- 解析
解析
| CTF補正 | タイプ: NONE | ||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 3次元再構成 | 解像度: 3.68 Å / 解像度の算出法: FSC 0.143 CUT-OFF / 粒子像の数: 20571 / 対称性のタイプ: POINT | ||||||||||||||||||||||||
| 精密化 | 最高解像度: 3.68 Å 立体化学のターゲット値: REAL-SPACE (WEIGHTED MAP SUM AT ATOM CENTERS) | ||||||||||||||||||||||||
| 拘束条件 |
|
 ムービー
ムービー コントローラー
コントローラー








 PDBj
PDBj