+ データを開く
データを開く
- 基本情報
基本情報
| 登録情報 | データベース: PDB / ID: 8bqs | |||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
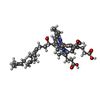
| タイトル | Cryo-EM structure of the I-II-III2-IV2 respiratory supercomplex from Tetrahymena thermophila | |||||||||||||||
 要素 要素 |
| |||||||||||||||
 キーワード キーワード | ELECTRON TRANSPORT / Ciliate / Mitochondrial / Supercomplex | |||||||||||||||
| 機能・相同性 |  機能・相同性情報 機能・相同性情報lipid-A-disaccharide synthase / lipid-A-disaccharide synthase activity / quinol-cytochrome-c reductase / NADH:ubiquinone reductase (H+-translocating) / mitochondrial electron transport, succinate to ubiquinone / P450-containing electron transport chain / membrane protein complex / succinate dehydrogenase (quinone) activity / succinate dehydrogenase / NADH dehydrogenase complex ...lipid-A-disaccharide synthase / lipid-A-disaccharide synthase activity / quinol-cytochrome-c reductase / NADH:ubiquinone reductase (H+-translocating) / mitochondrial electron transport, succinate to ubiquinone / P450-containing electron transport chain / membrane protein complex / succinate dehydrogenase (quinone) activity / succinate dehydrogenase / NADH dehydrogenase complex / respiratory chain complex IV / mitochondrial envelope / cytochrome-c oxidase / mitochondrial electron transport, cytochrome c to oxygen / 3 iron, 4 sulfur cluster binding / cytochrome-c oxidase activity / mitochondrial electron transport, ubiquinol to cytochrome c / lipid A biosynthetic process / ligase activity / NADH:ubiquinone reductase (H+-translocating) / electron transport coupled proton transport / mitochondrial electron transport, NADH to ubiquinone / acyl binding / mitochondrial respiratory chain complex I assembly / NADH dehydrogenase activity / oxidoreductase activity, acting on NAD(P)H / respiratory chain complex I / NADH dehydrogenase (ubiquinone) activity / acyl carrier activity / catalytic complex / quinone binding / ATP synthesis coupled electron transport / tricarboxylic acid cycle / protein folding chaperone / aerobic respiration / respiratory electron transport chain / electron transport chain / phospholipid binding / 2 iron, 2 sulfur cluster binding / mitochondrial membrane / NAD binding / metallopeptidase activity / unfolded protein binding / FMN binding / flavin adenine dinucleotide binding / protein transport / protein-folding chaperone binding / 4 iron, 4 sulfur cluster binding / response to oxidative stress / electron transfer activity / oxidoreductase activity / mitochondrial inner membrane / ribosome / DNA-binding transcription factor activity / copper ion binding / heme binding / protein-containing complex binding / mitochondrion / proteolysis / zinc ion binding / membrane / metal ion binding / nucleus / plasma membrane / cytoplasm 類似検索 - 分子機能 | |||||||||||||||
| 生物種 |  Tetrahymena thermophila SB210 (真核生物) Tetrahymena thermophila SB210 (真核生物) | |||||||||||||||
| 手法 | 電子顕微鏡法 / 単粒子再構成法 / クライオ電子顕微鏡法 / 解像度: 2.9 Å | |||||||||||||||
 データ登録者 データ登録者 | Muhleip, A. / Kock Flygaard, R. / Baradaran, R. / Amunts, A. | |||||||||||||||
| 資金援助 |  スウェーデン, European Union, 4件 スウェーデン, European Union, 4件
| |||||||||||||||
 引用 引用 |  ジャーナル: Nature / 年: 2023 ジャーナル: Nature / 年: 2023タイトル: Structural basis of mitochondrial membrane bending by the I-II-III-IV supercomplex. 著者: Alexander Mühleip / Rasmus Kock Flygaard / Rozbeh Baradaran / Outi Haapanen / Thomas Gruhl / Victor Tobiasson / Amandine Maréchal / Vivek Sharma / Alexey Amunts /      要旨: Mitochondrial energy conversion requires an intricate architecture of the inner mitochondrial membrane. Here we show that a supercomplex containing all four respiratory chain components contributes ...Mitochondrial energy conversion requires an intricate architecture of the inner mitochondrial membrane. Here we show that a supercomplex containing all four respiratory chain components contributes to membrane curvature induction in ciliates. We report cryo-electron microscopy and cryo-tomography structures of the supercomplex that comprises 150 different proteins and 311 bound lipids, forming a stable 5.8-MDa assembly. Owing to subunit acquisition and extension, complex I associates with a complex IV dimer, generating a wedge-shaped gap that serves as a binding site for complex II. Together with a tilted complex III dimer association, it results in a curved membrane region. Using molecular dynamics simulations, we demonstrate that the divergent supercomplex actively contributes to the membrane curvature induction and tubulation of cristae. Our findings highlight how the evolution of protein subunits of respiratory complexes has led to the I-II-III-IV supercomplex that contributes to the shaping of the bioenergetic membrane, thereby enabling its functional specialization. | |||||||||||||||
| 履歴 |
|
- 構造の表示
構造の表示
| 構造ビューア | 分子:  Molmil Molmil Jmol/JSmol Jmol/JSmol |
|---|
- ダウンロードとリンク
ダウンロードとリンク
- ダウンロード
ダウンロード
| PDBx/mmCIF形式 |  8bqs.cif.gz 8bqs.cif.gz | 18.4 MB | 表示 |  PDBx/mmCIF形式 PDBx/mmCIF形式 |
|---|---|---|---|---|
| PDB形式 |  pdb8bqs.ent.gz pdb8bqs.ent.gz | 表示 |  PDB形式 PDB形式 | |
| PDBx/mmJSON形式 |  8bqs.json.gz 8bqs.json.gz | ツリー表示 |  PDBx/mmJSON形式 PDBx/mmJSON形式 | |
| その他 |  その他のダウンロード その他のダウンロード |
-検証レポート
| アーカイブディレクトリ |  https://data.pdbj.org/pub/pdb/validation_reports/bq/8bqs https://data.pdbj.org/pub/pdb/validation_reports/bq/8bqs ftp://data.pdbj.org/pub/pdb/validation_reports/bq/8bqs ftp://data.pdbj.org/pub/pdb/validation_reports/bq/8bqs | HTTPS FTP |
|---|
-関連構造データ
| 関連構造データ |  16184MC  8b6fC  8b6gC  8b6hC  8b6jC M: このデータのモデリングに利用したマップデータ C: 同じ文献を引用 ( |
|---|---|
| 類似構造データ | 類似検索 - 機能・相同性  F&H 検索 F&H 検索 |
- リンク
リンク
- 集合体
集合体
| 登録構造単位 | 
|
|---|---|
| 1 |
|
- 要素
要素
+タンパク質 , 82種, 123分子 A0A1A2A3A4A5A7A8AFAGAJANASAYAZB1B2BCBEBFBGBIBJBKBNBPBRBSBTBU...
+Transmembrane ... , 34種, 50分子 A6A9B0B3B4B5BABBBDBLBMBXCMCFCKCJCNCCHhIiKkDEDeDGDgDHDh...
+NADH dehydrogenase subunit ... , 6種, 6分子 AAAEAOATB6BH
+NADH-ubiquinone oxidoreductase ... , 7種, 7分子 ABACAHAIALAUAX
+NADH dehydrogenase [ubiquinone] ... , 8種, 10分子 ADAPAQARBOBQDIDiDTDt
+Gamma-carbonic ... , 2種, 2分子 AKAM
+Acyl carrier ... , 2種, 2分子 AVAW
+タンパク質・ペプチド , 3種, 4分子 COCDLl
+Cytochrome c oxidase subunit ... , 3種, 6分子 DADaDBDbDDDd
+Zf-Tim10 DDP domain-containing ... , 2種, 4分子 ETEtEXEx
+非ポリマー , 24種, 384分子 












































+詳細
-実験情報
-実験
| 実験 | 手法: 電子顕微鏡法 |
|---|---|
| EM実験 | 試料の集合状態: PARTICLE / 3次元再構成法: 単粒子再構成法 |
- 試料調製
試料調製
| 構成要素 | 名称: respiratory chain supercomplex from the ciliate Tetrahymena thermophila タイプ: COMPLEX / Entity ID: #1-#149 / 由来: NATURAL |
|---|---|
| 分子量 | 実験値: NO |
| 由来(天然) | 生物種:  Tetrahymena thermophila SB210 (真核生物) Tetrahymena thermophila SB210 (真核生物) |
| 緩衝液 | pH: 7.4 |
| 試料 | 包埋: NO / シャドウイング: NO / 染色: NO / 凍結: YES |
| 急速凍結 | 凍結剤: ETHANE |
- 電子顕微鏡撮影
電子顕微鏡撮影
| 実験機器 |  モデル: Titan Krios / 画像提供: FEI Company |
|---|---|
| 顕微鏡 | モデル: FEI TITAN KRIOS |
| 電子銃 | 電子線源:  FIELD EMISSION GUN / 加速電圧: 300 kV / 照射モード: FLOOD BEAM FIELD EMISSION GUN / 加速電圧: 300 kV / 照射モード: FLOOD BEAM |
| 電子レンズ | モード: BRIGHT FIELD / 最大 デフォーカス(公称値): 2200 nm / 最小 デフォーカス(公称値): 600 nm |
| 撮影 | 電子線照射量: 31 e/Å2 / 検出モード: COUNTING フィルム・検出器のモデル: GATAN K2 QUANTUM (4k x 4k) |
- 解析
解析
| EMソフトウェア | 名称: PHENIX / バージョン: 1.20.1_4487 / カテゴリ: モデル精密化 | ||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| CTF補正 | タイプ: PHASE FLIPPING AND AMPLITUDE CORRECTION | ||||||||||||||||||||||||
| 3次元再構成 | 解像度: 2.9 Å / 解像度の算出法: FSC 0.143 CUT-OFF / 粒子像の数: 138746 / 対称性のタイプ: POINT | ||||||||||||||||||||||||
| 精密化 | 交差検証法: NONE | ||||||||||||||||||||||||
| 拘束条件 |
|
 ムービー
ムービー コントローラー
コントローラー








 PDBj
PDBj




























































