+ データを開く
データを開く
- 基本情報
基本情報
| 登録情報 | データベース: PDB / ID: 7zki | ||||||
|---|---|---|---|---|---|---|---|
| タイトル | Cryo-EM structure of aIF1A:aIF5B:Met-tRNAiMet complex from a Pyrococcus abyssi 30S initiation complex | ||||||
 要素 要素 |
| ||||||
 キーワード キーワード | TRANSLATION / Initiation complex / translation initiation / small ribosomal subunit / aIF5b | ||||||
| 機能・相同性 |  機能・相同性情報 機能・相同性情報nucleoside diphosphate phosphatase activity / intein-mediated protein splicing / intron homing / translation initiation factor activity / endonuclease activity / GTPase activity / calcium ion binding / GTP binding / RNA binding / cytoplasm 類似検索 - 分子機能 | ||||||
| 生物種 |    Pyrococcus abyssi GE5 (古細菌) Pyrococcus abyssi GE5 (古細菌) | ||||||
| 手法 | 電子顕微鏡法 / 単粒子再構成法 / クライオ電子顕微鏡法 / 解像度: 3.6 Å | ||||||
 データ登録者 データ登録者 | Coureux, P.D. / Bourgeois, G. / Mechulam, Y. / Schmitt, E. / Kazan, R. | ||||||
| 資金援助 |  フランス, 1件 フランス, 1件
| ||||||
 引用 引用 |  ジャーナル: Nucleic Acids Res / 年: 2022 ジャーナル: Nucleic Acids Res / 年: 2022タイトル: Role of aIF5B in archaeal translation initiation. 著者: Ramy Kazan / Gabrielle Bourgeois / Christine Lazennec-Schurdevin / Eric Larquet / Yves Mechulam / Pierre-Damien Coureux / Emmanuelle Schmitt /  要旨: In eukaryotes and in archaea late steps of translation initiation involve the two initiation factors e/aIF5B and e/aIF1A. In eukaryotes, the role of eIF5B in ribosomal subunit joining is established ...In eukaryotes and in archaea late steps of translation initiation involve the two initiation factors e/aIF5B and e/aIF1A. In eukaryotes, the role of eIF5B in ribosomal subunit joining is established and structural data showing eIF5B bound to the full ribosome were obtained. To achieve its function, eIF5B collaborates with eIF1A. However, structural data illustrating how these two factors interact on the small ribosomal subunit have long been awaited. The role of the archaeal counterparts, aIF5B and aIF1A, remains to be extensively addressed. Here, we study the late steps of Pyrococcus abyssi translation initiation. Using in vitro reconstituted initiation complexes and light scattering, we show that aIF5B bound to GTP accelerates subunit joining without the need for GTP hydrolysis. We report the crystallographic structures of aIF5B bound to GDP and GTP and analyze domain movements associated to these two nucleotide states. Finally, we present the cryo-EM structure of an initiation complex containing 30S bound to mRNA, Met-tRNAiMet, aIF5B and aIF1A at 2.7 Å resolution. Structural data shows how archaeal 5B and 1A factors cooperate to induce a conformation of the initiator tRNA favorable to subunit joining. Archaeal and eukaryotic features of late steps of translation initiation are discussed. | ||||||
| 履歴 |
|
- 構造の表示
構造の表示
| 構造ビューア | 分子:  Molmil Molmil Jmol/JSmol Jmol/JSmol |
|---|
- ダウンロードとリンク
ダウンロードとリンク
- ダウンロード
ダウンロード
| PDBx/mmCIF形式 |  7zki.cif.gz 7zki.cif.gz | 170.6 KB | 表示 |  PDBx/mmCIF形式 PDBx/mmCIF形式 |
|---|---|---|---|---|
| PDB形式 |  pdb7zki.ent.gz pdb7zki.ent.gz | 132.8 KB | 表示 |  PDB形式 PDB形式 |
| PDBx/mmJSON形式 |  7zki.json.gz 7zki.json.gz | ツリー表示 |  PDBx/mmJSON形式 PDBx/mmJSON形式 | |
| その他 |  その他のダウンロード その他のダウンロード |
-検証レポート
| 文書・要旨 |  7zki_validation.pdf.gz 7zki_validation.pdf.gz | 1 MB | 表示 |  wwPDB検証レポート wwPDB検証レポート |
|---|---|---|---|---|
| 文書・詳細版 |  7zki_full_validation.pdf.gz 7zki_full_validation.pdf.gz | 1 MB | 表示 | |
| XML形式データ |  7zki_validation.xml.gz 7zki_validation.xml.gz | 33.6 KB | 表示 | |
| CIF形式データ |  7zki_validation.cif.gz 7zki_validation.cif.gz | 47.2 KB | 表示 | |
| アーカイブディレクトリ |  https://data.pdbj.org/pub/pdb/validation_reports/zk/7zki https://data.pdbj.org/pub/pdb/validation_reports/zk/7zki ftp://data.pdbj.org/pub/pdb/validation_reports/zk/7zki ftp://data.pdbj.org/pub/pdb/validation_reports/zk/7zki | HTTPS FTP |
-関連構造データ
| 関連構造データ | 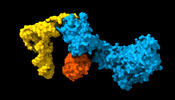 14763MC  7yypC  7yznC  7zagC  7zahC  7zaiC  7zhgC C: 同じ文献を引用 ( M: このデータのモデリングに利用したマップデータ |
|---|---|
| 類似構造データ | 類似検索 - 機能・相同性  F&H 検索 F&H 検索 |
- リンク
リンク
- 集合体
集合体
| 登録構造単位 | 
|
|---|---|
| 1 |
|
- 要素
要素
-RNA鎖 , 1種, 1分子 4
| #1: RNA鎖 | 分子量: 24833.904 Da / 分子数: 1 / 変異: C1A, A72U / 由来タイプ: 組換発現 / 由来: (組換発現)   |
|---|
-Translation initiation factor ... , 2種, 2分子 67
| #2: タンパク質 | 分子量: 15336.709 Da / 分子数: 1 / 由来タイプ: 組換発現 / 由来: (組換発現)   Pyrococcus abyssi GE5 (古細菌) / 遺伝子: eIF1A, aif1A, PYRAB05910, PAB2441 / 株: GE5 / Orsay / 発現宿主: Pyrococcus abyssi GE5 (古細菌) / 遺伝子: eIF1A, aif1A, PYRAB05910, PAB2441 / 株: GE5 / Orsay / 発現宿主:  |
|---|---|
| #3: タンパク質 | 分子量: 69122.945 Da / 分子数: 1 / 由来タイプ: 組換発現 / 由来: (組換発現)   Pyrococcus abyssi GE5 (古細菌) / 遺伝子: WBA_LOCUS12468, infB, PYRAB11390, PAB0755 / 株: GE5 / Orsay / 発現宿主: Pyrococcus abyssi GE5 (古細菌) / 遺伝子: WBA_LOCUS12468, infB, PYRAB11390, PAB0755 / 株: GE5 / Orsay / 発現宿主:  |
-非ポリマー , 3種, 3分子 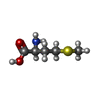




| #4: 化合物 | ChemComp-MET / |
|---|---|
| #5: 化合物 | ChemComp-GNP / |
| #6: 化合物 | ChemComp-MG / |
-詳細
| 研究の焦点であるリガンドがあるか | Y |
|---|
-実験情報
-実験
| 実験 | 手法: 電子顕微鏡法 |
|---|---|
| EM実験 | 試料の集合状態: PARTICLE / 3次元再構成法: 単粒子再構成法 |
- 試料調製
試料調製
| 構成要素 |
| ||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 分子量 | 実験値: NO | ||||||||||||||||||||||||
| 由来(天然) |
| ||||||||||||||||||||||||
| 由来(組換発現) |
| ||||||||||||||||||||||||
| 緩衝液 | pH: 6.7 | ||||||||||||||||||||||||
| 試料 | 包埋: NO / シャドウイング: NO / 染色: NO / 凍結: YES | ||||||||||||||||||||||||
| 試料支持 | グリッドの材料: COPPER / グリッドのタイプ: Quantifoil R2/1 | ||||||||||||||||||||||||
| 急速凍結 | 凍結剤: ETHANE |
- 電子顕微鏡撮影
電子顕微鏡撮影
| 実験機器 |  モデル: Titan Krios / 画像提供: FEI Company |
|---|---|
| 顕微鏡 | モデル: TFS KRIOS |
| 電子銃 | 電子線源:  FIELD EMISSION GUN / 加速電圧: 300 kV / 照射モード: FLOOD BEAM FIELD EMISSION GUN / 加速電圧: 300 kV / 照射モード: FLOOD BEAM |
| 電子レンズ | モード: BRIGHT FIELD / 最大 デフォーカス(公称値): 2500 nm / 最小 デフォーカス(公称値): 800 nm |
| 試料ホルダ | 試料ホルダーモデル: FEI TITAN KRIOS AUTOGRID HOLDER |
| 撮影 | 電子線照射量: 39 e/Å2 フィルム・検出器のモデル: GATAN K3 BIOQUANTUM (6k x 4k) |
- 解析
解析
| ソフトウェア | 名称: PHENIX / バージョン: 1.19_4092: / 分類: 精密化 | ||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| CTF補正 | タイプ: PHASE FLIPPING AND AMPLITUDE CORRECTION | ||||||||||||||||||||||||
| 粒子像の選択 | 選択した粒子像数: 2000000 | ||||||||||||||||||||||||
| 3次元再構成 | 解像度: 3.6 Å / 解像度の算出法: FSC 0.143 CUT-OFF / 粒子像の数: 37000 詳細: Resolution calculated by the post-processing procedure in Relion. 対称性のタイプ: POINT | ||||||||||||||||||||||||
| 拘束条件 |
|
 ムービー
ムービー コントローラー
コントローラー



 PDBj
PDBj



































