+ データを開く
データを開く
- 基本情報
基本情報
| 登録情報 | データベース: PDB / ID: 7nz3 | ||||||
|---|---|---|---|---|---|---|---|
| タイトル | Cryo-EM structure of apposed MukBEF-MatP monomers on DNA | ||||||
 要素 要素 |
| ||||||
 キーワード キーワード | DNA BINDING PROTEIN / SMC-kleisin complex / ATPase | ||||||
| 機能・相同性 |  機能・相同性情報 機能・相同性情報nucleoid / chromosome condensation / acyl carrier activity / chromosome segregation / DNA replication / sequence-specific DNA binding / cell cycle / cell division / calcium ion binding / regulation of DNA-templated transcription ...nucleoid / chromosome condensation / acyl carrier activity / chromosome segregation / DNA replication / sequence-specific DNA binding / cell cycle / cell division / calcium ion binding / regulation of DNA-templated transcription / DNA binding / ATP binding / cytoplasm 類似検索 - 分子機能 | ||||||
| 生物種 |  Photorhabdus thracensis (バクテリア) Photorhabdus thracensis (バクテリア) | ||||||
| 手法 | 電子顕微鏡法 / 単粒子再構成法 / クライオ電子顕微鏡法 / 解像度: 11 Å | ||||||
 データ登録者 データ登録者 | Buermann, F. / Lowe, J. | ||||||
 引用 引用 |  ジャーナル: Mol Cell / 年: 2021 ジャーナル: Mol Cell / 年: 2021タイトル: Cryo-EM structure of MukBEF reveals DNA loop entrapment at chromosomal unloading sites. 著者: Frank Bürmann / Louise F H Funke / Jason W Chin / Jan Löwe /  要旨: The ring-like structural maintenance of chromosomes (SMC) complex MukBEF folds the genome of Escherichia coli and related bacteria into large loops, presumably by active DNA loop extrusion. MukBEF ...The ring-like structural maintenance of chromosomes (SMC) complex MukBEF folds the genome of Escherichia coli and related bacteria into large loops, presumably by active DNA loop extrusion. MukBEF activity within the replication terminus macrodomain is suppressed by the sequence-specific unloader MatP. Here, we present the complete atomic structure of MukBEF in complex with MatP and DNA as determined by electron cryomicroscopy (cryo-EM). The complex binds two distinct DNA double helices corresponding to the arms of a plectonemic loop. MatP-bound DNA threads through the MukBEF ring, while the second DNA is clamped by the kleisin MukF, MukE, and the MukB ATPase heads. Combinatorial cysteine cross-linking confirms this topology of DNA loop entrapment in vivo. Our findings illuminate how a class of near-ubiquitous DNA organizers with important roles in genome maintenance interacts with the bacterial chromosome. #1:  ジャーナル: Biorxiv / 年: 2021 ジャーナル: Biorxiv / 年: 2021タイトル: DNA entrapment revealed by the structure of bacterial condensin MukBEF 著者: Buermann, F. / Funke, L.F.H. / Chin, J.W. / Lowe, J. | ||||||
| 履歴 |
|
- 構造の表示
構造の表示
| ムービー |
 ムービービューア ムービービューア |
|---|---|
| 構造ビューア | 分子:  Molmil Molmil Jmol/JSmol Jmol/JSmol |
- ダウンロードとリンク
ダウンロードとリンク
- ダウンロード
ダウンロード
| PDBx/mmCIF形式 |  7nz3.cif.gz 7nz3.cif.gz | 2.9 MB | 表示 |  PDBx/mmCIF形式 PDBx/mmCIF形式 |
|---|---|---|---|---|
| PDB形式 |  pdb7nz3.ent.gz pdb7nz3.ent.gz | 表示 |  PDB形式 PDB形式 | |
| PDBx/mmJSON形式 |  7nz3.json.gz 7nz3.json.gz | ツリー表示 |  PDBx/mmJSON形式 PDBx/mmJSON形式 | |
| その他 |  その他のダウンロード その他のダウンロード |
-検証レポート
| 文書・要旨 |  7nz3_validation.pdf.gz 7nz3_validation.pdf.gz | 1.3 MB | 表示 |  wwPDB検証レポート wwPDB検証レポート |
|---|---|---|---|---|
| 文書・詳細版 |  7nz3_full_validation.pdf.gz 7nz3_full_validation.pdf.gz | 1.5 MB | 表示 | |
| XML形式データ |  7nz3_validation.xml.gz 7nz3_validation.xml.gz | 182.8 KB | 表示 | |
| CIF形式データ |  7nz3_validation.cif.gz 7nz3_validation.cif.gz | 268 KB | 表示 | |
| アーカイブディレクトリ |  https://data.pdbj.org/pub/pdb/validation_reports/nz/7nz3 https://data.pdbj.org/pub/pdb/validation_reports/nz/7nz3 ftp://data.pdbj.org/pub/pdb/validation_reports/nz/7nz3 ftp://data.pdbj.org/pub/pdb/validation_reports/nz/7nz3 | HTTPS FTP |
-関連構造データ
| 関連構造データ |  12663MC  7nywC  7nyxC  7nyyC  7nyzC  7nz0C  7nz2C  7nz4C M: このデータのモデリングに利用したマップデータ C: 同じ文献を引用 ( |
|---|---|
| 類似構造データ | |
| 電子顕微鏡画像生データ |  EMPIAR-10755 (タイトル: MukBEF(E1407Q)-MatP-DNA in the presence of ATP EMPIAR-10755 (タイトル: MukBEF(E1407Q)-MatP-DNA in the presence of ATPData size: 8.5 TB Data #1: Unaligned multi-frame images of MukBEF(E1407Q)-MatP-DNA in the presence of ATP - Dataset 1 [micrographs - multiframe] Data #2: Unaligned multi-frame images of MukBEF(E1407Q)-MatP-DNA in the presence of ATP - Dataset 2 [micrographs - multiframe] Data #3: Unaligned multi-frame images of MukBEF(E1407Q)-MatP-DNA in the presence of ATP - Dataset 3, grid 1 [micrographs - multiframe] Data #4: Unaligned multi-frame images of MukBEF(E1407Q)-MatP-DNA in the presence of ATP - Dataset 3, grid 2 [micrographs - multiframe] Data #5: Unaligned multi-frame images of MukBEF(E1407Q)-MatP-DNA in the presence of ATP - Dataset 3, grid 3 [micrographs - multiframe]) |
- リンク
リンク
- 集合体
集合体
| 登録構造単位 | 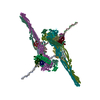
|
|---|---|
| 1 |
|
- 要素
要素
-Chromosome partition protein ... , 3種, 12分子 A1A2B1B2C1C2D1D2E1E2F1F2
| #1: タンパク質 | 分子量: 170240.188 Da / 分子数: 4 / 変異: E1407Q / 由来タイプ: 組換発現 由来: (組換発現)  Photorhabdus thracensis (バクテリア) Photorhabdus thracensis (バクテリア)遺伝子: mukB, VY86_15870 / 発現宿主:  #2: タンパク質 | 分子量: 50193.305 Da / 分子数: 4 / 由来タイプ: 組換発現 由来: (組換発現)  Photorhabdus thracensis (バクテリア) Photorhabdus thracensis (バクテリア)遺伝子: mukF, VY86_15860 / 発現宿主:  #3: タンパク質 | 分子量: 27423.848 Da / 分子数: 4 / 由来タイプ: 組換発現 由来: (組換発現)  Photorhabdus thracensis (バクテリア) Photorhabdus thracensis (バクテリア)遺伝子: mukE, VY86_15865 / 発現宿主:  |
|---|
-タンパク質 , 2種, 8分子 G1G2H1H2I1I2J1J2
| #4: タンパク質 | 分子量: 8645.460 Da / 分子数: 4 / 由来タイプ: 天然 / 由来: (天然)  #5: タンパク質 | 分子量: 18032.613 Da / 分子数: 4 / 由来タイプ: 組換発現 由来: (組換発現)  Photorhabdus thracensis (バクテリア) Photorhabdus thracensis (バクテリア)遺伝子: matP, VY86_22090 / 発現宿主:  |
|---|
-MatS2 DNA 80 b, oligo ... , 2種, 4分子 K1M1L1N1
| #6: DNA鎖 | 分子量: 24625.713 Da / 分子数: 2 / 由来タイプ: 合成 / 詳細: Synthetic sequence / 由来: (合成)  Photorhabdus thracensis (バクテリア) Photorhabdus thracensis (バクテリア)#7: DNA鎖 | 分子量: 24715.855 Da / 分子数: 2 / 由来タイプ: 合成 / 詳細: Synthetic sequence / 由来: (合成)  Photorhabdus thracensis (バクテリア) Photorhabdus thracensis (バクテリア) |
|---|
-非ポリマー , 3種, 12分子 

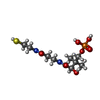


| #8: 化合物 | ChemComp-MG / #9: 化合物 | ChemComp-ATP / #10: 化合物 | ChemComp-PNS / |
|---|
-詳細
| 研究の焦点であるリガンドがあるか | N |
|---|
-実験情報
-実験
| 実験 | 手法: 電子顕微鏡法 |
|---|---|
| EM実験 | 試料の集合状態: PARTICLE / 3次元再構成法: 単粒子再構成法 |
- 試料調製
試料調製
| 構成要素 |
| ||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 分子量 | 実験値: NO | ||||||||||||||||||||||||||||||
| 由来(天然) |
| ||||||||||||||||||||||||||||||
| 由来(組換発現) |
| ||||||||||||||||||||||||||||||
| 緩衝液 | pH: 7.3 | ||||||||||||||||||||||||||||||
| 試料 | 包埋: NO / シャドウイング: NO / 染色: NO / 凍結: YES | ||||||||||||||||||||||||||||||
| 急速凍結 | 凍結剤: ETHANE |
- 電子顕微鏡撮影
電子顕微鏡撮影
| 実験機器 |  モデル: Titan Krios / 画像提供: FEI Company |
|---|---|
| 顕微鏡 | モデル: FEI TITAN KRIOS |
| 電子銃 | 電子線源:  FIELD EMISSION GUN / 加速電圧: 300 kV / 照射モード: OTHER FIELD EMISSION GUN / 加速電圧: 300 kV / 照射モード: OTHER |
| 電子レンズ | モード: BRIGHT FIELD |
| 撮影 | 電子線照射量: 40 e/Å2 / フィルム・検出器のモデル: GATAN K3 (6k x 4k) |
- 解析
解析
| ソフトウェア | 名称: UCSF ChimeraX / バージョン: 1.1/v9 / 分類: モデル構築 / URL: https://www.rbvi.ucsf.edu/chimerax/ / Os: Windows / タイプ: package |
|---|---|
| CTF補正 | タイプ: PHASE FLIPPING AND AMPLITUDE CORRECTION |
| 3次元再構成 | 解像度: 11 Å / 解像度の算出法: FSC 0.143 CUT-OFF / 粒子像の数: 8561 / 対称性のタイプ: POINT |
 ムービー
ムービー コントローラー
コントローラー















 PDBj
PDBj










































