+ データを開く
データを開く
- 基本情報
基本情報
| 登録情報 | データベース: PDB / ID: 5gan | ||||||
|---|---|---|---|---|---|---|---|
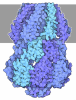
| タイトル | The overall structure of the yeast spliceosomal U4/U6.U5 tri-snRNP at 3.7 Angstrom | ||||||
 要素 要素 |
| ||||||
 キーワード キーワード | TRANSCRIPTION / pre-mRNA splicing / snRNP / GTPase / U5 snRNA / Prp8 / spliceosome / U4/U6 snRNP / Brr2 / Snu114 | ||||||
| 機能・相同性 |  機能・相同性情報 機能・相同性情報spliceosomal conformational changes to generate catalytic conformation / mRNA decay by 5' to 3' exoribonuclease / snoRNA splicing / maturation of 5S rRNA / snoRNA guided rRNA 2'-O-methylation / Lsm1-7-Pat1 complex / U6 snRNP / positive regulation of primary miRNA processing / positive regulation of RNA binding / generation of catalytic spliceosome for first transesterification step ...spliceosomal conformational changes to generate catalytic conformation / mRNA decay by 5' to 3' exoribonuclease / snoRNA splicing / maturation of 5S rRNA / snoRNA guided rRNA 2'-O-methylation / Lsm1-7-Pat1 complex / U6 snRNP / positive regulation of primary miRNA processing / positive regulation of RNA binding / generation of catalytic spliceosome for first transesterification step / box C/D sno(s)RNA 3'-end processing / deadenylation-dependent decapping of nuclear-transcribed mRNA / splicing factor binding / spliceosome conformational change to release U4 (or U4atac) and U1 (or U11) / P-body assembly / U4/U6 snRNP / 7-methylguanosine cap hypermethylation / pICln-Sm protein complex / small nuclear ribonucleoprotein complex / sno(s)RNA-containing ribonucleoprotein complex / SMN-Sm protein complex / spliceosomal tri-snRNP complex / U4 snRNA binding / poly(U) RNA binding / box C/D methylation guide snoRNP complex / mRNA cis splicing, via spliceosome / commitment complex / U2-type prespliceosome assembly / U2-type catalytic step 2 spliceosome / U4 snRNP / U2 snRNP / tRNA processing / U1 snRNP / U3 snoRNA binding / nuclear-transcribed mRNA catabolic process / U2-type prespliceosome / positive regulation of miRNA metabolic process / precatalytic spliceosome / Major pathway of rRNA processing in the nucleolus and cytosol / generation of catalytic spliceosome for second transesterification step / spliceosomal complex assembly / mRNA 5'-splice site recognition / mRNA 3'-splice site recognition / spliceosomal tri-snRNP complex assembly / U5 snRNA binding / U5 snRNP / U2 snRNA binding / U6 snRNA binding / spliceosomal snRNP assembly / pre-mRNA intronic binding / U1 snRNA binding / U4/U6 x U5 tri-snRNP complex / catalytic step 2 spliceosome / maturation of SSU-rRNA from tricistronic rRNA transcript (SSU-rRNA, 5.8S rRNA, LSU-rRNA) / maturation of LSU-rRNA / maturation of SSU-rRNA / small-subunit processome / spliceosomal complex / P-body / mRNA splicing, via spliceosome / rRNA processing / metallopeptidase activity / nucleic acid binding / cytosolic large ribosomal subunit / RNA helicase activity / RNA helicase / GTPase activity / mRNA binding / nucleolus / GTP binding / ATP hydrolysis activity / mitochondrion / RNA binding / nucleoplasm / ATP binding / identical protein binding / nucleus / cytoplasm / cytosol 類似検索 - 分子機能 | ||||||
| 生物種 |  | ||||||
| 手法 | 電子顕微鏡法 / 単粒子再構成法 / 解像度: 3.7 Å | ||||||
 データ登録者 データ登録者 | Nguyen, T.H.D. / Galej, W.P. / Bai, X.C. / Oubridge, C. / Scheres, S.H.W. / Newman, A.J. / Nagai, K. | ||||||
| 資金援助 |  英国, 1件 英国, 1件
| ||||||
 引用 引用 |  ジャーナル: Nature / 年: 2016 ジャーナル: Nature / 年: 2016タイトル: Cryo-EM structure of the yeast U4/U6.U5 tri-snRNP at 3.7 Å resolution. 著者: Thi Hoang Duong Nguyen / Wojciech P Galej / Xiao-Chen Bai / Chris Oubridge / Andrew J Newman / Sjors H W Scheres / Kiyoshi Nagai /  要旨: U4/U6.U5 tri-snRNP represents a substantial part of the spliceosome before activation. A cryo-electron microscopy structure of Saccharomyces cerevisiae U4/U6.U5 tri-snRNP at 3.7 Å resolution led ...U4/U6.U5 tri-snRNP represents a substantial part of the spliceosome before activation. A cryo-electron microscopy structure of Saccharomyces cerevisiae U4/U6.U5 tri-snRNP at 3.7 Å resolution led to an essentially complete atomic model comprising 30 proteins plus U4/U6 and U5 small nuclear RNAs (snRNAs). The structure reveals striking interweaving interactions of the protein and RNA components, including extended polypeptides penetrating into subunit interfaces. The invariant ACAGAGA sequence of U6 snRNA, which base-pairs with the 5'-splice site during catalytic activation, forms a hairpin stabilized by Dib1 and Prp8 while the adjacent nucleotides interact with the exon binding loop 1 of U5 snRNA. Snu114 harbours GTP, but its putative catalytic histidine is held away from the γ-phosphate by hydrogen bonding to a tyrosine in the amino-terminal domain of Prp8. Mutation of this histidine to alanine has no detectable effect on yeast growth. The structure provides important new insights into the spliceosome activation process leading to the formation of the catalytic centre. #1:  ジャーナル: Nature / 年: 2015 ジャーナル: Nature / 年: 2015タイトル: The architecture of the spliceosomal U4/U6.U5 tri-snRNP. 著者: Thi Hoang Duong Nguyen / Wojciech P Galej / Xiao-chen Bai / Christos G Savva / Andrew J Newman / Sjors H W Scheres / Kiyoshi Nagai /  要旨: U4/U6.U5 tri-snRNP is a 1.5-megadalton pre-assembled spliceosomal complex comprising U5 small nuclear RNA (snRNA), extensively base-paired U4/U6 snRNAs and more than 30 proteins, including the key ...U4/U6.U5 tri-snRNP is a 1.5-megadalton pre-assembled spliceosomal complex comprising U5 small nuclear RNA (snRNA), extensively base-paired U4/U6 snRNAs and more than 30 proteins, including the key components Prp8, Brr2 and Snu114. The tri-snRNP combines with a precursor messenger RNA substrate bound to U1 and U2 small nuclear ribonucleoprotein particles (snRNPs), and transforms into a catalytically active spliceosome after extensive compositional and conformational changes triggered by unwinding of the U4 and U6 (U4/U6) snRNAs. Here we use cryo-electron microscopy single-particle reconstruction of Saccharomyces cerevisiae tri-snRNP at 5.9 Å resolution to reveal the essentially complete organization of its RNA and protein components. The single-stranded region of U4 snRNA between its 3' stem-loop and the U4/U6 snRNA stem I is loaded into the Brr2 helicase active site ready for unwinding. Snu114 and the amino-terminal domain of Prp8 position U5 snRNA to insert its loop I, which aligns the exons for splicing, into the Prp8 active site cavity. The structure provides crucial insights into the activation process and the active site of the spliceosome. | ||||||
| 履歴 |
|
- 構造の表示
構造の表示
| ムービー |
 ムービービューア ムービービューア |
|---|---|
| 構造ビューア | 分子:  Molmil Molmil Jmol/JSmol Jmol/JSmol |
- ダウンロードとリンク
ダウンロードとリンク
- ダウンロード
ダウンロード
| PDBx/mmCIF形式 |  5gan.cif.gz 5gan.cif.gz | 1.8 MB | 表示 |  PDBx/mmCIF形式 PDBx/mmCIF形式 |
|---|---|---|---|---|
| PDB形式 |  pdb5gan.ent.gz pdb5gan.ent.gz | 1.4 MB | 表示 |  PDB形式 PDB形式 |
| PDBx/mmJSON形式 |  5gan.json.gz 5gan.json.gz | ツリー表示 |  PDBx/mmJSON形式 PDBx/mmJSON形式 | |
| その他 |  その他のダウンロード その他のダウンロード |
-検証レポート
| 文書・要旨 |  5gan_validation.pdf.gz 5gan_validation.pdf.gz | 1.4 MB | 表示 |  wwPDB検証レポート wwPDB検証レポート |
|---|---|---|---|---|
| 文書・詳細版 |  5gan_full_validation.pdf.gz 5gan_full_validation.pdf.gz | 1.5 MB | 表示 | |
| XML形式データ |  5gan_validation.xml.gz 5gan_validation.xml.gz | 223.6 KB | 表示 | |
| CIF形式データ |  5gan_validation.cif.gz 5gan_validation.cif.gz | 363.5 KB | 表示 | |
| アーカイブディレクトリ |  https://data.pdbj.org/pub/pdb/validation_reports/ga/5gan https://data.pdbj.org/pub/pdb/validation_reports/ga/5gan ftp://data.pdbj.org/pub/pdb/validation_reports/ga/5gan ftp://data.pdbj.org/pub/pdb/validation_reports/ga/5gan | HTTPS FTP |
-関連構造データ
| 関連構造データ |  8012MC  8006C  8007C  8008C  8009C  8010C  8011C  8013C  8014C  5gamC  5gaoC  5gapC M: このデータのモデリングに利用したマップデータ C: 同じ文献を引用 ( |
|---|---|
| 類似構造データ | |
| 電子顕微鏡画像生データ |  EMPIAR-10073 (タイトル: Cryo-EM structure of the yeast U4/U6.U5 tri-snRNP at 3.7 Angstrom (particle images) EMPIAR-10073 (タイトル: Cryo-EM structure of the yeast U4/U6.U5 tri-snRNP at 3.7 Angstrom (particle images)Data size: 75.2 Data #1: Aligned particle images of the yeast U4/U6.U5 tri-snRNP [picked particles - multiframe - processed]) |
- リンク
リンク
- 集合体
集合体
| 登録構造単位 | 
|
|---|---|
| 1 |
|
- 要素
要素
-RNA鎖 , 3種, 3分子 VWU
| #1: RNA鎖 | 分子量: 51186.023 Da / 分子数: 1 / 由来タイプ: 天然 / 由来: (天然)  |
|---|---|
| #2: RNA鎖 | 分子量: 35883.176 Da / 分子数: 1 / 由来タイプ: 天然 / 由来: (天然)  |
| #19: RNA鎖 | 分子量: 68643.344 Da / 分子数: 1 / 由来タイプ: 天然 / 由来: (天然)  |
-Pre-mRNA-splicing factor ... , 3種, 3分子 AJC
| #3: タンパク質 | 分子量: 279867.469 Da / 分子数: 1 / 由来タイプ: 天然 / 由来: (天然)  |
|---|---|
| #5: タンパク質 | 分子量: 104370.133 Da / 分子数: 1 / 由来タイプ: 天然 / 由来: (天然)  |
| #28: タンパク質 | 分子量: 114132.086 Da / 分子数: 1 / 由来タイプ: 天然 / 由来: (天然)  |
-U4/U6 small nuclear ribonucleoprotein ... , 2種, 2分子 HG
| #4: タンパク質 | 分子量: 52506.984 Da / 分子数: 1 / 由来タイプ: 天然 / 由来: (天然)  |
|---|---|
| #8: タンパク質 | 分子量: 55974.320 Da / 分子数: 1 / 由来タイプ: 天然 / 由来: (天然)  |
-タンパク質 , 7種, 8分子 DFBxkbEK
| #6: タンパク質 | 分子量: 16798.387 Da / 分子数: 1 / 由来タイプ: 天然 / 由来: (天然)  | ||||
|---|---|---|---|---|---|
| #7: タンパク質 | 分子量: 56382.516 Da / 分子数: 1 / 由来タイプ: 天然 / 由来: (天然)  | ||||
| #9: タンパク質 | 分子量: 246470.266 Da / 分子数: 1 / 由来タイプ: 天然 / 由来: (天然)  | ||||
| #10: タンパク質 | 分子量: 8528.504 Da / 分子数: 1 / 由来タイプ: 天然 / 由来: (天然)  | ||||
| #11: タンパク質 | 分子量: 22426.990 Da / 分子数: 2 / 由来タイプ: 天然 / 由来: (天然)  #18: タンパク質 | | 分子量: 28660.018 Da / 分子数: 1 / 由来タイプ: 天然 詳細: Snu66 is mostly fitted as polyAla into helices and extended polypeptides within the EM map. The authors do not believe that the sequence number is correct. 由来: (天然)  #20: タンパク質 | | 分子量: 13582.855 Da / 分子数: 1 / 由来タイプ: 天然 / 由来: (天然)  |
-Small nuclear ribonucleoprotein ... , 6種, 12分子 lhmjndpeqfrg
| #12: タンパク質 | 分子量: 16296.798 Da / 分子数: 2 / 由来タイプ: 天然 / 由来: (天然)  #13: タンパク質 | 分子量: 12876.066 Da / 分子数: 2 / 由来タイプ: 天然 / 由来: (天然)  #14: タンパク質 | 分子量: 11240.139 Da / 分子数: 2 / 由来タイプ: 天然 / 由来: (天然)  #15: タンパク質 | 分子量: 10385.098 Da / 分子数: 2 / 由来タイプ: 天然 / 由来: (天然)  #16: タンパク質 | 分子量: 9669.945 Da / 分子数: 2 / 由来タイプ: 天然 / 由来: (天然)  #17: タンパク質 | 分子量: 8490.809 Da / 分子数: 2 / 由来タイプ: 天然 / 由来: (天然)  |
|---|
-U6 snRNA-associated Sm-like protein ... , 7種, 7分子 2345678
| #21: タンパク質 | 分子量: 11177.888 Da / 分子数: 1 / 由来タイプ: 天然 / 由来: (天然)  |
|---|---|
| #22: タンパク質 | 分子量: 10039.262 Da / 分子数: 1 / 由来タイプ: 天然 / 由来: (天然)  |
| #23: タンパク質 | 分子量: 21298.070 Da / 分子数: 1 / 由来タイプ: 天然 / 由来: (天然)  |
| #24: タンパク質 | 分子量: 10432.954 Da / 分子数: 1 / 由来タイプ: 天然 / 由来: (天然)  |
| #25: タンパク質 | 分子量: 9406.579 Da / 分子数: 1 / 由来タイプ: 天然 / 由来: (天然)  |
| #26: タンパク質 | 分子量: 13027.045 Da / 分子数: 1 / 由来タイプ: 天然 / 由来: (天然)  |
| #27: タンパク質 | 分子量: 12403.378 Da / 分子数: 1 / 由来タイプ: 天然 / 由来: (天然)  |
-非ポリマー , 1種, 1分子 
| #29: 化合物 | ChemComp-GTP / |
|---|
-実験情報
-実験
| 実験 | 手法: 電子顕微鏡法 |
|---|---|
| EM実験 | 試料の集合状態: PARTICLE / 3次元再構成法: 単粒子再構成法 |
- 試料調製
試料調製
| 構成要素 | 名称: The overall structure of the yeast spliceosomal U4/U6.U5 tri-snRNP タイプ: COMPLEX / 詳細: 30 proteins and 3 snRNAs / Entity ID: all / 由来: NATURAL |
|---|---|
| 分子量 | 値: 1.5 MDa / 実験値: NO |
| 由来(天然) | 生物種:  |
| 緩衝液 | pH: 7.9 |
| 緩衝液成分 | 濃度: 1 mM / 名称: DTT |
| 試料 | 濃度: 0.2 mg/ml / 包埋: NO / シャドウイング: NO / 染色: NO / 凍結: NO |
| 試料支持 | 詳細: Grids are made of holey carbon, carbon-coated and glow discharged in N-amylamine. グリッドの材料: COPPER / グリッドのサイズ: 400 divisions/in. / グリッドのタイプ: Quantifoil R1.2/1.3 |
- 電子顕微鏡撮影
電子顕微鏡撮影
| 実験機器 |  モデル: Titan Krios / 画像提供: FEI Company |
|---|---|
| 顕微鏡 | モデル: FEI TITAN KRIOS |
| 電子銃 | 電子線源:  FIELD EMISSION GUN / 加速電圧: 300 kV / 照射モード: FLOOD BEAM FIELD EMISSION GUN / 加速電圧: 300 kV / 照射モード: FLOOD BEAM |
| 電子レンズ | モード: BRIGHT FIELD / 倍率(公称値): 81000 X / 倍率(補正後): 35714 X / 最大 デフォーカス(公称値): 3500 nm / 最小 デフォーカス(公称値): 500 nm / Cs: 2 mm |
| 試料ホルダ | 凍結剤: NITROGEN 試料ホルダーモデル: FEI TITAN KRIOS AUTOGRID HOLDER |
| 撮影 | 平均露光時間: 16 sec. / 電子線照射量: 38 e/Å2 / 検出モード: SUPER-RESOLUTION フィルム・検出器のモデル: GATAN K2 SUMMIT (4k x 4k) 実像数: 2477 |
| 電子光学装置 | エネルギーフィルター名称: GIF Quantum |
| 画像スキャン | 動画フレーム数/画像: 20 / 利用したフレーム数/画像: 1-20 |
- 解析
解析
| ソフトウェア | 名称: REFMAC / バージョン: 5.8.0124 / 分類: 精密化 | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| EMソフトウェア |
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| CTF補正 | タイプ: PHASE FLIPPING ONLY | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 粒子像の選択 | 選択した粒子像数: 473827 | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 対称性 | 点対称性: C1 (非対称) | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 3次元再構成 | 解像度: 3.7 Å / 解像度の算出法: FSC 0.143 CUT-OFF / 粒子像の数: 140155 / クラス平均像の数: 1 / 対称性のタイプ: POINT | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 原子モデル構築 | 空間: RECIPROCAL | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 精密化 | 解像度: 3.7→3.7 Å / Cor.coef. Fo:Fc: 0.974 / SU B: 26.326 / SU ML: 0.371 / ESU R: 0.409 立体化学のターゲット値: MAXIMUM LIKELIHOOD WITH PHASES 詳細: HYDROGENS HAVE BEEN ADDED IN THE RIDING POSITIONS
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 溶媒の処理 | 溶媒モデル: PARAMETERS FOR MASK CACLULATION | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 原子変位パラメータ | Biso mean: 397.886 Å2
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 精密化ステップ | サイクル: 1 / 合計: 77375 | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 拘束条件 |
|
 ムービー
ムービー コントローラー
コントローラー










 PDBj
PDBj