+ データを開く
データを開く
- 基本情報
基本情報
| 登録情報 | データベース: EMDB / ID: EMD-7059 | |||||||||
|---|---|---|---|---|---|---|---|---|---|---|
| タイトル | The cryo-EM structure of a bacterial class I transcription activation complex | |||||||||
 マップデータ マップデータ | Class I transcription activation complex | |||||||||
 試料 試料 |
| |||||||||
 キーワード キーワード | transcription / RNA polymerase / catabolite activator protein / cAMP / TRANSCRIPTION-TRANSFERASE-DNA-RNA complex | |||||||||
| 機能・相同性 |  機能・相同性情報 機能・相同性情報sigma factor antagonist complex / regulation of DNA-templated transcription initiation / sigma factor activity / cytosolic DNA-directed RNA polymerase complex / cAMP binding / DNA-directed RNA polymerase complex / DNA-templated transcription initiation / protein-DNA complex / ribonucleoside binding / DNA-directed RNA polymerase ...sigma factor antagonist complex / regulation of DNA-templated transcription initiation / sigma factor activity / cytosolic DNA-directed RNA polymerase complex / cAMP binding / DNA-directed RNA polymerase complex / DNA-templated transcription initiation / protein-DNA complex / ribonucleoside binding / DNA-directed RNA polymerase / DNA-directed RNA polymerase activity / response to heat / sequence-specific DNA binding / protein dimerization activity / transcription cis-regulatory region binding / DNA-binding transcription factor activity / negative regulation of DNA-templated transcription / regulation of DNA-templated transcription / DNA-templated transcription / positive regulation of DNA-templated transcription / magnesium ion binding / DNA binding / zinc ion binding / cytoplasm / cytosol 類似検索 - 分子機能 | |||||||||
| 生物種 |      | |||||||||
| 手法 | 単粒子再構成法 / クライオ電子顕微鏡法 / 解像度: 3.9 Å | |||||||||
 データ登録者 データ登録者 | Liu B / Hong C | |||||||||
| 資金援助 |  米国, 1件 米国, 1件
| |||||||||
 引用 引用 |  ジャーナル: Science / 年: 2017 ジャーナル: Science / 年: 2017タイトル: Structural basis of bacterial transcription activation. 著者: Bin Liu / Chuan Hong / Rick K Huang / Zhiheng Yu / Thomas A Steitz /  要旨: In bacteria, the activation of gene transcription at many promoters is simple and only involves a single activator. The cyclic adenosine 3',5'-monophosphate receptor protein (CAP), a classic ...In bacteria, the activation of gene transcription at many promoters is simple and only involves a single activator. The cyclic adenosine 3',5'-monophosphate receptor protein (CAP), a classic activator, is able to activate transcription independently through two different mechanisms. Understanding the class I mechanism requires an intact transcription activation complex (TAC) structure at a high resolution. Here we report a high-resolution cryo-electron microscopy structure of an intact class I TAC containing a CAP dimer, a σ-RNA polymerase (RNAP) holoenzyme, a complete class I CAP-dependent promoter DNA, and a de novo synthesized RNA oligonucleotide. The structure shows how CAP wraps the upstream DNA and how the interactions recruit RNAP. Our study provides a structural basis for understanding how activators activate transcription through the class I recruitment mechanism. | |||||||||
| 履歴 |
|
- 構造の表示
構造の表示
| ムービー |
 ムービービューア ムービービューア |
|---|---|
| 構造ビューア | EMマップ:  SurfView SurfView Molmil Molmil Jmol/JSmol Jmol/JSmol |
| 添付画像 |
- ダウンロードとリンク
ダウンロードとリンク
-EMDBアーカイブ
| マップデータ |  emd_7059.map.gz emd_7059.map.gz | 4.3 MB |  EMDBマップデータ形式 EMDBマップデータ形式 | |
|---|---|---|---|---|
| ヘッダ (付随情報) |  emd-7059-v30.xml emd-7059-v30.xml emd-7059.xml emd-7059.xml | 29.9 KB 29.9 KB | 表示 表示 |  EMDBヘッダ EMDBヘッダ |
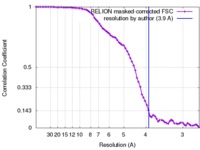
| FSC (解像度算出) |  emd_7059_fsc.xml emd_7059_fsc.xml | 7.1 KB | 表示 |  FSCデータファイル FSCデータファイル |
| 画像 |  emd_7059.png emd_7059.png | 76.8 KB | ||
| Filedesc metadata |  emd-7059.cif.gz emd-7059.cif.gz | 9.8 KB | ||
| アーカイブディレクトリ |  http://ftp.pdbj.org/pub/emdb/structures/EMD-7059 http://ftp.pdbj.org/pub/emdb/structures/EMD-7059 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-7059 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-7059 | HTTPS FTP |
-関連構造データ
- リンク
リンク
| EMDBのページ |  EMDB (EBI/PDBe) / EMDB (EBI/PDBe) /  EMDataResource EMDataResource |
|---|---|
| 「今月の分子」の関連する項目 |
- マップ
マップ
| ファイル |  ダウンロード / ファイル: emd_7059.map.gz / 形式: CCP4 / 大きさ: 30.5 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) ダウンロード / ファイル: emd_7059.map.gz / 形式: CCP4 / 大きさ: 30.5 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | Class I transcription activation complex | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 投影像・断面図 | 画像のコントロール
画像は Spider により作成 | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| ボクセルのサイズ | X=Y=Z: 1.35 Å | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 密度 |
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 対称性 | 空間群: 1 | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 詳細 | EMDB XML:
CCP4マップ ヘッダ情報:
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
-添付データ
- 試料の構成要素
試料の構成要素
+全体 : The complex of class-I bacterial transcription activation complex
+超分子 #1: The complex of class-I bacterial transcription activation complex
+分子 #1: DNA-directed RNA polymerase subunit alpha
+分子 #2: DNA-directed RNA polymerase subunit beta
+分子 #3: DNA-directed RNA polymerase subunit beta'
+分子 #4: DNA-directed RNA polymerase subunit omega
+分子 #5: RNA polymerase sigma factor RpoD
+分子 #6: cAMP-activated global transcriptional regulator CRP
+分子 #7: DNA-directed RNA polymerase subunit alpha
+分子 #8: SYNTHETIC NONTEMPLATE STRAND DNA (88-MER)
+分子 #9: SYNTHETIC TEMPLATE STRAND DNA (88-MER)
+分子 #10: NASCENT RNA 3-MER
+分子 #11: ZINC ION
+分子 #12: MAGNESIUM ION
+分子 #13: ADENOSINE-3',5'-CYCLIC-MONOPHOSPHATE
-実験情報
-構造解析
| 手法 | クライオ電子顕微鏡法 |
|---|---|
 解析 解析 | 単粒子再構成法 |
| 試料の集合状態 | particle |
- 試料調製
試料調製
| 濃度 | 3 mg/mL | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 緩衝液 | pH: 7.5 構成要素:
詳細: 20 mM TRIS pH 7.5, 50 mM sodium chloride, 0.1mM EDTA, 5 mM MgCl2, 5 mM DTT | ||||||||||||
| グリッド | モデル: Quantifoil R1.2/1.3 / 材質: GOLD / メッシュ: 400 / 前処理 - タイプ: GLOW DISCHARGE / 前処理 - 時間: 60 sec. / 前処理 - 雰囲気: AIR / 前処理 - 気圧: 0.038 kPa | ||||||||||||
| 凍結 | 凍結剤: ETHANE / チャンバー内湿度: 100 % / チャンバー内温度: 277 K / 装置: FEI VITROBOT MARK IV / 詳細: 3 second blotting. |
- 電子顕微鏡法
電子顕微鏡法
| 顕微鏡 | FEI TITAN KRIOS |
|---|---|
| 温度 | 最低: 80.0 K / 最高: 80.0 K |
| 特殊光学系 | エネルギーフィルター - 名称: GIF Quantum LS エネルギーフィルター - エネルギー下限: 0 eV エネルギーフィルター - エネルギー上限: 20 eV |
| 詳細 | Cs corrector |
| 撮影 | フィルム・検出器のモデル: GATAN K2 SUMMIT (4k x 4k) 検出モード: SUPER-RESOLUTION / デジタル化 - サイズ - 横: 7676 pixel / デジタル化 - サイズ - 縦: 7420 pixel / デジタル化 - 画像ごとのフレーム数: 1-40 / 撮影したグリッド数: 1 / 実像数: 2382 / 平均露光時間: 0.25 sec. / 平均電子線量: 1.37 e/Å2 |
| 電子線 | 加速電圧: 300 kV / 電子線源:  FIELD EMISSION GUN FIELD EMISSION GUN |
| 電子光学系 | C2レンズ絞り径: 70.0 µm / 最大 デフォーカス(補正後): 2.6 µm / 最小 デフォーカス(補正後): 1.2 µm / 倍率(補正後): 37037 / 照射モード: FLOOD BEAM / 撮影モード: BRIGHT FIELD / Cs: 0.01 mm / 最大 デフォーカス(公称値): 2.5 µm / 最小 デフォーカス(公称値): 1.3 µm / 倍率(公称値): 81000 |
| 試料ステージ | 試料ホルダーモデル: FEI TITAN KRIOS AUTOGRID HOLDER ホルダー冷却材: NITROGEN |
| 実験機器 |  モデル: Titan Krios / 画像提供: FEI Company |
+ 画像解析
画像解析
-原子モデル構築 1
| 精密化 | 空間: REAL / プロトコル: RIGID BODY FIT / 当てはまり具合の基準: correlation coefficient |
|---|---|
| 得られたモデル |  PDB-6b6h: |
 ムービー
ムービー コントローラー
コントローラー



















 Z (Sec.)
Z (Sec.) Y (Row.)
Y (Row.) X (Col.)
X (Col.)