+ データを開く
データを開く
- 基本情報
基本情報
| 登録情報 |  | |||||||||
|---|---|---|---|---|---|---|---|---|---|---|
| タイトル | A 3.3 angstrom cryo-EM structure of an engineered high-affinity human prothrombinase complex | |||||||||
 マップデータ マップデータ | unsharpened map | |||||||||
 試料 試料 |
| |||||||||
 キーワード キーワード | enzyme / complex / prothrombinase / BLOOD CLOTTING | |||||||||
| 機能・相同性 |  機能・相同性情報 機能・相同性情報response to vitamin K / coagulation factor Xa / platelet alpha granule / Cargo concentration in the ER / COPII-coated ER to Golgi transport vesicle / Defective factor IX causes thrombophilia / Defective cofactor function of FVIIIa variant / Defective F9 variant does not activate FX / COPII-mediated vesicle transport / : ...response to vitamin K / coagulation factor Xa / platelet alpha granule / Cargo concentration in the ER / COPII-coated ER to Golgi transport vesicle / Defective factor IX causes thrombophilia / Defective cofactor function of FVIIIa variant / Defective F9 variant does not activate FX / COPII-mediated vesicle transport / : / blood circulation / positive regulation of TOR signaling / Transport of gamma-carboxylated protein precursors from the endoplasmic reticulum to the Golgi apparatus / : / Gamma-carboxylation of protein precursors / Removal of aminoterminal propeptides from gamma-carboxylated proteins / : / endoplasmic reticulum-Golgi intermediate compartment membrane / platelet alpha granule lumen / Post-translational protein phosphorylation / phospholipid binding / Golgi lumen / Regulation of Insulin-like Growth Factor (IGF) transport and uptake by Insulin-like Growth Factor Binding Proteins (IGFBPs) / blood coagulation / Platelet degranulation / extracellular vesicle / positive regulation of cell migration / endoplasmic reticulum lumen / copper ion binding / serine-type endopeptidase activity / external side of plasma membrane / calcium ion binding / proteolysis / : / extracellular region / membrane / plasma membrane 類似検索 - 分子機能 | |||||||||
| 生物種 |  Homo sapiens (ヒト) Homo sapiens (ヒト) | |||||||||
| 手法 | 単粒子再構成法 / クライオ電子顕微鏡法 / 解像度: 3.28 Å | |||||||||
 データ登録者 データ登録者 | Huntington JA / Faille A / Ustok FI | |||||||||
| 資金援助 |  英国, 2件 英国, 2件
| |||||||||
 引用 引用 |  ジャーナル: Blood / 年: 2026 ジャーナル: Blood / 年: 2026タイトル: A 3.3-Å cryo-EM structure of an engineered high-affinity human prothrombinase complex. 著者: Fatma Işık Üstok / Alexandre Faille / James A Huntington /  要旨: Thrombin is generated from prothrombin through cleavage at 2 sites by the enzyme prothrombinase, composed of factor Xa (fXa) and fVa. The affinity of fXa for fVa is low, with assembly and function ...Thrombin is generated from prothrombin through cleavage at 2 sites by the enzyme prothrombinase, composed of factor Xa (fXa) and fVa. The affinity of fXa for fVa is low, with assembly and function dependent on phospholipid (PL) membranes. Some snakes have evolved venom versions of fXa that bind to fVa with high affinity and efficiently activate prothrombin in the absence of PL. We created a similar high-affinity, PL-independent human prothrombinase with 17 mutations to human fXa (M17). The increase in affinity enabled cryogenic electron microscopy (cryo-EM) structure determination of M17-prothrombinase to a resolution of 3.3 Å. All protein domains were well resolved in the map, except for the γ-carboxyglutamic acid domain of fXa. The main contacts involve the serine protease and epidermal growth factor-like domain 2 (EGF2) domains of fXa and the A2 and A3 domains of fVa, resulting in the burying of a total surface area of 4900 Å2. The map is of sufficient quality to resolve side-chain interactions, including several key M17 mutations. To aid in the placement of the loop C-terminal to the A2 domain (a2-loop), we solved a high-resolution crystal structure of fXa in complex with a synthetic a2 peptide. The acidic a2-loop interacts with the basic heparin-binding site of fXa, involving a conserved antiparallel β-strand interaction. The M17-prothrombinase structure is compatible with data from biochemical and mutagenesis research and provides important new insights into the assembly and function of the prothrombinase complex. | |||||||||
| 履歴 |
|
- 構造の表示
構造の表示
| 添付画像 |
|---|
- ダウンロードとリンク
ダウンロードとリンク
-EMDBアーカイブ
| マップデータ |  emd_52585.map.gz emd_52585.map.gz | 162.2 MB |  EMDBマップデータ形式 EMDBマップデータ形式 | |
|---|---|---|---|---|
| ヘッダ (付随情報) |  emd-52585-v30.xml emd-52585-v30.xml emd-52585.xml emd-52585.xml | 26.6 KB 26.6 KB | 表示 表示 |  EMDBヘッダ EMDBヘッダ |
| FSC (解像度算出) |  emd_52585_fsc.xml emd_52585_fsc.xml | 14.6 KB | 表示 |  FSCデータファイル FSCデータファイル |
| 画像 |  emd_52585.png emd_52585.png | 74.8 KB | ||
| Filedesc metadata |  emd-52585.cif.gz emd-52585.cif.gz | 8 KB | ||
| その他 |  emd_52585_additional_1.map.gz emd_52585_additional_1.map.gz emd_52585_half_map_1.map.gz emd_52585_half_map_1.map.gz emd_52585_half_map_2.map.gz emd_52585_half_map_2.map.gz | 304.5 MB 301.9 MB 301.8 MB | ||
| アーカイブディレクトリ |  http://ftp.pdbj.org/pub/emdb/structures/EMD-52585 http://ftp.pdbj.org/pub/emdb/structures/EMD-52585 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-52585 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-52585 | HTTPS FTP |
-関連構造データ
| 関連構造データ |  9i2hMC  9i24C M: このマップから作成された原子モデル C: 同じ文献を引用 ( |
|---|---|
| 類似構造データ | 類似検索 - 機能・相同性  F&H 検索 F&H 検索 |
- リンク
リンク
| EMDBのページ |  EMDB (EBI/PDBe) / EMDB (EBI/PDBe) /  EMDataResource EMDataResource |
|---|---|
| 「今月の分子」の関連する項目 |
- マップ
マップ
| ファイル |  ダウンロード / ファイル: emd_52585.map.gz / 形式: CCP4 / 大きさ: 325 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) ダウンロード / ファイル: emd_52585.map.gz / 形式: CCP4 / 大きさ: 325 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) | ||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | unsharpened map | ||||||||||||||||||||||||||||||||||||
| 投影像・断面図 | 画像のコントロール
画像は Spider により作成 | ||||||||||||||||||||||||||||||||||||
| ボクセルのサイズ | X=Y=Z: 0.83 Å | ||||||||||||||||||||||||||||||||||||
| 密度 |
| ||||||||||||||||||||||||||||||||||||
| 対称性 | 空間群: 1 | ||||||||||||||||||||||||||||||||||||
| 詳細 | EMDB XML:
|
-添付データ
-追加マップ: sharpened map
| ファイル | emd_52585_additional_1.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | sharpened map | ||||||||||||
| 投影像・断面図 |
| ||||||||||||
| 密度ヒストグラム |
-ハーフマップ: half map 2
| ファイル | emd_52585_half_map_1.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | half map 2 | ||||||||||||
| 投影像・断面図 |
| ||||||||||||
| 密度ヒストグラム |
-ハーフマップ: half map 1
| ファイル | emd_52585_half_map_2.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | half map 1 | ||||||||||||
| 投影像・断面図 |
| ||||||||||||
| 密度ヒストグラム |
- 試料の構成要素
試料の構成要素
-全体 : prothrombinase, a complex of fVa and fXa
| 全体 | 名称: prothrombinase, a complex of fVa and fXa |
|---|---|
| 要素 |
|
-超分子 #1: prothrombinase, a complex of fVa and fXa
| 超分子 | 名称: prothrombinase, a complex of fVa and fXa / タイプ: complex / ID: 1 / 親要素: 0 / 含まれる分子: #1-#4 詳細: M17-prothrombinase was formed by mixing fVa with EGRCK-inhibited M17-fXa at a 1:6 molar ratio with a final concentration of 1.68uM in 20mM HEPES pH 7.5, 150mM NaCl and 5mM CaCl2 |
|---|---|
| 由来(天然) | 生物種:  Homo sapiens (ヒト) Homo sapiens (ヒト) |
-分子 #1: Activated factor Xa heavy chain
| 分子 | 名称: Activated factor Xa heavy chain / タイプ: protein_or_peptide / ID: 1 詳細: Mutations given using chymotrypsin template numbering as in the coordinates. コピー数: 1 / 光学異性体: LEVO |
|---|---|
| 由来(天然) | 生物種:  Homo sapiens (ヒト) Homo sapiens (ヒト) |
| 分子量 | 理論値: 28.789916 KDa |
| 組換発現 | 生物種:  Cytomegalovirus (ウイルス) Cytomegalovirus (ウイルス) |
| 配列 | 文字列: IVGGQECKDG ECPWQALLIN EENEGFCGGT ILSEFYILTA AHCLYQAKRF KVRVGDRNTE QEEGGEAVHE VEVVIKHNRF TKETYDFDI AVLRLKTPIT FRMNVAPACL PERDWANETL MKQDTGIVSG FGRTHEKGRQ STRLKMLEVP YVDRHSCMLS S DFRITQNM ...文字列: IVGGQECKDG ECPWQALLIN EENEGFCGGT ILSEFYILTA AHCLYQAKRF KVRVGDRNTE QEEGGEAVHE VEVVIKHNRF TKETYDFDI AVLRLKTPIT FRMNVAPACL PERDWANETL MKQDTGIVSG FGRTHEKGRQ STRLKMLEVP YVDRHSCMLS S DFRITQNM FCAGYDTKQE DACQGDSGGP HVTRFKDTYF VTGIVSWGEG CARKGKYGIY TKVTRFLKWI KRSMKTRGLP KA KSHAPEV ITSSPLK UniProtKB: Coagulation factor X |
-分子 #2: Factor X light chain
| 分子 | 名称: Factor X light chain / タイプ: protein_or_peptide / ID: 2 / コピー数: 1 / 光学異性体: LEVO |
|---|---|
| 由来(天然) | 生物種:  Homo sapiens (ヒト) Homo sapiens (ヒト) |
| 分子量 | 理論値: 15.765613 KDa |
| 組換発現 | 生物種:  Cytomegalovirus (ウイルス) Cytomegalovirus (ウイルス) |
| 配列 | 文字列: ANSFLEEMKK GHLERECMEE TCSYEEAREV FEDSDKTNEF WNKYKDGDQC ETSPCQNQGK CKDGLGEYTC TCLEGFEGKN CELFTRKLC RAFNGDCDQF CKRVQSSVVC SCARGYTLAD NGKACIPTGP YPCGKQTLER UniProtKB: Coagulation factor X |
-分子 #3: Coagulation factor V heavy chain
| 分子 | 名称: Coagulation factor V heavy chain / タイプ: protein_or_peptide / ID: 3 / 詳細: TYS is a sulphated Tyrosine. / コピー数: 1 / 光学異性体: LEVO |
|---|---|
| 由来(天然) | 生物種:  Homo sapiens (ヒト) Homo sapiens (ヒト) |
| 分子量 | 理論値: 81.354453 KDa |
| 組換発現 | 生物種: unidentified plasmid (未定義) |
| 配列 | 文字列: AQLRQFYVAA QGISWSYRPE PTNSSLNLSV TSFKKIVYRE YEPYFKKEKP QSTISGLLGP TLYAEVGDII KVHFKNKADK PLSIHPQGI RYSKLSEGAS YLDHTFPAEK MDDAVAPGRE YTYEWSISED SGPTHDDPPC LTHIYYSHEN LIEDFNSGLI G PLLICKKG ...文字列: AQLRQFYVAA QGISWSYRPE PTNSSLNLSV TSFKKIVYRE YEPYFKKEKP QSTISGLLGP TLYAEVGDII KVHFKNKADK PLSIHPQGI RYSKLSEGAS YLDHTFPAEK MDDAVAPGRE YTYEWSISED SGPTHDDPPC LTHIYYSHEN LIEDFNSGLI G PLLICKKG TLTEGGTQKT FDKQIVLLFA VFDESKSWSQ SSSLMYTVNG YVNGTMPDIT VCAHDHISWH LLGMSSGPEL FS IHFNGQV LEQNHHKVSA ITLVSATSTT ANMTVGPEGK WIISSLTPKH LQAGMQAYID IKNCPKKTRN LKKITREQRR HMK RWEYFI AAEEVIWDYA PVIPANMDKK YRSQHLDNFS NQIGKHYKKV MYTQYEDESF TKHTVNPNMK EDGILGPIIR AQVR DTLKI VFKNMASRPY SIYPHGVTFS PYEDEVNSSF TSGRNNTMIR AVQPGETYTY KWNILEFDEP TENDAQCLTR PYYSD VDIM RDIASGLIGL LLICKSRSLD RRGIQRAADI EQQAVFAVFD ENKSWYLEDN INKFCENPDE VKRDDPKFYE SNIMST ING YVPESITTLG FCFDDTVQWH FCSVGTQNEI LTIHFTGHSF IYGKRHEDTL TLFPMRGESV TVTMDNVGTW MLTSMNS SP RSKKLRLKFR DVKCIPDDDE DS(TYS)EIFEPPE STVMATRKMH DRLEPEDEES DADYDYQNRL AAALGIR UniProtKB: Coagulation factor V |
-分子 #4: Coagulation factor V light chain
| 分子 | 名称: Coagulation factor V light chain / タイプ: protein_or_peptide / ID: 4 / コピー数: 1 / 光学異性体: LEVO |
|---|---|
| 由来(天然) | 生物種:  Homo sapiens (ヒト) Homo sapiens (ヒト) |
| 分子量 | 理論値: 75.283008 KDa |
| 組換発現 | 生物種: unidentified plasmid (未定義) |
| 配列 | 文字列: SNNGNRRNYY IAAEEISWDY SEFVQRETDI EDSDDIPEDT TYKKVVFRKY LDSTFTKRDP RGEYEEHLGI LGPIIRAEVD DVIQVRFKN LASRPYSLHA HGLSYEKSSE GKTYEDDSPE WFKEDNAVQP NSSYTYVWHA TERSGPESPG SACRAWAYYS A VNPEKDIH ...文字列: SNNGNRRNYY IAAEEISWDY SEFVQRETDI EDSDDIPEDT TYKKVVFRKY LDSTFTKRDP RGEYEEHLGI LGPIIRAEVD DVIQVRFKN LASRPYSLHA HGLSYEKSSE GKTYEDDSPE WFKEDNAVQP NSSYTYVWHA TERSGPESPG SACRAWAYYS A VNPEKDIH SGLIGPLLIC QKGILHKDSN MPMDMREFVL LFMTFDEKKS WYYEKKSRSS WRLTSSEMKK SHEFHAINGM IY SLPGLKM YEQEWVRLHL LNIGGSQDIH VVHFHGQTLL ENGNKQHQLG VWPLLPGSFK TLEMKASKPG WWLLNTEVGE NQR AGMQTP FLIMDRDCRM PMGLSTGIIS DSQIKASEFL GYWEPRLARL NNGGSYNAWS VEKLAAEFAS KPWIQVDMQK EVII TGIQT QGAKHYLKSC YTTEFYVAYS SNQINWQIFK GNSTRNVMYF NGNSDASTIK ENQFDPPIVA RYIRISPTRA YNRPT LRLE LQGCEVNGCS TPLGMENGKI ENKQITASSF KKSWWGDYWE PFRARLNAQG RVNAWQAKAN NNKQWLEIDL LKIKKI TAI ITQGCKSLSS EMYVKSYTIH YSEQGVEWKP YRLKSSMVDK IFEGNTNTKG HVKNFFNPPI ISRFIRVIPK TWNQSIA LR LELFGCDIY UniProtKB: Coagulation factor V |
-分子 #9: CALCIUM ION
| 分子 | 名称: CALCIUM ION / タイプ: ligand / ID: 9 / コピー数: 2 / 式: CA |
|---|---|
| 分子量 | 理論値: 40.078 Da |
-分子 #10: SODIUM ION
| 分子 | 名称: SODIUM ION / タイプ: ligand / ID: 10 / コピー数: 1 |
|---|---|
| 分子量 | 理論値: 22.99 Da |
-分子 #11: L-alpha-glutamyl-N-{(1S)-4-{[amino(iminio)methyl]amino}-1-[(1S)-2...
| 分子 | 名称: L-alpha-glutamyl-N-{(1S)-4-{[amino(iminio)methyl]amino}-1-[(1S)-2-chloro-1-hydroxyethyl]butyl}glycinamide タイプ: ligand / ID: 11 / コピー数: 1 / 式: 0GJ |
|---|---|
| 分子量 | 理論値: 395.862 Da |
| Chemical component information | 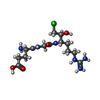 ChemComp-0GJ: |
-分子 #12: COPPER (II) ION
| 分子 | 名称: COPPER (II) ION / タイプ: ligand / ID: 12 / コピー数: 1 / 式: CU |
|---|---|
| 分子量 | 理論値: 63.546 Da |
| Chemical component information |  ChemComp-CU: |
-実験情報
-構造解析
| 手法 | クライオ電子顕微鏡法 |
|---|---|
 解析 解析 | 単粒子再構成法 |
| 試料の集合状態 | particle |
- 試料調製
試料調製
| 緩衝液 | pH: 7.5 / 詳細: 20mM HEPES, 150mM NaCl and 5mM CaCl2 |
|---|---|
| グリッド | モデル: Quantifoil R0.6/1 / 材質: GOLD / メッシュ: 300 / 前処理 - タイプ: GLOW DISCHARGE / 前処理 - 時間: 60 sec. / 前処理 - 雰囲気: AIR / 前処理 - 気圧: 0.025 kPa / 詳細: using a Pelco EasiGlow |
| 凍結 | 凍結剤: ETHANE / 装置: FEI VITROBOT MARK IV |
| 詳細 | M17-prothrombinase was formed by mixing fVa with EGRCK-inhibited M17-fXa at a 1:6 molar ratio with a final concentration of 1.68uM |
- 電子顕微鏡法
電子顕微鏡法
| 顕微鏡 | TFS KRIOS |
|---|---|
| 撮影 | フィルム・検出器のモデル: GATAN K3 (6k x 4k) / 平均電子線量: 45.74 e/Å2 |
| 電子線 | 加速電圧: 300 kV / 電子線源:  FIELD EMISSION GUN FIELD EMISSION GUN |
| 電子光学系 | 照射モード: FLOOD BEAM / 撮影モード: BRIGHT FIELD / 最大 デフォーカス(公称値): 2.0 µm / 最小 デフォーカス(公称値): 1.0 µm |
| 実験機器 |  モデル: Titan Krios / 画像提供: FEI Company |
 ムービー
ムービー コントローラー
コントローラー
















 Z (Sec.)
Z (Sec.) Y (Row.)
Y (Row.) X (Col.)
X (Col.)













































