+ データを開く
データを開く
- 基本情報
基本情報
| 登録情報 | データベース: EMDB / ID: EMD-4919 | |||||||||
|---|---|---|---|---|---|---|---|---|---|---|
| タイトル | STRUCTURE OF THE MECHANOSENSITIVE CHANNEL MSCS EMBEDDED IN THE MEMBRANE BILAYER | |||||||||
 マップデータ マップデータ | RELION post-processed map; no mask; applied b-factor of -139; new box 250 px | |||||||||
 試料 試料 |
| |||||||||
 キーワード キーワード |  MEMBRANE PROTEIN (膜タンパク質) / CHANNEL / MECHANOSENSITIVE MEMBRANE PROTEIN (膜タンパク質) / CHANNEL / MECHANOSENSITIVE | |||||||||
| 機能・相同性 |  機能・相同性情報 機能・相同性情報intracellular water homeostasis / mechanosensitive monoatomic ion channel activity / monoatomic ion transmembrane transport / protein homooligomerization /  生体膜 / identical protein binding / 生体膜 / identical protein binding /  細胞膜 細胞膜類似検索 - 分子機能 | |||||||||
| 生物種 |   Escherichia coli K-12 (大腸菌) Escherichia coli K-12 (大腸菌) | |||||||||
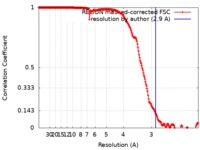
| 手法 |  単粒子再構成法 / 解像度: 2.9 Å 単粒子再構成法 / 解像度: 2.9 Å | |||||||||
 データ登録者 データ登録者 | Rasmussen T / Flegler VJ | |||||||||
| 資金援助 |  ドイツ, 2件 ドイツ, 2件
| |||||||||
 引用 引用 |  ジャーナル: J Mol Biol / 年: 2019 ジャーナル: J Mol Biol / 年: 2019タイトル: Structure of the Mechanosensitive Channel MscS Embedded in the Membrane Bilayer. 著者: Tim Rasmussen / Vanessa J Flegler / Akiko Rasmussen / Bettina Böttcher /  要旨: Since life has emerged, gradients of osmolytes over the cell membrane cause pressure changes in the cell and require tight regulation to prevent cell rupture. The mechanosensitive channel of small ...Since life has emerged, gradients of osmolytes over the cell membrane cause pressure changes in the cell and require tight regulation to prevent cell rupture. The mechanosensitive channel of small conductance (MscS) releases solutes and water when a hypo-osmotic shock raises the pressure in the cell. It is a member of a large family of MscS-like channels found in bacteria, archaea, fungi and plants and model for mechanosensation. MscS senses the increase of tension in the membrane directly by the force from the lipids, but the molecular mechanism is still elusive. We determined the lipid interactions of MscS by resolving the structure of Escherichia coli MscS embedded in membrane discs to 2.9-Å resolution using cryo-electron microscopy. The membrane is attached only to parts of the sensor paddles of MscS, but phospholipid molecules move through grooves into remote pockets on the cytosolic side. On the periplasmic side, a lipid bound by R88 at the pore entrance is separated from the membrane by TM1 helices. The N-terminus interacts with the periplasmic membrane surface. We demonstrate that the unique membrane domain of MscS promotes deep penetration of lipid molecules and shows multimodal interaction with the membrane to fine-tune tension sensing. | |||||||||
| 履歴 |
|
- 構造の表示
構造の表示
| ムービー |
 ムービービューア ムービービューア |
|---|---|
| 構造ビューア | EMマップ:  SurfView SurfView Molmil Molmil Jmol/JSmol Jmol/JSmol |
| 添付画像 |
- ダウンロードとリンク
ダウンロードとリンク
-EMDBアーカイブ
| マップデータ |  emd_4919.map.gz emd_4919.map.gz | 55.2 MB |  EMDBマップデータ形式 EMDBマップデータ形式 | |
|---|---|---|---|---|
| ヘッダ (付随情報) |  emd-4919-v30.xml emd-4919-v30.xml emd-4919.xml emd-4919.xml | 17.6 KB 17.6 KB | 表示 表示 |  EMDBヘッダ EMDBヘッダ |
| FSC (解像度算出) |  emd_4919_fsc.xml emd_4919_fsc.xml | 21.1 KB | 表示 |  FSCデータファイル FSCデータファイル |
| 画像 |  emd_4919.png emd_4919.png | 52.2 KB | ||
| Filedesc metadata |  emd-4919.cif.gz emd-4919.cif.gz | 5.4 KB | ||
| その他 |  emd_4919_half_map_1.map.gz emd_4919_half_map_1.map.gz emd_4919_half_map_2.map.gz emd_4919_half_map_2.map.gz | 54 MB 54.1 MB | ||
| アーカイブディレクトリ |  http://ftp.pdbj.org/pub/emdb/structures/EMD-4919 http://ftp.pdbj.org/pub/emdb/structures/EMD-4919 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-4919 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-4919 | HTTPS FTP |
-関連構造データ
- リンク
リンク
| EMDBのページ |  EMDB (EBI/PDBe) / EMDB (EBI/PDBe) /  EMDataResource EMDataResource |
|---|---|
| 「今月の分子」の関連する項目 |
- マップ
マップ
| ファイル |  ダウンロード / ファイル: emd_4919.map.gz / 形式: CCP4 / 大きさ: 59.6 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) ダウンロード / ファイル: emd_4919.map.gz / 形式: CCP4 / 大きさ: 59.6 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | RELION post-processed map; no mask; applied b-factor of -139; new box 250 px | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| ボクセルのサイズ | X=Y=Z: 1.0635 Å | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 密度 |
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 対称性 | 空間群: 1 | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 詳細 | EMDB XML:
CCP4マップ ヘッダ情報:
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
-添付データ
-ハーフマップ: RELION unfiltered half map; last refinement; new box 250 px
| ファイル | emd_4919_half_map_1.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | RELION unfiltered half map; last refinement; new box 250 px | ||||||||||||
| 投影像・断面図 |
| ||||||||||||
| 密度ヒストグラム |
-ハーフマップ: RELION unfiltered half map; last refinement; new box 250 px
| ファイル | emd_4919_half_map_2.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | RELION unfiltered half map; last refinement; new box 250 px | ||||||||||||
| 投影像・断面図 |
| ||||||||||||
| 密度ヒストグラム |
- 試料の構成要素
試料の構成要素
-全体 : MSCS IN NANODISCS
| 全体 | 名称: MSCS IN NANODISCS Microsoft Clustering Service Microsoft Clustering Service |
|---|---|
| 要素 |
|
-超分子 #1: MSCS IN NANODISCS
| 超分子 | 名称: MSCS IN NANODISCS / タイプ: complex / ID: 1 / 親要素: 0 / 含まれる分子: #1 / 詳細: MSCS WITH MSP1E3D1 AND AZOLECTINE |
|---|---|
| 由来(天然) | 生物種:   Escherichia coli K-12 (大腸菌) Escherichia coli K-12 (大腸菌) |
-分子 #1: Small-conductance mechanosensitive channel
| 分子 | 名称: Small-conductance mechanosensitive channel / タイプ: protein_or_peptide / ID: 1 / コピー数: 7 / 光学異性体: LEVO |
|---|---|
| 由来(天然) | 生物種:   Escherichia coli K-12 (大腸菌) Escherichia coli K-12 (大腸菌) |
| 分子量 | 理論値: 30.922898 KDa |
| 配列 | 文字列: MEDLNVVDSI NGAGSWLVAN QALLLSYAVN IVAALAIIIV GLIIARMISN AVNRLMISRK IDATVADFLS ALVRYGIIAF TLIAALGRV GVQTASVIAV LGAAGLAVGL ALQGSLSNLA AGVLLVMFRP FRAGEYVDLG GVAGTVLSVQ IFSTTMRTAD G KIIVIPNG ...文字列: MEDLNVVDSI NGAGSWLVAN QALLLSYAVN IVAALAIIIV GLIIARMISN AVNRLMISRK IDATVADFLS ALVRYGIIAF TLIAALGRV GVQTASVIAV LGAAGLAVGL ALQGSLSNLA AGVLLVMFRP FRAGEYVDLG GVAGTVLSVQ IFSTTMRTAD G KIIVIPNG KIIAGNIINF SREPVRRNEF IIGVAYDSDI DQVKQILTNI IQSEDRILKD REMTVRLNEL GASSINFVVR VW SNSGDLQ NVYWDVLERI KREFDAAGIS FPYPQMDVNF KRVKEDKAA UniProtKB: Small-conductance mechanosensitive channel |
-分子 #2: 1,2-DIOLEOYL-SN-GLYCERO-3-PHOSPHOCHOLINE
| 分子 | 名称: 1,2-DIOLEOYL-SN-GLYCERO-3-PHOSPHOCHOLINE / タイプ: ligand / ID: 2 / コピー数: 21 / 式: PCW |
|---|---|
| 分子量 | 理論値: 787.121 Da |
| Chemical component information |  ChemComp-PCW: |
-実験情報
-構造解析
 解析 解析 |  単粒子再構成法 単粒子再構成法 |
|---|---|
| 試料の集合状態 | particle |
- 試料調製
試料調製
| 濃度 | 0.40 mg/mL |
|---|---|
| 緩衝液 | pH: 7.5 |
| グリッド | 詳細: QUANTIFOIL R1.2/1.3 |
- 電子顕微鏡法
電子顕微鏡法
| 顕微鏡 | FEI TITAN KRIOS |
|---|---|
| 電子線 | 加速電圧: 300 kV / 電子線源:  FIELD EMISSION GUN FIELD EMISSION GUN |
| 電子光学系 | C2レンズ絞り径: 70.0 µm / 照射モード: FLOOD BEAM / 撮影モード: BRIGHT FIELD Bright-field microscopy / Cs: 2.7 mm / 最大 デフォーカス(公称値): 2.4 µm / 最小 デフォーカス(公称値): 0.9 µm / 倍率(公称値): 75000 Bright-field microscopy / Cs: 2.7 mm / 最大 デフォーカス(公称値): 2.4 µm / 最小 デフォーカス(公称値): 0.9 µm / 倍率(公称値): 75000 |
| 試料ステージ | 試料ホルダーモデル: FEI TITAN KRIOS AUTOGRID HOLDER ホルダー冷却材: NITROGEN |
| 撮影 | #0 - Image recording ID: 1 #0 - フィルム・検出器のモデル: FEI FALCON III (4k x 4k) #0 - 検出モード: COUNTING / #0 - 実像数: 4160 / #0 - 平均電子線量: 50.0 e/Å2 / #1 - Image recording ID: 2 #1 - フィルム・検出器のモデル: FEI FALCON III (4k x 4k) #1 - 検出モード: COUNTING / #1 - 実像数: 1133 / #1 - 平均電子線量: 56.0 e/Å2 / #2 - Image recording ID: 3 #2 - フィルム・検出器のモデル: FEI FALCON III (4k x 4k) #2 - 検出モード: INTEGRATING / #2 - 実像数: 3086 / #2 - 平均電子線量: 75.0 e/Å2 / #3 - Image recording ID: 4 #3 - フィルム・検出器のモデル: FEI FALCON III (4k x 4k) #3 - 検出モード: INTEGRATING / #3 - 実像数: 3738 / #3 - 平均電子線量: 100.0 e/Å2 |
| 実験機器 |  モデル: Titan Krios / 画像提供: FEI Company |
 ムービー
ムービー コントローラー
コントローラー














 Z
Z Y
Y X
X