+ データを開く
データを開く
- 基本情報
基本情報
| 登録情報 |  | |||||||||
|---|---|---|---|---|---|---|---|---|---|---|
| タイトル | Short chain dehydrogenase (SCR) cryoEM structure with NADP and ethyl 4-chloroacetoacetate | |||||||||
 マップデータ マップデータ | ||||||||||
 試料 試料 |
| |||||||||
 キーワード キーワード | Rossman fold / tetramer / tag-free / wild type with NADPH / OXIDOREDUCTASE | |||||||||
| 機能・相同性 | 酸化還元酵素; CH-OHの結合に対し酸化酵素として働く; NAD又はNADPを用いる / Enoyl-(Acyl carrier protein) reductase / Short-chain dehydrogenase/reductase SDR / oxidoreductase activity / NAD(P)-binding domain superfamily / Carbonyl Reductase 機能・相同性情報 機能・相同性情報 | |||||||||
| 生物種 |  Candida parapsilosis (酵母) Candida parapsilosis (酵母) | |||||||||
| 手法 | 単粒子再構成法 / クライオ電子顕微鏡法 / 解像度: 3.13 Å | |||||||||
 データ登録者 データ登録者 | Li YH / Zhang RZ | |||||||||
| 資金援助 |  中国, 2件 中国, 2件
| |||||||||
 引用 引用 |  ジャーナル: EMBO J / 年: 2022 ジャーナル: EMBO J / 年: 2022タイトル: Oligomeric interactions maintain active-site structure in a noncooperative enzyme family. 著者: Yaohui Li / Rongzhen Zhang / Chi Wang / Farhad Forouhar / Oliver B Clarke / Sergey Vorobiev / Shikha Singh / Gaetano T Montelione / Thomas Szyperski / Yan Xu / John F Hunt /   要旨: The evolutionary benefit accounting for widespread conservation of oligomeric structures in proteins lacking evidence of intersubunit cooperativity remains unclear. Here, crystal and cryo-EM ...The evolutionary benefit accounting for widespread conservation of oligomeric structures in proteins lacking evidence of intersubunit cooperativity remains unclear. Here, crystal and cryo-EM structures, and enzymological data, demonstrate that a conserved tetramer interface maintains the active-site structure in one such class of proteins, the short-chain dehydrogenase/reductase (SDR) superfamily. Phylogenetic comparisons support a significantly longer polypeptide being required to maintain an equivalent active-site structure in the context of a single subunit. Oligomerization therefore enhances evolutionary fitness by reducing the metabolic cost of enzyme biosynthesis. The large surface area of the structure-stabilizing oligomeric interface yields a synergistic gain in fitness by increasing tolerance to activity-enhancing yet destabilizing mutations. We demonstrate that two paralogous SDR superfamily enzymes with different specificities can form mixed heterotetramers that combine their individual enzymological properties. This suggests that oligomerization can also diversify the functions generated by a given metabolic investment, enhancing the fitness advantage provided by this architectural strategy. | |||||||||
| 履歴 |
|
- 構造の表示
構造の表示
| 添付画像 |
|---|
- ダウンロードとリンク
ダウンロードとリンク
-EMDBアーカイブ
| マップデータ |  emd_32211.map.gz emd_32211.map.gz | 59.7 MB |  EMDBマップデータ形式 EMDBマップデータ形式 | |
|---|---|---|---|---|
| ヘッダ (付随情報) |  emd-32211-v30.xml emd-32211-v30.xml emd-32211.xml emd-32211.xml | 12 KB 12 KB | 表示 表示 |  EMDBヘッダ EMDBヘッダ |
| 画像 |  emd_32211.png emd_32211.png | 208.2 KB | ||
| Filedesc metadata |  emd-32211.cif.gz emd-32211.cif.gz | 5.7 KB | ||
| アーカイブディレクトリ |  http://ftp.pdbj.org/pub/emdb/structures/EMD-32211 http://ftp.pdbj.org/pub/emdb/structures/EMD-32211 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-32211 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-32211 | HTTPS FTP |
-検証レポート
| 文書・要旨 |  emd_32211_validation.pdf.gz emd_32211_validation.pdf.gz | 536.5 KB | 表示 |  EMDB検証レポート EMDB検証レポート |
|---|---|---|---|---|
| 文書・詳細版 |  emd_32211_full_validation.pdf.gz emd_32211_full_validation.pdf.gz | 536.1 KB | 表示 | |
| XML形式データ |  emd_32211_validation.xml.gz emd_32211_validation.xml.gz | 6.2 KB | 表示 | |
| CIF形式データ |  emd_32211_validation.cif.gz emd_32211_validation.cif.gz | 7 KB | 表示 | |
| アーカイブディレクトリ |  https://ftp.pdbj.org/pub/emdb/validation_reports/EMD-32211 https://ftp.pdbj.org/pub/emdb/validation_reports/EMD-32211 ftp://ftp.pdbj.org/pub/emdb/validation_reports/EMD-32211 ftp://ftp.pdbj.org/pub/emdb/validation_reports/EMD-32211 | HTTPS FTP |
-関連構造データ
| 関連構造データ |  7vyqMC  7dldC  7dllC  7dlmC  7dmgC  7dn1C M: このマップから作成された原子モデル C: 同じ文献を引用 ( |
|---|---|
| 類似構造データ | 類似検索 - 機能・相同性  F&H 検索 F&H 検索 |
| 電子顕微鏡画像生データ |  EMPIAR-10872 (タイトル: Oligomeric interactions maintain active-site structure in a non-cooperative enzyme family EMPIAR-10872 (タイトル: Oligomeric interactions maintain active-site structure in a non-cooperative enzyme familyData size: 902.0 Data #1: Native-SCR-tetramer-frames [micrographs - multiframe]) |
- リンク
リンク
| EMDBのページ |  EMDB (EBI/PDBe) / EMDB (EBI/PDBe) /  EMDataResource EMDataResource |
|---|---|
| 「今月の分子」の関連する項目 |
- マップ
マップ
| ファイル |  ダウンロード / ファイル: emd_32211.map.gz / 形式: CCP4 / 大きさ: 64 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) ダウンロード / ファイル: emd_32211.map.gz / 形式: CCP4 / 大きさ: 64 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) | ||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 投影像・断面図 | 画像のコントロール
画像は Spider により作成 | ||||||||||||||||||||||||||||||||||||
| ボクセルのサイズ | X=Y=Z: 0.837 Å | ||||||||||||||||||||||||||||||||||||
| 密度 |
| ||||||||||||||||||||||||||||||||||||
| 対称性 | 空間群: 1 | ||||||||||||||||||||||||||||||||||||
| 詳細 | EMDB XML:
|
-添付データ
- 試料の構成要素
試料の構成要素
-全体 : Ternary complex of SCR with NADP and ethyl 4-chloroacetoacetate
| 全体 | 名称: Ternary complex of SCR with NADP and ethyl 4-chloroacetoacetate |
|---|---|
| 要素 |
|
-超分子 #1: Ternary complex of SCR with NADP and ethyl 4-chloroacetoacetate
| 超分子 | 名称: Ternary complex of SCR with NADP and ethyl 4-chloroacetoacetate タイプ: complex / ID: 1 / 親要素: 0 / 含まれる分子: #1 |
|---|---|
| 由来(天然) | 生物種:  Candida parapsilosis (酵母) Candida parapsilosis (酵母) |
-分子 #1: Carbonyl Reductase
| 分子 | 名称: Carbonyl Reductase / タイプ: protein_or_peptide / ID: 1 / コピー数: 4 / 光学異性体: LEVO EC番号: 酸化還元酵素; CH-OHの結合に対し酸化酵素として働く; NAD又はNADPを用いる |
|---|---|
| 由来(天然) | 生物種:  Candida parapsilosis (酵母) Candida parapsilosis (酵母) |
| 分子量 | 理論値: 30.204873 KDa |
| 組換発現 | 生物種:  |
| 配列 | 文字列: SMGEIESYCN KELGPLPTKA PTLSKNVLDL FSLKGKVASV TGSSGGIGWA VAEAYAQAGA DVAIWYNSHP ADEKAEHLQK TYGVHSKAY KCNISDPKSV EETISQQEKD FGTIDVFVAN AGVTWTQGPE IDVDNYDSWN KIISVDLNGV YYCSHNIGKI F KKNGKGSL ...文字列: SMGEIESYCN KELGPLPTKA PTLSKNVLDL FSLKGKVASV TGSSGGIGWA VAEAYAQAGA DVAIWYNSHP ADEKAEHLQK TYGVHSKAY KCNISDPKSV EETISQQEKD FGTIDVFVAN AGVTWTQGPE IDVDNYDSWN KIISVDLNGV YYCSHNIGKI F KKNGKGSL IITSSISGKI VNIPQLQAPY NTAKAACTHL AKSLAIEWAP FARVNTISPG YIDTDITDFA SKDMKAKWWQ LT PLGREGL TQELVGGYLY LASNASTFTT GSDVVIDGGY TCP UniProtKB: Carbonyl Reductase |
-分子 #2: NADP NICOTINAMIDE-ADENINE-DINUCLEOTIDE PHOSPHATE
| 分子 | 名称: NADP NICOTINAMIDE-ADENINE-DINUCLEOTIDE PHOSPHATE / タイプ: ligand / ID: 2 / コピー数: 4 / 式: NAP |
|---|---|
| 分子量 | 理論値: 743.405 Da |
| Chemical component information |  ChemComp-NAP: |
-分子 #3: ethyl 4-chloranyl-3-oxidanylidene-butanoate
| 分子 | 名称: ethyl 4-chloranyl-3-oxidanylidene-butanoate / タイプ: ligand / ID: 3 / コピー数: 4 / 式: 83I |
|---|---|
| 分子量 | 理論値: 164.587 Da |
| Chemical component information | 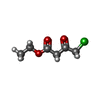 ChemComp-83I: |
-実験情報
-構造解析
| 手法 | クライオ電子顕微鏡法 |
|---|---|
 解析 解析 | 単粒子再構成法 |
| 試料の集合状態 | particle |
- 試料調製
試料調製
| 濃度 | 3 mg/mL |
|---|---|
| 緩衝液 | pH: 6 |
| 凍結 | 凍結剤: ETHANE |
- 電子顕微鏡法
電子顕微鏡法
| 顕微鏡 | FEI TITAN KRIOS |
|---|---|
| 撮影 | フィルム・検出器のモデル: GATAN K3 BIOQUANTUM (6k x 4k) 撮影したグリッド数: 1 / 実像数: 2885 / 平均露光時間: 2.5 sec. / 平均電子線量: 56.15 e/Å2 |
| 電子線 | 加速電圧: 300 kV / 電子線源:  FIELD EMISSION GUN FIELD EMISSION GUN |
| 電子光学系 | 照射モード: FLOOD BEAM / 撮影モード: BRIGHT FIELD / 最大 デフォーカス(公称値): 2.17 µm / 最小 デフォーカス(公称値): 1.37 µm / 倍率(公称値): 105000 |
| 実験機器 |  モデル: Titan Krios / 画像提供: FEI Company |
- 画像解析
画像解析
| 初期モデル | モデルのタイプ: PDB ENTRY |
|---|---|
| 最終 再構成 | 想定した対称性 - 点群: D2 (2回x2回 2面回転対称) 解像度のタイプ: BY AUTHOR / 解像度: 3.13 Å / 解像度の算出法: FSC 0.143 CUT-OFF / ソフトウェア - 名称: cryoSPARC / 使用した粒子像数: 104278 |
| 初期 角度割当 | タイプ: MAXIMUM LIKELIHOOD |
| 最終 角度割当 | タイプ: MAXIMUM LIKELIHOOD |
 ムービー
ムービー コントローラー
コントローラー








 Z (Sec.)
Z (Sec.) Y (Row.)
Y (Row.) X (Col.)
X (Col.)




















