+ データを開く
データを開く
- 基本情報
基本情報
| 登録情報 | データベース: EMDB / ID: EMD-30321 | |||||||||
|---|---|---|---|---|---|---|---|---|---|---|
| タイトル | Coxsackievirus B5 (CVB5) F-particle | |||||||||
 マップデータ マップデータ | ||||||||||
 試料 試料 |
| |||||||||
 キーワード キーワード | Echovirus B / mature / VIRUS | |||||||||
| 機能・相同性 |  機能・相同性情報 機能・相同性情報symbiont-mediated suppression of host cytoplasmic pattern recognition receptor signaling pathway via inhibition of RIG-I activity / picornain 2A / symbiont-mediated suppression of host mRNA export from nucleus / symbiont genome entry into host cell via pore formation in plasma membrane / picornain 3C / T=pseudo3 icosahedral viral capsid / host cell cytoplasmic vesicle membrane / viral capsid / ribonucleoside triphosphate phosphatase activity / host cell ...symbiont-mediated suppression of host cytoplasmic pattern recognition receptor signaling pathway via inhibition of RIG-I activity / picornain 2A / symbiont-mediated suppression of host mRNA export from nucleus / symbiont genome entry into host cell via pore formation in plasma membrane / picornain 3C / T=pseudo3 icosahedral viral capsid / host cell cytoplasmic vesicle membrane / viral capsid / ribonucleoside triphosphate phosphatase activity / host cell / nucleoside-triphosphate phosphatase / channel activity / monoatomic ion transmembrane transport / host cell cytoplasm / DNA replication / RNA helicase activity / endocytosis involved in viral entry into host cell / symbiont-mediated activation of host autophagy / RNA-directed RNA polymerase / cysteine-type endopeptidase activity / viral RNA genome replication / RNA-directed RNA polymerase activity / symbiont entry into host cell / DNA-templated transcription / virion attachment to host cell / host cell nucleus / structural molecule activity / proteolysis / RNA binding / zinc ion binding / ATP binding / cytoplasm 類似検索 - 分子機能 | |||||||||
| 生物種 |  Coxsackievirus B5 (コクサッキーウイルス) Coxsackievirus B5 (コクサッキーウイルス) | |||||||||
| 手法 | 単粒子再構成法 / クライオ電子顕微鏡法 / 解像度: 3.5 Å | |||||||||
 データ登録者 データ登録者 | Wang K / Rao Z | |||||||||
| 資金援助 |  中国, 1件 中国, 1件
| |||||||||
 引用 引用 |  ジャーナル: Nat Commun / 年: 2020 ジャーナル: Nat Commun / 年: 2020タイトル: Structures of Echovirus 30 in complex with its receptors inform a rational prediction for enterovirus receptor usage. 著者: Kang Wang / Ling Zhu / Yao Sun / Minhao Li / Xin Zhao / Lunbiao Cui / Li Zhang / George F Gao / Weiwei Zhai / Fengcai Zhu / Zihe Rao / Xiangxi Wang /  要旨: Receptor usage that determines cell tropism and drives viral classification closely correlates with the virus structure. Enterovirus B (EV-B) consists of several subgroups according to receptor ...Receptor usage that determines cell tropism and drives viral classification closely correlates with the virus structure. Enterovirus B (EV-B) consists of several subgroups according to receptor usage, among which echovirus 30 (E30), a leading causative agent for human aseptic meningitis, utilizes FcRn as an uncoating receptor. However, receptors for many EVs remain unknown. Here we analyzed the atomic structures of E30 mature virion, empty- and A-particles, which reveals serotype-specific epitopes and striking conformational differences between the subgroups within EV-Bs. Of these, the VP1 BC loop markedly distinguishes E30 from other EV-Bs, indicative of a role as a structural marker for EV-B. By obtaining cryo-electron microscopy structures of E30 in complex with its receptor FcRn and CD55 and comparing its homologs, we deciphered the underlying molecular basis for receptor recognition. Together with experimentally derived viral receptor identifications, we developed a structure-based in silico algorithm to inform a rational prediction for EV receptor usage. | |||||||||
| 履歴 |
|
- 構造の表示
構造の表示
| ムービー |
 ムービービューア ムービービューア |
|---|---|
| 構造ビューア | EMマップ:  SurfView SurfView Molmil Molmil Jmol/JSmol Jmol/JSmol |
| 添付画像 |
- ダウンロードとリンク
ダウンロードとリンク
-EMDBアーカイブ
| マップデータ |  emd_30321.map.gz emd_30321.map.gz | 166.8 MB |  EMDBマップデータ形式 EMDBマップデータ形式 | |
|---|---|---|---|---|
| ヘッダ (付随情報) |  emd-30321-v30.xml emd-30321-v30.xml emd-30321.xml emd-30321.xml | 15.3 KB 15.3 KB | 表示 表示 |  EMDBヘッダ EMDBヘッダ |
| 画像 |  emd_30321.png emd_30321.png | 135.3 KB | ||
| Filedesc metadata |  emd-30321.cif.gz emd-30321.cif.gz | 6 KB | ||
| アーカイブディレクトリ |  http://ftp.pdbj.org/pub/emdb/structures/EMD-30321 http://ftp.pdbj.org/pub/emdb/structures/EMD-30321 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-30321 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-30321 | HTTPS FTP |
-関連構造データ
- リンク
リンク
| EMDBのページ |  EMDB (EBI/PDBe) / EMDB (EBI/PDBe) /  EMDataResource EMDataResource |
|---|---|
| 「今月の分子」の関連する項目 |
- マップ
マップ
| ファイル |  ダウンロード / ファイル: emd_30321.map.gz / 形式: CCP4 / 大きさ: 178 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) ダウンロード / ファイル: emd_30321.map.gz / 形式: CCP4 / 大きさ: 178 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 投影像・断面図 | 画像のコントロール
画像は Spider により作成 | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| ボクセルのサイズ | X=Y=Z: 1.345 Å | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 密度 |
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 対称性 | 空間群: 1 | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 詳細 | EMDB XML:
CCP4マップ ヘッダ情報:
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
-添付データ
- 試料の構成要素
試料の構成要素
-全体 : Coxsackievirus B5
| 全体 | 名称:  Coxsackievirus B5 (コクサッキーウイルス) Coxsackievirus B5 (コクサッキーウイルス) |
|---|---|
| 要素 |
|
-超分子 #1: Coxsackievirus B5
| 超分子 | 名称: Coxsackievirus B5 / タイプ: virus / ID: 1 / 親要素: 0 / 含まれる分子: #1-#4 詳細: Particles purified from the cell cultures innoculated with the live CB5. NCBI-ID: 12074 / 生物種: Coxsackievirus B5 / ウイルスタイプ: VIRION / ウイルス・単離状態: SEROTYPE / ウイルス・エンベロープ: No / ウイルス・中空状態: No |
|---|---|
| 宿主 | 生物種:  Homo sapiens (ヒト) Homo sapiens (ヒト) |
| ウイルス殻 | Shell ID: 1 / 直径: 30.0 Å / T番号(三角分割数): 3 |
-分子 #1: VP1
| 分子 | 名称: VP1 / タイプ: protein_or_peptide / ID: 1 / コピー数: 1 / 光学異性体: LEVO |
|---|---|
| 由来(天然) | 生物種:  Coxsackievirus B5 (コクサッキーウイルス) Coxsackievirus B5 (コクサッキーウイルス) |
| 分子量 | 理論値: 31.574322 KDa |
| 配列 | 文字列: GPTGEAVERA IARVADTIGS GPVNSESIPA LTAAETGHTS QVVPADTMQT RHVKNYHSRS ESTVENFLCR SACVFYTTYR NHGTDGDNF GYWVISTRQV AQLRRKLEMF TYARFDLELT FVITSTQEQS TIQGQDSPVL THQIMYVPPG GPVPTKVNSY S WQTSTNPS ...文字列: GPTGEAVERA IARVADTIGS GPVNSESIPA LTAAETGHTS QVVPADTMQT RHVKNYHSRS ESTVENFLCR SACVFYTTYR NHGTDGDNF GYWVISTRQV AQLRRKLEMF TYARFDLELT FVITSTQEQS TIQGQDSPVL THQIMYVPPG GPVPTKVNSY S WQTSTNPS VFWTEGSAPP RMSIPFISIG NAYSMFYDGW AKFDKQGTYG INTLNNMGTL YMRHVNDGSP GPIVSTVRIY FK PKHVKTW VPRPPRLCQY QKAGNVNFEP TGVTESRTDI TTMQTT UniProtKB: Genome polyprotein |
-分子 #2: VP2
| 分子 | 名称: VP2 / タイプ: protein_or_peptide / ID: 2 / コピー数: 1 / 光学異性体: LEVO |
|---|---|
| 由来(天然) | 生物種:  Coxsackievirus B5 (コクサッキーウイルス) Coxsackievirus B5 (コクサッキーウイルス) |
| 分子量 | 理論値: 28.626143 KDa |
| 配列 | 文字列: SPSAEECGYS DRVRSITLGN STITTQECAN VVVGYGVWPT YLNDDEATAE DQPTQPDVAT CRFYTLESVM WQQSSPGWWW KFPDALSNM GLFGQNMQYH YLGRAGYTVH VQCNASKFHQ GCLLVVCVPE AEMGCATLAN KPDQKSLSNG ETANMFESQN S TGQTAVQA ...文字列: SPSAEECGYS DRVRSITLGN STITTQECAN VVVGYGVWPT YLNDDEATAE DQPTQPDVAT CRFYTLESVM WQQSSPGWWW KFPDALSNM GLFGQNMQYH YLGRAGYTVH VQCNASKFHQ GCLLVVCVPE AEMGCATLAN KPDQKSLSNG ETANMFESQN S TGQTAVQA NVINAGMGVG VGNLTIFPHQ WINLRTNNSA TIVMPYINSV PMDNMFRHNN FTLMIIPFAP LSYSTGATTY VP ITVTVAP MCAEYNGLRL AGKQ |
-分子 #3: VP3
| 分子 | 名称: VP3 / タイプ: protein_or_peptide / ID: 3 / コピー数: 1 / 光学異性体: LEVO |
|---|---|
| 由来(天然) | 生物種:  Coxsackievirus B5 (コクサッキーウイルス) Coxsackievirus B5 (コクサッキーウイルス) |
| 分子量 | 理論値: 26.163672 KDa |
| 配列 | 文字列: GLPTMLTPGS NQFLTSDDFQ SPSAMPQFDV TPEMDIPGQV NNLMEIAEVD SVVPVNNTEG KVLSIESYQI PVQSNSTNGS QVFGFPLMP GASSVLNRTL LGEILNYYTH WSGSIKLTFM FCGSAMATGK FLLAYSPPGA GAPTTRKEAM LGTHVIWDVG L QSSCVLCI ...文字列: GLPTMLTPGS NQFLTSDDFQ SPSAMPQFDV TPEMDIPGQV NNLMEIAEVD SVVPVNNTEG KVLSIESYQI PVQSNSTNGS QVFGFPLMP GASSVLNRTL LGEILNYYTH WSGSIKLTFM FCGSAMATGK FLLAYSPPGA GAPTTRKEAM LGTHVIWDVG L QSSCVLCI PWISQTHYRY VVVDEYTAGG YITCWYQTNI VVPADTQSDC KILCFVSACN DFSVRMLKDT PFIKQDNFYQ UniProtKB: Genome polyprotein |
-分子 #4: VP4
| 分子 | 名称: VP4 / タイプ: protein_or_peptide / ID: 4 / コピー数: 1 / 光学異性体: LEVO |
|---|---|
| 由来(天然) | 生物種:  Coxsackievirus B5 (コクサッキーウイルス) Coxsackievirus B5 (コクサッキーウイルス) |
| 分子量 | 理論値: 7.326025 KDa |
| 配列 | 文字列: GAQVSTQKTG AHETGLSASG NSIIHYTNVN YYKDAASNSA NRQDFTQDPG KFTEPVKDIM IKSMPALN |
-分子 #5: PALMITIC ACID
| 分子 | 名称: PALMITIC ACID / タイプ: ligand / ID: 5 / コピー数: 1 / 式: PLM |
|---|---|
| 分子量 | 理論値: 256.424 Da |
| Chemical component information |  ChemComp-PLM: |
-分子 #6: MYRISTIC ACID
| 分子 | 名称: MYRISTIC ACID / タイプ: ligand / ID: 6 / コピー数: 1 / 式: MYR |
|---|---|
| 分子量 | 理論値: 228.371 Da |
| Chemical component information | 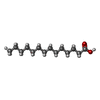 ChemComp-MYR: |
-実験情報
-構造解析
| 手法 | クライオ電子顕微鏡法 |
|---|---|
 解析 解析 | 単粒子再構成法 |
| 試料の集合状態 | particle |
- 試料調製
試料調製
| 緩衝液 | pH: 7.4 |
|---|---|
| グリッド | モデル: Quantifoil R1.2/1.3 / 材質: GOLD / 支持フィルム - 材質: CARBON / 支持フィルム - トポロジー: HOLEY / 前処理 - タイプ: PLASMA CLEANING / 前処理 - 時間: 60 sec. |
| 凍結 | 凍結剤: ETHANE / チャンバー内湿度: 100 % / 装置: FEI VITROBOT MARK I |
- 電子顕微鏡法
電子顕微鏡法
| 顕微鏡 | FEI TITAN KRIOS |
|---|---|
| 撮影 | フィルム・検出器のモデル: GATAN K2 SUMMIT (4k x 4k) 検出モード: SUPER-RESOLUTION / 平均電子線量: 30.0 e/Å2 |
| 電子線 | 加速電圧: 300 kV / 電子線源:  FIELD EMISSION GUN FIELD EMISSION GUN |
| 電子光学系 | 照射モード: FLOOD BEAM / 撮影モード: DARK FIELD / Cs: 2.7 mm / 最大 デフォーカス(公称値): 2.5 µm / 最小 デフォーカス(公称値): 1.2 µm |
| 試料ステージ | 試料ホルダーモデル: FEI TITAN KRIOS AUTOGRID HOLDER ホルダー冷却材: NITROGEN |
| 実験機器 |  モデル: Titan Krios / 画像提供: FEI Company |
- 画像解析
画像解析
| 初期モデル | モデルのタイプ: INSILICO MODEL |
|---|---|
| 最終 再構成 | 想定した対称性 - 点群: I (正20面体型対称) / 解像度のタイプ: BY AUTHOR / 解像度: 3.5 Å / 解像度の算出法: FSC 0.143 CUT-OFF / ソフトウェア - 名称: RELION (ver. 3.0) / 使用した粒子像数: 8890 |
| 初期 角度割当 | タイプ: PROJECTION MATCHING |
| 最終 角度割当 | タイプ: PROJECTION MATCHING / ソフトウェア - 名称: RELION |
-原子モデル構築 1
| 精密化 | 空間: REAL / プロトコル: RIGID BODY FIT |
|---|---|
| 得られたモデル |  PDB-7c9y: |
 ムービー
ムービー コントローラー
コントローラー


































 Z (Sec.)
Z (Sec.) Y (Row.)
Y (Row.) X (Col.)
X (Col.)





















