+ データを開く
データを開く
- 基本情報
基本情報
| 登録情報 |  | |||||||||
|---|---|---|---|---|---|---|---|---|---|---|
| タイトル | CryoEM of the soluble OPA1 dimer from the apo helical assembly on a lipid membrane | |||||||||
 マップデータ マップデータ | sOPA1 apo helical assembly full map | |||||||||
 試料 試料 |
| |||||||||
 キーワード キーワード | GTPase / Dynamin-family protein / mitochondrial fusion protein / mitochondria / Optic Atrophy / LIPID BINDING PROTEIN | |||||||||
| 機能・相同性 |  機能・相同性情報 機能・相同性情報Regulation of Apoptosis / membrane tubulation / inner mitochondrial membrane organization / dynamin GTPase / cardiolipin binding / mitochondrial genome maintenance / phosphatidic acid binding / mitochondrial fission / GTP metabolic process / mitochondrial fusion ...Regulation of Apoptosis / membrane tubulation / inner mitochondrial membrane organization / dynamin GTPase / cardiolipin binding / mitochondrial genome maintenance / phosphatidic acid binding / mitochondrial fission / GTP metabolic process / mitochondrial fusion / axonal transport of mitochondrion / negative regulation of release of cytochrome c from mitochondria / mitochondrial crista / negative regulation of endoplasmic reticulum stress-induced intrinsic apoptotic signaling pathway / axon cytoplasm / Mitochondrial protein degradation / visual perception / mitochondrion organization / neural tube closure / mitochondrial membrane / mitochondrial intermembrane space / cellular senescence / protein complex oligomerization / microtubule binding / microtubule / mitochondrial outer membrane / mitochondrial inner membrane / GTPase activity / apoptotic process / dendrite / GTP binding / negative regulation of apoptotic process / magnesium ion binding / mitochondrion / nucleoplasm / membrane / cytoplasm / cytosol 類似検索 - 分子機能 | |||||||||
| 生物種 |  Homo sapiens (ヒト) Homo sapiens (ヒト) | |||||||||
| 手法 | らせん対称体再構成法 / クライオ電子顕微鏡法 / 解像度: 9.68 Å | |||||||||
 データ登録者 データ登録者 | Nyenhuis SB / Wu X / Stanton AE / Strub MP / Yim YI / Canagarajah B / Hinshaw JE | |||||||||
| 資金援助 |  米国, 1件 米国, 1件
| |||||||||
 引用 引用 |  ジャーナル: Nature / 年: 2023 ジャーナル: Nature / 年: 2023タイトル: OPA1 helical structures give perspective to mitochondrial dysfunction. 著者: Sarah B Nyenhuis / Xufeng Wu / Marie-Paule Strub / Yang-In Yim / Abigail E Stanton / Valentina Baena / Zulfeqhar A Syed / Bertram Canagarajah / John A Hammer / Jenny E Hinshaw /  要旨: Dominant optic atrophy is one of the leading causes of childhood blindness. Around 60-80% of cases are caused by mutations of the gene that encodes optic atrophy protein 1 (OPA1), a protein that has ...Dominant optic atrophy is one of the leading causes of childhood blindness. Around 60-80% of cases are caused by mutations of the gene that encodes optic atrophy protein 1 (OPA1), a protein that has a key role in inner mitochondrial membrane fusion and remodelling of cristae and is crucial for the dynamic organization and regulation of mitochondria. Mutations in OPA1 result in the dysregulation of the GTPase-mediated fusion process of the mitochondrial inner and outer membranes. Here we used cryo-electron microscopy methods to solve helical structures of OPA1 assembled on lipid membrane tubes, in the presence and absence of nucleotide. These helical assemblies organize into densely packed protein rungs with minimal inter-rung connectivity, and exhibit nucleotide-dependent dimerization of the GTPase domains-a hallmark of the dynamin superfamily of proteins. OPA1 also contains several unique secondary structures in the paddle domain that strengthen its membrane association, including membrane-inserting helices. The structural features identified in this study shed light on the effects of pathogenic point mutations on protein folding, inter-protein assembly and membrane interactions. Furthermore, mutations that disrupt the assembly interfaces and membrane binding of OPA1 cause mitochondrial fragmentation in cell-based assays, providing evidence of the biological relevance of these interactions. | |||||||||
| 履歴 |
|
- 構造の表示
構造の表示
| 添付画像 |
|---|
- ダウンロードとリンク
ダウンロードとリンク
-EMDBアーカイブ
| マップデータ |  emd_28074.map.gz emd_28074.map.gz | 204.3 MB |  EMDBマップデータ形式 EMDBマップデータ形式 | |
|---|---|---|---|---|
| ヘッダ (付随情報) |  emd-28074-v30.xml emd-28074-v30.xml emd-28074.xml emd-28074.xml | 15.3 KB 15.3 KB | 表示 表示 |  EMDBヘッダ EMDBヘッダ |
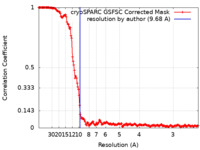
| FSC (解像度算出) |  emd_28074_fsc.xml emd_28074_fsc.xml | 15.9 KB | 表示 |  FSCデータファイル FSCデータファイル |
| 画像 |  emd_28074.png emd_28074.png | 90.4 KB | ||
| マスクデータ |  emd_28074_msk_1.map emd_28074_msk_1.map | 421.9 MB |  マスクマップ マスクマップ | |
| その他 |  emd_28074_half_map_1.map.gz emd_28074_half_map_1.map.gz emd_28074_half_map_2.map.gz emd_28074_half_map_2.map.gz | 391.1 MB 391.1 MB | ||
| アーカイブディレクトリ |  http://ftp.pdbj.org/pub/emdb/structures/EMD-28074 http://ftp.pdbj.org/pub/emdb/structures/EMD-28074 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-28074 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-28074 | HTTPS FTP |
-検証レポート
| 文書・要旨 |  emd_28074_validation.pdf.gz emd_28074_validation.pdf.gz | 1.3 MB | 表示 |  EMDB検証レポート EMDB検証レポート |
|---|---|---|---|---|
| 文書・詳細版 |  emd_28074_full_validation.pdf.gz emd_28074_full_validation.pdf.gz | 1.3 MB | 表示 | |
| XML形式データ |  emd_28074_validation.xml.gz emd_28074_validation.xml.gz | 24.4 KB | 表示 | |
| CIF形式データ |  emd_28074_validation.cif.gz emd_28074_validation.cif.gz | 31.7 KB | 表示 | |
| アーカイブディレクトリ |  https://ftp.pdbj.org/pub/emdb/validation_reports/EMD-28074 https://ftp.pdbj.org/pub/emdb/validation_reports/EMD-28074 ftp://ftp.pdbj.org/pub/emdb/validation_reports/EMD-28074 ftp://ftp.pdbj.org/pub/emdb/validation_reports/EMD-28074 | HTTPS FTP |
-関連構造データ
| 関連構造データ |  8ef7MC  8efsMC  8eftMC  8eewC  8effC  8efrC M: このマップから作成された原子モデル C: 同じ文献を引用 ( |
|---|---|
| 類似構造データ | 類似検索 - 機能・相同性  F&H 検索 F&H 検索 |
- リンク
リンク
| EMDBのページ |  EMDB (EBI/PDBe) / EMDB (EBI/PDBe) /  EMDataResource EMDataResource |
|---|
- マップ
マップ
| ファイル |  ダウンロード / ファイル: emd_28074.map.gz / 形式: CCP4 / 大きさ: 421.9 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) ダウンロード / ファイル: emd_28074.map.gz / 形式: CCP4 / 大きさ: 421.9 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) | ||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | sOPA1 apo helical assembly full map | ||||||||||||||||||||
| ボクセルのサイズ | X=Y=Z: 1.2518 Å | ||||||||||||||||||||
| 密度 |
| ||||||||||||||||||||
| 対称性 | 空間群: 1 | ||||||||||||||||||||
| 詳細 | EMDB XML:
|
-添付データ
-マスク #1
| ファイル |  emd_28074_msk_1.map emd_28074_msk_1.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 投影像・断面図 |
| ||||||||||||
| 密度ヒストグラム |
-ハーフマップ: sOPA1 apo helical assembly half map A
| ファイル | emd_28074_half_map_1.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | sOPA1 apo helical assembly half map A | ||||||||||||
| 投影像・断面図 |
| ||||||||||||
| 密度ヒストグラム |
-ハーフマップ: sOPA1 apo helical assembly half map B
| ファイル | emd_28074_half_map_2.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | sOPA1 apo helical assembly half map B | ||||||||||||
| 投影像・断面図 |
| ||||||||||||
| 密度ヒストグラム |
- 試料の構成要素
試料の構成要素
-全体 : cryoEM of the soluble OPA1 helical assembly on a lipid membrane i...
| 全体 | 名称: cryoEM of the soluble OPA1 helical assembly on a lipid membrane in the apo state |
|---|---|
| 要素 |
|
-超分子 #1: cryoEM of the soluble OPA1 helical assembly on a lipid membrane i...
| 超分子 | 名称: cryoEM of the soluble OPA1 helical assembly on a lipid membrane in the apo state タイプ: complex / ID: 1 / 親要素: 0 / 含まれる分子: all |
|---|---|
| 由来(天然) | 生物種:  Homo sapiens (ヒト) Homo sapiens (ヒト) |
-分子 #1: Dynamin-like 120 kDa protein, form S1
| 分子 | 名称: Dynamin-like 120 kDa protein, form S1 / タイプ: protein_or_peptide / ID: 1 / コピー数: 2 / 光学異性体: LEVO |
|---|---|
| 由来(天然) | 生物種:  Homo sapiens (ヒト) Homo sapiens (ヒト) |
| 分子量 | 理論値: 89.262516 KDa |
| 組換発現 | 生物種:  |
| 配列 | 文字列: ATDRGSESDK HFRKVSDKEK IDQLQEELLH TQLKYQRILE RLEKENKELR KLVLQKDDKG IHHRKLKKSL IDMYSEVLDV LSDYDASYN TQDHLPRVVV VGDQSAGKTS VLEMIAQARI FPRGSGEMMT RSPVKVTLSE GPHHVALFKD SSREFDLTKE E DLAALRHE ...文字列: ATDRGSESDK HFRKVSDKEK IDQLQEELLH TQLKYQRILE RLEKENKELR KLVLQKDDKG IHHRKLKKSL IDMYSEVLDV LSDYDASYN TQDHLPRVVV VGDQSAGKTS VLEMIAQARI FPRGSGEMMT RSPVKVTLSE GPHHVALFKD SSREFDLTKE E DLAALRHE IELRMRKNVK EGCTVSPETI SLNVKGPGLQ RMVLVDLPGV INTVTSGMAP DTKETIFSIS KAYMQNPNAI IL CIQDGSV DAERSIVTDL VSQMDPHGRR TIFVLTKVDL AEKNVASPSR IQQIIEGKLF PMKALGYFAV VTGKGNSSES IEA IREYEE EFFQNSKLLK TSMLKAHQVT TRNLSLAVSD CFWKMVRESV EQQADSFKAT RFNLETEWKN NYPRLRELDR NELF EKAKN EILDEVISLS QVTPKHWEEI LQQSLWERVS THVIENIYLP AAQTMNSGTF NTTVDIKLKQ WTDKQLPNKA VEVAW ETLQ EEFSRFMTEP KGKEHDDIFD KLKEAVKEES IKRHKWNDFA EDSLRVIQHN ALEDRSISDK QQWDAAIYFM EEALQA RLK DTENAIENMV GPDWKKRWLY WKNRTQEQCV HNETKNELEK MLKCNEEHPA YLASDEITTV RKNLESRGVE VDPSLIK DT WHQVYRRHFL KTALNHCNLC RRGFYYYQRH FVDSELECND VVLFWRIQRM LAITANTLRQ QLTNTEVRRL EKNVKEVL E DFAEDGEKKI KLLTGKRVQL AEDLKKVREI QEKLDAFIEA LHQEK UniProtKB: Dynamin-like GTPase OPA1, mitochondrial |
-実験情報
-構造解析
| 手法 | クライオ電子顕微鏡法 |
|---|---|
 解析 解析 | らせん対称体再構成法 |
| 試料の集合状態 | helical array |
- 試料調製
試料調製
| 緩衝液 | pH: 7.2 |
|---|---|
| 凍結 | 凍結剤: ETHANE |
- 電子顕微鏡法
電子顕微鏡法
| 顕微鏡 | TFS GLACIOS |
|---|---|
| 撮影 | フィルム・検出器のモデル: GATAN K3 BIOQUANTUM (6k x 4k) 平均電子線量: 24.86 e/Å2 |
| 電子線 | 加速電圧: 200 kV / 電子線源:  FIELD EMISSION GUN FIELD EMISSION GUN |
| 電子光学系 | 照射モード: FLOOD BEAM / 撮影モード: BRIGHT FIELD / 最大 デフォーカス(公称値): 2.4 µm / 最小 デフォーカス(公称値): 0.6 µm |
- 画像解析
画像解析
-原子モデル構築 1
| 精密化 | 空間: REAL / プロトコル: FLEXIBLE FIT |
|---|---|
| 得られたモデル |  PDB-8ef7:  PDB-8efs:  PDB-8eft: |
 ムービー
ムービー コントローラー
コントローラー





















 Z
Z Y
Y X
X