+ データを開く
データを開く
- 基本情報
基本情報
| 登録情報 |  | |||||||||
|---|---|---|---|---|---|---|---|---|---|---|
| タイトル | Purification of Enterovirus A71, strain 4643, WT capsid | |||||||||
 マップデータ マップデータ | Purification of Enterovirus A71, strain 4643, WT capsid | |||||||||
 試料 試料 |
| |||||||||
 キーワード キーワード | enterovirus / thermostability / capsid / VIRUS | |||||||||
| 機能・相同性 |  機能・相同性情報 機能・相同性情報symbiont-mediated suppression of host cytoplasmic pattern recognition receptor signaling pathway via inhibition of MDA-5 activity / picornain 2A / symbiont-mediated suppression of host mRNA export from nucleus / symbiont genome entry into host cell via pore formation in plasma membrane / picornain 3C / T=pseudo3 icosahedral viral capsid / host cell cytoplasmic vesicle membrane / nucleoside-triphosphate phosphatase / channel activity / monoatomic ion transmembrane transport ...symbiont-mediated suppression of host cytoplasmic pattern recognition receptor signaling pathway via inhibition of MDA-5 activity / picornain 2A / symbiont-mediated suppression of host mRNA export from nucleus / symbiont genome entry into host cell via pore formation in plasma membrane / picornain 3C / T=pseudo3 icosahedral viral capsid / host cell cytoplasmic vesicle membrane / nucleoside-triphosphate phosphatase / channel activity / monoatomic ion transmembrane transport / DNA replication / RNA helicase activity / endocytosis involved in viral entry into host cell / symbiont-mediated activation of host autophagy / RNA-directed RNA polymerase / cysteine-type endopeptidase activity / viral RNA genome replication / RNA-directed RNA polymerase activity / DNA-templated transcription / virion attachment to host cell / host cell nucleus / structural molecule activity / ATP hydrolysis activity / proteolysis / RNA binding / zinc ion binding / ATP binding / membrane 類似検索 - 分子機能 | |||||||||
| 生物種 |   Enterovirus A71 (エンテロウイルス) / Enterovirus A71 (エンテロウイルス) /   Human enterovirus 71 (エンテロウイルス) Human enterovirus 71 (エンテロウイルス) | |||||||||
| 手法 | 単粒子再構成法 / クライオ電子顕微鏡法 / 解像度: 7.1 Å | |||||||||
 データ登録者 データ登録者 | Catching A / Capponi S / Andino R | |||||||||
| 資金援助 |  米国, 1件 米国, 1件
| |||||||||
 引用 引用 |  ジャーナル: Nat Commun / 年: 2023 ジャーナル: Nat Commun / 年: 2023タイトル: A tradeoff between enterovirus A71 particle stability and cell entry. 著者: Adam Catching / Ming Te Yeh / Simone Bianco / Sara Capponi / Raul Andino /  要旨: A central role of viral capsids is to protect the viral genome from the harsh extracellular environment while facilitating initiation of infection when the virus encounters a target cell. Viruses are ...A central role of viral capsids is to protect the viral genome from the harsh extracellular environment while facilitating initiation of infection when the virus encounters a target cell. Viruses are thought to have evolved an optimal equilibrium between particle stability and efficiency of cell entry. In this study, we genetically perturb this equilibrium in a non-enveloped virus, enterovirus A71 to determine its structural basis. We isolate a single-point mutation variant with increased particle thermotolerance and decreased efficiency of cell entry. Using cryo-electron microscopy and molecular dynamics simulations, we determine that the thermostable native particles have acquired an expanded conformation that results in a significant increase in protein dynamics. Examining the intermediate states of the thermostable variant reveals a potential pathway for uncoating. We propose a sequential release of the lipid pocket factor, followed by internal VP4 and ultimately the viral RNA. | |||||||||
| 履歴 |
|
- 構造の表示
構造の表示
| 添付画像 |
|---|
- ダウンロードとリンク
ダウンロードとリンク
-EMDBアーカイブ
| マップデータ |  emd_27863.map.gz emd_27863.map.gz | 26.1 MB |  EMDBマップデータ形式 EMDBマップデータ形式 | |
|---|---|---|---|---|
| ヘッダ (付随情報) |  emd-27863-v30.xml emd-27863-v30.xml emd-27863.xml emd-27863.xml | 19.7 KB 19.7 KB | 表示 表示 |  EMDBヘッダ EMDBヘッダ |
| FSC (解像度算出) |  emd_27863_fsc.xml emd_27863_fsc.xml | 9.2 KB | 表示 |  FSCデータファイル FSCデータファイル |
| 画像 |  emd_27863.png emd_27863.png | 129.3 KB | ||
| マスクデータ |  emd_27863_msk_1.map emd_27863_msk_1.map | 1.1 MB |  マスクマップ マスクマップ | |
| Filedesc metadata |  emd-27863.cif.gz emd-27863.cif.gz | 6.3 KB | ||
| その他 |  emd_27863_half_map_1.map.gz emd_27863_half_map_1.map.gz emd_27863_half_map_2.map.gz emd_27863_half_map_2.map.gz | 49.5 MB 49.5 MB | ||
| アーカイブディレクトリ |  http://ftp.pdbj.org/pub/emdb/structures/EMD-27863 http://ftp.pdbj.org/pub/emdb/structures/EMD-27863 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-27863 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-27863 | HTTPS FTP |
-検証レポート
| 文書・要旨 |  emd_27863_validation.pdf.gz emd_27863_validation.pdf.gz | 1.2 MB | 表示 |  EMDB検証レポート EMDB検証レポート |
|---|---|---|---|---|
| 文書・詳細版 |  emd_27863_full_validation.pdf.gz emd_27863_full_validation.pdf.gz | 1.2 MB | 表示 | |
| XML形式データ |  emd_27863_validation.xml.gz emd_27863_validation.xml.gz | 16.3 KB | 表示 | |
| CIF形式データ |  emd_27863_validation.cif.gz emd_27863_validation.cif.gz | 21.4 KB | 表示 | |
| アーカイブディレクトリ |  https://ftp.pdbj.org/pub/emdb/validation_reports/EMD-27863 https://ftp.pdbj.org/pub/emdb/validation_reports/EMD-27863 ftp://ftp.pdbj.org/pub/emdb/validation_reports/EMD-27863 ftp://ftp.pdbj.org/pub/emdb/validation_reports/EMD-27863 | HTTPS FTP |
-関連構造データ
| 関連構造データ |  8e3cMC  8e2xC  8e2yC  8e31C  8e38C  8e39C  8e3aC  8e3bC M: このマップから作成された原子モデル C: 同じ文献を引用 ( |
|---|---|
| 類似構造データ | 類似検索 - 機能・相同性  F&H 検索 F&H 検索 |
- リンク
リンク
| EMDBのページ |  EMDB (EBI/PDBe) / EMDB (EBI/PDBe) /  EMDataResource EMDataResource |
|---|---|
| 「今月の分子」の関連する項目 |
- マップ
マップ
| ファイル |  ダウンロード / ファイル: emd_27863.map.gz / 形式: CCP4 / 大きさ: 64 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) ダウンロード / ファイル: emd_27863.map.gz / 形式: CCP4 / 大きさ: 64 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) | ||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
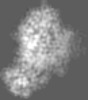
| 注釈 | Purification of Enterovirus A71, strain 4643, WT capsid | ||||||||||||||||||||||||||||||||||||
| 投影像・断面図 | 画像のコントロール
画像は Spider により作成 | ||||||||||||||||||||||||||||||||||||
| ボクセルのサイズ | X=Y=Z: 1.44 Å | ||||||||||||||||||||||||||||||||||||
| 密度 |
| ||||||||||||||||||||||||||||||||||||
| 対称性 | 空間群: 1 | ||||||||||||||||||||||||||||||||||||
| 詳細 | EMDB XML:
|
-添付データ
-マスク #1
| ファイル |  emd_27863_msk_1.map emd_27863_msk_1.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 投影像・断面図 |
| ||||||||||||
| 密度ヒストグラム |
-ハーフマップ: Purification of Enterovirus A71, strain 4643, WT capsid
| ファイル | emd_27863_half_map_1.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | Purification of Enterovirus A71, strain 4643, WT capsid | ||||||||||||
| 投影像・断面図 |
| ||||||||||||
| 密度ヒストグラム |
-ハーフマップ: Purification of Enterovirus A71, strain 4643, WT capsid
| ファイル | emd_27863_half_map_2.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | Purification of Enterovirus A71, strain 4643, WT capsid | ||||||||||||
| 投影像・断面図 |
| ||||||||||||
| 密度ヒストグラム |
- 試料の構成要素
試料の構成要素
-全体 : Human enterovirus 71
| 全体 | 名称:   Human enterovirus 71 (エンテロウイルス) Human enterovirus 71 (エンテロウイルス) |
|---|---|
| 要素 |
|
-超分子 #1: Human enterovirus 71
| 超分子 | 名称: Human enterovirus 71 / タイプ: virus / ID: 1 / 親要素: 0 / 含まれる分子: all / NCBI-ID: 39054 / 生物種: Human enterovirus 71 / ウイルスタイプ: VIRUS-LIKE PARTICLE / ウイルス・単離状態: STRAIN / ウイルス・エンベロープ: No / ウイルス・中空状態: No |
|---|---|
| 宿主 | 生物種:  Homo sapiens (ヒト) Homo sapiens (ヒト) |
| ウイルス殻 | Shell ID: 1 / 名称: Capsid / 直径: 300.0 Å / T番号(三角分割数): 1 |
-分子 #1: VP1
| 分子 | 名称: VP1 / タイプ: protein_or_peptide / ID: 1 / コピー数: 1 / 光学異性体: LEVO / EC番号: picornain 2A |
|---|---|
| 由来(天然) | 生物種:   Enterovirus A71 (エンテロウイルス) / 株: Tainan/4643/98 Enterovirus A71 (エンテロウイルス) / 株: Tainan/4643/98 |
| 分子量 | 理論値: 25.366697 KDa |
| 組換発現 | 生物種:  Homo sapiens (ヒト) Homo sapiens (ヒト) |
| 配列 | 文字列: SHSTAETTLD SFFSRAGLVG EIDLPLEGTT NPNGYANWDI DITGYAQMRR KVELFTYMRF DAEFTFVACT PTGQVVPQLL QYMFVPPGA PEPDSRESLA WQTATNPSVF VKLSDPPAQV SVPFMSPASA YQWFYDGYPT FGEHKQEKDL EYGACPNNMM G TFSVRTVG ...文字列: SHSTAETTLD SFFSRAGLVG EIDLPLEGTT NPNGYANWDI DITGYAQMRR KVELFTYMRF DAEFTFVACT PTGQVVPQLL QYMFVPPGA PEPDSRESLA WQTATNPSVF VKLSDPPAQV SVPFMSPASA YQWFYDGYPT FGEHKQEKDL EYGACPNNMM G TFSVRTVG TSKSKYPLVI RIYMRMKHVR AWIPRPMRNQ NYLFKANPNY AGNFIKPTGA SRTAITT UniProtKB: Genome polyprotein |
-分子 #2: VP2
| 分子 | 名称: VP2 / タイプ: protein_or_peptide / ID: 2 / コピー数: 1 / 光学異性体: LEVO |
|---|---|
| 由来(天然) | 生物種:   Enterovirus A71 (エンテロウイルス) / 株: Tainan/4643/98 Enterovirus A71 (エンテロウイルス) / 株: Tainan/4643/98 |
| 分子量 | 理論値: 25.803088 KDa |
| 組換発現 | 生物種:  Homo sapiens (ヒト) Homo sapiens (ヒト) |
| 配列 | 文字列: LTIGNSTITT QEAANIIVGY GEWPSYCSDS DATAVDKPTR PDVSVNRFYT LDTKLWEKSS KGWYWKFPDV LTETGVFGQN AQFHYLYRS GFCIHVQCNA SKFHQGALLV AVLPEYVIGT VAGGTGTEDS HPPYKQTQPG ADGFELQHPY VLDAGIPISQ L TVCPHQWI ...文字列: LTIGNSTITT QEAANIIVGY GEWPSYCSDS DATAVDKPTR PDVSVNRFYT LDTKLWEKSS KGWYWKFPDV LTETGVFGQN AQFHYLYRS GFCIHVQCNA SKFHQGALLV AVLPEYVIGT VAGGTGTEDS HPPYKQTQPG ADGFELQHPY VLDAGIPISQ L TVCPHQWI NLRTNNCATI IVPYINALPF DSALNHCNFG LLVVPISPLD YDQGATPVIP ITITLAPMCS EFAGLRQ UniProtKB: Genome polyprotein |
-分子 #3: VP3
| 分子 | 名称: VP3 / タイプ: protein_or_peptide / ID: 3 / コピー数: 1 / 光学異性体: LEVO |
|---|---|
| 由来(天然) | 生物種:   Enterovirus A71 (エンテロウイルス) / 株: Tainan/4643/98 Enterovirus A71 (エンテロウイルス) / 株: Tainan/4643/98 |
| 分子量 | 理論値: 25.811473 KDa |
| 組換発現 | 生物種:  Homo sapiens (ヒト) Homo sapiens (ヒト) |
| 配列 | 文字列: GFPTELKPGT NQFLTTDDGV SAPILPNFHP TPCIHIPGEV RNLLELCQVE TILEVNNVPT NATSLMERLR FPVSAQAGKG ELCAVFRAD PGRSGPWQST LLGQLCGYYT QWSGSLEVTF MFTGSFMATG KMLIAYTPPG GPLPKDRATA MLGTHVIWDF G LQSSVTLV ...文字列: GFPTELKPGT NQFLTTDDGV SAPILPNFHP TPCIHIPGEV RNLLELCQVE TILEVNNVPT NATSLMERLR FPVSAQAGKG ELCAVFRAD PGRSGPWQST LLGQLCGYYT QWSGSLEVTF MFTGSFMATG KMLIAYTPPG GPLPKDRATA MLGTHVIWDF G LQSSVTLV IPWISNTHYR AHARDGVFDY YTTGLVSIWY QTNYVVPIGA PNTAYIIALA AAQKNFTMQL CKDASDIL UniProtKB: Genome polyprotein |
-実験情報
-構造解析
| 手法 | クライオ電子顕微鏡法 |
|---|---|
 解析 解析 | 単粒子再構成法 |
| 試料の集合状態 | particle |
- 試料調製
試料調製
| 緩衝液 | pH: 7 |
|---|---|
| グリッド | モデル: Quantifoil R2/1 / 材質: COPPER / メッシュ: 200 / 支持フィルム - 材質: CARBON / 支持フィルム - トポロジー: CONTINUOUS / 支持フィルム - Film thickness: 0.2 |
| 凍結 | 凍結剤: ETHANE / チャンバー内湿度: 100 % / チャンバー内温度: 297 K / 装置: FEI VITROBOT MARK IV |
- 電子顕微鏡法
電子顕微鏡法
| 顕微鏡 | FEI TECNAI ARCTICA |
|---|---|
| 撮影 | フィルム・検出器のモデル: GATAN K3 (6k x 4k) / デジタル化 - サイズ - 横: 6000 pixel / デジタル化 - サイズ - 縦: 4000 pixel / 撮影したグリッド数: 1 / 平均露光時間: 6.0 sec. / 平均電子線量: 64.1 e/Å2 |
| 電子線 | 加速電圧: 200 kV / 電子線源:  FIELD EMISSION GUN FIELD EMISSION GUN |
| 電子光学系 | 照射モード: FLOOD BEAM / 撮影モード: BRIGHT FIELD / Cs: 2.7 mm / 最大 デフォーカス(公称値): 2.0 µm / 最小 デフォーカス(公称値): 1.5 µm / 倍率(公称値): 45000 |
| 試料ステージ | ホルダー冷却材: NITROGEN |
| 実験機器 |  モデル: Talos Arctica / 画像提供: FEI Company |
 ムービー
ムービー コントローラー
コントローラー












 Z (Sec.)
Z (Sec.) Y (Row.)
Y (Row.) X (Col.)
X (Col.)