+ データを開く
データを開く
- 基本情報
基本情報
| 登録情報 |  | |||||||||
|---|---|---|---|---|---|---|---|---|---|---|
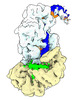
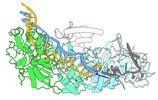
| タイトル | gRAMP-TPR-CHAT Non match PFS target RNA(Craspase) | |||||||||
 マップデータ マップデータ | ||||||||||
 試料 試料 |
| |||||||||
 キーワード キーワード | CRISPR / GRAMP / RNA BINDING PROTEIN / Craspase / RNA BINDING PROTEIN-RNA complex | |||||||||
| 機能・相同性 | CHAT domain / CHAT domain / CRISPR type III-associated protein / RAMP superfamily / defense response to virus / RNA binding / RAMP superfamily protein / CHAT domain protein 機能・相同性情報 機能・相同性情報 | |||||||||
| 生物種 |  Candidatus Scalindua brodae (バクテリア) Candidatus Scalindua brodae (バクテリア) | |||||||||
| 手法 | 単粒子再構成法 / クライオ電子顕微鏡法 / 解像度: 2.57 Å | |||||||||
 データ登録者 データ登録者 | Hu C / Nam KH / Schuler G / Ke A | |||||||||
| 資金援助 |  米国, 1件 米国, 1件
| |||||||||
 引用 引用 |  ジャーナル: Science / 年: 2022 ジャーナル: Science / 年: 2022タイトル: Craspase is a CRISPR RNA-guided, RNA-activated protease. 著者: Chunyi Hu / Sam P B van Beljouw / Ki Hyun Nam / Gabriel Schuler / Fran Ding / Yanru Cui / Alicia Rodríguez-Molina / Anna C Haagsma / Menno Valk / Martin Pabst / Stan J J Brouns / Ailong Ke /    要旨: The CRISPR-Cas type III-E RNA-targeting effector complex gRAMP/Cas7-11 is associated with a caspase-like protein (TPR-CHAT/Csx29) to form Craspase (CRISPR-guided caspase). Here, we use cryo-electron ...The CRISPR-Cas type III-E RNA-targeting effector complex gRAMP/Cas7-11 is associated with a caspase-like protein (TPR-CHAT/Csx29) to form Craspase (CRISPR-guided caspase). Here, we use cryo-electron microscopy snapshots of Craspase to explain its target RNA cleavage and protease activation mechanisms. Target-guide pairing extending into the 5' region of the guide RNA displaces a gating loop in gRAMP, which triggers an extensive conformational relay that allosterically aligns the protease catalytic dyad and opens an amino acid side-chain-binding pocket. We further define Csx30 as the endogenous protein substrate that is site-specifically proteolyzed by RNA-activated Craspase. This protease activity is switched off by target RNA cleavage by gRAMP and is not activated by RNA targets containing a matching protospacer flanking sequence. We thus conclude that Craspase is a target RNA-activated protease with self-regulatory capacity. | |||||||||
| 履歴 |
|
- 構造の表示
構造の表示
| 添付画像 |
|---|
- ダウンロードとリンク
ダウンロードとリンク
-EMDBアーカイブ
| マップデータ |  emd_27261.map.gz emd_27261.map.gz | 27.5 MB |  EMDBマップデータ形式 EMDBマップデータ形式 | |
|---|---|---|---|---|
| ヘッダ (付随情報) |  emd-27261-v30.xml emd-27261-v30.xml emd-27261.xml emd-27261.xml | 20.6 KB 20.6 KB | 表示 表示 |  EMDBヘッダ EMDBヘッダ |
| 画像 |  emd_27261.png emd_27261.png | 124.3 KB | ||
| Filedesc metadata |  emd-27261.cif.gz emd-27261.cif.gz | 6.9 KB | ||
| その他 |  emd_27261_additional_1.map.gz emd_27261_additional_1.map.gz emd_27261_half_map_1.map.gz emd_27261_half_map_1.map.gz emd_27261_half_map_2.map.gz emd_27261_half_map_2.map.gz | 27.8 MB 48.9 MB 48.9 MB | ||
| アーカイブディレクトリ |  http://ftp.pdbj.org/pub/emdb/structures/EMD-27261 http://ftp.pdbj.org/pub/emdb/structures/EMD-27261 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-27261 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-27261 | HTTPS FTP |
-検証レポート
| 文書・要旨 |  emd_27261_validation.pdf.gz emd_27261_validation.pdf.gz | 944.4 KB | 表示 |  EMDB検証レポート EMDB検証レポート |
|---|---|---|---|---|
| 文書・詳細版 |  emd_27261_full_validation.pdf.gz emd_27261_full_validation.pdf.gz | 944 KB | 表示 | |
| XML形式データ |  emd_27261_validation.xml.gz emd_27261_validation.xml.gz | 11.7 KB | 表示 | |
| CIF形式データ |  emd_27261_validation.cif.gz emd_27261_validation.cif.gz | 13.7 KB | 表示 | |
| アーカイブディレクトリ |  https://ftp.pdbj.org/pub/emdb/validation_reports/EMD-27261 https://ftp.pdbj.org/pub/emdb/validation_reports/EMD-27261 ftp://ftp.pdbj.org/pub/emdb/validation_reports/EMD-27261 ftp://ftp.pdbj.org/pub/emdb/validation_reports/EMD-27261 | HTTPS FTP |
-関連構造データ
| 関連構造データ |  8d9gMC  8d8nC  8d97C  8d9eC  8d9fC  8d9hC  8d9iC M: このマップから作成された原子モデル C: 同じ文献を引用 ( |
|---|---|
| 類似構造データ | 類似検索 - 機能・相同性  F&H 検索 F&H 検索 |
- リンク
リンク
| EMDBのページ |  EMDB (EBI/PDBe) / EMDB (EBI/PDBe) /  EMDataResource EMDataResource |
|---|
- マップ
マップ
| ファイル |  ダウンロード / ファイル: emd_27261.map.gz / 形式: CCP4 / 大きさ: 52.7 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) ダウンロード / ファイル: emd_27261.map.gz / 形式: CCP4 / 大きさ: 52.7 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) | ||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| ボクセルのサイズ | X=Y=Z: 1.07 Å | ||||||||||||||||||||
| 密度 |
| ||||||||||||||||||||
| 対称性 | 空間群: 1 | ||||||||||||||||||||
| 詳細 | EMDB XML:
|
-添付データ
-追加マップ: #1
| ファイル | emd_27261_additional_1.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 投影像・断面図 |
| ||||||||||||
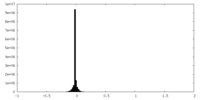
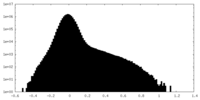
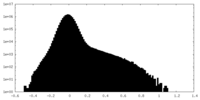
| 密度ヒストグラム |
-ハーフマップ: #2
| ファイル | emd_27261_half_map_1.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 投影像・断面図 |
| ||||||||||||
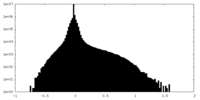
| 密度ヒストグラム |
-ハーフマップ: #1
| ファイル | emd_27261_half_map_2.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 投影像・断面図 |
| ||||||||||||
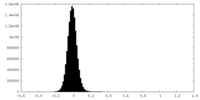
| 密度ヒストグラム |
- 試料の構成要素
試料の構成要素
-全体 : gRAMP-TPR-CHAT with Non match PFS target RNA Craspase
| 全体 | 名称: gRAMP-TPR-CHAT with Non match PFS target RNA Craspase |
|---|---|
| 要素 |
|
-超分子 #1: gRAMP-TPR-CHAT with Non match PFS target RNA Craspase
| 超分子 | 名称: gRAMP-TPR-CHAT with Non match PFS target RNA Craspase タイプ: complex / ID: 1 / 親要素: 0 / 含まれる分子: #1-#4 |
|---|---|
| 由来(天然) | 生物種:  Candidatus Scalindua brodae (バクテリア) Candidatus Scalindua brodae (バクテリア) |
-分子 #1: CHAT domain protein
| 分子 | 名称: CHAT domain protein / タイプ: protein_or_peptide / ID: 1 / コピー数: 1 / 光学異性体: LEVO |
|---|---|
| 由来(天然) | 生物種:  Candidatus Scalindua brodae (バクテリア) Candidatus Scalindua brodae (バクテリア) |
| 分子量 | 理論値: 78.403711 KDa |
| 組換発現 | 生物種:  |
| 配列 | 文字列: PTREDIDRKE AERLLDEAFN PRTKPVDRKK IINSALKILI GLYKEKKDDL TSASFISIAR AYYLVSITIL PKGTTIPEKK KEALRKGIE FIDRAINKFN GSILDSQRAF RIKSVLSIEF NRIDREKCDN IKLKNLLNEA VDKGCTDFDT YEWDIQIAIR L CELGVDME ...文字列: PTREDIDRKE AERLLDEAFN PRTKPVDRKK IINSALKILI GLYKEKKDDL TSASFISIAR AYYLVSITIL PKGTTIPEKK KEALRKGIE FIDRAINKFN GSILDSQRAF RIKSVLSIEF NRIDREKCDN IKLKNLLNEA VDKGCTDFDT YEWDIQIAIR L CELGVDME GHFDNLIKSN KANDLQKAKA YYFIKKDDHK AKEHMDKCTA SLKYTPCSHR LWDETVGFIE RLKGDSSTLW RD FAIKTYR SCRVQEKETG TLRLRWYWSR HRVLYDMAFL AVKEQADDEE PDVNVKQAKI KKLAEISDSL KSRFSLRLSD MEK MPKSDD ESNHEFKKFL DKCVTAYRSI YVINRKLLEL TQVPEGWVVV HFYLNKLEGM GNAIVFDKCA NSWQYKEFQY KELF EVFLT WQANYNLYKE NAAEHLVTLC KKIGETMPFL FCDNFIPNGK DVLFVPHDFL HRLPLHGSIE NKTNGKLFLE NHSCC YLPA WSFASEKEAS TSDEYVLLKN FDQGHFETLQ NNQIWGTQSV KDGASSDDLE NIRNNPRLLT ILCHGEANMS NPFRSM LKL ANGGITYLEI LNSVKGLKGS QVILGACETD LVPPLSDVMD EHYSVATALL LIGAAGVVGT MWKVRSNKTK SLIEWKL EN IEYKLNEWQK ETGGAAYKDH PPTFYRSIAF RSIGFPL UniProtKB: CHAT domain protein |
-分子 #2: RAMP superfamily protein
| 分子 | 名称: RAMP superfamily protein / タイプ: protein_or_peptide / ID: 2 / コピー数: 1 / 光学異性体: LEVO |
|---|---|
| 由来(天然) | 生物種:  Candidatus Scalindua brodae (バクテリア) Candidatus Scalindua brodae (バクテリア) |
| 分子量 | 理論値: 147.151625 KDa |
| 組換発現 | 生物種:  |
| 配列 | 文字列: MNITVELTFF EPYRLVEWFD WDARKKSHSA MRGQAFAQWT WKGKGRTAGK SFITGTLVRS AVIKAVEELL SLNNGKWEGV PCCNGSFQT DESKGKKPSF LRKRHTLQWQ ANNKNICDKE EACPFCILLG RFDNAGKVHE RNKDYDIHFS NFDLDHKQEK N DLRLVDIA ...文字列: MNITVELTFF EPYRLVEWFD WDARKKSHSA MRGQAFAQWT WKGKGRTAGK SFITGTLVRS AVIKAVEELL SLNNGKWEGV PCCNGSFQT DESKGKKPSF LRKRHTLQWQ ANNKNICDKE EACPFCILLG RFDNAGKVHE RNKDYDIHFS NFDLDHKQEK N DLRLVDIA SGRILNRVDF DTGKAKDYFR TWEADYETYG TYTGRITLRN EHAKKLLLAS LGFVDKLCGA LCRIEVIKDH ND ELRKQAE VIVEAFKQND KLEKIRILAD AIRTLRLHGE GVIEKDELPD GKEERDKGHH LWDIKVQGTA LRTKLKELWQ SNK DIGWRK FTEMLGSNLY LIYKKETGGV STRFRILGDT EYYSKAHDSE GSDLFIPVTP PEGIETKEWI IVGRLKAATP FYFG VQQPS DSIPGKEKKS EDSLVINEHT SFNILLDKEN RYRIPRSALR GALRRDLRTA FGSGCNVSLG GQILCNCKVC IEMRR ITLK DSVSDFSEPP EIRYRIAKNP GTATVEDGSL FDIEVGPEGL TFPFVLRYRG HKFPEQLSSV IRYWEENDGK NGMAWL GGL DSTGKGRFAL KDIKIFEWDL NQKINEYIKE RGMRGKEKEL LEMGESSLPD GLIPYKFFEE RECLFPYKEN LKPQWSE VQ YTIEVGSPLL TADTISALTE PGNRDAIAYK KRVYNDGNNA IEPEPRFAVK SETHRGIFRT AVGRRTGDLG KEDHEDCT C DMCIIFGNEH ESSKIRFEDL ELINGNEFEK LEKHIDHVAI DRFTGGALDK AKFDTYPLAG SPKKPLKLKG RFWIKKGFS GDHKLLITTA LSDIRDGLYP LGSKGGVGYG WVAGISIDDN VPDDFKEMIN KTNNDYVHPG HQSPKQDHKN KNIYYPHYFL DSGSKVYRE KDIITHEEFT EELLSGKINC KLETLTPLII PDTSDENGLK LQGNKPGHKN YKFFNINGEL MIPGSELRGM L RTHFEALT KSCFAIFGED STLSWASKTL GGKLDKALHP CTGLSDGLCP GCHLFGTTDY KGRVKFGFAK YENGPEWLIT RG NNPERSL TLGVLESPRP AFSIPDDESE IPGRKFYLHH NGWRIIRQKQ LEIRETVQPE RNVTTEVMDK GNVFSFDVRF ENL REWELG LLLQSLDPGK NIAHKLGKGK PYGFGSVKIK IDSLHTFKIN SNNDKIKRVP QSDIREYINK GYQKLIEWSG NNSI QKGNV LPQWHVIPHI DKLYKLLWVP FLNDSKLEPD VRYPVLNEES KGYIEGSDYT YKKLGDKDNL PYKTRVKGLT TPWSP WNPF QV UniProtKB: RAMP superfamily protein, RAMP superfamily protein |
-分子 #3: RNA (36-MER)
| 分子 | 名称: RNA (36-MER) / タイプ: rna / ID: 3 / コピー数: 1 |
|---|---|
| 由来(天然) | 生物種:  Candidatus Scalindua brodae (バクテリア) Candidatus Scalindua brodae (バクテリア) |
| 分子量 | 理論値: 11.423787 KDa |
| 配列 | 文字列: GACUUAAUGU CACGGUACCC AAUUUUCUGC CCCGGA |
-分子 #4: RNA (5'-R(P*UP*CP*CP*GP*GP*GP*GP*CP*AP*GP*AP*AP*AP*AP*UP*UP*GP*GP...
| 分子 | 名称: RNA (5'-R(P*UP*CP*CP*GP*GP*GP*GP*CP*AP*GP*AP*AP*AP*AP*UP*UP*GP*GP*AP*CP*GP*AP*U)-3') タイプ: rna / ID: 4 / コピー数: 1 |
|---|---|
| 由来(天然) | 生物種:  Candidatus Scalindua brodae (バクテリア) Candidatus Scalindua brodae (バクテリア) |
| 分子量 | 理論値: 7.466521 KDa |
| 配列 | 文字列: UCCGGGGCAG AAAAUUGGAC GAU |
-分子 #5: ZINC ION
| 分子 | 名称: ZINC ION / タイプ: ligand / ID: 5 / コピー数: 4 / 式: ZN |
|---|---|
| 分子量 | 理論値: 65.409 Da |
-実験情報
-構造解析
| 手法 | クライオ電子顕微鏡法 |
|---|---|
 解析 解析 | 単粒子再構成法 |
| 試料の集合状態 | particle |
- 試料調製
試料調製
| 緩衝液 | pH: 7.5 |
|---|---|
| 凍結 | 凍結剤: ETHANE |
- 電子顕微鏡法
電子顕微鏡法
| 顕微鏡 | FEI TITAN KRIOS |
|---|---|
| 撮影 | フィルム・検出器のモデル: GATAN K3 BIOQUANTUM (6k x 4k) 平均電子線量: 50.0 e/Å2 |
| 電子線 | 加速電圧: 300 kV / 電子線源:  FIELD EMISSION GUN FIELD EMISSION GUN |
| 電子光学系 | 照射モード: FLOOD BEAM / 撮影モード: BRIGHT FIELD / 最大 デフォーカス(公称値): 2.5 µm / 最小 デフォーカス(公称値): 1.0 µm |
| 実験機器 |  モデル: Titan Krios / 画像提供: FEI Company |
- 画像解析
画像解析
| 初期モデル | モデルのタイプ: NONE |
|---|---|
| 最終 再構成 | 解像度のタイプ: BY AUTHOR / 解像度: 2.57 Å / 解像度の算出法: FSC 0.143 CUT-OFF / 使用した粒子像数: 340526 |
| 初期 角度割当 | タイプ: NOT APPLICABLE |
| 最終 角度割当 | タイプ: NOT APPLICABLE |
 ムービー
ムービー コントローラー
コントローラー





 Z
Z Y
Y X
X