+ データを開く
データを開く
- 基本情報
基本情報
| 登録情報 | データベース: EMDB / ID: EMD-25438 | |||||||||
|---|---|---|---|---|---|---|---|---|---|---|
| タイトル | Cryo-EM structure of human NatB in complex with CoA-Alpha-Synuclein | |||||||||
 マップデータ マップデータ | ||||||||||
 試料 試料 |
| |||||||||
 キーワード キーワード | NatB / NAA20 / NAA25 / TRANSFERASE / alpha Synuclein | |||||||||
| 機能・相同性 |  機能・相同性情報 機能・相同性情報N-terminal peptidyl-glutamine acetylation / N-terminal methionine Nalpha-acetyltransferase NatB / N-terminal peptidyl-aspartic acid acetylation / N-terminal peptidyl-glutamic acid acetylation / NatB complex / N-terminal protein amino acid acetylation / protein N-terminal-methionine acetyltransferase activity / protein-N-terminal amino-acid acetyltransferase activity / acetyltransferase activator activity / negative regulation of mitochondrial electron transport, NADH to ubiquinone ...N-terminal peptidyl-glutamine acetylation / N-terminal methionine Nalpha-acetyltransferase NatB / N-terminal peptidyl-aspartic acid acetylation / N-terminal peptidyl-glutamic acid acetylation / NatB complex / N-terminal protein amino acid acetylation / protein N-terminal-methionine acetyltransferase activity / protein-N-terminal amino-acid acetyltransferase activity / acetyltransferase activator activity / negative regulation of mitochondrial electron transport, NADH to ubiquinone / : / neutral lipid metabolic process / regulation of acyl-CoA biosynthetic process / negative regulation of dopamine uptake involved in synaptic transmission / negative regulation of norepinephrine uptake / response to desipramine / positive regulation of SNARE complex assembly / positive regulation of hydrogen peroxide catabolic process / supramolecular fiber / mitochondrial membrane organization / regulation of synaptic vesicle recycling / negative regulation of chaperone-mediated autophagy / regulation of reactive oxygen species biosynthetic process / negative regulation of platelet-derived growth factor receptor signaling pathway / positive regulation of protein localization to cell periphery / negative regulation of exocytosis / regulation of glutamate secretion / dopamine biosynthetic process / SNARE complex assembly / regulation of norepinephrine uptake / response to iron(II) ion / positive regulation of neurotransmitter secretion / positive regulation of inositol phosphate biosynthetic process / regulation of locomotion / negative regulation of dopamine metabolic process / transporter regulator activity / regulation of macrophage activation / negative regulation of microtubule polymerization / synaptic vesicle transport / synaptic vesicle priming / dopamine uptake involved in synaptic transmission / protein kinase inhibitor activity / mitochondrial ATP synthesis coupled electron transport / regulation of dopamine secretion / dynein complex binding / positive regulation of receptor recycling / negative regulation of thrombin-activated receptor signaling pathway / cuprous ion binding / nuclear outer membrane / response to magnesium ion / positive regulation of endocytosis / positive regulation of exocytosis / synaptic vesicle exocytosis / kinesin binding / enzyme inhibitor activity / synaptic vesicle endocytosis / cysteine-type endopeptidase inhibitor activity / negative regulation of serotonin uptake / response to type II interferon / regulation of presynapse assembly / alpha-tubulin binding / beta-tubulin binding / phospholipase binding / behavioral response to cocaine / supramolecular fiber organization / phospholipid metabolic process / cellular response to fibroblast growth factor stimulus / inclusion body / axon terminus / Hsp70 protein binding / cellular response to epinephrine stimulus / cytoskeleton organization / response to interleukin-1 / regulation of microtubule cytoskeleton organization / cellular response to copper ion / positive regulation of release of sequestered calcium ion into cytosol / SNARE binding / adult locomotory behavior / excitatory postsynaptic potential / regulation of actin cytoskeleton organization / protein tetramerization / phosphoprotein binding / fatty acid metabolic process / microglial cell activation / ferrous iron binding / regulation of long-term neuronal synaptic plasticity / synapse organization / protein destabilization / PKR-mediated signaling / phospholipid binding / receptor internalization / tau protein binding / long-term synaptic potentiation / terminal bouton / positive regulation of inflammatory response / synaptic vesicle membrane / actin cytoskeleton / actin binding / growth cone / cellular response to oxidative stress 類似検索 - 分子機能 | |||||||||
| 生物種 |  Homo sapiens (ヒト) Homo sapiens (ヒト) | |||||||||
| 手法 | 単粒子再構成法 / クライオ電子顕微鏡法 / 解像度: 3.14 Å | |||||||||
 データ登録者 データ登録者 | Deng S / Marmorstein R | |||||||||
| 資金援助 |  米国, 1件 米国, 1件
| |||||||||
 引用 引用 |  ジャーナル: Not Published ジャーナル: Not Publishedタイトル: Cryo-EM structure of human NatB in complex with CoA-Alpha-Synuclein 著者: Deng S / Marmorstein R | |||||||||
| 履歴 |
|
- 構造の表示
構造の表示
| ムービー |
 ムービービューア ムービービューア |
|---|---|
| 構造ビューア | EMマップ:  SurfView SurfView Molmil Molmil Jmol/JSmol Jmol/JSmol |
| 添付画像 |
- ダウンロードとリンク
ダウンロードとリンク
-EMDBアーカイブ
| マップデータ |  emd_25438.map.gz emd_25438.map.gz | 9.8 MB |  EMDBマップデータ形式 EMDBマップデータ形式 | |
|---|---|---|---|---|
| ヘッダ (付随情報) |  emd-25438-v30.xml emd-25438-v30.xml emd-25438.xml emd-25438.xml | 15 KB 15 KB | 表示 表示 |  EMDBヘッダ EMDBヘッダ |
| 画像 |  emd_25438.png emd_25438.png | 168.9 KB | ||
| Filedesc metadata |  emd-25438.cif.gz emd-25438.cif.gz | 6.1 KB | ||
| アーカイブディレクトリ |  http://ftp.pdbj.org/pub/emdb/structures/EMD-25438 http://ftp.pdbj.org/pub/emdb/structures/EMD-25438 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-25438 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-25438 | HTTPS FTP |
-検証レポート
| 文書・要旨 |  emd_25438_validation.pdf.gz emd_25438_validation.pdf.gz | 372.7 KB | 表示 |  EMDB検証レポート EMDB検証レポート |
|---|---|---|---|---|
| 文書・詳細版 |  emd_25438_full_validation.pdf.gz emd_25438_full_validation.pdf.gz | 372.3 KB | 表示 | |
| XML形式データ |  emd_25438_validation.xml.gz emd_25438_validation.xml.gz | 6.3 KB | 表示 | |
| CIF形式データ |  emd_25438_validation.cif.gz emd_25438_validation.cif.gz | 7.2 KB | 表示 | |
| アーカイブディレクトリ |  https://ftp.pdbj.org/pub/emdb/validation_reports/EMD-25438 https://ftp.pdbj.org/pub/emdb/validation_reports/EMD-25438 ftp://ftp.pdbj.org/pub/emdb/validation_reports/EMD-25438 ftp://ftp.pdbj.org/pub/emdb/validation_reports/EMD-25438 | HTTPS FTP |
-関連構造データ
- リンク
リンク
| EMDBのページ |  EMDB (EBI/PDBe) / EMDB (EBI/PDBe) /  EMDataResource EMDataResource |
|---|---|
| 「今月の分子」の関連する項目 |
- マップ
マップ
| ファイル |  ダウンロード / ファイル: emd_25438.map.gz / 形式: CCP4 / 大きさ: 91.1 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) ダウンロード / ファイル: emd_25438.map.gz / 形式: CCP4 / 大きさ: 91.1 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 投影像・断面図 | 画像のコントロール
画像は Spider により作成 | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| ボクセルのサイズ | X=Y=Z: 0.83 Å | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 密度 |
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 対称性 | 空間群: 1 | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 詳細 | EMDB XML:
CCP4マップ ヘッダ情報:
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
-添付データ
- 試料の構成要素
試料の構成要素
-全体 : human NatB complex
| 全体 | 名称: human NatB complex |
|---|---|
| 要素 |
|
-超分子 #1: human NatB complex
| 超分子 | 名称: human NatB complex / タイプ: complex / ID: 1 / 親要素: 0 / 含まれる分子: #1-#2 |
|---|
-超分子 #2: N-alpha-acetyltransferase 20, N-alpha-acetyltransferase 25, NatB ...
| 超分子 | 名称: N-alpha-acetyltransferase 20, N-alpha-acetyltransferase 25, NatB auxiliary subunit タイプ: complex / ID: 2 / 親要素: 1 / 含まれる分子: #1-#2 |
|---|---|
| 由来(天然) | 生物種:  Homo sapiens (ヒト) Homo sapiens (ヒト) |
-超分子 #3: MDVFM peptide
| 超分子 | 名称: MDVFM peptide / タイプ: complex / ID: 3 / 親要素: 1 / 含まれる分子: #3 |
|---|---|
| 由来(天然) | 生物種:  Homo sapiens (ヒト) Homo sapiens (ヒト) |
-分子 #1: N-alpha-acetyltransferase 20
| 分子 | 名称: N-alpha-acetyltransferase 20 / タイプ: protein_or_peptide / ID: 1 / コピー数: 1 / 光学異性体: LEVO EC番号: N-terminal methionine Nalpha-acetyltransferase NatB |
|---|---|
| 由来(天然) | 生物種:  Homo sapiens (ヒト) Homo sapiens (ヒト) |
| 分子量 | 理論値: 20.390133 KDa |
| 組換発現 | 生物種:  |
| 配列 | 文字列: MTTLRAFTCD DLFRFNNINL DPLTETYGIP FYLQYLAHWP EYFIVAEAPG GELMGYIMGK AEGSVAREEW HGHVTALSVA PEFRRLGLA AKLMELLEEI SERKGGFFVD LFVRVSNQVA VNMYKQLGYS VYRTVIEYYS ASNGEPDEDA YDMRKALSRD T EKKSIIPL PHPVRPEDIE UniProtKB: N-alpha-acetyltransferase 20 |
-分子 #2: N-alpha-acetyltransferase 25, NatB auxiliary subunit
| 分子 | 名称: N-alpha-acetyltransferase 25, NatB auxiliary subunit タイプ: protein_or_peptide / ID: 2 / コピー数: 1 / 光学異性体: LEVO |
|---|---|
| 由来(天然) | 生物種:  Homo sapiens (ヒト) Homo sapiens (ヒト) |
| 分子量 | 理論値: 109.64225 KDa |
| 組換発現 | 生物種:  |
| 配列 | 文字列: (UNK)(UNK)(UNK)(UNK)(UNK)(UNK)(UNK)(UNK)(UNK)(UNK) (UNK)(UNK)(UNK)(UNK)(UNK)(UNK) (UNK)(UNK)(UNK) (UNK)(UNK)(UNK)(UNK)(UNK)(UNK)(UNK)(UNK)(UNK)H CAKVLKAIGL QRTGKQEEA FTLAQEVAAL EPTDDNSLQA ...文字列: (UNK)(UNK)(UNK)(UNK)(UNK)(UNK)(UNK)(UNK)(UNK)(UNK) (UNK)(UNK)(UNK)(UNK)(UNK)(UNK) (UNK)(UNK)(UNK) (UNK)(UNK)(UNK)(UNK)(UNK)(UNK)(UNK)(UNK)(UNK)H CAKVLKAIGL QRTGKQEEA FTLAQEVAAL EPTDDNSLQA LTILYREMHR PELVTKLYEA AVKKVPNSEE YHSHLFMAYA RVGEYKKMQQ AGMALYKIVP KNPYYFWSV MSLIMQSISA QDENLSKTMF LPLAERMVEK MVKEDKIEAE AEVELYYMIL ERLGKYQEAL DVIRGKLGEK L TSEIQSRE NKCMAMYKKL SRWPECNALS RRLLLKNSDD WQFYLTYFDS VFRLIEEAWS PPAEGEHSLE GEVHYSAEKA VK FIEDRIT EESKSSRHLR GPHLAKLELI RRLRSQGCND EYKLGDPEEL MFQYFKKFGD KPCCFTDLKV FVDLLPATQC TKF INQLLG VVPLSTPTED KLALPADIRA LQQHLCVVQL TRLLGLYHTM DKNQKLSVVR ELMLRYQHGL EFGKTCLKTE LQFS DYYCL LAVHALIDVW RETGDETTVW QALTLLEEGL THSPSNAQFK LLLVRIYCML GAFEPVVDLY SSLDAKHIQH DTIGY LLTR YAESLGQYAA ASQSCNFALR FFHSNQKDTS EYIIQAYKYG AFEKIPEFIA FRNRLNNSLH FAQVRTERML LDLLLE ANI STSLAESIKS MNLRPEEDDI PWEDLRDNRD LNVFFSWDPK DRDVSEEHKK LSLEEETLWL RIRSLTLRLI SGLPSLN HP VEPKNSEKTA ENGVSSRIDI LRLLLQQLEA TLETGKRFIE KDIQYPFLGP VPTRMGGFFN SGCSQCQISS FYLVNDIY E LDTSGLEDTM EIQERIENSF KSLLDQLKDV FSKCKGDLLE VKDGNLKTHP TLLENLVFFV ETISVILWVS SYCESVLRP YKLNLQKKKK KKKETSIIMP PVFTSFQDYV TGLQTLISNV VDHIKGLETH LIALKLEELI LEDTSLSPEE RKFSKTVQGK VQSSYLHSL LEMGELLKKR LETTKKLKI UniProtKB: N-alpha-acetyltransferase 25, NatB auxiliary subunit |
-分子 #3: Alpha-synuclein
| 分子 | 名称: Alpha-synuclein / タイプ: protein_or_peptide / ID: 3 / コピー数: 1 / 光学異性体: LEVO |
|---|---|
| 由来(天然) | 生物種:  Homo sapiens (ヒト) Homo sapiens (ヒト) |
| 分子量 | 理論値: 667.837 Da |
| 組換発現 | 生物種:  |
| 配列 | 文字列: (ACE)MDVFM UniProtKB: Alpha-synuclein |
-分子 #4: COENZYME A
| 分子 | 名称: COENZYME A / タイプ: ligand / ID: 4 / コピー数: 1 / 式: COA |
|---|---|
| 分子量 | 理論値: 767.534 Da |
| Chemical component information | 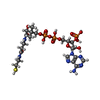 ChemComp-COA: |
-実験情報
-構造解析
| 手法 | クライオ電子顕微鏡法 |
|---|---|
 解析 解析 | 単粒子再構成法 |
| 試料の集合状態 | particle |
- 試料調製
試料調製
| 濃度 | 1.0 mg/mL | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 緩衝液 | pH: 7 構成要素:
| ||||||||||||
| 凍結 | 凍結剤: ETHANE / チャンバー内湿度: 100 % / チャンバー内温度: 289 K / 装置: FEI VITROBOT MARK II |
- 電子顕微鏡法
電子顕微鏡法
| 顕微鏡 | FEI TITAN KRIOS |
|---|---|
| 撮影 | #0 - Image recording ID: 1 #0 - フィルム・検出器のモデル: GATAN K3 (6k x 4k) #0 - 平均電子線量: 1.6 e/Å2 / #1 - Image recording ID: 2 #1 - フィルム・検出器のモデル: GATAN K3 (6k x 4k) #1 - 平均電子線量: 1.3 e/Å2 |
| 電子線 | 加速電圧: 300 kV / 電子線源:  FIELD EMISSION GUN FIELD EMISSION GUN |
| 電子光学系 | 照射モード: FLOOD BEAM / 撮影モード: BRIGHT FIELD |
| 実験機器 |  モデル: Titan Krios / 画像提供: FEI Company |
+ 画像解析
画像解析
-原子モデル構築 1
| 精密化 | 空間: REAL / プロトコル: AB INITIO MODEL |
|---|---|
| 得られたモデル |  PDB-7stx: |
 ムービー
ムービー コントローラー
コントローラー



















 Z (Sec.)
Z (Sec.) Y (Row.)
Y (Row.) X (Col.)
X (Col.)





















