+ データを開く
データを開く
- 基本情報
基本情報
| 登録情報 | データベース: EMDB / ID: EMD-24615 | ||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| タイトル | Cryo-EM structure of murine Dispatched 'T' conformation | ||||||||||||||||||
 マップデータ マップデータ | DISP1-A "T" - auto-sharpened map from cryoSPARC nonuniform refinement (paper version), units of standard deviation above mean density. | ||||||||||||||||||
 試料 試料 |
| ||||||||||||||||||
 キーワード キーワード | RND transporter / Hedgehog binding / Sterol sensing domain / sodium binding / MEMBRANE PROTEIN | ||||||||||||||||||
| 機能・相同性 |  機能・相同性情報 機能・相同性情報patched ligand maturation / diaphragm development / embryonic pattern specification / dorsal/ventral pattern formation / peptide transport / determination of left/right symmetry / molecular carrier activity / smoothened signaling pathway / membrane 類似検索 - 分子機能 | ||||||||||||||||||
| 生物種 |  | ||||||||||||||||||
| 手法 | 単粒子再構成法 / クライオ電子顕微鏡法 / 解像度: 2.5 Å | ||||||||||||||||||
 データ登録者 データ登録者 | Asarnow D / Wang Q | ||||||||||||||||||
| 資金援助 |  米国, 5件 米国, 5件
| ||||||||||||||||||
 引用 引用 |  ジャーナル: Nature / 年: 2021 ジャーナル: Nature / 年: 2021タイトル: Dispatched uses Na flux to power release of lipid-modified Hedgehog. 著者: Qianqian Wang / Daniel E Asarnow / Ke Ding / Randall K Mann / Jason Hatakeyama / Yunxiao Zhang / Yong Ma / Yifan Cheng / Philip A Beachy /   要旨: The Dispatched protein, which is related to the NPC1 and PTCH1 cholesterol transporters and to H-driven transporters of the RND family, enables tissue-patterning activity of the lipid-modified ...The Dispatched protein, which is related to the NPC1 and PTCH1 cholesterol transporters and to H-driven transporters of the RND family, enables tissue-patterning activity of the lipid-modified Hedgehog protein by releasing it from tightly -localized sites of embryonic expression. Here we determine a cryo-electron microscopy structure of the mouse protein Dispatched homologue 1 (DISP1), revealing three Na ions coordinated within a channel that traverses its transmembrane domain. We find that the rate of Hedgehog export is dependent on the Na gradient across the plasma membrane. The transmembrane channel and Na binding are disrupted in DISP1-NNN, a variant with asparagine substitutions for three intramembrane aspartate residues that each coordinate and neutralize the charge of one of the three Na ions. DISP1-NNN and variants that disrupt single Na sites retain binding to, but are impaired in export of the lipid-modified Hedgehog protein to the SCUBE2 acceptor. Interaction of the amino-terminal signalling domain of the Sonic hedgehog protein (ShhN) with DISP1 occurs via an extensive buried surface area and contacts with an extended furin-cleaved DISP1 arm. Variability analysis reveals that ShhN binding is restricted to one extreme of a continuous series of DISP1 conformations. The bound and unbound DISP1 conformations display distinct Na-site occupancies, which suggests a mechanism by which transmembrane Na flux may power extraction of the lipid-linked Hedgehog signal from the membrane. Na-coordinating residues in DISP1 are conserved in PTCH1 and other metazoan RND family members, suggesting that Na flux powers their conformationally driven activities. | ||||||||||||||||||
| 履歴 |
|
- 構造の表示
構造の表示
| ムービー |
 ムービービューア ムービービューア |
|---|---|
| 構造ビューア | EMマップ:  SurfView SurfView Molmil Molmil Jmol/JSmol Jmol/JSmol |
| 添付画像 |
- ダウンロードとリンク
ダウンロードとリンク
-EMDBアーカイブ
| マップデータ |  emd_24615.map.gz emd_24615.map.gz | 114.5 MB |  EMDBマップデータ形式 EMDBマップデータ形式 | |
|---|---|---|---|---|
| ヘッダ (付随情報) |  emd-24615-v30.xml emd-24615-v30.xml emd-24615.xml emd-24615.xml | 27.8 KB 27.8 KB | 表示 表示 |  EMDBヘッダ EMDBヘッダ |
| 画像 |  emd_24615.png emd_24615.png | 132.7 KB | ||
| マスクデータ |  emd_24615_msk_1.map emd_24615_msk_1.map emd_24615_msk_2.map emd_24615_msk_2.map | 125 MB 125 MB |  マスクマップ マスクマップ | |
| Filedesc metadata |  emd-24615.cif.gz emd-24615.cif.gz | 7.6 KB | ||
| その他 |  emd_24615_additional_1.map.gz emd_24615_additional_1.map.gz emd_24615_additional_2.map.gz emd_24615_additional_2.map.gz emd_24615_half_map_1.map.gz emd_24615_half_map_1.map.gz emd_24615_half_map_2.map.gz emd_24615_half_map_2.map.gz | 118.1 MB 62.8 MB 116 MB 116 MB | ||
| アーカイブディレクトリ |  http://ftp.pdbj.org/pub/emdb/structures/EMD-24615 http://ftp.pdbj.org/pub/emdb/structures/EMD-24615 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-24615 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-24615 | HTTPS FTP |
-関連構造データ
- リンク
リンク
| EMDBのページ |  EMDB (EBI/PDBe) / EMDB (EBI/PDBe) /  EMDataResource EMDataResource |
|---|---|
| 「今月の分子」の関連する項目 |
- マップ
マップ
| ファイル |  ダウンロード / ファイル: emd_24615.map.gz / 形式: CCP4 / 大きさ: 125 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) ダウンロード / ファイル: emd_24615.map.gz / 形式: CCP4 / 大きさ: 125 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | DISP1-A "T" - auto-sharpened map from cryoSPARC nonuniform refinement (paper version), units of standard deviation above mean density. | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 投影像・断面図 | 画像のコントロール
画像は Spider により作成 | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| ボクセルのサイズ | X=Y=Z: 0.835 Å | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 密度 |
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 対称性 | 空間群: 1 | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 詳細 | EMDB XML:
CCP4マップ ヘッダ情報:
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
-添付データ
-マスク #1
| ファイル |  emd_24615_msk_1.map emd_24615_msk_1.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 投影像・断面図 |
| ||||||||||||
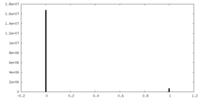
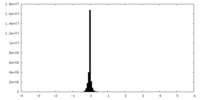
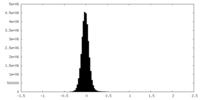
| 密度ヒストグラム |
-マスク #2
| ファイル |  emd_24615_msk_2.map emd_24615_msk_2.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 投影像・断面図 |
| ||||||||||||
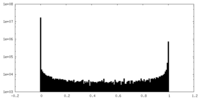
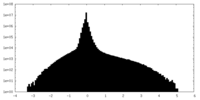
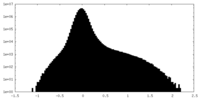
| 密度ヒストグラム |
-追加マップ: DISP1-A "T" - auto-sharpened map from cryoSPARC nonuniform...
| ファイル | emd_24615_additional_1.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | DISP1-A "T" - auto-sharpened map from cryoSPARC nonuniform refinement (paper version). | ||||||||||||
| 投影像・断面図 |
| ||||||||||||
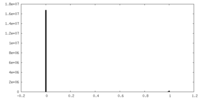
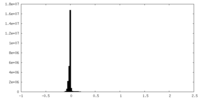
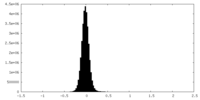
| 密度ヒストグラム |
-追加マップ: DISP1-A "T" - raw map from cryoSPARC nonuniform...
| ファイル | emd_24615_additional_2.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | DISP1-A "T" - raw map from cryoSPARC nonuniform refinement (paper version). | ||||||||||||
| 投影像・断面図 |
| ||||||||||||
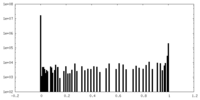
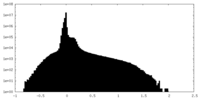
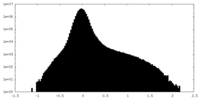
| 密度ヒストグラム |
-ハーフマップ: DISP1-A "T" - half map 1 from cryoSPARC...
| ファイル | emd_24615_half_map_1.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | DISP1-A "T" - half map 1 from cryoSPARC nonuniform refinement (paper version). | ||||||||||||
| 投影像・断面図 |
| ||||||||||||
| 密度ヒストグラム |
-ハーフマップ: DISP1-A "T" - half map 2 from cryoSPARC...
| ファイル | emd_24615_half_map_2.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | DISP1-A "T" - half map 2 from cryoSPARC nonuniform refinement (paper version). | ||||||||||||
| 投影像・断面図 |
| ||||||||||||
| 密度ヒストグラム |
- 試料の構成要素
試料の構成要素
-全体 : Dispatched protein 'T' conformation
| 全体 | 名称: Dispatched protein 'T' conformation |
|---|---|
| 要素 |
|
-超分子 #1: Dispatched protein 'T' conformation
| 超分子 | 名称: Dispatched protein 'T' conformation / タイプ: complex / ID: 1 / 親要素: 0 / 含まれる分子: #1 |
|---|---|
| 由来(天然) | 生物種:  |
| 分子量 | 理論値: 151.91493 KDa |
-分子 #1: Protein dispatched homolog 1
| 分子 | 名称: Protein dispatched homolog 1 / タイプ: protein_or_peptide / ID: 1 / コピー数: 1 / 光学異性体: LEVO |
|---|---|
| 由来(天然) | 生物種:  |
| 分子量 | 理論値: 152.071141 KDa |
| 組換発現 | 生物種:  Homo sapiens (ヒト) Homo sapiens (ヒト) |
| 配列 | 文字列: MARPFKFPRS YAALLADWPV VVLGMCTLLI VVCALVGVLV PELPDFSDPL LGFEPRGTTI GQRLVTWNNM MRNTGYKATL ANYPYKYAE EQARSHRDDR WSDDHHERER REVDWNFQKD SFFCDVPSDG YSRVVFASAG GETLWNLPAI KSMCDVDNSR I RSHPQFSD ...文字列: MARPFKFPRS YAALLADWPV VVLGMCTLLI VVCALVGVLV PELPDFSDPL LGFEPRGTTI GQRLVTWNNM MRNTGYKATL ANYPYKYAE EQARSHRDDR WSDDHHERER REVDWNFQKD SFFCDVPSDG YSRVVFASAG GETLWNLPAI KSMCDVDNSR I RSHPQFSD LCQRTTAVSC CPSWTLGNYI AILNNRSSCQ KIVERDVSHT LKLLRTCAKH YQNGTLGPDC WDKAARRKDQ LK CTNVPRK CTKYNAVYQI LHYLVDKDFM TPKTADYAVP ALKYSMLFSP TEKGESMMNI YLDNFENWNS SDGITTVTGI EFG IKHSLF QDYLLMDTVY PAIAIAIVLL IMCVYTKSMF ITLMTMFAII SSLIVSYFLY RVVFNFEFFP FMNLTALIIL VGIG ADDAF VLCDVWNYTK FDKPRAETSE AVSVTLQHAA LSMFVTSFTT AAAFYANYVS NITAIRCFGV YAGTAILVNY VLMVT WLPA VIVLHERYLL NIFTCFRKPQ PQAYDKSCWA VLCQKCRRVL FAVSEASRIF FEKVLPCIVI KFRYLWLIWF LALTVG GAY IVCVNPKMKL PSLELSEFQV FRSSHPFERY DAEFKKLFMF ERVHHGEELH MPITVIWGVS PEDSGDPLNP KSKGELT LD STFNIASPAS QAWILHFCQK LRNQTFFHQT EQQDFTSCFI ETFKQWMENQ DCDEPALYPC CSHCSFPYKQ EVFELCIK K AIMELDRSTG YHLNNKTPGP RFDINDTIRA VVLEFQSTFL FTLAYEKMQQ FYKEVDSWIS HELSSAPEGL SRGWFVSNL EFYDLQDSLS DGTLIAMGLS VAVAFSVMLL TTWNIIISLY AIVSIAGTIF VTVGSLVLLG WELNVLESVT ISVAVGLSVD FAVHYGVAY RLAPDPDREG KVIFSLSRMG SAIAMAALTT FVAGAMMMPS TVLAYTQLGT FMMLVMCVSW AFATFFFQCL C RCLGPQGT CGQIPFPTKL QCSPFSHTLS ARPGDRGPSK THAASAYSVD ARGQKSQLEH EFYELQPLAS HSCTSSEKTT YE EPHTCSE FFNGQAKNLR MPVPAAYSSE LTKSPSSEPG SALLQSCLEQ DTVCHFSLNP RCNCRDAYTH LQYGLPEIHC QQM GDSLCH KCASTAGGFV QIQSSVAPLK ASHQAAEGLL HPAQHMLPPG MQNSRPRNFF LHSVQHFQAQ ENLGRTSTHS TDER LPRTA ELSPPPSDSR STESFQRACC HPENNQRRLC KSRDPGDTEG SGGTKSKVSG LPNQTDKEEK QVEPSLLQTD ETVNS EHLN HNESNFTFSH LPGEAGCRSC PNSPQSCRSI MRSKCGTEDC QTPNLEANVP AVPTHSDLSG ESLLIKTL UniProtKB: Protein dispatched homolog 1 |
-分子 #2: CHOLESTEROL HEMISUCCINATE
| 分子 | 名称: CHOLESTEROL HEMISUCCINATE / タイプ: ligand / ID: 2 / コピー数: 26 / 式: Y01 |
|---|---|
| 分子量 | 理論値: 486.726 Da |
| Chemical component information |  ChemComp-Y01: |
-分子 #3: Lauryl Maltose Neopentyl Glycol
| 分子 | 名称: Lauryl Maltose Neopentyl Glycol / タイプ: ligand / ID: 3 / コピー数: 2 / 式: AV0 |
|---|---|
| 分子量 | 理論値: 1.005188 KDa |
| Chemical component information |  ChemComp-AV0: |
-分子 #4: 2-acetamido-2-deoxy-beta-D-glucopyranose
| 分子 | 名称: 2-acetamido-2-deoxy-beta-D-glucopyranose / タイプ: ligand / ID: 4 / コピー数: 5 / 式: NAG |
|---|---|
| 分子量 | 理論値: 221.208 Da |
| Chemical component information |  ChemComp-NAG: |
-分子 #5: SODIUM ION
| 分子 | 名称: SODIUM ION / タイプ: ligand / ID: 5 / コピー数: 2 |
|---|---|
| 分子量 | 理論値: 22.99 Da |
-分子 #6: water
| 分子 | 名称: water / タイプ: ligand / ID: 6 / コピー数: 43 / 式: HOH |
|---|---|
| 分子量 | 理論値: 18.015 Da |
| Chemical component information |  ChemComp-HOH: |
-実験情報
-構造解析
| 手法 | クライオ電子顕微鏡法 |
|---|---|
 解析 解析 | 単粒子再構成法 |
| 試料の集合状態 | particle |
- 試料調製
試料調製
| 濃度 | 1.56 mg/mL | |||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 緩衝液 | pH: 7.5 構成要素:
| |||||||||||||||||||||
| 凍結 | 凍結剤: ETHANE / チャンバー内湿度: 100 % / チャンバー内温度: 281 K / 装置: FEI VITROBOT MARK IV 詳細: Wait time 20 seconds, blot time 4 seconds, blotting force 0. |
- 電子顕微鏡法
電子顕微鏡法
| 顕微鏡 | FEI TITAN KRIOS |
|---|---|
| 特殊光学系 | エネルギーフィルター - 名称: GIF Bioquantum / エネルギーフィルター - スリット幅: 20 eV |
| 詳細 | Automated data collection in SerialEM using 3x3 image shift pattern (one shot per hole), using beam tilt compensation. |
| 撮影 | フィルム・検出器のモデル: GATAN K3 BIOQUANTUM (6k x 4k) 撮影したグリッド数: 1 / 実像数: 4487 / 平均電子線量: 66.7 e/Å2 |
| 電子線 | 加速電圧: 300 kV / 電子線源:  FIELD EMISSION GUN FIELD EMISSION GUN |
| 電子光学系 | C2レンズ絞り径: 100.0 µm / 倍率(補正後): 59880 / 照射モード: FLOOD BEAM / 撮影モード: BRIGHT FIELD / Cs: 2.7 mm / 最大 デフォーカス(公称値): 1.5 µm / 最小 デフォーカス(公称値): 0.5 µm / 倍率(公称値): 105000 |
| 試料ステージ | 試料ホルダーモデル: FEI TITAN KRIOS AUTOGRID HOLDER ホルダー冷却材: NITROGEN |
| 実験機器 |  モデル: Titan Krios / 画像提供: FEI Company |
+ 画像解析
画像解析
-原子モデル構築 1
| 精密化 | 空間: REAL / プロトコル: FLEXIBLE FIT / 温度因子: 72.1 |
|---|---|
| 得られたモデル |  PDB-7rpi: |
 ムービー
ムービー コントローラー
コントローラー



















 Z (Sec.)
Z (Sec.) Y (Row.)
Y (Row.) X (Col.)
X (Col.)