+ データを開く
データを開く
- 基本情報
基本情報
| 登録情報 | データベース: EMDB / ID: EMD-21652 | |||||||||
|---|---|---|---|---|---|---|---|---|---|---|
| タイトル | NanR dimer-DNA hetero-complex | |||||||||
 マップデータ マップデータ | Relion local resolution filtered map. Sharpening B-factor -100 | |||||||||
 試料 試料 |
| |||||||||
 キーワード キーワード | NanR dimer-DNA hetero-complex / transcriptional regulator / GntR superfamily / sialic acid / Neu5Ac / cooperativity. / GENE REGULATION | |||||||||
| 機能・相同性 |  機能・相同性情報 機能・相同性情報DNA-binding transcription factor activity / negative regulation of DNA-templated transcription / DNA binding 類似検索 - 分子機能 | |||||||||
| 生物種 |  | |||||||||
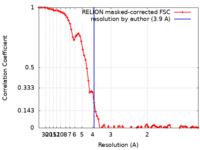
| 手法 | 単粒子再構成法 / クライオ電子顕微鏡法 / 解像度: 3.9 Å | |||||||||
 データ登録者 データ登録者 | Hariprasad V / Horne C | |||||||||
| 資金援助 |  ニュージーランド, 1件 ニュージーランド, 1件
| |||||||||
 引用 引用 |  ジャーナル: Nat Commun / 年: 2021 ジャーナル: Nat Commun / 年: 2021タイトル: Mechanism of NanR gene repression and allosteric induction of bacterial sialic acid metabolism. 著者: Christopher R Horne / Hariprasad Venugopal / Santosh Panjikar / David M Wood / Amy Henrickson / Emre Brookes / Rachel A North / James M Murphy / Rosmarie Friemann / Michael D W Griffin / ...著者: Christopher R Horne / Hariprasad Venugopal / Santosh Panjikar / David M Wood / Amy Henrickson / Emre Brookes / Rachel A North / James M Murphy / Rosmarie Friemann / Michael D W Griffin / Georg Ramm / Borries Demeler / Renwick C J Dobson /      要旨: Bacteria respond to environmental changes by inducing transcription of some genes and repressing others. Sialic acids, which coat human cell surfaces, are a nutrient source for pathogenic and ...Bacteria respond to environmental changes by inducing transcription of some genes and repressing others. Sialic acids, which coat human cell surfaces, are a nutrient source for pathogenic and commensal bacteria. The Escherichia coli GntR-type transcriptional repressor, NanR, regulates sialic acid metabolism, but the mechanism is unclear. Here, we demonstrate that three NanR dimers bind a (GGTATA)-repeat operator cooperatively and with high affinity. Single-particle cryo-electron microscopy structures reveal the DNA-binding domain is reorganized to engage DNA, while three dimers assemble in close proximity across the (GGTATA)-repeat operator. Such an interaction allows cooperative protein-protein interactions between NanR dimers via their N-terminal extensions. The effector, N-acetylneuraminate, binds NanR and attenuates the NanR-DNA interaction. The crystal structure of NanR in complex with N-acetylneuraminate reveals a domain rearrangement upon N-acetylneuraminate binding to lock NanR in a conformation that weakens DNA binding. Our data provide a molecular basis for the regulation of bacterial sialic acid metabolism. | |||||||||
| 履歴 |
|
- 構造の表示
構造の表示
| ムービー |
 ムービービューア ムービービューア |
|---|---|
| 構造ビューア | EMマップ:  SurfView SurfView Molmil Molmil Jmol/JSmol Jmol/JSmol |
| 添付画像 |
- ダウンロードとリンク
ダウンロードとリンク
-EMDBアーカイブ
| マップデータ |  emd_21652.map.gz emd_21652.map.gz | 31.5 MB |  EMDBマップデータ形式 EMDBマップデータ形式 | |
|---|---|---|---|---|
| ヘッダ (付随情報) |  emd-21652-v30.xml emd-21652-v30.xml emd-21652.xml emd-21652.xml | 23.8 KB 23.8 KB | 表示 表示 |  EMDBヘッダ EMDBヘッダ |
| FSC (解像度算出) |  emd_21652_fsc.xml emd_21652_fsc.xml | 8.1 KB | 表示 |  FSCデータファイル FSCデータファイル |
| 画像 |  emd_21652.png emd_21652.png | 158.5 KB | ||
| マスクデータ |  emd_21652_msk_1.map emd_21652_msk_1.map | 42.9 MB |  マスクマップ マスクマップ | |
| Filedesc metadata |  emd-21652.cif.gz emd-21652.cif.gz | 6.6 KB | ||
| その他 |  emd_21652_additional_1.map.gz emd_21652_additional_1.map.gz emd_21652_additional_2.map.gz emd_21652_additional_2.map.gz emd_21652_half_map_1.map.gz emd_21652_half_map_1.map.gz emd_21652_half_map_2.map.gz emd_21652_half_map_2.map.gz | 32.4 MB 7.1 MB 33 MB 33 MB | ||
| アーカイブディレクトリ |  http://ftp.pdbj.org/pub/emdb/structures/EMD-21652 http://ftp.pdbj.org/pub/emdb/structures/EMD-21652 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-21652 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-21652 | HTTPS FTP |
-検証レポート
| 文書・要旨 |  emd_21652_validation.pdf.gz emd_21652_validation.pdf.gz | 652.3 KB | 表示 |  EMDB検証レポート EMDB検証レポート |
|---|---|---|---|---|
| 文書・詳細版 |  emd_21652_full_validation.pdf.gz emd_21652_full_validation.pdf.gz | 651.8 KB | 表示 | |
| XML形式データ |  emd_21652_validation.xml.gz emd_21652_validation.xml.gz | 13.7 KB | 表示 | |
| CIF形式データ |  emd_21652_validation.cif.gz emd_21652_validation.cif.gz | 19.5 KB | 表示 | |
| アーカイブディレクトリ |  https://ftp.pdbj.org/pub/emdb/validation_reports/EMD-21652 https://ftp.pdbj.org/pub/emdb/validation_reports/EMD-21652 ftp://ftp.pdbj.org/pub/emdb/validation_reports/EMD-21652 ftp://ftp.pdbj.org/pub/emdb/validation_reports/EMD-21652 | HTTPS FTP |
-関連構造データ
| 関連構造データ |  6wfqMC  6wg7C M: このマップから作成された原子モデル C: 同じ文献を引用 ( |
|---|---|
| 類似構造データ | |
| 電子顕微鏡画像生データ |  EMPIAR-10836 (タイトル: CryoEM single particle dataset for NanR dimer-DNA hetero-complex. EMPIAR-10836 (タイトル: CryoEM single particle dataset for NanR dimer-DNA hetero-complex.Data size: 2.9 TB Data #1: Uncorrected movie frames [micrographs - multiframe]) |
- リンク
リンク
| EMDBのページ |  EMDB (EBI/PDBe) / EMDB (EBI/PDBe) /  EMDataResource EMDataResource |
|---|
- マップ
マップ
| ファイル |  ダウンロード / ファイル: emd_21652.map.gz / 形式: CCP4 / 大きさ: 42.9 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) ダウンロード / ファイル: emd_21652.map.gz / 形式: CCP4 / 大きさ: 42.9 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | Relion local resolution filtered map. Sharpening B-factor -100 | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| ボクセルのサイズ | X=Y=Z: 0.68 Å | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 密度 |
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 対称性 | 空間群: 1 | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 詳細 | EMDB XML:
CCP4マップ ヘッダ情報:
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
-添付データ
-マスク #1
| ファイル |  emd_21652_msk_1.map emd_21652_msk_1.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
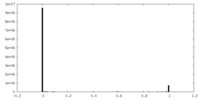
| 投影像・断面図 |
| ||||||||||||
| 密度ヒストグラム |
-追加マップ: #2
| ファイル | emd_21652_additional_1.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
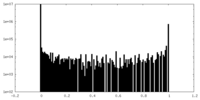
| 投影像・断面図 |
| ||||||||||||
| 密度ヒストグラム |
-追加マップ: #1
| ファイル | emd_21652_additional_2.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
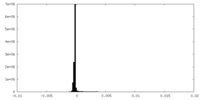
| 投影像・断面図 |
| ||||||||||||
| 密度ヒストグラム |
-ハーフマップ: #2
| ファイル | emd_21652_half_map_1.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
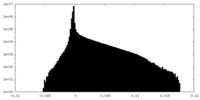
| 投影像・断面図 |
| ||||||||||||
| 密度ヒストグラム |
-ハーフマップ: #1
| ファイル | emd_21652_half_map_2.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 投影像・断面図 |
| ||||||||||||
| 密度ヒストグラム |
- 試料の構成要素
試料の構成要素
-全体 : NanR-DNA hetero-complex
| 全体 | 名称: NanR-DNA hetero-complex |
|---|---|
| 要素 |
|
-超分子 #1: NanR-DNA hetero-complex
| 超分子 | 名称: NanR-DNA hetero-complex / タイプ: complex / ID: 1 / 親要素: 0 / 含まれる分子: all / 詳細: Dimeric NanR-DNA hetero-complex |
|---|---|
| 由来(天然) | 生物種:  |
| 分子量 | 理論値: 72.8 KDa |
-分子 #1: HTH-type transcriptional repressor NanR
| 分子 | 名称: HTH-type transcriptional repressor NanR / タイプ: protein_or_peptide / ID: 1 / コピー数: 2 / 光学異性体: LEVO |
|---|---|
| 由来(天然) | 生物種:  |
| 分子量 | 理論値: 29.566354 KDa |
| 組換発現 | 生物種:  |
| 配列 | 文字列: MGLMNAFDSQ TEDSSPAIGR NLRSRPLARK KLSEMVEEEL EQMIRRREFG EGEQLPSERE LMAFFNVGRP SVREALAALK RKGLVQINN GERARVSRPS ADTIIGELSG MAKDFLSHPG GIAHFEQLRL FFESSLVRYA AEHATDEQID LLAKALEINS Q SLDNNAAF ...文字列: MGLMNAFDSQ TEDSSPAIGR NLRSRPLARK KLSEMVEEEL EQMIRRREFG EGEQLPSERE LMAFFNVGRP SVREALAALK RKGLVQINN GERARVSRPS ADTIIGELSG MAKDFLSHPG GIAHFEQLRL FFESSLVRYA AEHATDEQID LLAKALEINS Q SLDNNAAF IRSDVDFHRV LAEIPGNPIF MAIHVALLDW LIAARPTVTD QALHEHNNVS YQQHIAIVDA IRRHDPDEAD RA LQSHLNS VSATWHAFGQ TTNKKK UniProtKB: HTH-type transcriptional repressor NanR |
-分子 #2: DNA (5'-D(P*GP*GP*TP*AP*TP*AP*AP*CP*AP*GP*GP*TP*AP*TP*A)-3')
| 分子 | 名称: DNA (5'-D(P*GP*GP*TP*AP*TP*AP*AP*CP*AP*GP*GP*TP*AP*TP*A)-3') タイプ: dna / ID: 2 / コピー数: 1 / 分類: DNA |
|---|---|
| 由来(天然) | 生物種: synthetic construct (人工物) |
| 分子量 | 理論値: 4.65706 KDa |
| 配列 | 文字列: (DG)(DG)(DT)(DA)(DT)(DA)(DA)(DC)(DA)(DG) (DG)(DT)(DA)(DT)(DA) |
-分子 #3: DNA (5'-D(P*TP*AP*TP*AP*CP*CP*TP*GP*TP*TP*AP*TP*AP*CP*C)-3')
| 分子 | 名称: DNA (5'-D(P*TP*AP*TP*AP*CP*CP*TP*GP*TP*TP*AP*TP*AP*CP*C)-3') タイプ: dna / ID: 3 / コピー数: 1 / 分類: DNA |
|---|---|
| 由来(天然) | 生物種: synthetic construct (人工物) |
| 分子量 | 理論値: 4.518959 KDa |
| 配列 | 文字列: (DT)(DA)(DT)(DA)(DC)(DC)(DT)(DG)(DT)(DT) (DA)(DT)(DA)(DC)(DC) |
-実験情報
-構造解析
| 手法 | クライオ電子顕微鏡法 |
|---|---|
 解析 解析 | 単粒子再構成法 |
| 試料の集合状態 | particle |
- 試料調製
試料調製
| 濃度 | 0.5 mg/mL | |||||||||
|---|---|---|---|---|---|---|---|---|---|---|
| 緩衝液 | pH: 8 構成要素:
詳細: 20mM Tris-HCL, 150mM NaCl, 100 microM ZnCl2, pH 8.0 | |||||||||
| グリッド | モデル: Quantifoil, UltrAuFoil, R1.2/1.3 / 材質: GOLD / メッシュ: 300 / 支持フィルム - 材質: GOLD / 支持フィルム - トポロジー: HOLEY / 前処理 - タイプ: GLOW DISCHARGE / 前処理 - 時間: 30 sec. / 前処理 - 雰囲気: AIR | |||||||||
| 凍結 | 凍結剤: ETHANE / チャンバー内湿度: 100 % / チャンバー内温度: 277.15 K / 装置: FEI VITROBOT MARK III 詳細: blotting conditions: 3 sec blotting time and -3 blot force.. |
- 電子顕微鏡法
電子顕微鏡法
| 顕微鏡 | TFS KRIOS |
|---|---|
| 特殊光学系 | エネルギーフィルター - 名称: GIF Bioquantum / エネルギーフィルター - スリット幅: 20 eV |
| 撮影 | フィルム・検出器のモデル: GATAN K2 SUMMIT (4k x 4k) 検出モード: COUNTING / デジタル化 - 画像ごとのフレーム数: 1-20 / 撮影したグリッド数: 1 / 実像数: 3465 / 平均露光時間: 12.8 sec. / 平均電子線量: 60.0 e/Å2 |
| 電子線 | 加速電圧: 300 kV / 電子線源:  FIELD EMISSION GUN FIELD EMISSION GUN |
| 電子光学系 | C2レンズ絞り径: 50.0 µm / 照射モード: FLOOD BEAM / 撮影モード: BRIGHT FIELD / Cs: 2.7 mm / 最大 デフォーカス(公称値): 2.5 µm / 最小 デフォーカス(公称値): 0.5 µm / 倍率(公称値): 215000 |
| 試料ステージ | 試料ホルダーモデル: FEI TITAN KRIOS AUTOGRID HOLDER ホルダー冷却材: NITROGEN |
| 実験機器 |  モデル: Titan Krios / 画像提供: FEI Company |
+ 画像解析
画像解析
-原子モデル構築 1
| 精密化 | 空間: REAL / プロトコル: FLEXIBLE FIT |
|---|---|
| 得られたモデル |  PDB-6wfq: |
 ムービー
ムービー コントローラー
コントローラー















 Z
Z Y
Y X
X